peptides
spectra
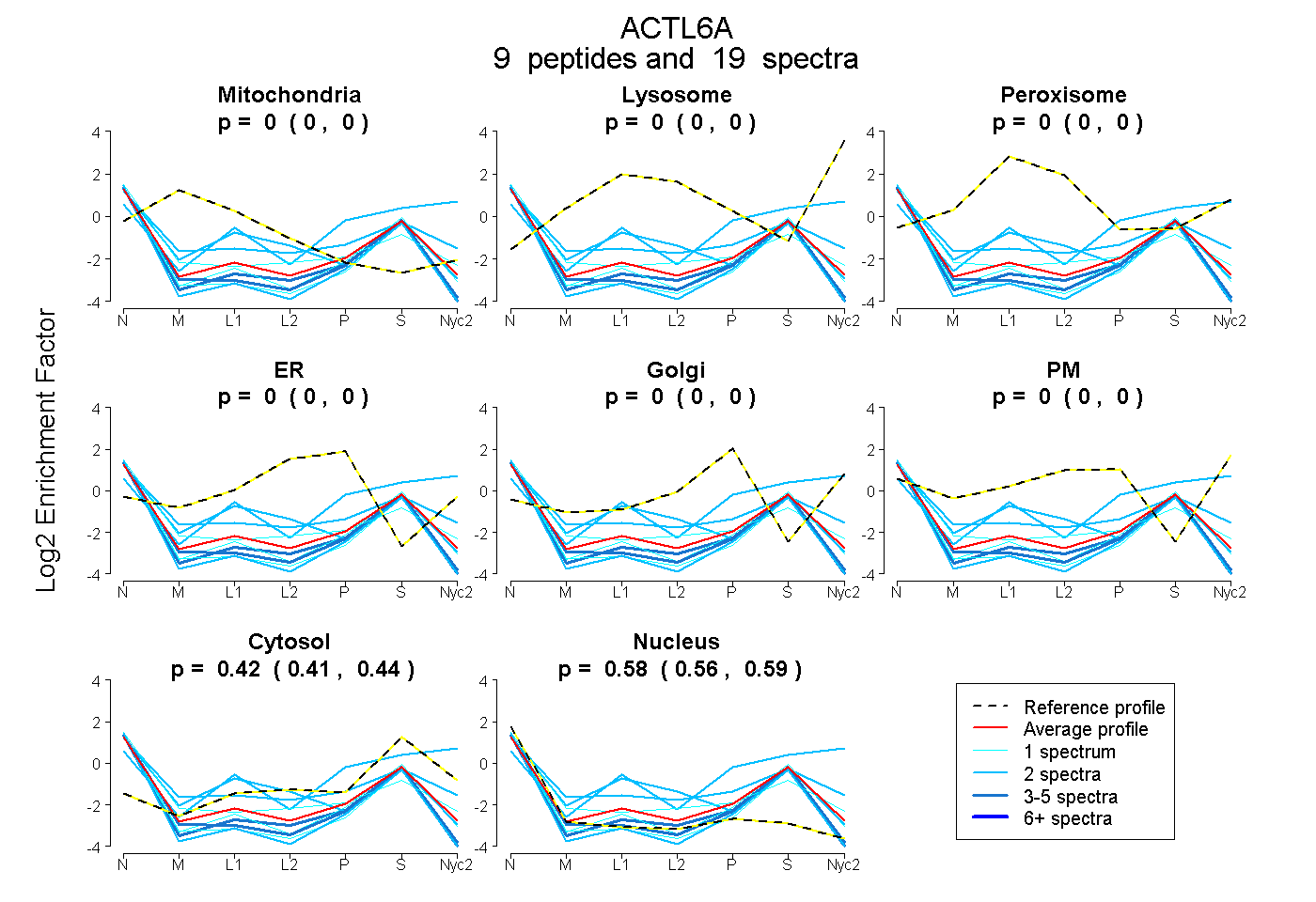
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.405 | 0.439
0.557 | 0.592
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
19 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.424 0.405 | 0.439 |
0.576 0.557 | 0.592 |
| 1 spectrum, QGGPTYYIDTNALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.225 | 0.775 | ||
| 2 spectra, IPEGLFDPSNVK | 0.000 | 0.000 | 0.220 | 0.000 | 0.000 | 0.000 | 0.260 | 0.520 | ||
| 2 spectra, EGSPANWK | 0.000 | 0.000 | 0.103 | 0.000 | 0.000 | 0.113 | 0.367 | 0.416 | ||
| 4 spectra, AGYAGEDCPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.294 | 0.706 | ||
| 1 spectrum, ESMEAISPLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.370 | 0.630 | ||
| 2 spectra, SPLAGDFITMQCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.304 | 0.623 | 0.073 | ||
| 1 spectrum, TAVLTAFANGR | 0.000 | 0.000 | 0.026 | 0.000 | 0.000 | 0.056 | 0.317 | 0.601 | ||
| 4 spectra, LIANNTTVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.283 | 0.717 | ||
| 2 spectra, VDFPTAIGVVLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.213 | 0.787 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
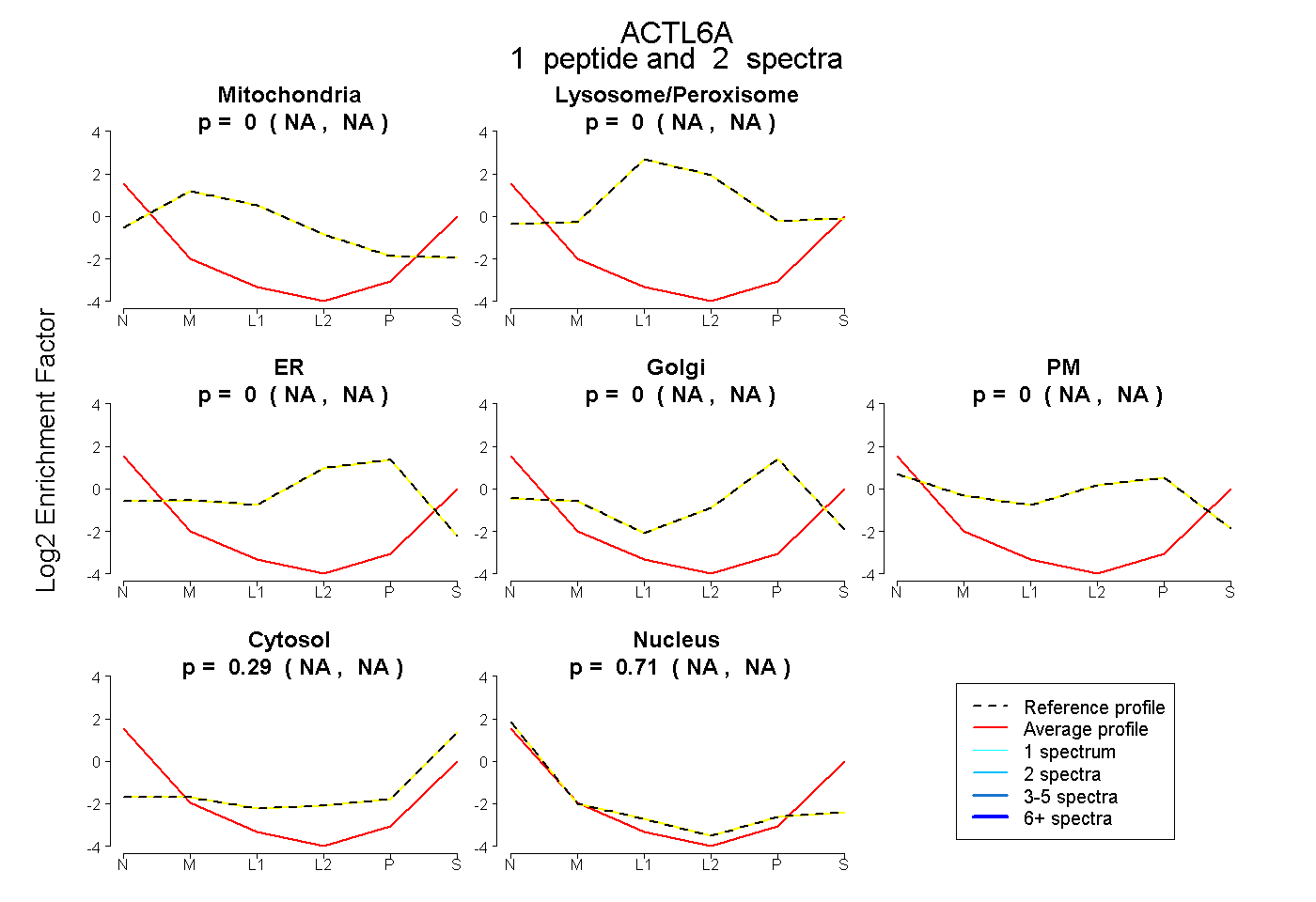 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.289 NA | NA |
0.711 NA | NA |