peptides
spectra
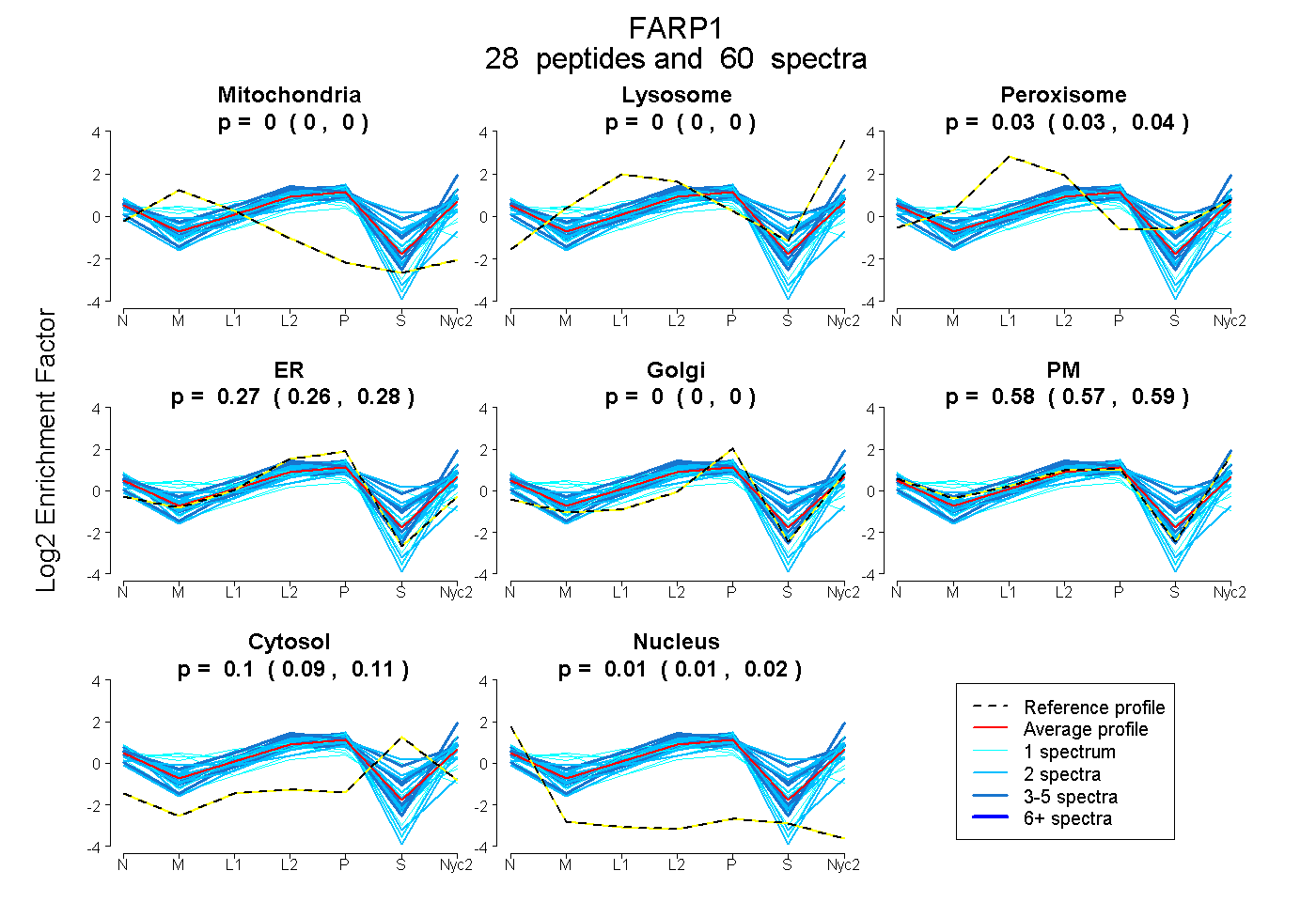
0.000 | 0.000
0.000 | 0.000
0.027 | 0.037
0.264 | 0.280
0.000 | 0.000
0.568 | 0.590
0.093 | 0.110
0.008 | 0.017
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
60 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.033 0.027 | 0.037 |
0.273 0.264 | 0.280 |
0.000 0.000 | 0.000 |
0.580 0.568 | 0.590 |
0.102 0.093 | 0.110 |
0.013 0.008 | 0.017 |
| 4 spectra, LALWEGR | 0.000 | 0.000 | 0.034 | 0.088 | 0.000 | 0.629 | 0.249 | 0.000 | ||
| 2 spectra, FHTNFLK | 0.009 | 0.000 | 0.000 | 0.364 | 0.000 | 0.627 | 0.000 | 0.000 | ||
| 1 spectrum, DFELQK | 0.000 | 0.000 | 0.000 | 0.547 | 0.000 | 0.000 | 0.453 | 0.000 | ||
| 1 spectrum, GQKPPPTPSGK | 0.000 | 0.000 | 0.029 | 0.195 | 0.000 | 0.741 | 0.035 | 0.000 | ||
| 1 spectrum, SPSGSK | 0.000 | 0.000 | 0.000 | 0.127 | 0.062 | 0.769 | 0.000 | 0.043 | ||
| 2 spectra, AESEYTFER | 0.000 | 0.000 | 0.000 | 0.319 | 0.000 | 0.534 | 0.120 | 0.027 | ||
| 4 spectra, AYYLAK | 0.000 | 0.000 | 0.090 | 0.144 | 0.006 | 0.584 | 0.176 | 0.000 | ||
| 2 spectra, FFPPDHTQLQEELTR | 0.000 | 0.000 | 0.015 | 0.110 | 0.000 | 0.726 | 0.149 | 0.000 | ||
| 2 spectra, SLIFPNFEPLHK | 0.000 | 0.000 | 0.000 | 0.333 | 0.000 | 0.640 | 0.018 | 0.010 | ||
| 2 spectra, QSIIVAASSR | 0.000 | 0.000 | 0.012 | 0.209 | 0.000 | 0.500 | 0.280 | 0.000 | ||
| 4 spectra, LGAPENSGISTLER | 0.000 | 0.000 | 0.014 | 0.226 | 0.000 | 0.723 | 0.037 | 0.000 | ||
| 1 spectrum, NIQGMK | 0.191 | 0.000 | 0.160 | 0.154 | 0.004 | 0.448 | 0.044 | 0.000 | ||
| 2 spectra, HHPPNHADFR | 0.000 | 0.000 | 0.234 | 0.255 | 0.000 | 0.351 | 0.157 | 0.004 | ||
| 2 spectra, EVSTTER | 0.000 | 0.000 | 0.000 | 0.316 | 0.058 | 0.568 | 0.024 | 0.033 | ||
| 2 spectra, ICVEHHAFFR | 0.054 | 0.000 | 0.000 | 0.790 | 0.000 | 0.068 | 0.000 | 0.088 | ||
| 5 spectra, EDSMPEALK | 0.000 | 0.082 | 0.041 | 0.211 | 0.000 | 0.350 | 0.316 | 0.000 | ||
| 2 spectra, VCTLEPGPR | 0.000 | 0.019 | 0.057 | 0.304 | 0.000 | 0.211 | 0.410 | 0.000 | ||
| 1 spectrum, SHVYYFR | 0.110 | 0.000 | 0.022 | 0.202 | 0.000 | 0.666 | 0.000 | 0.000 | ||
| 2 spectra, IGDVMLK | 0.000 | 0.000 | 0.096 | 0.003 | 0.000 | 0.685 | 0.215 | 0.000 | ||
| 1 spectrum, DLIGIDNLVIPGR | 0.233 | 0.000 | 0.091 | 0.334 | 0.000 | 0.342 | 0.000 | 0.000 | ||
| 1 spectrum, HSEALEALETSIK | 0.289 | 0.000 | 0.000 | 0.123 | 0.112 | 0.341 | 0.136 | 0.000 | ||
| 2 spectra, LEHFCR | 0.000 | 0.000 | 0.053 | 0.526 | 0.000 | 0.375 | 0.000 | 0.046 | ||
| 3 spectra, WMEVIR | 0.000 | 0.074 | 0.000 | 0.001 | 0.000 | 0.925 | 0.000 | 0.000 | ||
| 3 spectra, GLTASNQFK | 0.000 | 0.000 | 0.000 | 0.248 | 0.000 | 0.687 | 0.024 | 0.041 | ||
| 2 spectra, HLAAHLWK | 0.000 | 0.000 | 0.000 | 0.276 | 0.032 | 0.654 | 0.000 | 0.038 | ||
| 2 spectra, INAFNWAK | 0.000 | 0.000 | 0.000 | 0.373 | 0.000 | 0.576 | 0.000 | 0.051 | ||
| 2 spectra, QDLAQGR | 0.000 | 0.000 | 0.000 | 0.230 | 0.000 | 0.733 | 0.004 | 0.033 | ||
| 2 spectra, YVPQQDALEDK | 0.000 | 0.000 | 0.155 | 0.000 | 0.169 | 0.478 | 0.198 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
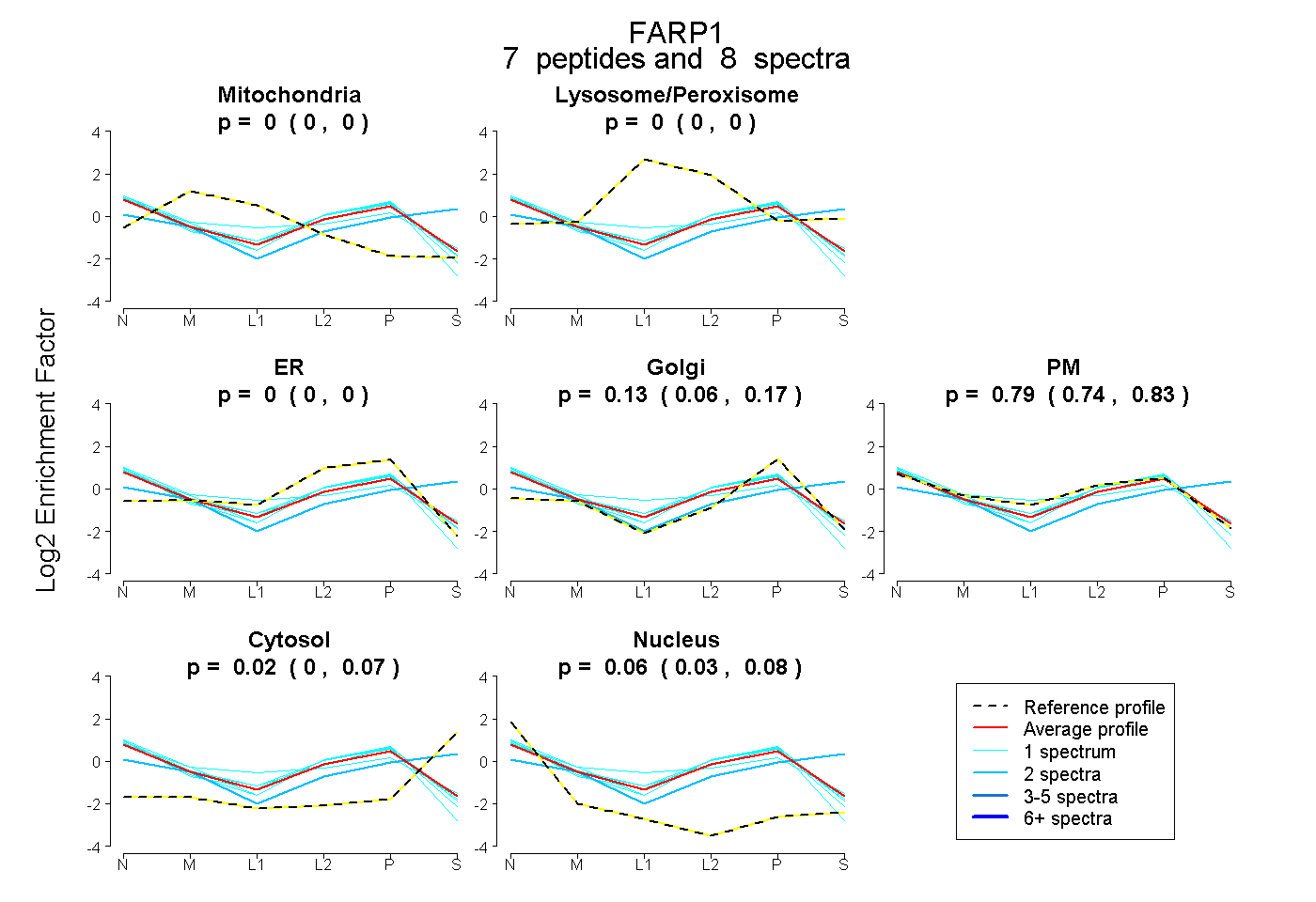 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.128 0.064 | 0.171 |
0.786 0.741 | 0.828 |
0.024 0.000 | 0.067 |
0.062 0.031 | 0.082 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
74 spectra |
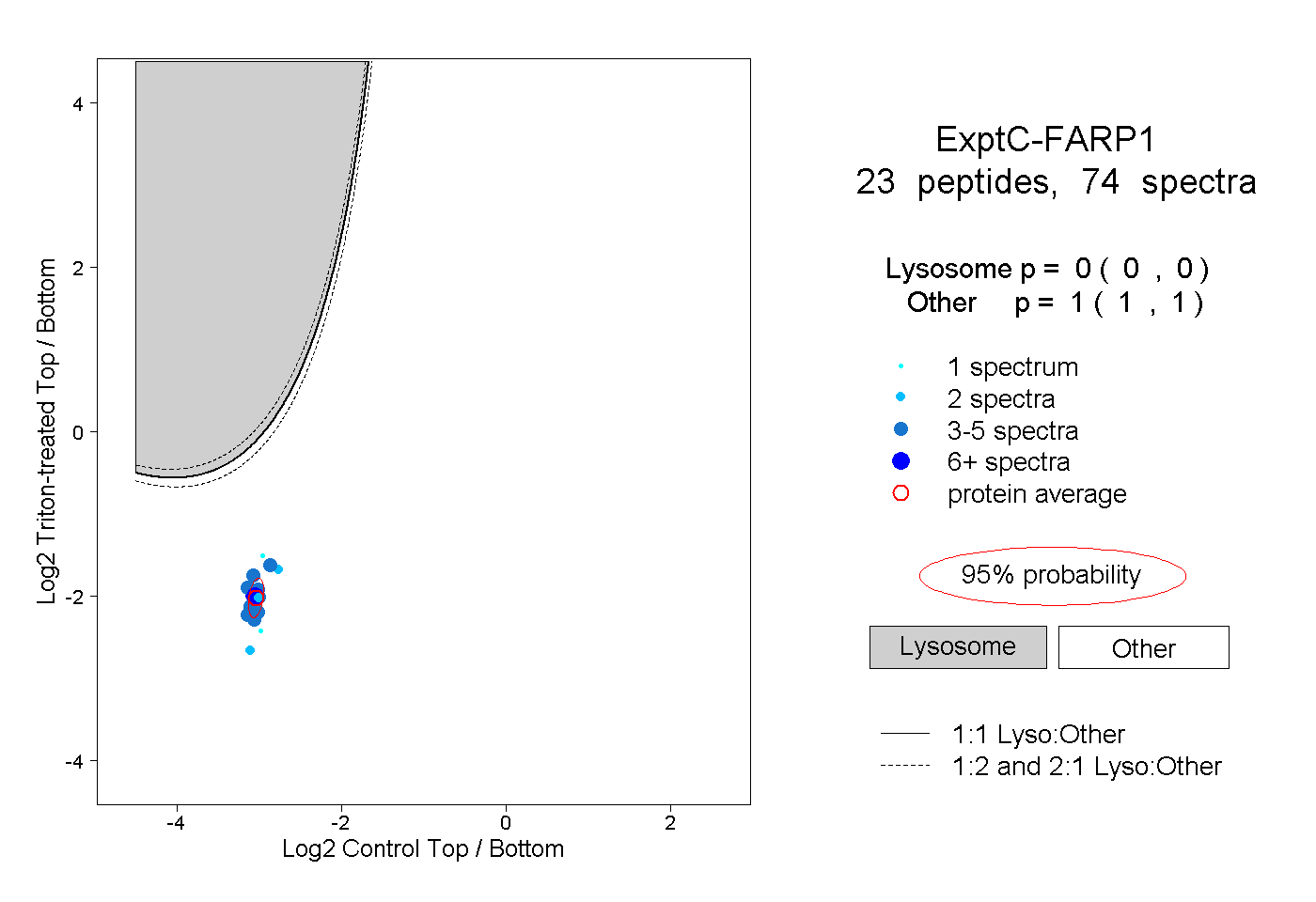 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
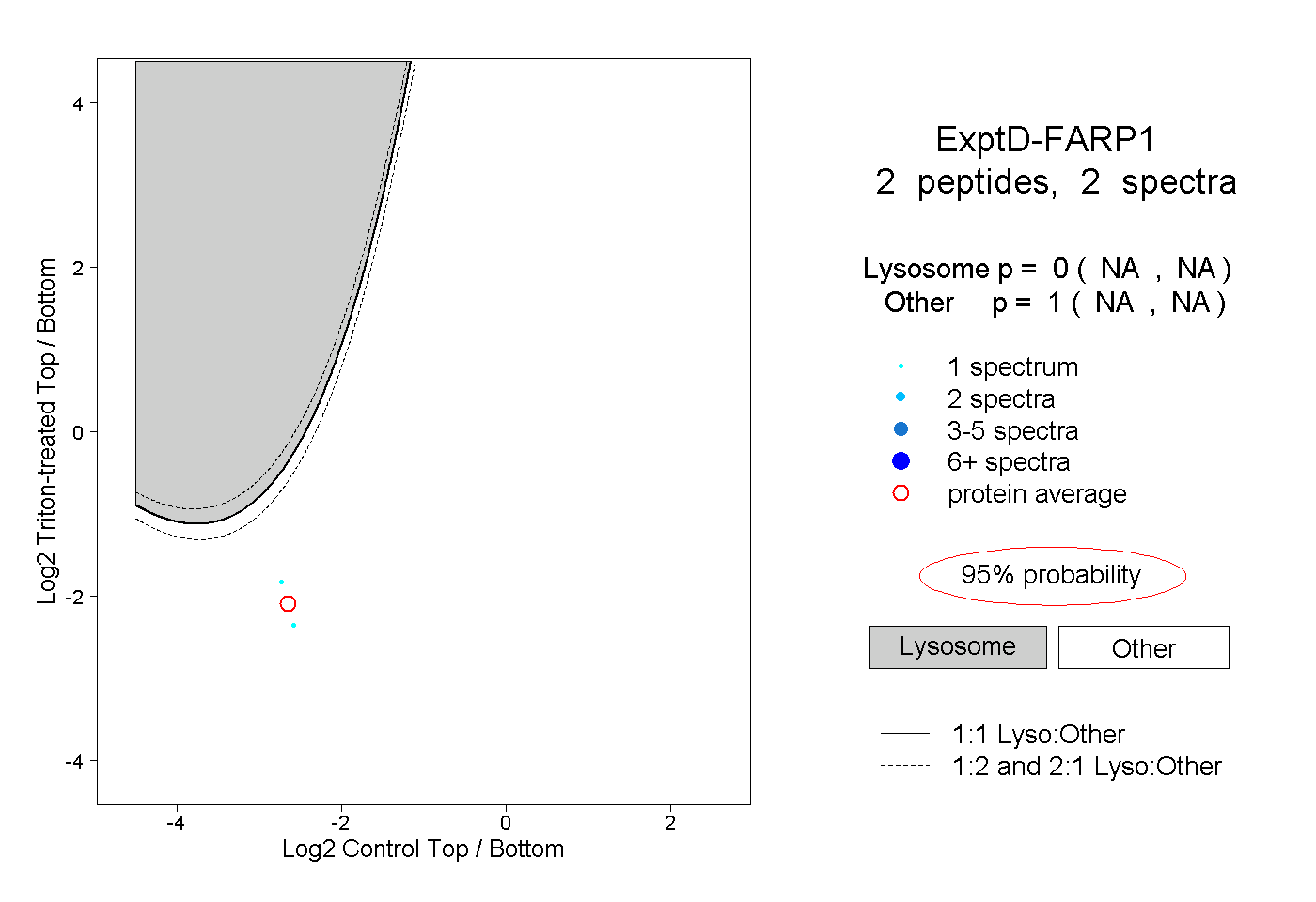 |
0.000 NA | NA |
1.000 NA | NA |