peptides
spectra
0.059 | 0.068
0.000 | 0.000
0.000 | 0.001
0.914 | 0.919
0.000 | 0.000
0.000 | 0.000
0.015 | 0.023
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.136 | 0.205
0.473 | 0.595
0.116 | 0.239
0.030 | 0.110
0.014 | 0.047
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
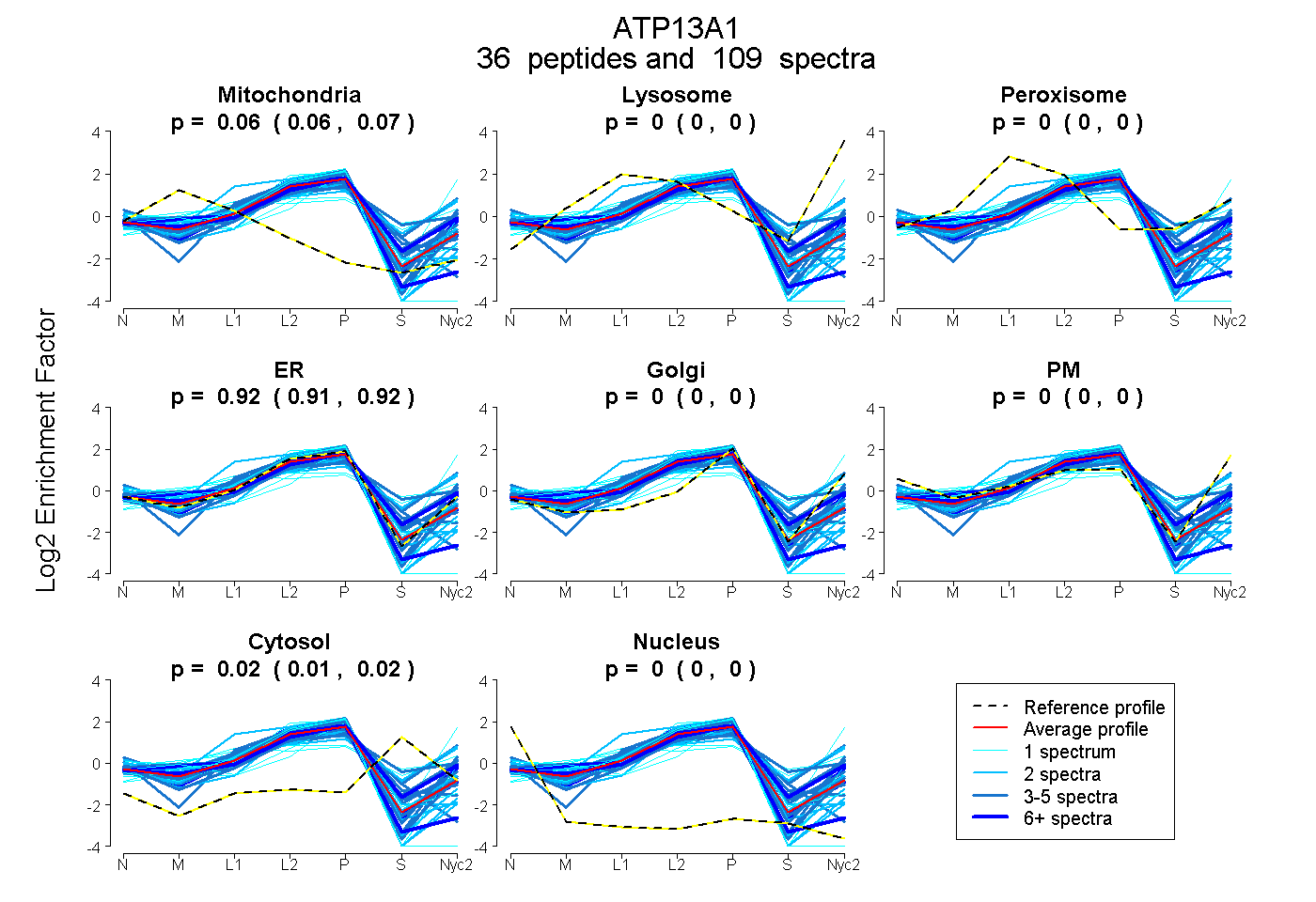
| Expt A |
peptides |
109 spectra |
 |
0.064 0.059 | 0.068 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.917 0.914 | 0.919 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.019 0.015 | 0.023 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
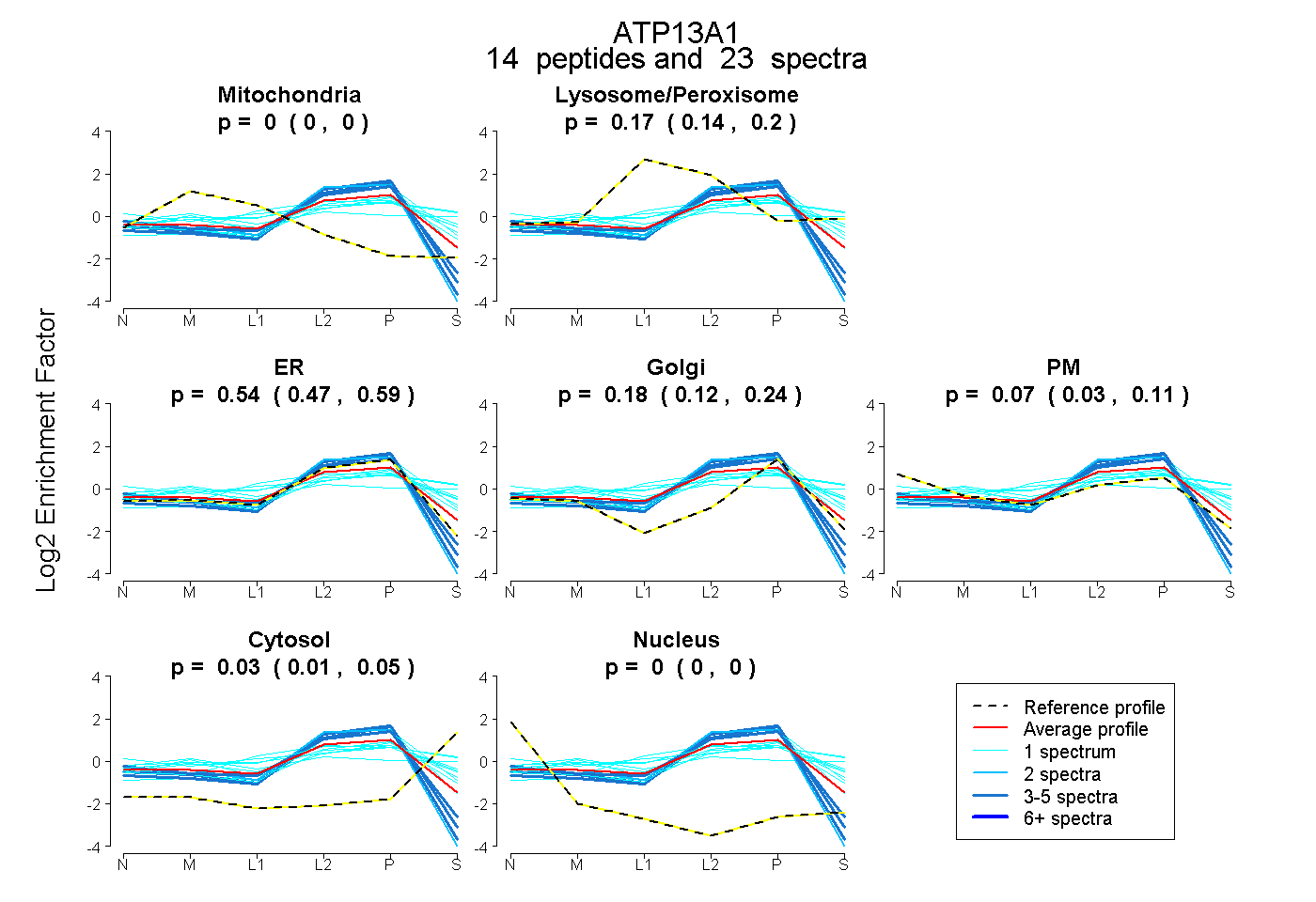
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.172 0.136 | 0.205 |
0.542 0.473 | 0.595 |
0.179 0.116 | 0.239 |
0.075 0.030 | 0.110 |
0.032 0.014 | 0.047 |
0.000 0.000 | 0.000 |
| 1 spectrum, EVTPVSSIPIETHR | 0.017 | 0.336 | 0.000 | 0.140 | 0.280 | 0.227 | 0.000 | |||
| 1 spectrum, VVPTPNNGSTELVALHR | 0.000 | 0.464 | 0.035 | 0.442 | 0.000 | 0.060 | 0.000 | |||
| 4 spectra, EPIEDLSPDR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AEMAVPDFSELFK | 0.000 | 0.068 | 0.794 | 0.000 | 0.000 | 0.138 | 0.000 | |||
| 1 spectrum, LGDASIAAPFTSK | 0.000 | 0.017 | 0.911 | 0.000 | 0.000 | 0.072 | 0.000 | |||
| 4 spectra, VLDLQADAR | 0.000 | 0.000 | 0.930 | 0.000 | 0.070 | 0.000 | 0.000 | |||
| 1 spectrum, WRPIASDDIVPGDIVSIGR | 0.000 | 0.368 | 0.081 | 0.521 | 0.003 | 0.027 | 0.000 | |||
| 3 spectra, GFQEDSDIR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LGSTDLCYIAAVK | 0.000 | 0.345 | 0.064 | 0.490 | 0.000 | 0.101 | 0.000 | |||
| 1 spectrum, EFVITSLK | 0.000 | 0.538 | 0.000 | 0.316 | 0.000 | 0.146 | 0.000 | |||
| 1 spectrum, DSPVLSNSGPR | 0.000 | 0.367 | 0.000 | 0.347 | 0.286 | 0.000 | 0.000 | |||
| 1 spectrum, ATSGLKPVDNGCVAFVLR | 0.000 | 0.430 | 0.000 | 0.417 | 0.095 | 0.058 | 0.000 | |||
| 1 spectrum, FVGFIVVSCPLK | 0.000 | 0.281 | 0.214 | 0.233 | 0.026 | 0.246 | 0.000 | |||
| 2 spectra, TGTLTSDSLVVR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
82 spectra |
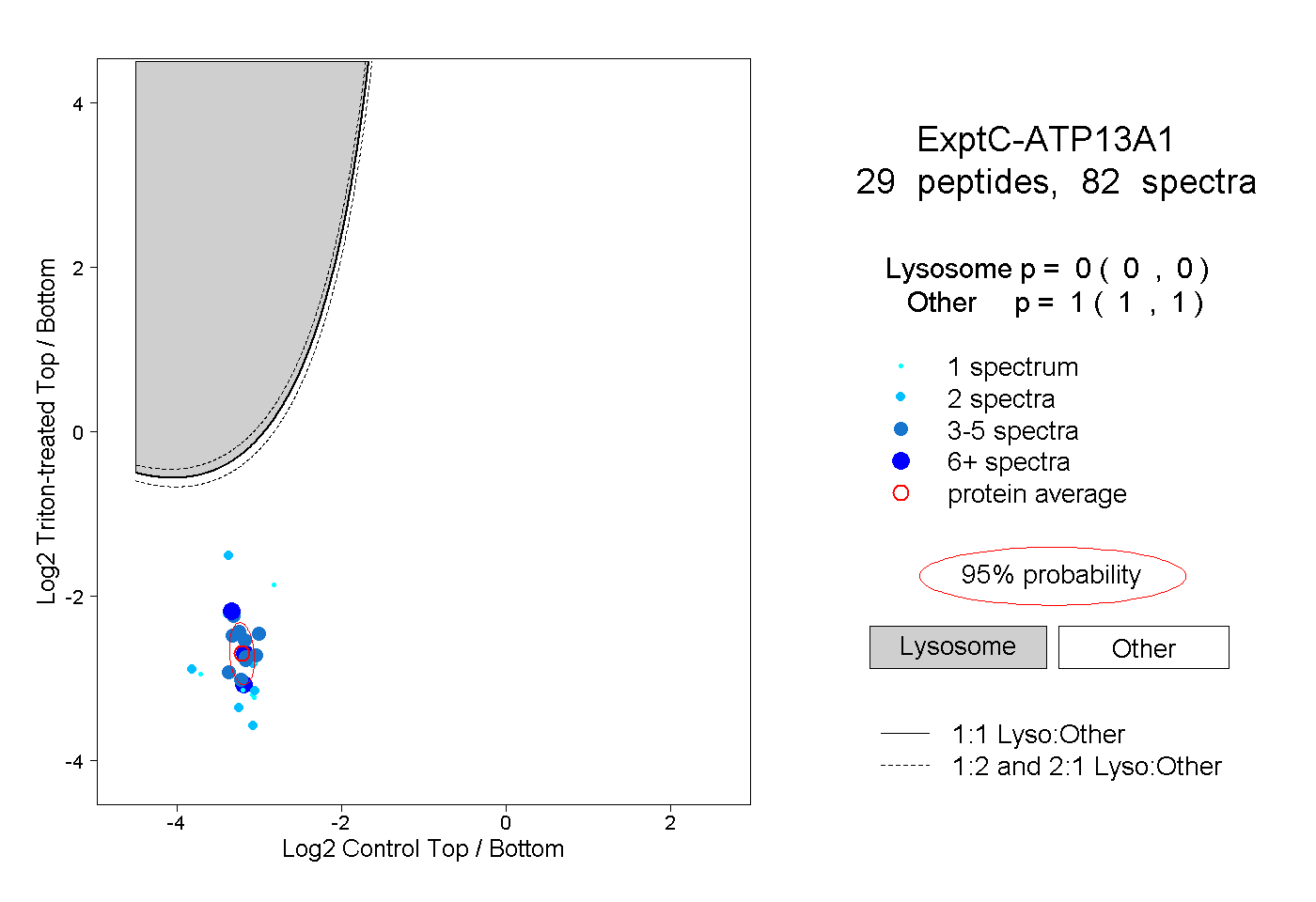 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |