peptides
spectra
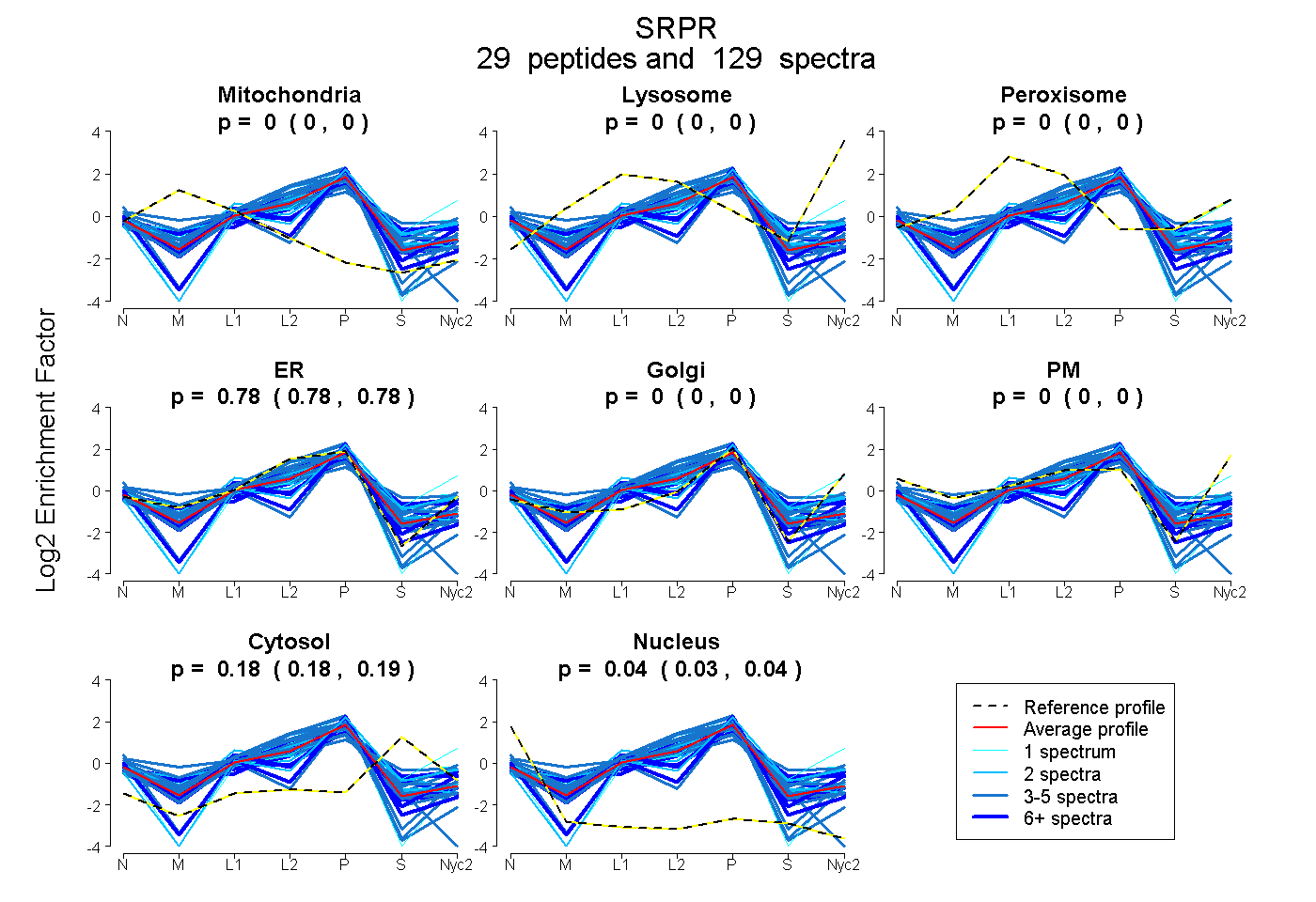
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.778 | 0.784
0.000 | 0.000
0.000 | 0.000
0.177 | 0.186
0.034 | 0.040
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
129 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.781 0.778 | 0.784 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.182 0.177 | 0.186 |
0.037 0.034 | 0.040 |
| 7 spectra, SMIETR | 0.000 | 0.000 | 0.022 | 0.510 | 0.306 | 0.000 | 0.087 | 0.075 | ||
| 3 spectra, LIDDVHR | 0.000 | 0.000 | 0.000 | 0.819 | 0.000 | 0.000 | 0.097 | 0.084 | ||
| 4 spectra, AGAVEQLR | 0.000 | 0.000 | 0.015 | 0.758 | 0.067 | 0.000 | 0.160 | 0.000 | ||
| 3 spectra, EAEESSK | 0.000 | 0.000 | 0.000 | 0.967 | 0.000 | 0.000 | 0.000 | 0.033 | ||
| 2 spectra, GGNNSFTHEALTLK | 0.000 | 0.000 | 0.049 | 0.654 | 0.000 | 0.000 | 0.297 | 0.000 | ||
| 3 spectra, MLDFFTIFSK | 0.000 | 0.000 | 0.141 | 0.408 | 0.084 | 0.047 | 0.321 | 0.000 | ||
| 3 spectra, QRPYVVTFCGVNGVGK | 0.032 | 0.000 | 0.000 | 0.747 | 0.000 | 0.000 | 0.088 | 0.132 | ||
| 5 spectra, DAAGIAMEAIAFAR | 0.000 | 0.000 | 0.000 | 0.860 | 0.000 | 0.000 | 0.140 | 0.000 | ||
| 2 spectra, VWELGGCANK | 0.000 | 0.000 | 0.000 | 0.244 | 0.405 | 0.000 | 0.351 | 0.000 | ||
| 4 spectra, STNLAK | 0.179 | 0.000 | 0.025 | 0.706 | 0.012 | 0.000 | 0.078 | 0.000 | ||
| 8 spectra, DIMDAQR | 0.043 | 0.000 | 0.000 | 0.836 | 0.000 | 0.000 | 0.103 | 0.019 | ||
| 5 spectra, TMVQLFEK | 0.000 | 0.000 | 0.000 | 0.820 | 0.000 | 0.000 | 0.180 | 0.000 | ||
| 1 spectrum, DHLIAK | 0.000 | 0.000 | 0.195 | 0.506 | 0.054 | 0.000 | 0.245 | 0.000 | ||
| 7 spectra, GTLGGMFGMLK | 0.000 | 0.000 | 0.038 | 0.389 | 0.259 | 0.000 | 0.314 | 0.000 | ||
| 8 spectra, ALADHSMAQTPR | 0.000 | 0.000 | 0.050 | 0.554 | 0.094 | 0.000 | 0.301 | 0.000 | ||
| 20 spectra, EDMESVLDK | 0.000 | 0.000 | 0.000 | 0.681 | 0.000 | 0.000 | 0.308 | 0.011 | ||
| 5 spectra, MQDNAPLMTALAK | 0.017 | 0.000 | 0.110 | 0.653 | 0.000 | 0.000 | 0.191 | 0.030 | ||
| 3 spectra, LIDGIVLTK | 0.000 | 0.000 | 0.000 | 0.805 | 0.000 | 0.000 | 0.134 | 0.061 | ||
| 4 spectra, VMGTFSTVTSTVK | 0.000 | 0.022 | 0.098 | 0.652 | 0.053 | 0.000 | 0.176 | 0.000 | ||
| 2 spectra, NQGFDVVLVDTAGR | 0.000 | 0.000 | 0.000 | 0.836 | 0.000 | 0.000 | 0.164 | 0.000 | ||
| 1 spectrum, ILTLTYVDK | 0.000 | 0.000 | 0.000 | 0.930 | 0.000 | 0.000 | 0.000 | 0.070 | ||
| 4 spectra, AVVAALMK | 0.000 | 0.000 | 0.000 | 0.761 | 0.000 | 0.000 | 0.197 | 0.041 | ||
| 3 spectra, EGSDGPLATSK | 0.000 | 0.000 | 0.000 | 0.524 | 0.143 | 0.000 | 0.000 | 0.333 | ||
| 2 spectra, GLVGSK | 0.000 | 0.000 | 0.000 | 0.715 | 0.000 | 0.000 | 0.210 | 0.075 | ||
| 2 spectra, LTALHPPEK | 0.000 | 0.000 | 0.094 | 0.587 | 0.109 | 0.000 | 0.210 | 0.000 | ||
| 4 spectra, SVLLQER | 0.000 | 0.000 | 0.000 | 0.955 | 0.000 | 0.000 | 0.000 | 0.045 | ||
| 6 spectra, TAPAEK | 0.000 | 0.000 | 0.000 | 0.449 | 0.282 | 0.000 | 0.027 | 0.241 | ||
| 7 spectra, FDTIDDK | 0.000 | 0.000 | 0.000 | 0.815 | 0.000 | 0.000 | 0.140 | 0.045 | ||
| 1 spectrum, SGLPVGPENGELSK | 0.000 | 0.000 | 0.000 | 0.204 | 0.502 | 0.000 | 0.294 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
40 spectra |
 |
0.000 0.000 | 0.000 |
0.061 0.049 | 0.073 |
0.803 0.787 | 0.818 |
0.000 0.000 | 0.000 |
0.019 0.004 | 0.031 |
0.116 0.107 | 0.124 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
169 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |