peptides
spectra
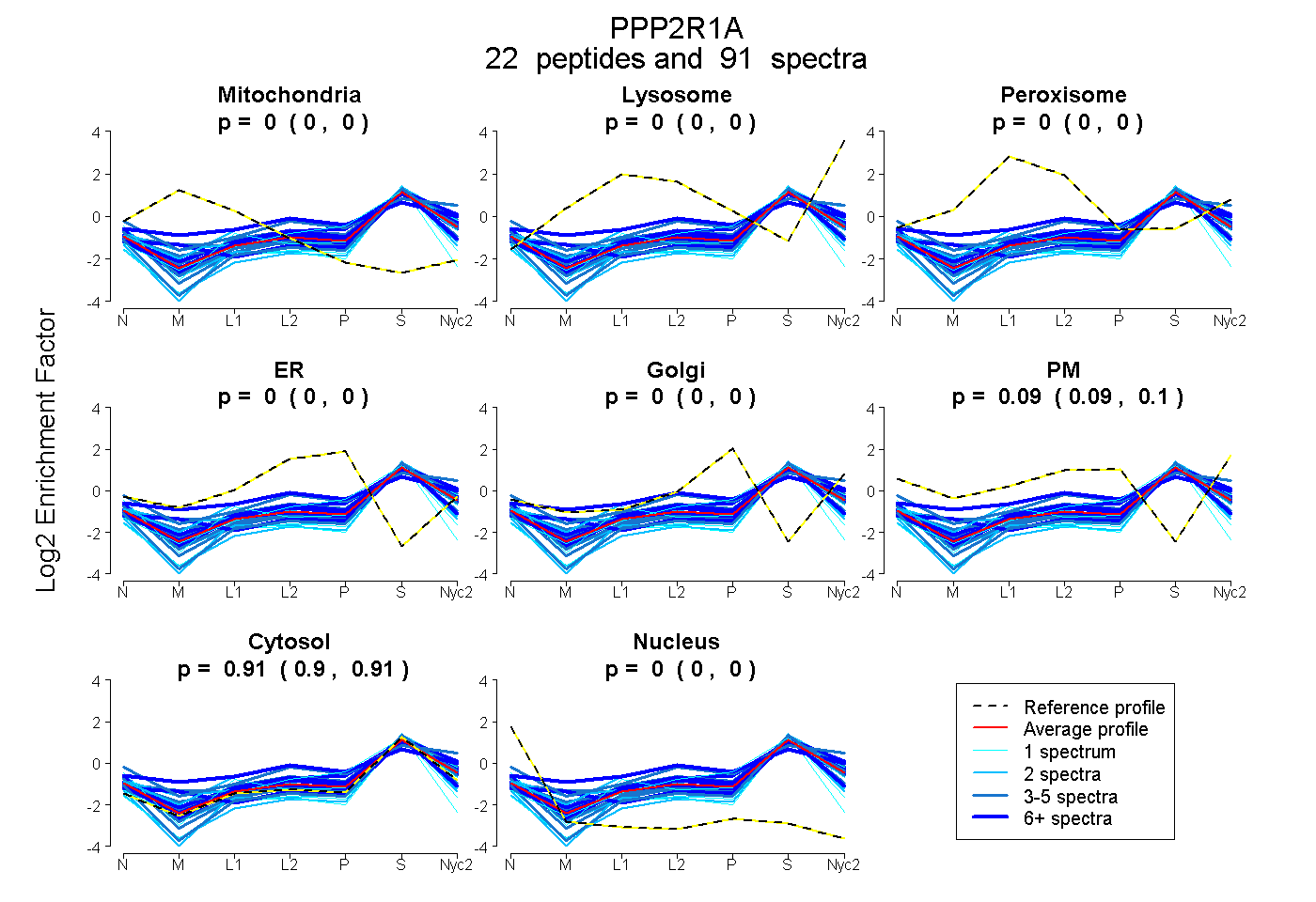
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.090 | 0.096
0.903 | 0.909
0.000 | 0.000
peptides
spectra
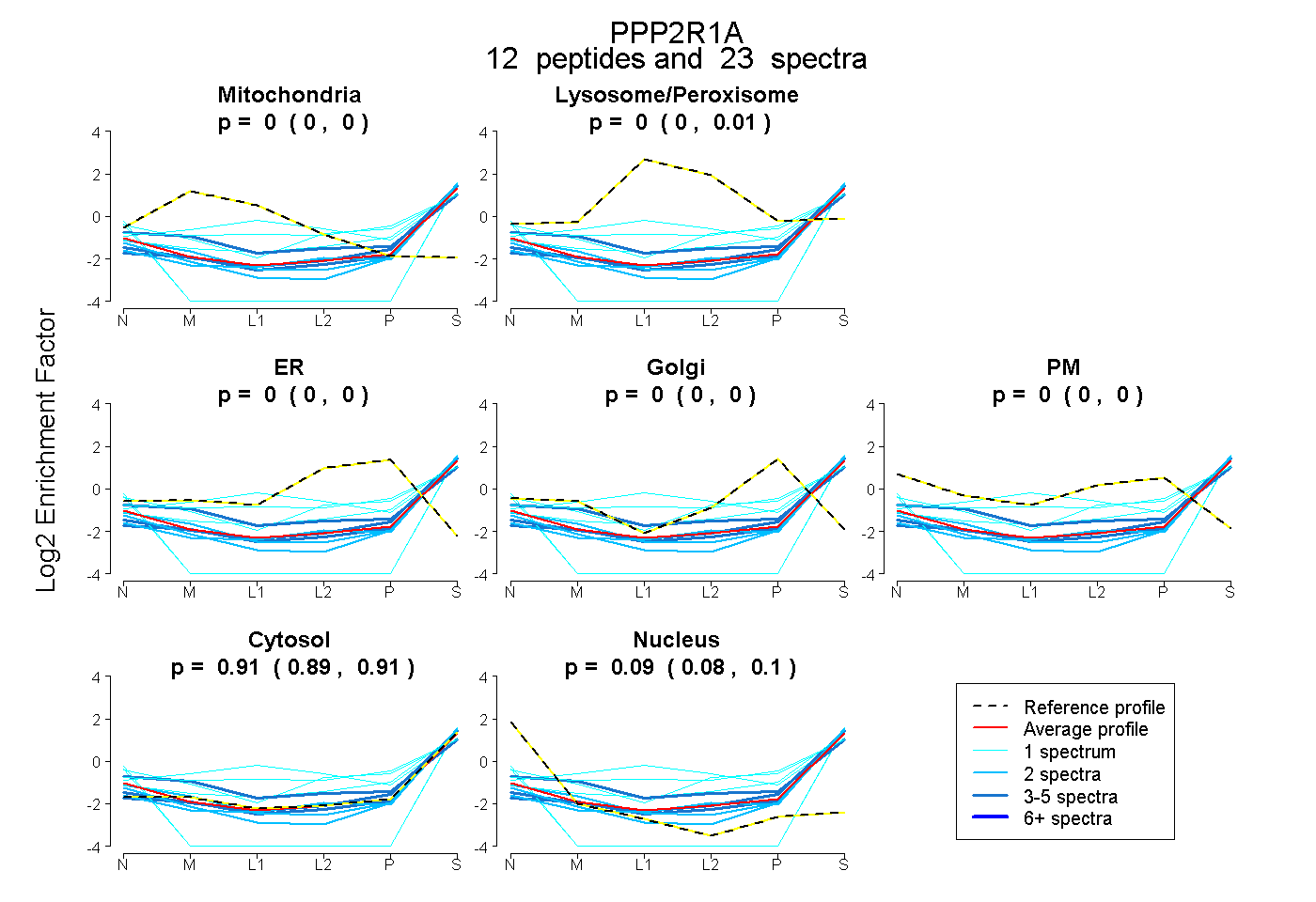
0.000 | 0.000
0.000 | 0.013
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.894 | 0.914
0.080 | 0.099
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
91 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.093 0.090 | 0.096 |
0.907 0.903 | 0.909 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.013 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.907 0.894 | 0.914 |
0.091 0.080 | 0.099 |
| 1 spectrum, EFCENLSADCR | 0.041 | 0.386 | 0.000 | 0.000 | 0.000 | 0.573 | 0.000 | |||
| 1 spectrum, AVGPEITK | 0.000 | 0.036 | 0.000 | 0.000 | 0.332 | 0.632 | 0.000 | |||
| 2 spectra, NEDVQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LTQDQDVDVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.637 | 0.363 | |||
| 2 spectra, LAGGDWFTSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.904 | 0.096 | |||
| 4 spectra, HMLPTVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.004 | |||
| 1 spectrum, LSTIALALGVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.660 | 0.340 | |||
| 1 spectrum, QLSQSLLPAIVELAEDAK | 0.000 | 0.113 | 0.000 | 0.066 | 0.028 | 0.792 | 0.000 | |||
| 4 spectra, MAGDPVANVR | 0.000 | 0.000 | 0.000 | 0.006 | 0.000 | 0.980 | 0.014 | |||
| 3 spectra, TSACGLFSVCYPR | 0.037 | 0.058 | 0.000 | 0.000 | 0.140 | 0.740 | 0.025 | |||
| 2 spectra, VLELDNVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.898 | 0.102 | |||
| 1 spectrum, VLAMSGDPNYLHR | 0.000 | 0.277 | 0.000 | 0.156 | 0.000 | 0.567 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
116 spectra |
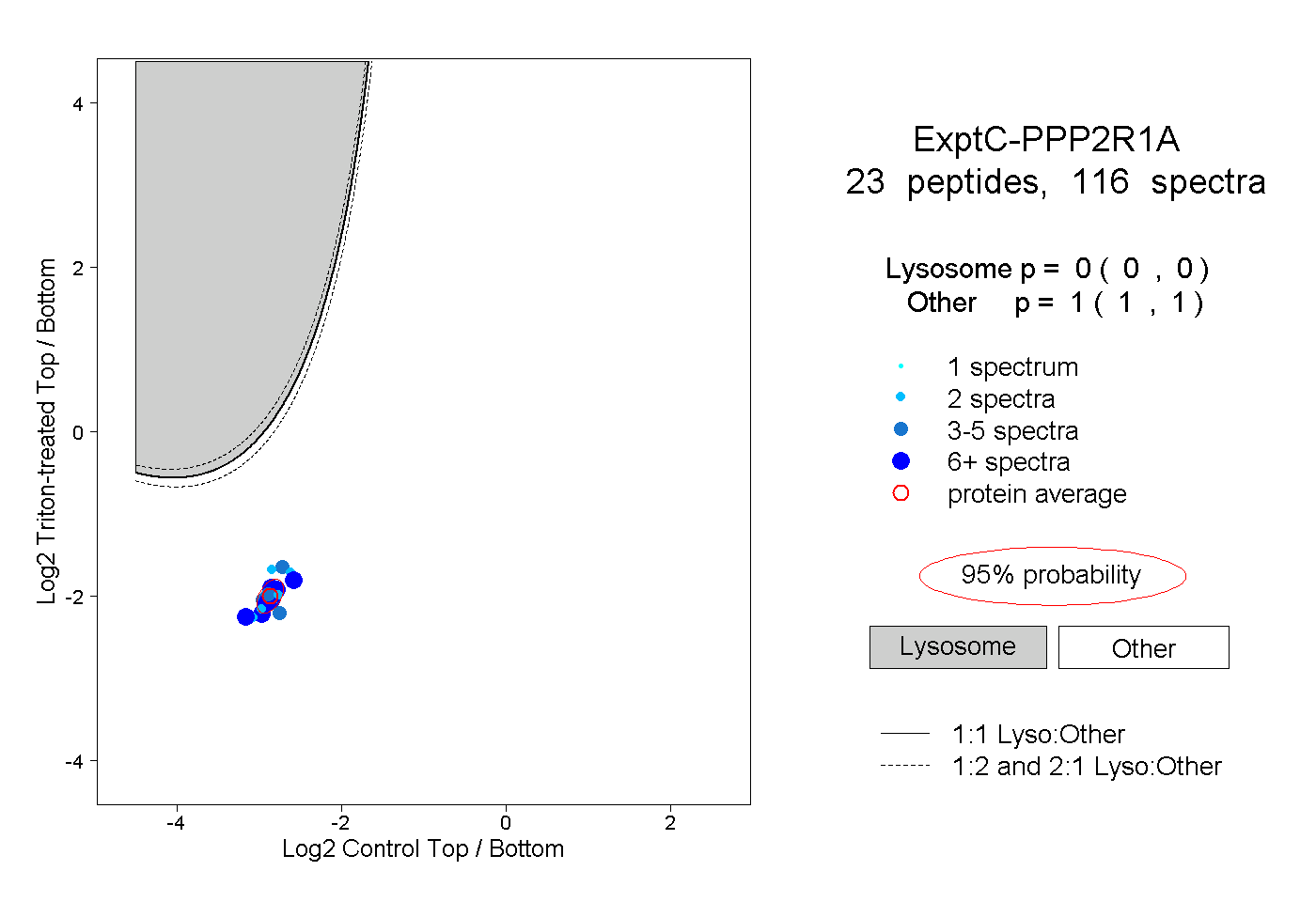 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
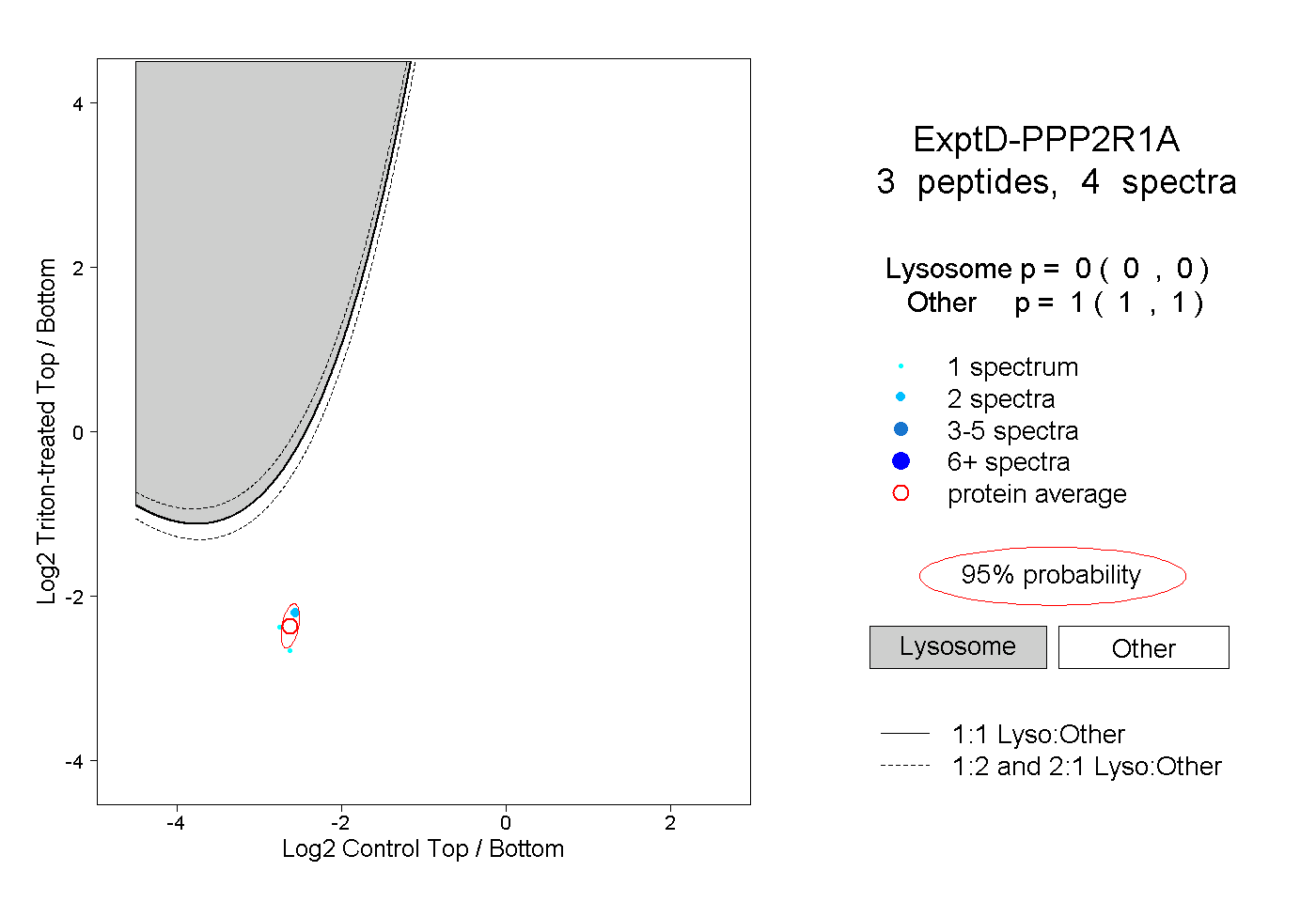 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |