peptides
spectra
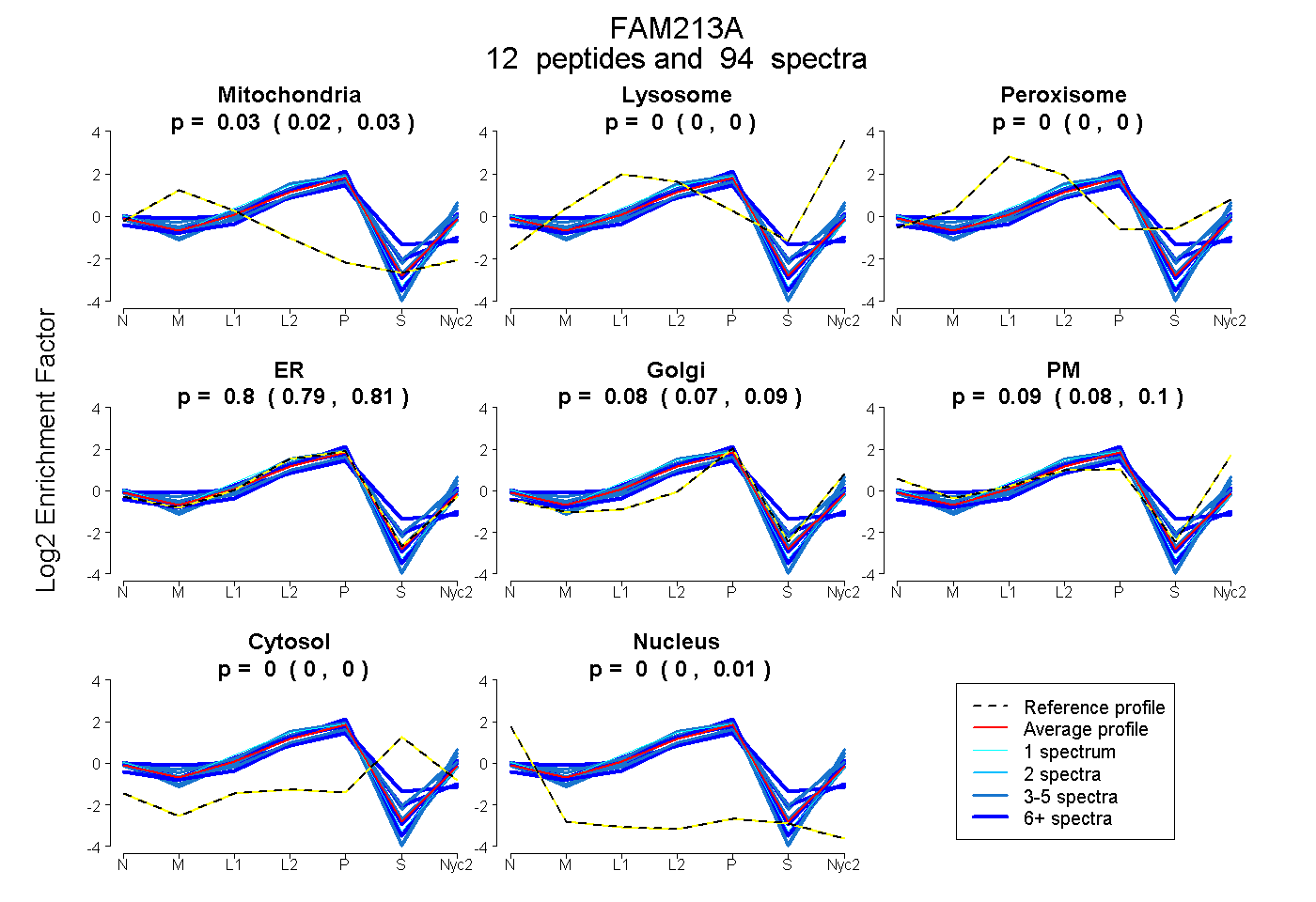
0.025 | 0.033
0.000 | 0.000
0.000 | 0.000
0.787 | 0.811
0.071 | 0.088
0.076 | 0.096
0.000 | 0.000
0.001 | 0.007
peptides
spectra
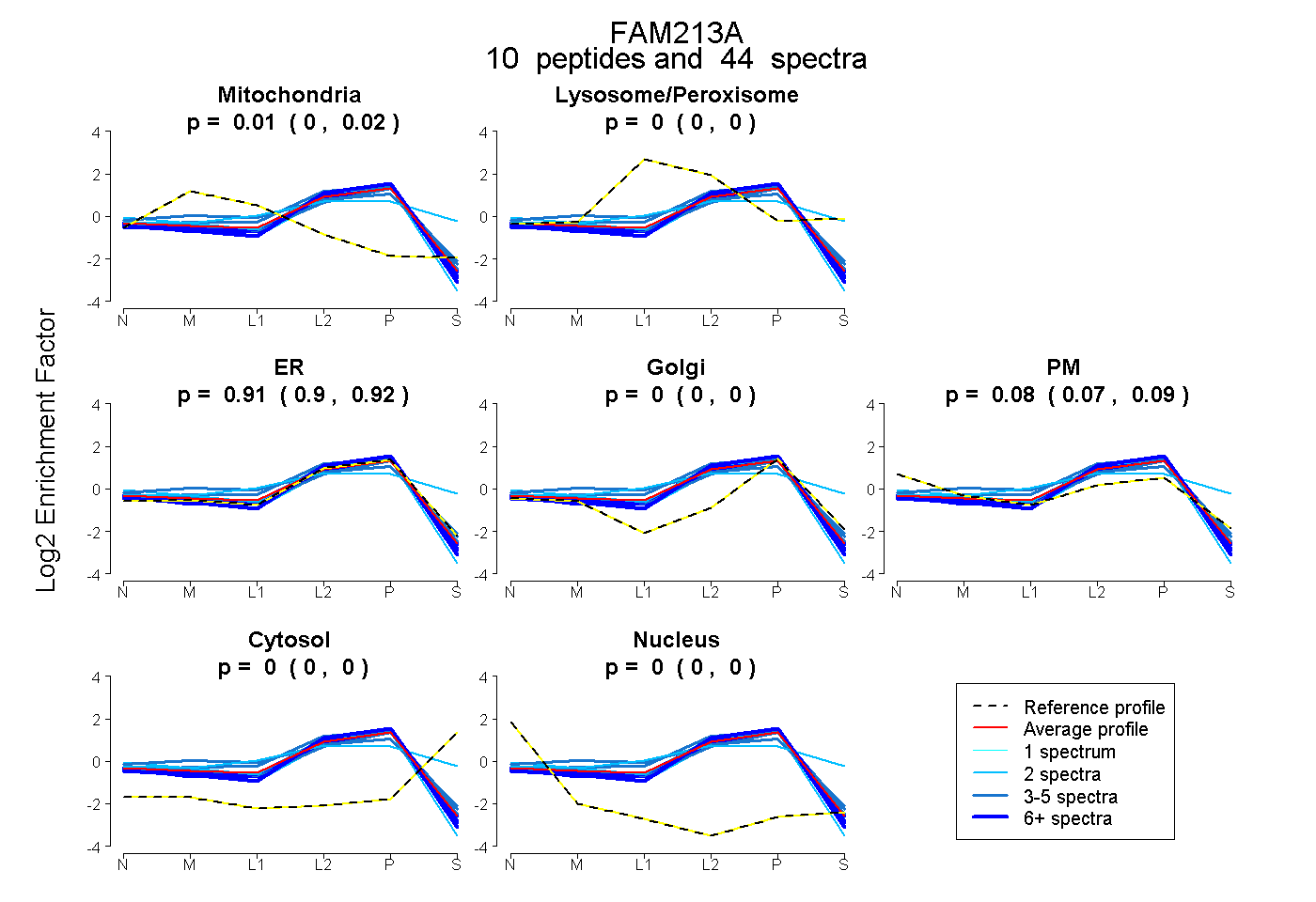
0.003 | 0.016
0.000 | 0.000
0.899 | 0.919
0.000 | 0.000
0.067 | 0.091
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
94 spectra |
 |
0.029 0.025 | 0.033 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.800 0.787 | 0.811 |
0.080 0.071 | 0.088 |
0.087 0.076 | 0.096 |
0.000 0.000 | 0.000 |
0.005 0.001 | 0.007 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
44 spectra |
 |
0.010 0.003 | 0.016 |
0.000 0.000 | 0.000 |
0.910 0.899 | 0.919 |
0.000 0.000 | 0.000 |
0.080 0.067 | 0.091 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, EVEDFQPYFK | 0.000 | 0.000 | 0.922 | 0.062 | 0.000 | 0.000 | 0.015 | |||
| 3 spectra, QGVLLEHR | 0.080 | 0.118 | 0.623 | 0.000 | 0.179 | 0.000 | 0.000 | |||
| 2 spectra, LGVWYNSFR | 0.000 | 0.000 | 0.928 | 0.000 | 0.072 | 0.000 | 0.000 | |||
| 6 spectra, GEIFLDEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, AALEYLEDIDLK | 0.000 | 0.000 | 0.987 | 0.000 | 0.000 | 0.000 | 0.013 | |||
| 3 spectra, IKPQTPASR | 0.000 | 0.000 | 0.771 | 0.019 | 0.210 | 0.000 | 0.000 | |||
| 7 spectra, LDELGVPLYAVVK | 0.000 | 0.000 | 0.970 | 0.000 | 0.019 | 0.000 | 0.011 | |||
| 2 spectra, RPGCFLCR | 0.000 | 0.501 | 0.000 | 0.428 | 0.000 | 0.071 | 0.000 | |||
| 5 spectra, NGAVIMAVR | 0.000 | 0.074 | 0.926 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, VNLLSVLEAVK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
81 spectra |
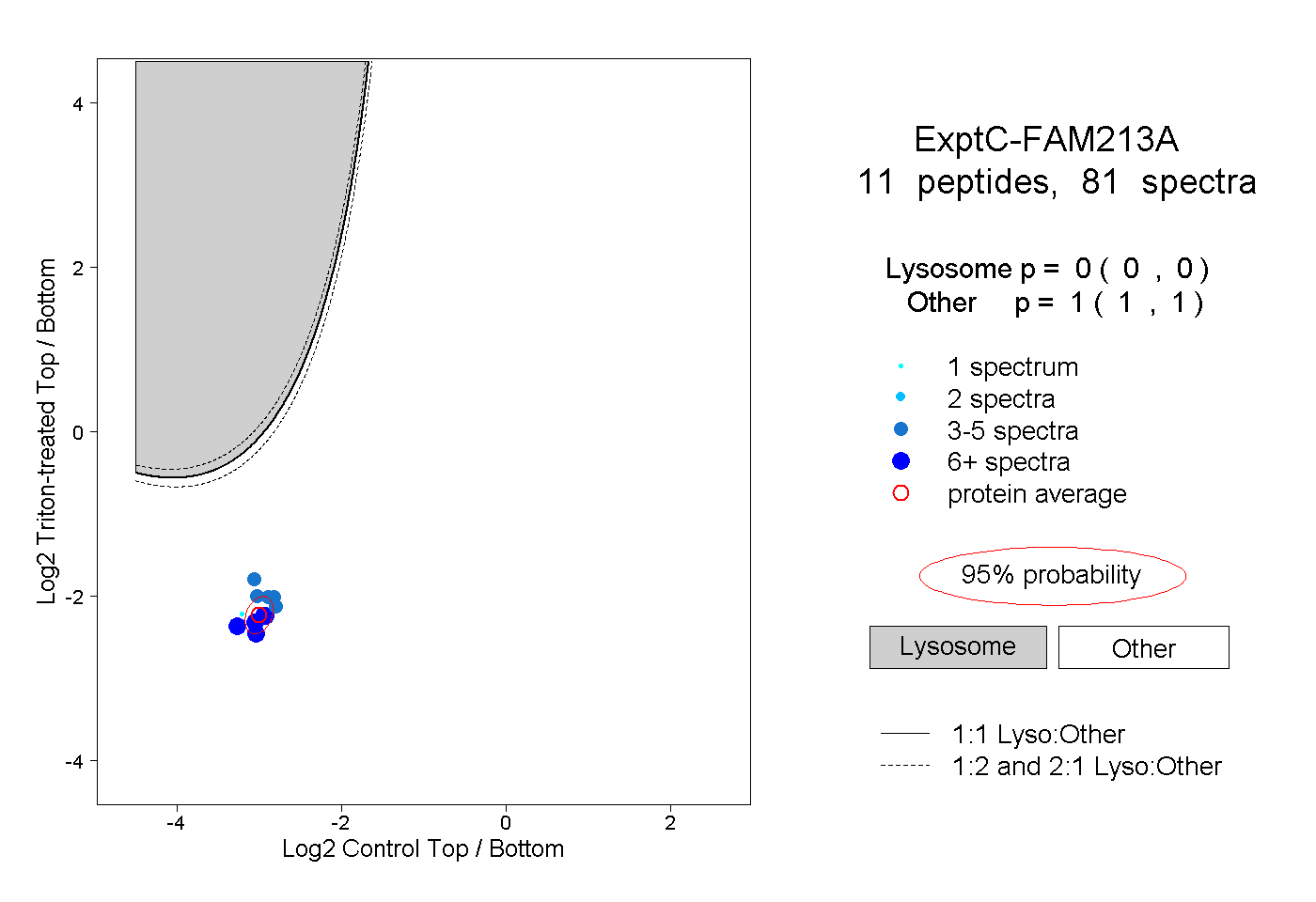 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
22 spectra |
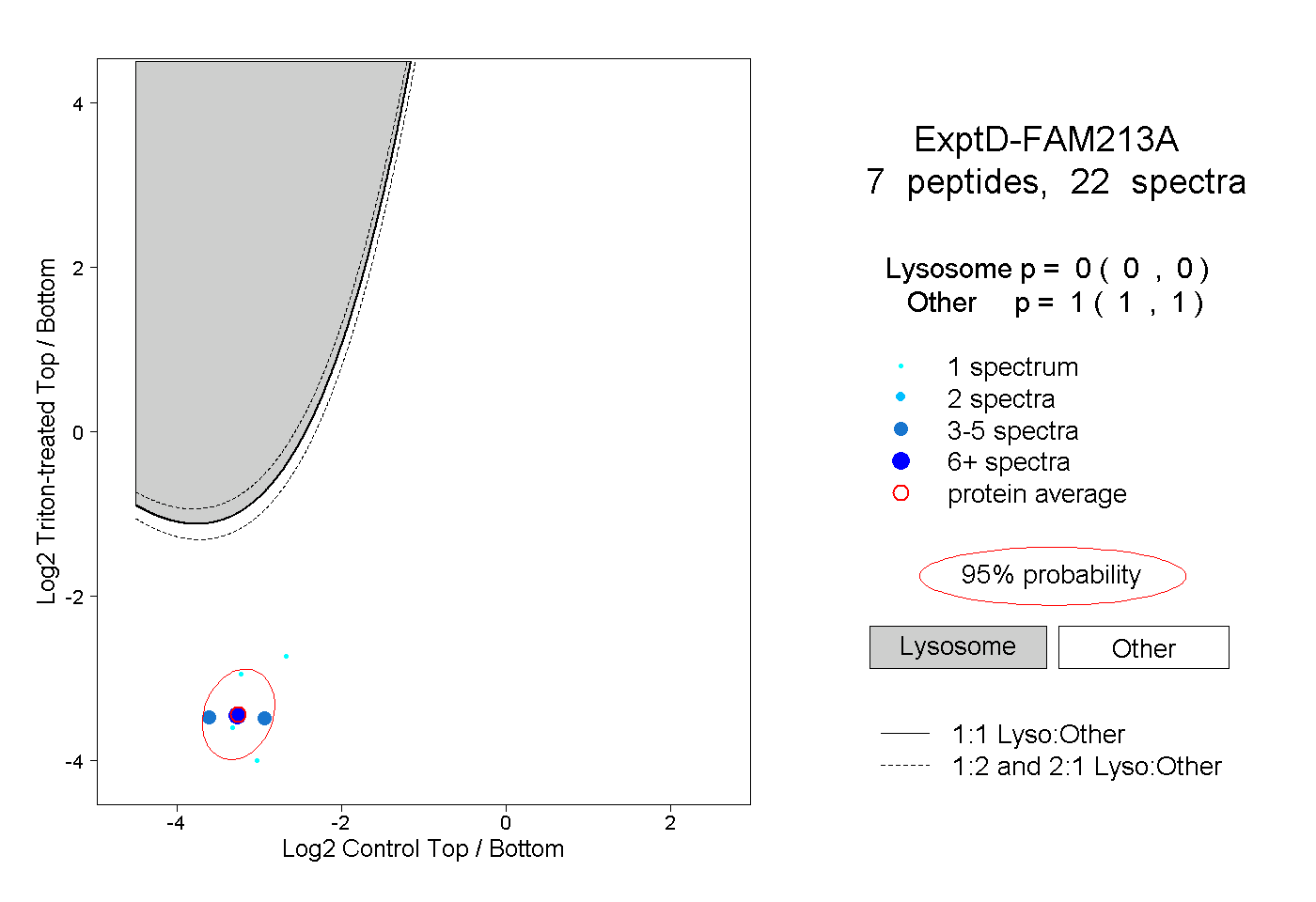 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |