peptides
spectra
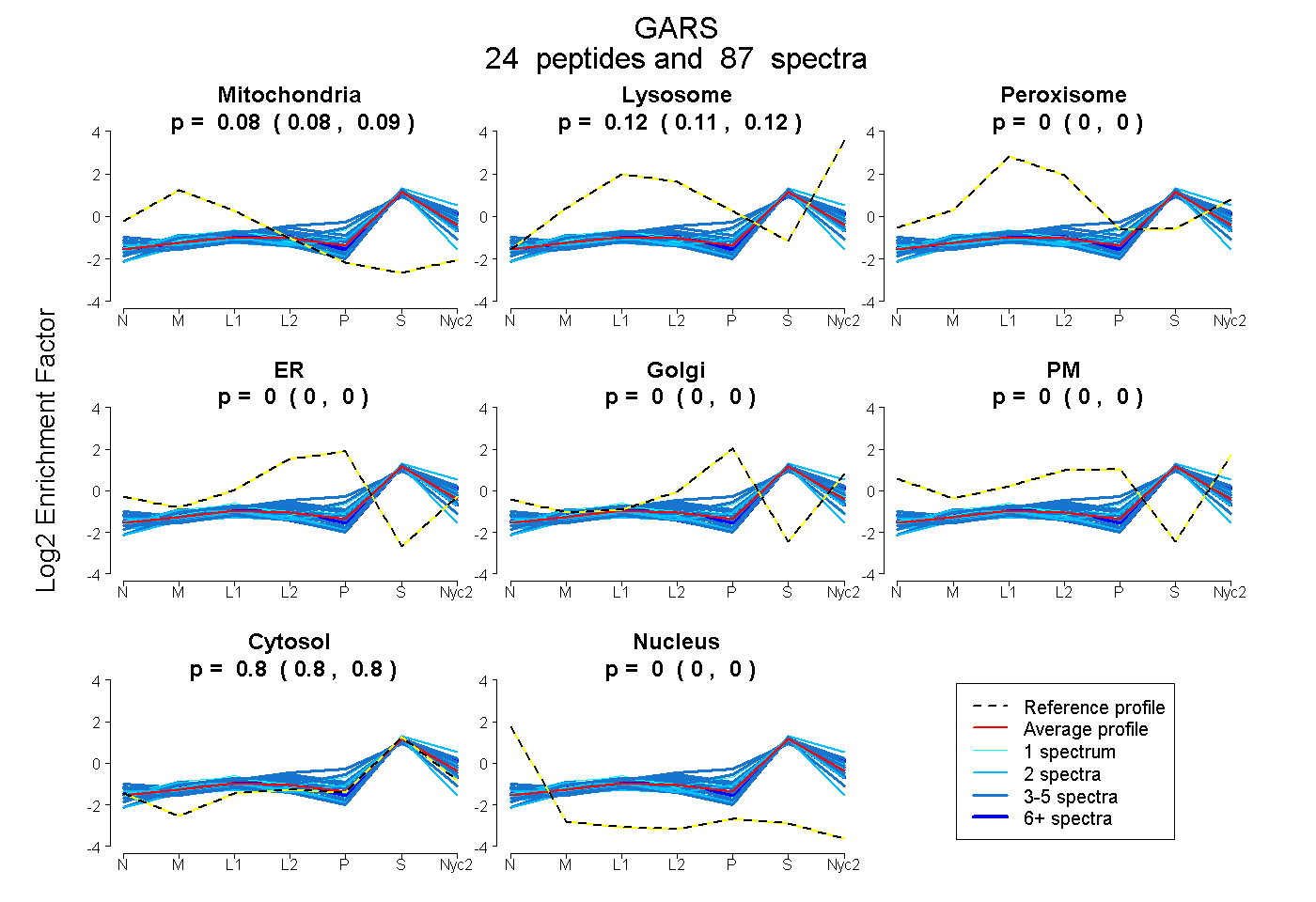
0.082 | 0.086
0.113 | 0.118
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.799 | 0.801
0.000 | 0.000
peptides
spectra
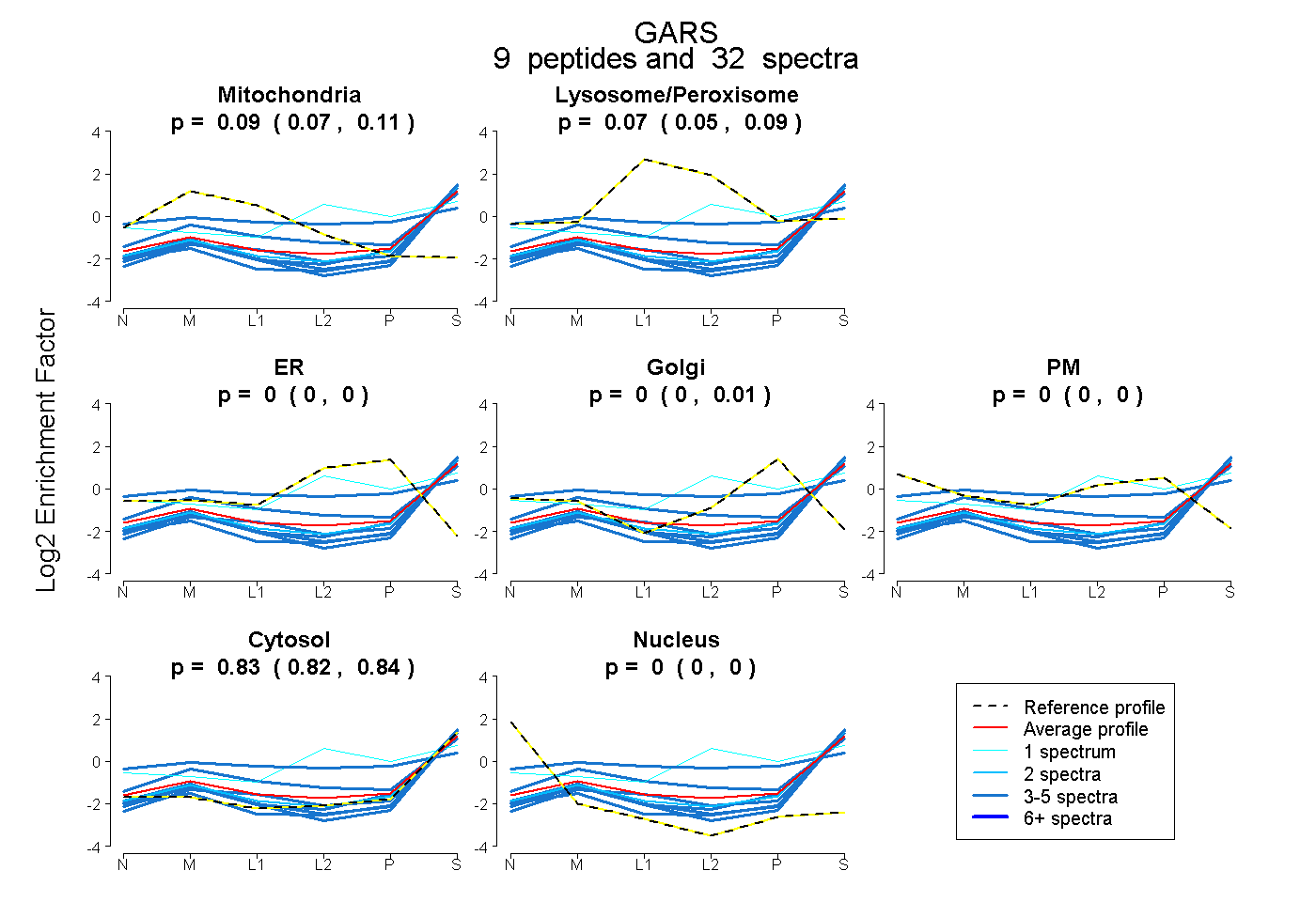
0.075 | 0.108
0.052 | 0.089
0.000 | 0.000
0.000 | 0.006
0.000 | 0.000
0.822 | 0.843
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
87 spectra |
 |
0.084 0.082 | 0.086 |
0.116 0.113 | 0.118 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.800 0.799 | 0.801 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
32 spectra |
 |
0.094 0.075 | 0.108 |
0.073 0.052 | 0.089 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.006 |
0.000 0.000 | 0.000 |
0.834 0.822 | 0.843 |
0.000 0.000 | 0.000 |
| 5 spectra, AQVTGQSAR | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.934 | 0.000 | |||
| 3 spectra, APQVDVDR | 0.031 | 0.000 | 0.000 | 0.000 | 0.000 | 0.969 | 0.000 | |||
| 5 spectra, AEVSELPSVVR | 0.149 | 0.179 | 0.000 | 0.000 | 0.000 | 0.672 | 0.000 | |||
| 4 spectra, ADHLLK | 0.026 | 0.037 | 0.000 | 0.000 | 0.000 | 0.937 | 0.000 | |||
| 3 spectra, VDDSSGSIGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, TVNVVQFEPNK | 0.075 | 0.003 | 0.000 | 0.000 | 0.000 | 0.922 | 0.000 | |||
| 4 spectra, ELSEALTR | 0.006 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.000 | |||
| 1 spectrum, LPFAAAQIGNSFR | 0.000 | 0.274 | 0.288 | 0.000 | 0.019 | 0.419 | 0.000 | |||
| 5 spectra, TLHVEEVVPSVIEPSFGLGR | 0.044 | 0.325 | 0.000 | 0.076 | 0.204 | 0.352 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
97 spectra |
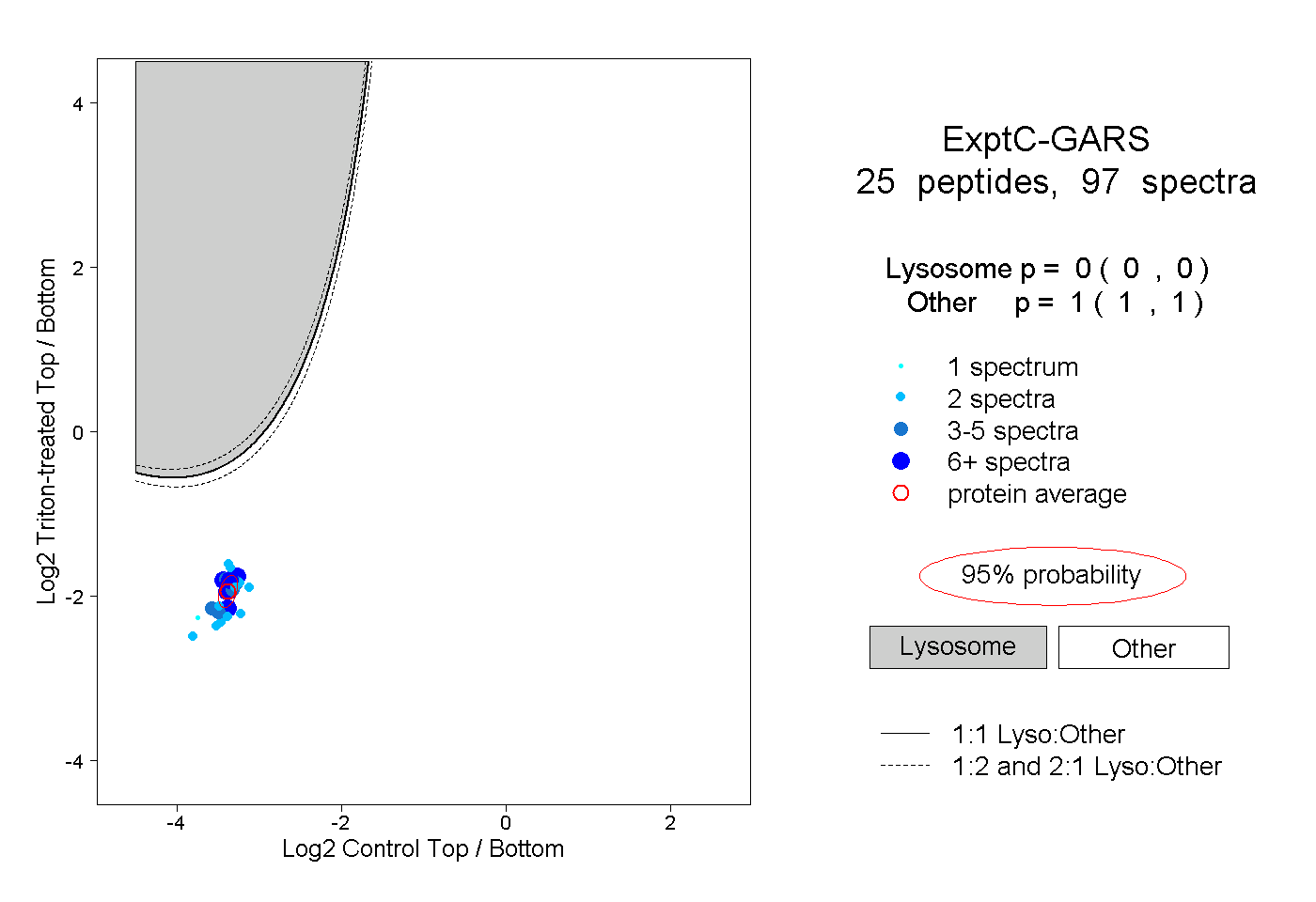 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
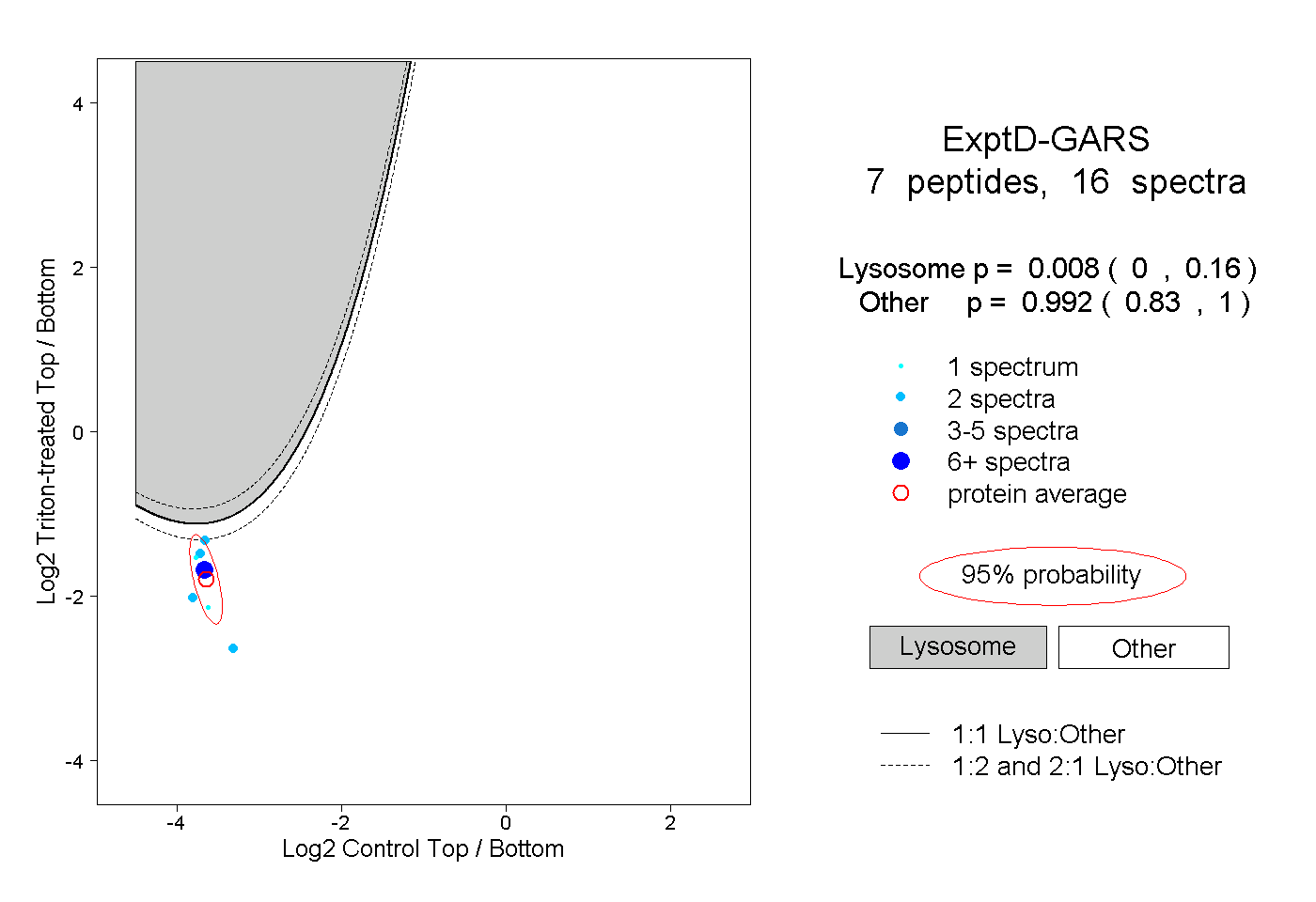 |
0.008 0.000 | 0.160 |
0.992 0.830 | 1.000 |