peptides
spectra
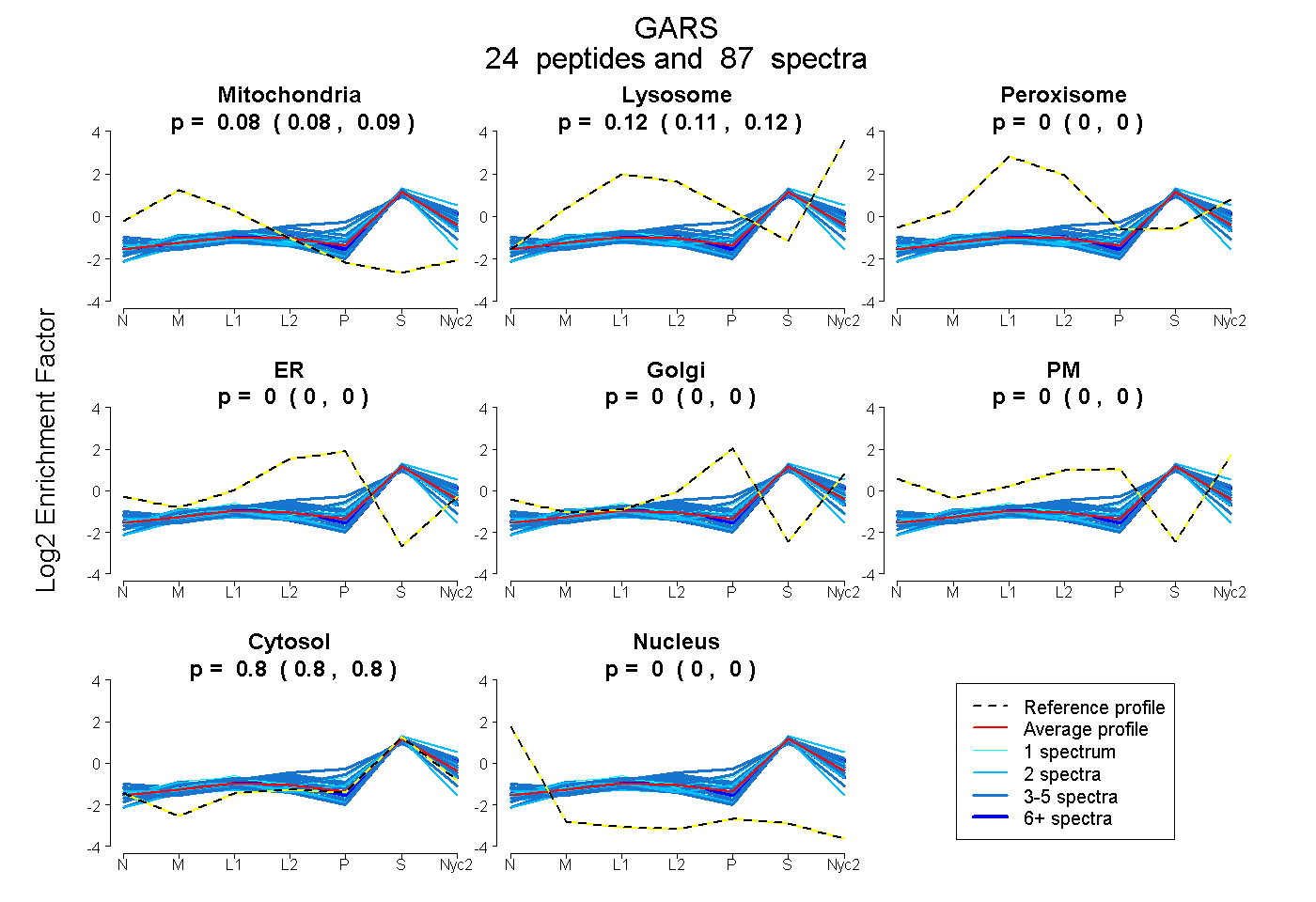
0.082 | 0.086
0.113 | 0.118
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.799 | 0.801
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
87 spectra |
 |
0.084 0.082 | 0.086 |
0.116 0.113 | 0.118 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.800 0.799 | 0.801 |
0.000 0.000 | 0.000 |
| 14 spectra, AQVTGQSAR | 0.124 | 0.025 | 0.006 | 0.000 | 0.000 | 0.000 | 0.844 | 0.000 | ||
| 4 spectra, AEVSELPSVVR | 0.106 | 0.120 | 0.000 | 0.000 | 0.000 | 0.000 | 0.774 | 0.000 | ||
| 5 spectra, ADHLLK | 0.061 | 0.089 | 0.078 | 0.020 | 0.000 | 0.000 | 0.753 | 0.000 | ||
| 5 spectra, NNIIQTWR | 0.085 | 0.157 | 0.000 | 0.000 | 0.000 | 0.000 | 0.757 | 0.000 | ||
| 1 spectrum, ELALQPK | 0.102 | 0.118 | 0.002 | 0.000 | 0.000 | 0.000 | 0.778 | 0.000 | ||
| 2 spectra, AVAELK | 0.050 | 0.066 | 0.067 | 0.000 | 0.000 | 0.000 | 0.817 | 0.000 | ||
| 3 spectra, TVNVVQFEPNK | 0.050 | 0.191 | 0.012 | 0.000 | 0.000 | 0.000 | 0.748 | 0.000 | ||
| 2 spectra, ELSEALTR | 0.099 | 0.016 | 0.000 | 0.000 | 0.000 | 0.000 | 0.884 | 0.000 | ||
| 1 spectrum, LPFAAAQIGNSFR | 0.090 | 0.151 | 0.042 | 0.000 | 0.000 | 0.000 | 0.717 | 0.000 | ||
| 5 spectra, APQVDVDR | 0.065 | 0.090 | 0.005 | 0.000 | 0.000 | 0.000 | 0.840 | 0.000 | ||
| 1 spectrum, QQGDFVR | 0.055 | 0.165 | 0.018 | 0.000 | 0.004 | 0.000 | 0.759 | 0.000 | ||
| 2 spectra, DLANGNITWADVEAR | 0.045 | 0.157 | 0.000 | 0.000 | 0.000 | 0.000 | 0.798 | 0.000 | ||
| 4 spectra, NEISPR | 0.044 | 0.212 | 0.000 | 0.000 | 0.000 | 0.000 | 0.744 | 0.000 | ||
| 4 spectra, TPHTATLR | 0.066 | 0.000 | 0.013 | 0.088 | 0.030 | 0.000 | 0.803 | 0.000 | ||
| 4 spectra, DMVSVK | 0.052 | 0.119 | 0.000 | 0.000 | 0.000 | 0.000 | 0.830 | 0.000 | ||
| 4 spectra, LLEFNQGK | 0.069 | 0.090 | 0.078 | 0.000 | 0.000 | 0.000 | 0.763 | 0.000 | ||
| 4 spectra, VDDSSGSIGR | 0.096 | 0.026 | 0.000 | 0.000 | 0.000 | 0.000 | 0.879 | 0.000 | ||
| 2 spectra, IYLYLTK | 0.000 | 0.171 | 0.000 | 0.000 | 0.000 | 0.000 | 0.829 | 0.000 | ||
| 4 spectra, FADFMVK | 0.104 | 0.047 | 0.000 | 0.000 | 0.000 | 0.000 | 0.849 | 0.000 | ||
| 7 spectra, GEFTIETEGK | 0.045 | 0.180 | 0.000 | 0.000 | 0.000 | 0.000 | 0.774 | 0.000 | ||
| 2 spectra, VGISPDK | 0.114 | 0.068 | 0.000 | 0.000 | 0.000 | 0.000 | 0.819 | 0.000 | ||
| 2 spectra, TSYGWIEIVGCADR | 0.229 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.771 | 0.000 | ||
| 4 spectra, DDIVDR | 0.000 | 0.074 | 0.126 | 0.000 | 0.144 | 0.000 | 0.656 | 0.000 | ||
| 1 spectrum, TLHVEEVVPSVIEPSFGLGR | 0.107 | 0.000 | 0.113 | 0.000 | 0.026 | 0.000 | 0.754 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
32 spectra |
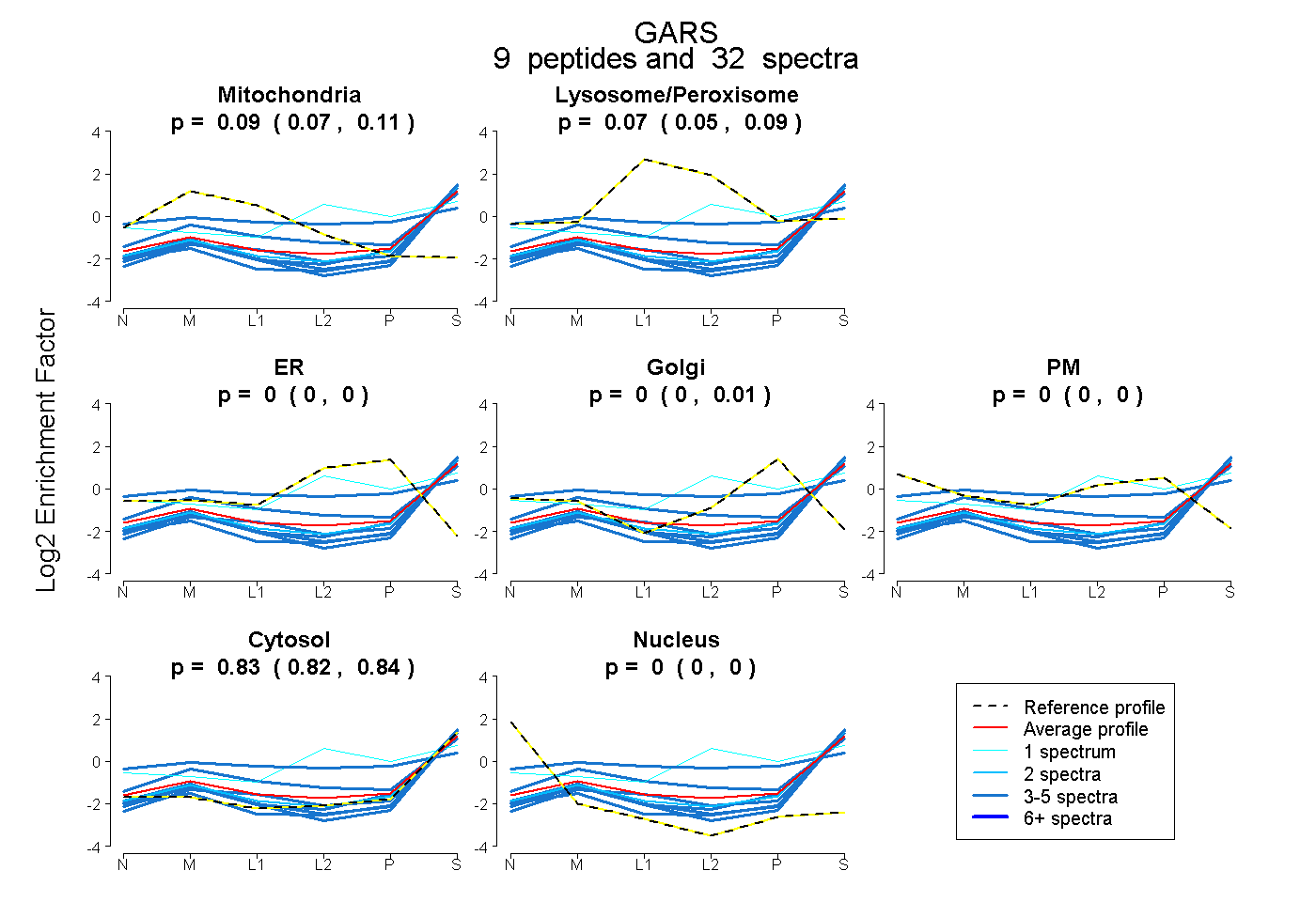 |
0.094 0.075 | 0.108 |
0.073 0.052 | 0.089 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.006 |
0.000 0.000 | 0.000 |
0.834 0.822 | 0.843 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
97 spectra |
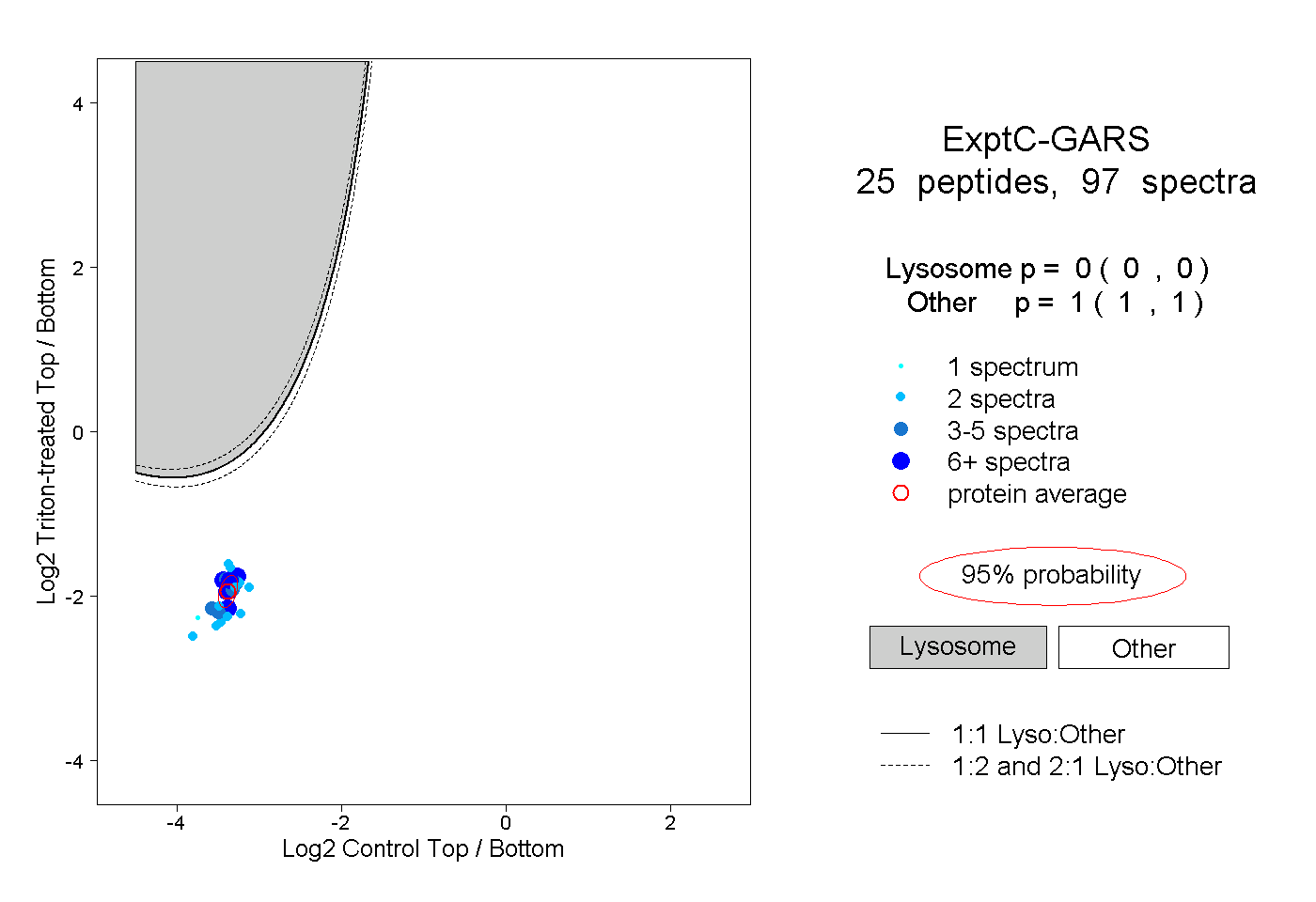 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
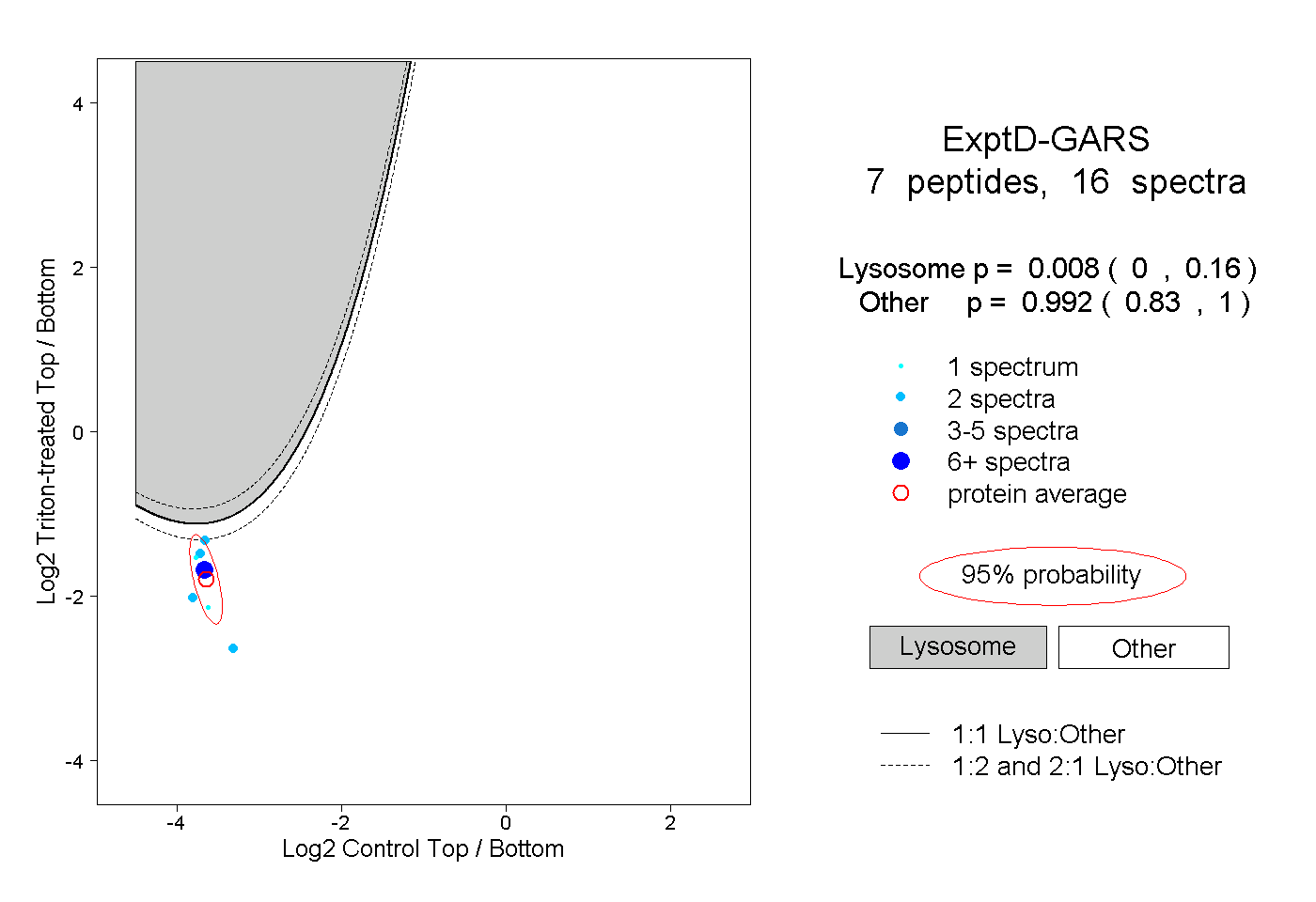 |
0.008 0.000 | 0.160 |
0.992 0.830 | 1.000 |