peptides
spectra
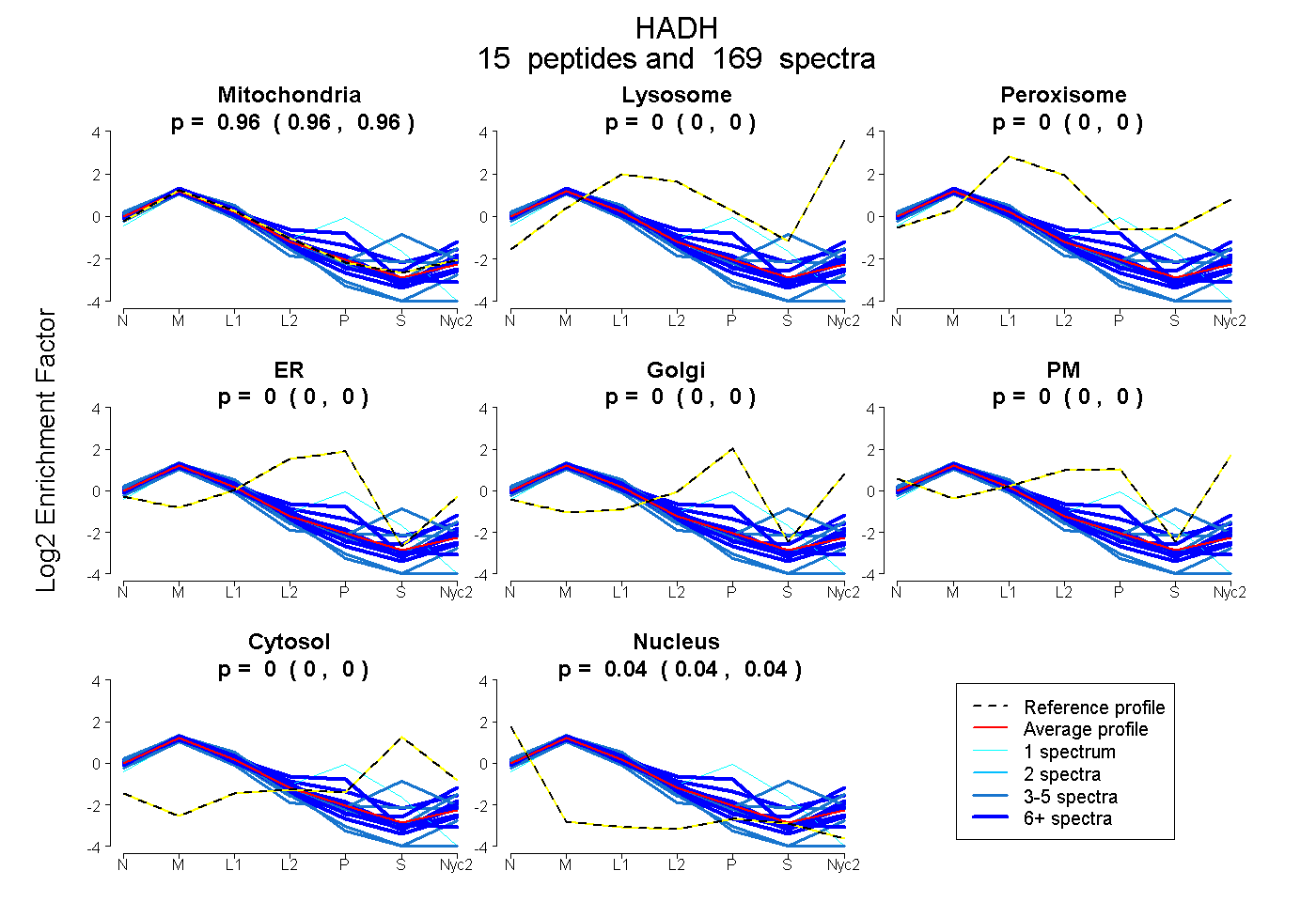
0.956 | 0.959
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.041 | 0.044
peptides
spectra
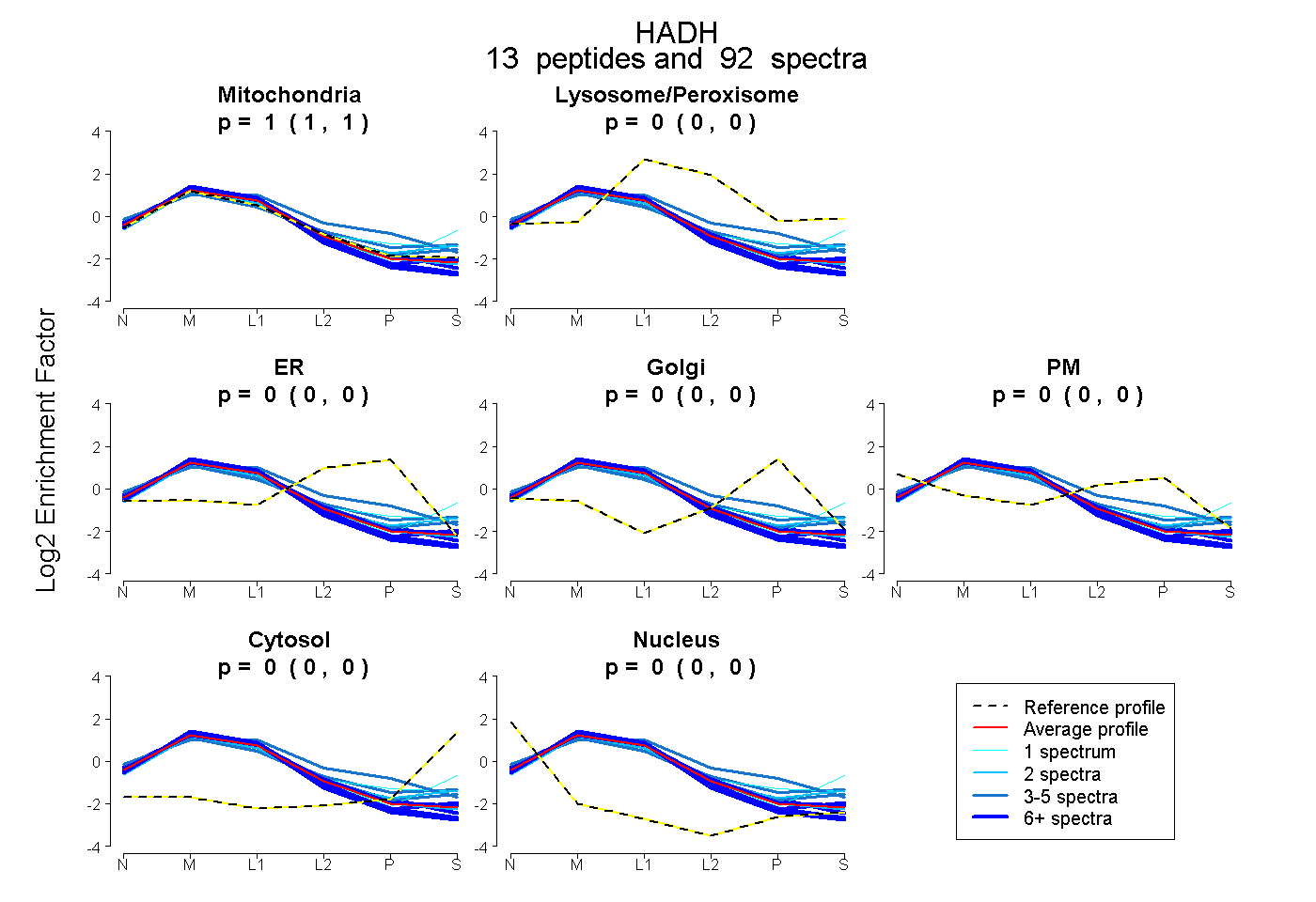
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
169 spectra |
 |
0.957 0.956 | 0.959 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.043 0.041 | 0.044 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
92 spectra |
 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, HPVSCK | 0.644 | 0.193 | 0.000 | 0.000 | 0.164 | 0.000 | 0.000 | |||
| 2 spectra, GIEESLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LGAGYPMGPFELLDYVGLDTTK | 0.898 | 0.038 | 0.000 | 0.000 | 0.000 | 0.065 | 0.000 | |||
| 4 spectra, FAGLHFFNPVPMMK | 0.792 | 0.081 | 0.000 | 0.000 | 0.068 | 0.059 | 0.000 | |||
| 6 spectra, LLVPYLIEAIR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, DTPGFIVNR | 0.975 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.025 | |||
| 18 spectra, TFESLVDFCK | 0.996 | 0.004 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FTENPK | 0.820 | 0.102 | 0.000 | 0.062 | 0.002 | 0.014 | 0.000 | |||
| 11 spectra, TGEGFYK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, LVEVLK | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | |||
| 1 spectrum, FAAEHTIFASNTSSLQITNIANATTR | 0.762 | 0.124 | 0.000 | 0.000 | 0.000 | 0.114 | 0.000 | |||
| 15 spectra, AADEFVEK | 0.989 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.011 | |||
| 3 spectra, EDIDTAMK | 0.921 | 0.030 | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1096 spectra |
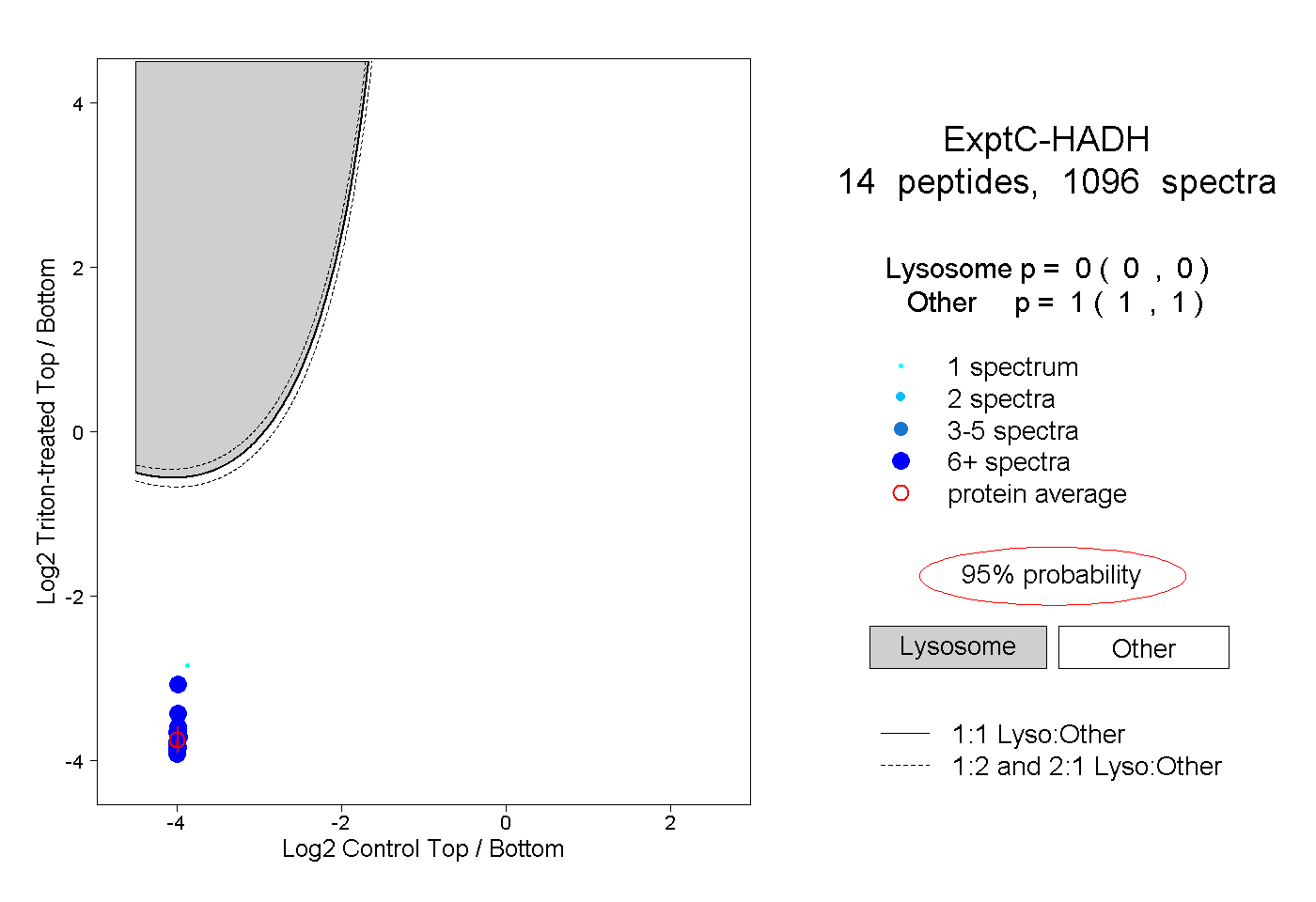 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
64 spectra |
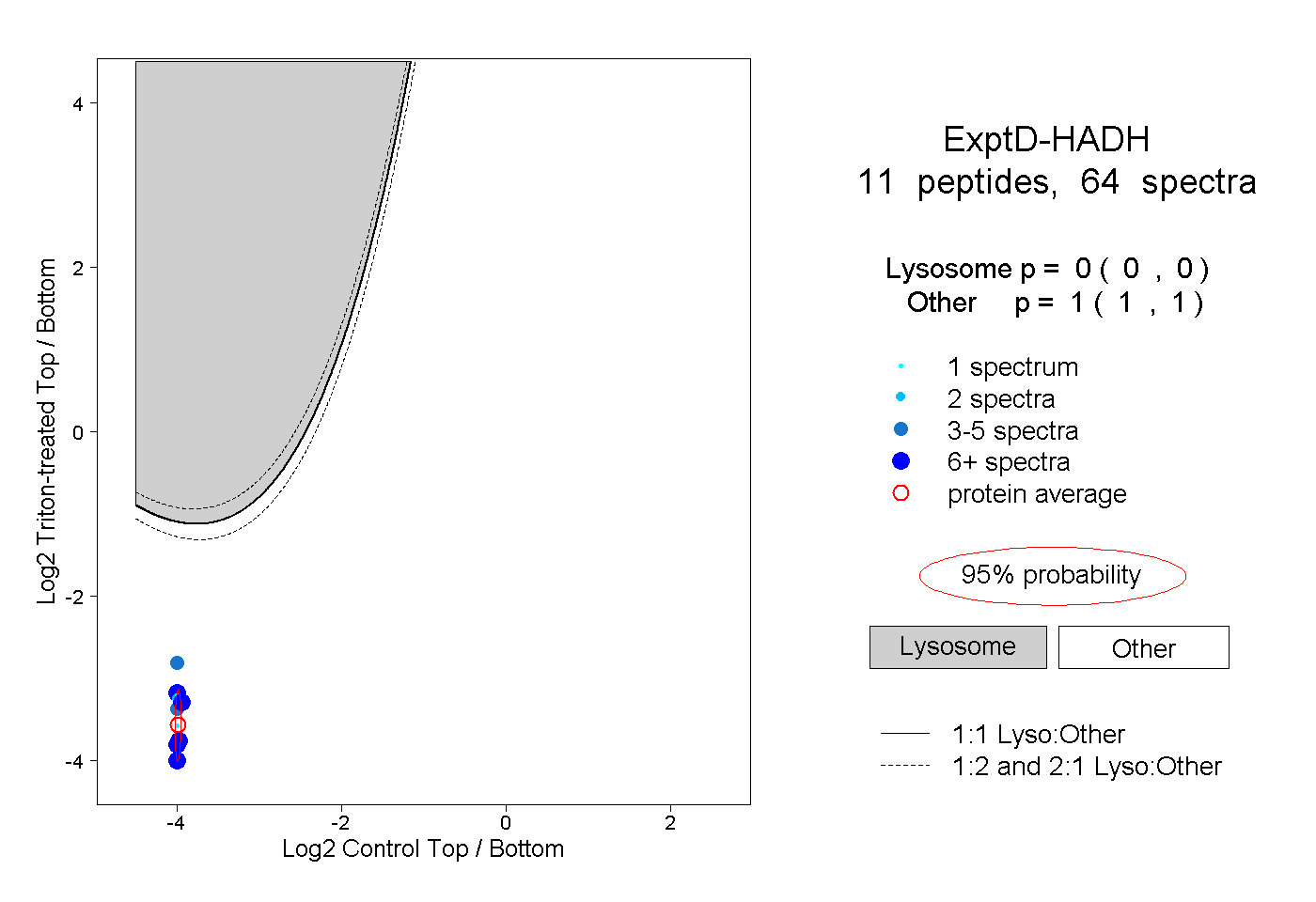 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |