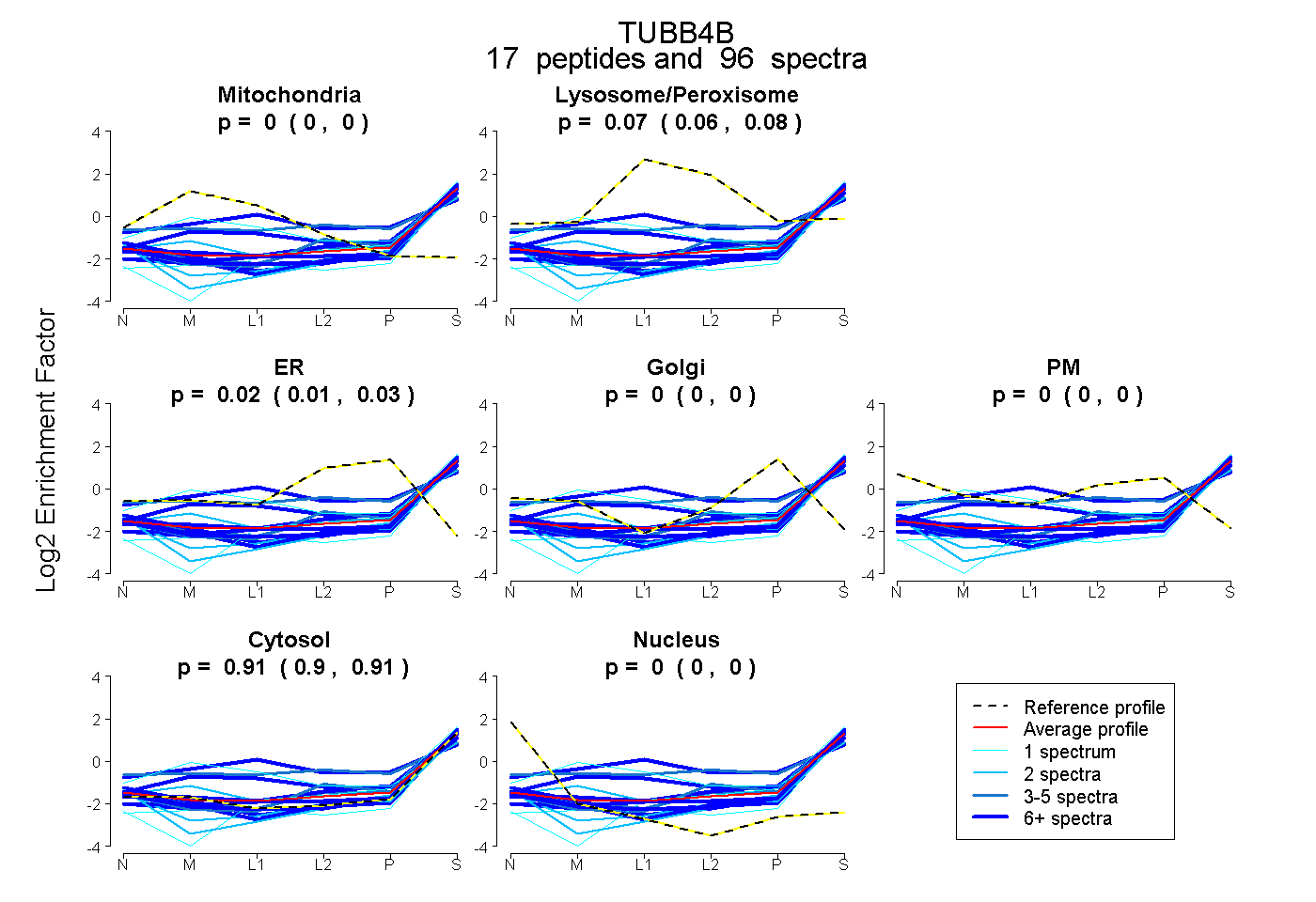
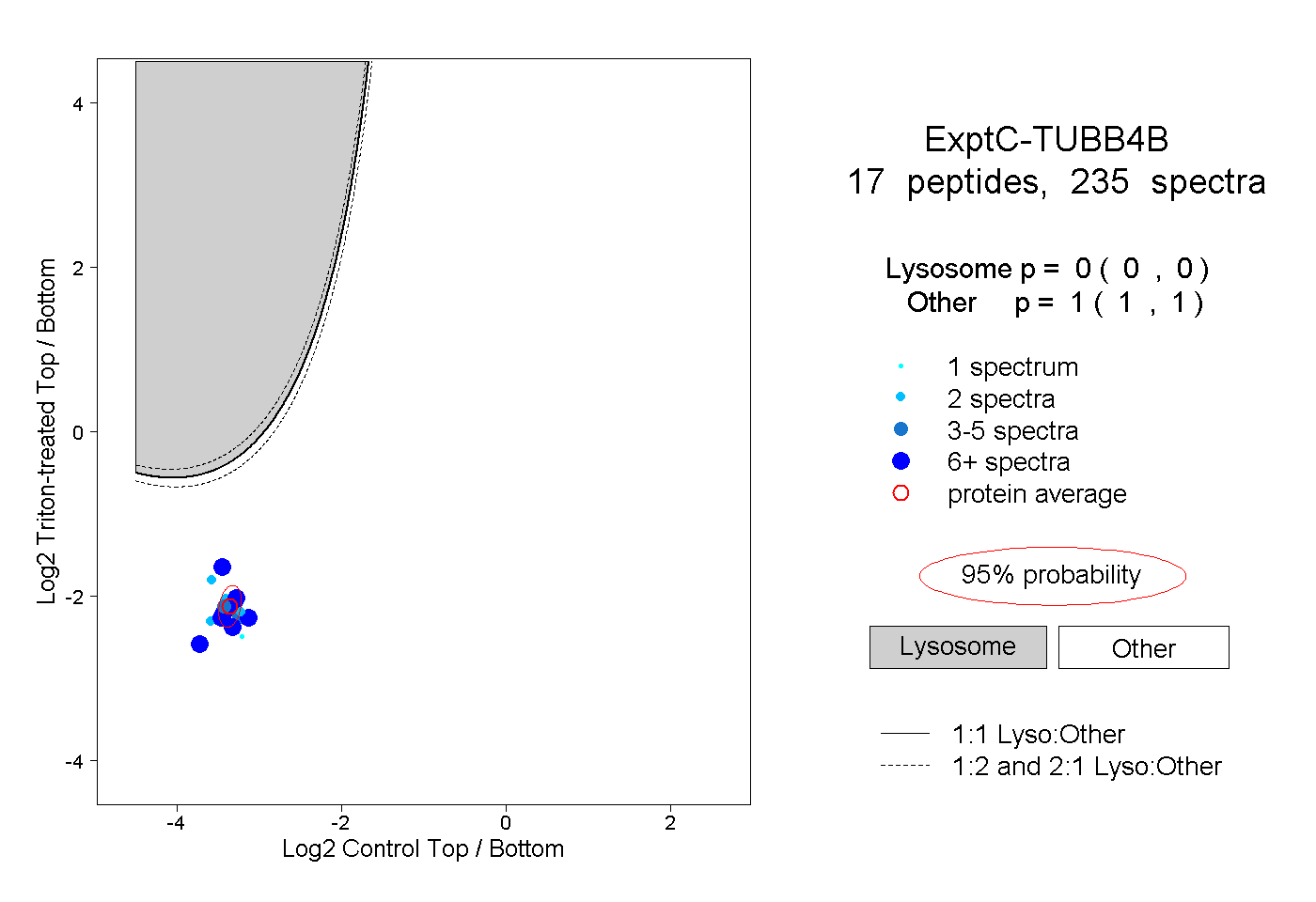
| 1 spectrum, MSATFIGNSTAIQELFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, ISEQFTAMFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EEYPDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EIVHLQAGQCGNQIGAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, YLTVAAVFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 53 spectra, LAVNMVPFPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ALTVPELTQQMFDAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NSSYFVEWIPNNVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, LHFFMPGFAPLTSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, AVLVDLEPGTMDSVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 67 spectra, TAVCDIPPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, FPGQLNADLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SGPFGQIFRPDNFVFGQSGAGNNWAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, INVYYNEATGGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, EIVHIQAGQCGNQIGAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, EVDEQMLNVQNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, NMMAACDPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |