peptides
spectra
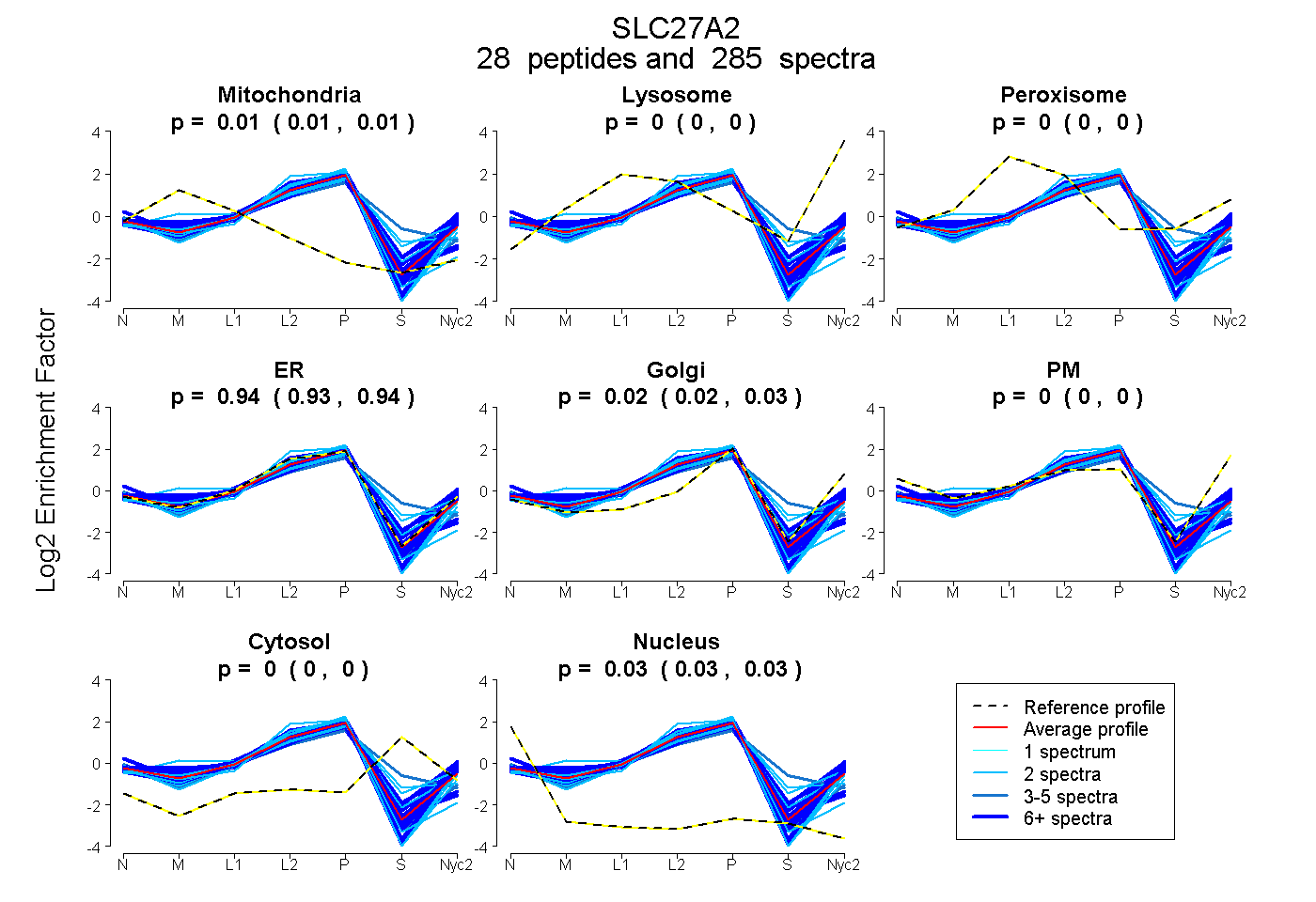
0.009 | 0.011
0.000 | 0.000
0.000 | 0.000
0.934 | 0.941
0.021 | 0.028
0.000 | 0.000
0.000 | 0.000
0.026 | 0.029
peptides
spectra
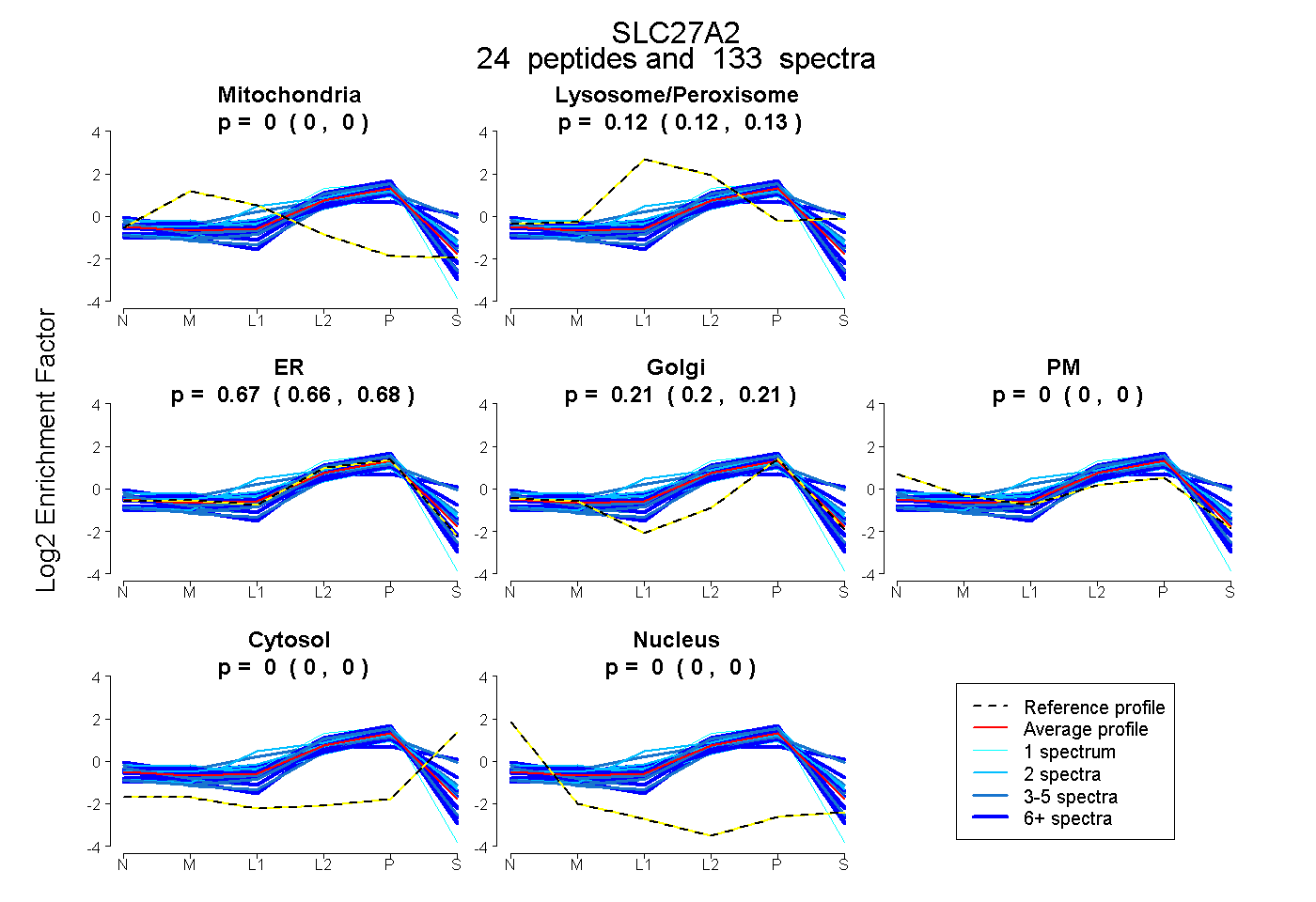
0.000 | 0.000
0.116 | 0.127
0.661 | 0.684
0.196 | 0.210
0.000 | 0.000
0.000 | 0.004
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
285 spectra |
 |
0.010 0.009 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.938 0.934 | 0.941 |
0.024 0.021 | 0.028 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.026 | 0.029 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
133 spectra |
 |
0.000 0.000 | 0.000 |
0.122 0.116 | 0.127 |
0.672 0.661 | 0.684 |
0.205 0.196 | 0.210 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.004 |
0.000 0.000 | 0.000 |
| 6 spectra, VGDTFR | 0.000 | 0.306 | 0.172 | 0.459 | 0.000 | 0.063 | 0.000 | |||
| 9 spectra, IALGNGLR | 0.000 | 0.000 | 0.935 | 0.032 | 0.000 | 0.000 | 0.033 | |||
| 9 spectra, ENFIYFHDR | 0.000 | 0.325 | 0.263 | 0.190 | 0.000 | 0.221 | 0.000 | |||
| 3 spectra, DETLTYAQVDR | 0.000 | 0.000 | 0.905 | 0.006 | 0.000 | 0.089 | 0.000 | |||
| 2 spectra, YLCNTPQKPNDR | 0.000 | 0.316 | 0.345 | 0.339 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VTLMEEGFNPSVIK | 0.000 | 0.158 | 0.578 | 0.000 | 0.000 | 0.265 | 0.000 | |||
| 7 spectra, AATINHHR | 0.000 | 0.197 | 0.384 | 0.174 | 0.245 | 0.000 | 0.000 | |||
| 11 spectra, ITELTPFFGYAGGK | 0.000 | 0.000 | 0.947 | 0.023 | 0.000 | 0.000 | 0.030 | |||
| 2 spectra, GEVGLLICK | 0.000 | 0.269 | 0.173 | 0.371 | 0.187 | 0.000 | 0.000 | |||
| 6 spectra, DTLYFMDDAEK | 0.000 | 0.000 | 0.783 | 0.217 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, TPHKPFLLFR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, TILHVFLEQAR | 0.000 | 0.040 | 0.919 | 0.029 | 0.002 | 0.000 | 0.010 | |||
| 6 spectra, LWYGTSLALR | 0.000 | 0.000 | 0.830 | 0.170 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FSASQFWDDCR | 0.000 | 0.278 | 0.084 | 0.534 | 0.104 | 0.000 | 0.000 | |||
| 1 spectrum, IGAVGR | 0.000 | 0.054 | 0.827 | 0.118 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, YNATVIQYIGELLR | 0.000 | 0.000 | 0.998 | 0.000 | 0.002 | 0.000 | 0.000 | |||
| 3 spectra, IGMASIK | 0.000 | 0.000 | 0.587 | 0.125 | 0.139 | 0.149 | 0.000 | |||
| 7 spectra, LGCPMACLNYNIR | 0.000 | 0.129 | 0.648 | 0.127 | 0.057 | 0.039 | 0.000 | |||
| 5 spectra, ENYLQK | 0.000 | 0.221 | 0.474 | 0.304 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, IQDTIEITGTFK | 0.000 | 0.335 | 0.417 | 0.248 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TYVPMTEDIYNAIIDK | 0.000 | 0.306 | 0.588 | 0.106 | 0.000 | 0.000 | 0.000 | |||
| 16 spectra, ALHDHLGLR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FFLQLANMAR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DANGYCIK | 0.000 | 0.117 | 0.702 | 0.181 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
321 spectra |
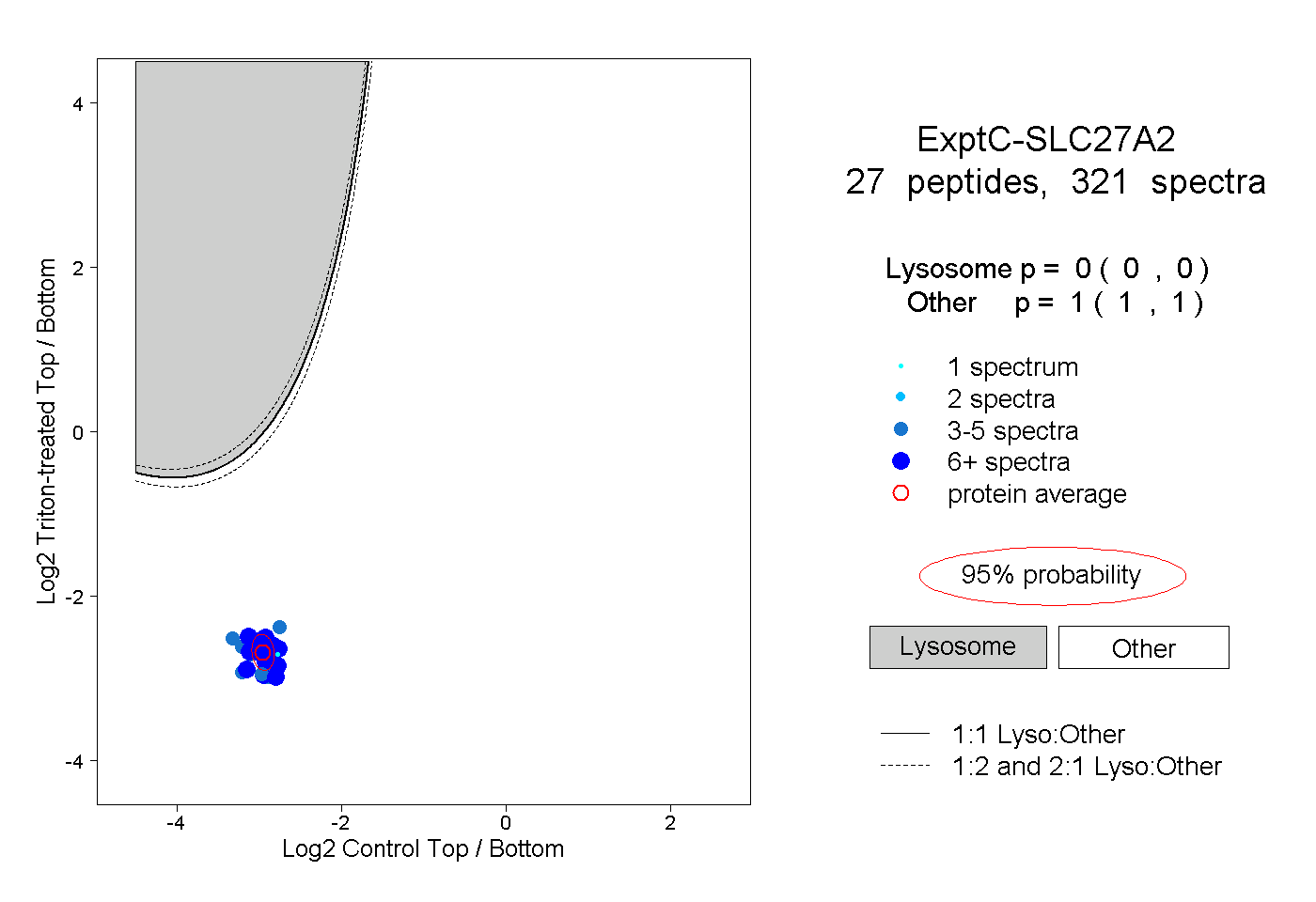 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
28 spectra |
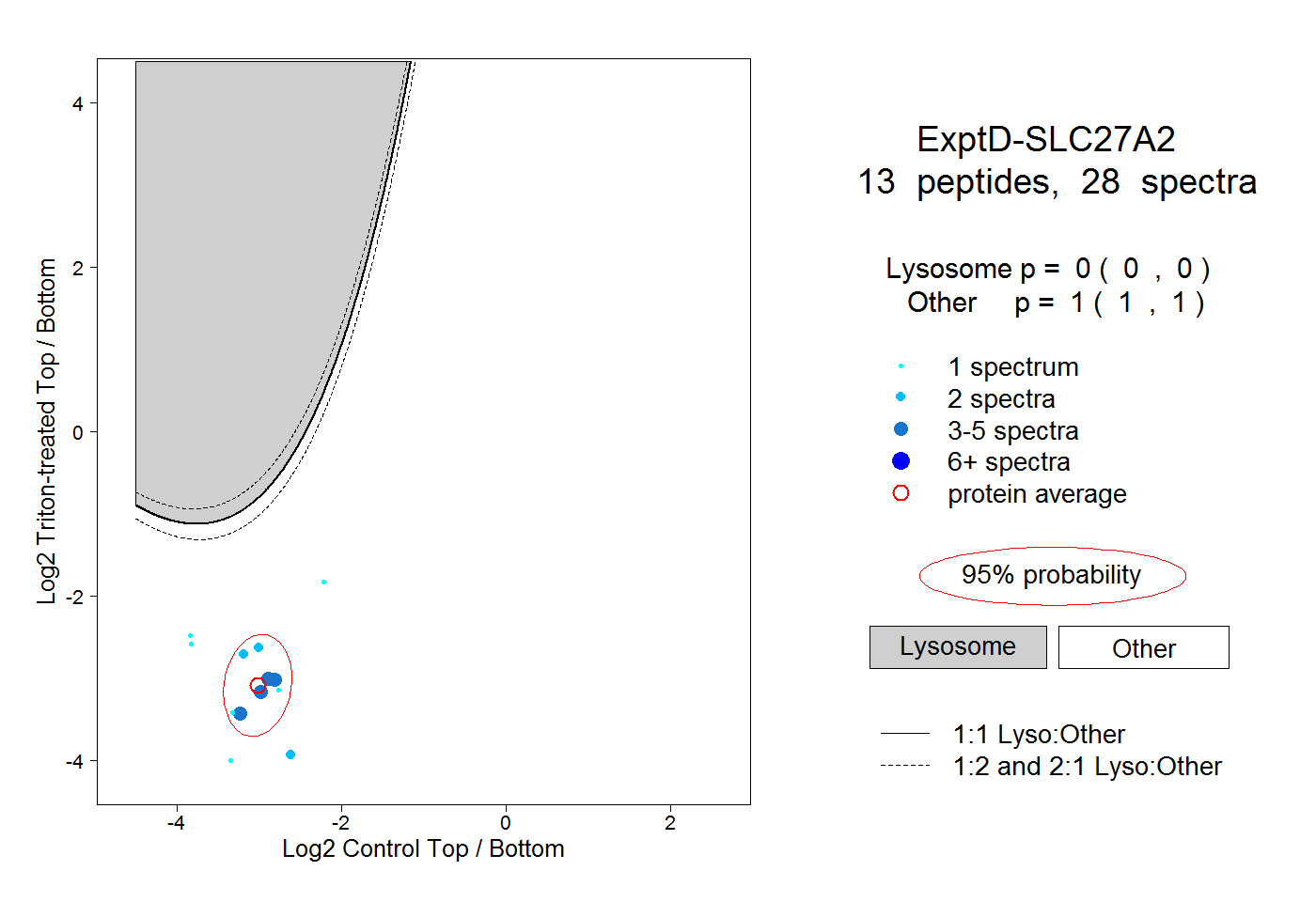 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |