peptides
spectra
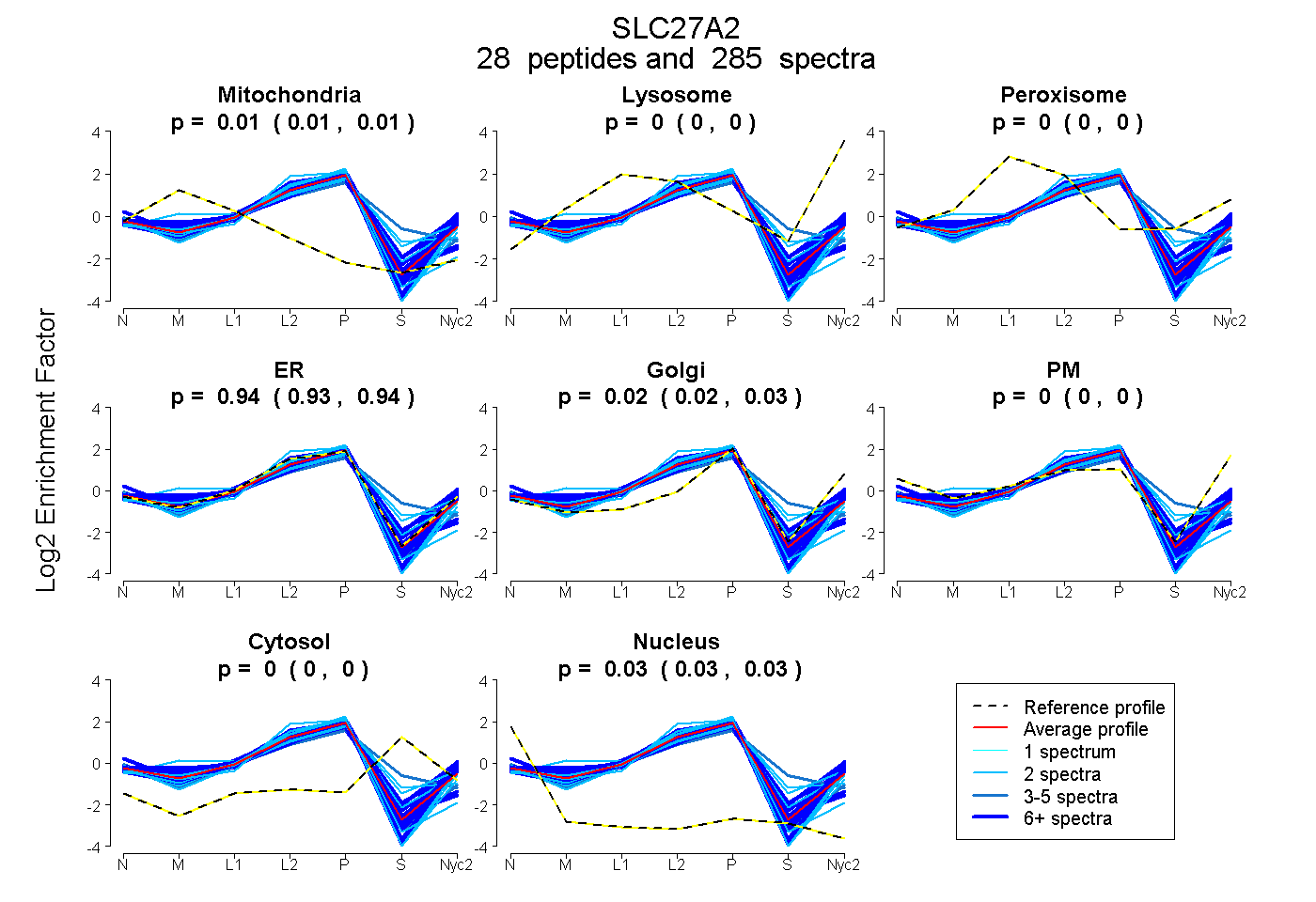
0.009 | 0.011
0.000 | 0.000
0.000 | 0.000
0.934 | 0.941
0.021 | 0.028
0.000 | 0.000
0.000 | 0.000
0.026 | 0.029
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
285 spectra |
 |
0.010 0.009 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.938 0.934 | 0.941 |
0.024 0.021 | 0.028 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.026 | 0.029 |
| 8 spectra, VGDTFR | 0.000 | 0.000 | 0.000 | 0.905 | 0.080 | 0.000 | 0.000 | 0.015 | ||
| 16 spectra, IALGNGLR | 0.000 | 0.000 | 0.000 | 0.862 | 0.048 | 0.089 | 0.000 | 0.000 | ||
| 12 spectra, ENFIYFHDR | 0.019 | 0.000 | 0.126 | 0.594 | 0.214 | 0.031 | 0.016 | 0.000 | ||
| 21 spectra, DETLTYAQVDR | 0.000 | 0.000 | 0.000 | 0.901 | 0.078 | 0.000 | 0.000 | 0.021 | ||
| 2 spectra, YLCNTPQKPNDR | 0.000 | 0.000 | 0.000 | 0.935 | 0.000 | 0.000 | 0.000 | 0.065 | ||
| 16 spectra, AATINHHR | 0.000 | 0.000 | 0.051 | 0.827 | 0.000 | 0.068 | 0.002 | 0.052 | ||
| 5 spectra, ITELTPFFGYAGGK | 0.000 | 0.000 | 0.000 | 0.903 | 0.064 | 0.000 | 0.000 | 0.033 | ||
| 4 spectra, GEVGLLICK | 0.000 | 0.000 | 0.044 | 0.673 | 0.000 | 0.000 | 0.283 | 0.000 | ||
| 39 spectra, DTLYFMDDAEK | 0.000 | 0.000 | 0.001 | 0.828 | 0.061 | 0.000 | 0.110 | 0.000 | ||
| 17 spectra, TPHKPFLLFR | 0.000 | 0.000 | 0.000 | 0.891 | 0.083 | 0.000 | 0.000 | 0.025 | ||
| 14 spectra, TILHVFLEQAR | 0.043 | 0.000 | 0.000 | 0.821 | 0.094 | 0.042 | 0.000 | 0.000 | ||
| 19 spectra, LWYGTSLALR | 0.000 | 0.000 | 0.000 | 0.968 | 0.032 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, FSASQFWDDCR | 0.046 | 0.000 | 0.000 | 0.905 | 0.000 | 0.000 | 0.000 | 0.048 | ||
| 17 spectra, IGAVGR | 0.104 | 0.000 | 0.000 | 0.776 | 0.120 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, YNATVIQYIGELLR | 0.000 | 0.000 | 0.000 | 0.978 | 0.000 | 0.000 | 0.000 | 0.022 | ||
| 6 spectra, LGCPMACLNYNIR | 0.027 | 0.000 | 0.000 | 0.892 | 0.000 | 0.000 | 0.000 | 0.081 | ||
| 13 spectra, IGMASIK | 0.000 | 0.000 | 0.000 | 0.869 | 0.116 | 0.000 | 0.000 | 0.016 | ||
| 13 spectra, ENYLQK | 0.015 | 0.000 | 0.000 | 0.877 | 0.082 | 0.026 | 0.000 | 0.000 | ||
| 2 spectra, SLLHCFQCCGAK | 0.000 | 0.000 | 0.037 | 0.772 | 0.000 | 0.000 | 0.191 | 0.000 | ||
| 2 spectra, IQDTIEITGTFK | 0.000 | 0.000 | 0.000 | 0.845 | 0.045 | 0.000 | 0.084 | 0.026 | ||
| 6 spectra, GDVYFNSGDLLMIDR | 0.000 | 0.000 | 0.000 | 0.867 | 0.124 | 0.000 | 0.000 | 0.008 | ||
| 2 spectra, ENYEFNGK | 0.144 | 0.000 | 0.000 | 0.850 | 0.006 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TYVPMTEDIYNAIIDK | 0.000 | 0.000 | 0.000 | 0.817 | 0.006 | 0.000 | 0.177 | 0.000 | ||
| 2 spectra, TQTEK | 0.000 | 0.000 | 0.000 | 0.991 | 0.000 | 0.000 | 0.000 | 0.009 | ||
| 2 spectra, SNQVAR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 22 spectra, ALHDHLGLR | 0.017 | 0.000 | 0.020 | 0.891 | 0.066 | 0.000 | 0.000 | 0.006 | ||
| 4 spectra, DANGYCIK | 0.000 | 0.000 | 0.000 | 0.931 | 0.000 | 0.000 | 0.000 | 0.069 | ||
| 10 spectra, FFLQLANMAR | 0.000 | 0.000 | 0.000 | 0.963 | 0.000 | 0.037 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
133 spectra |
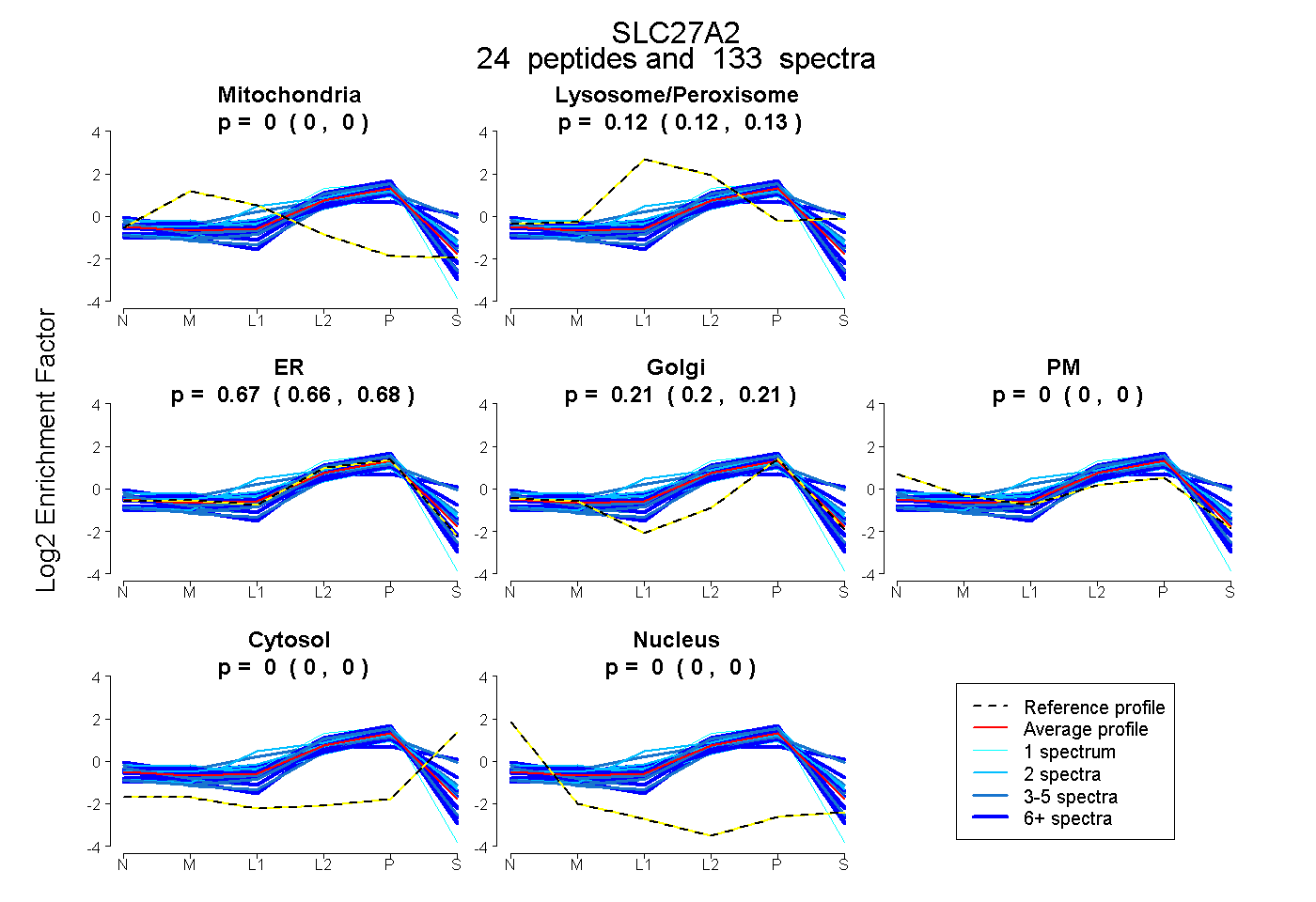 |
0.000 0.000 | 0.000 |
0.122 0.116 | 0.127 |
0.672 0.661 | 0.684 |
0.205 0.196 | 0.210 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.004 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
321 spectra |
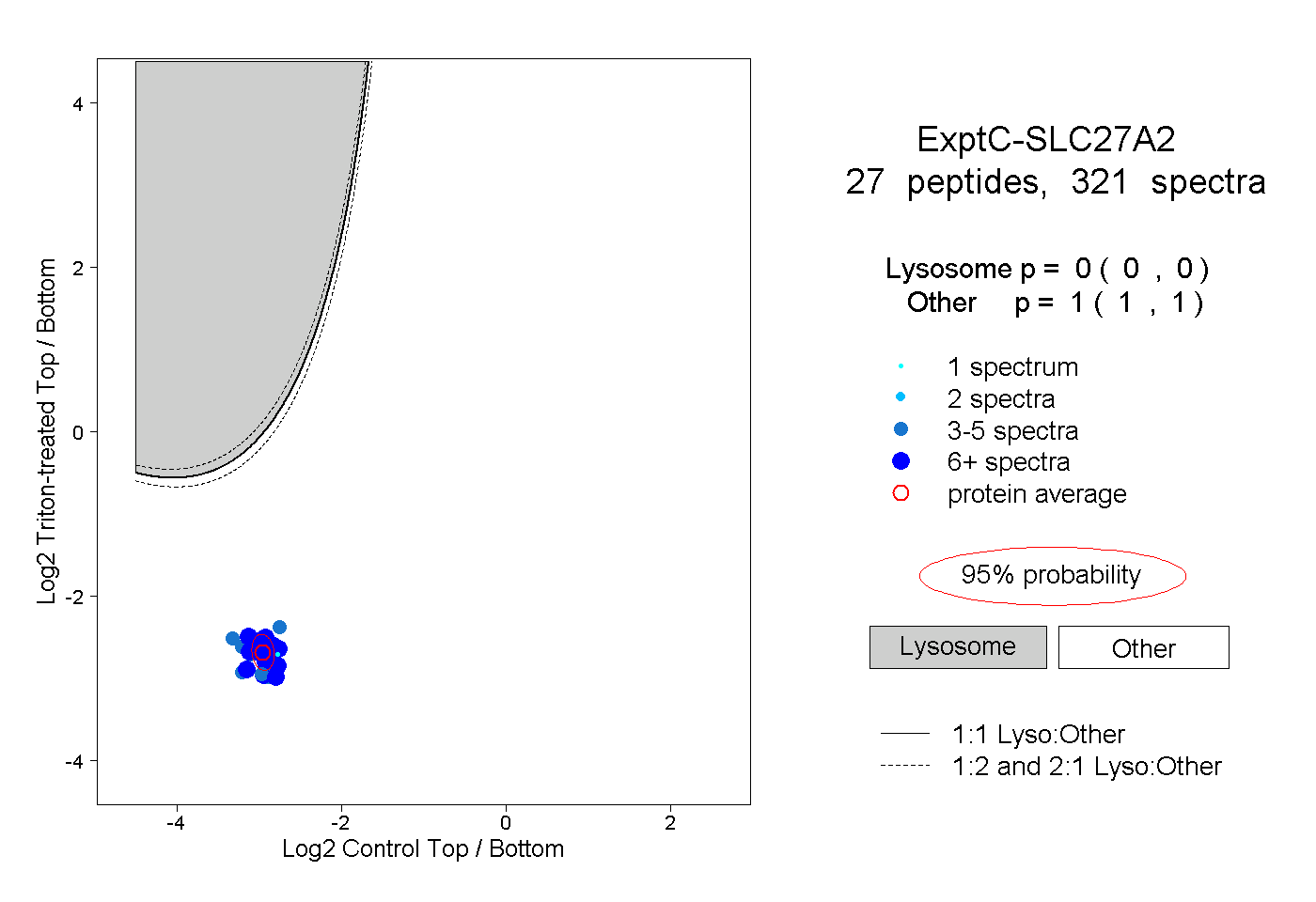 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
28 spectra |
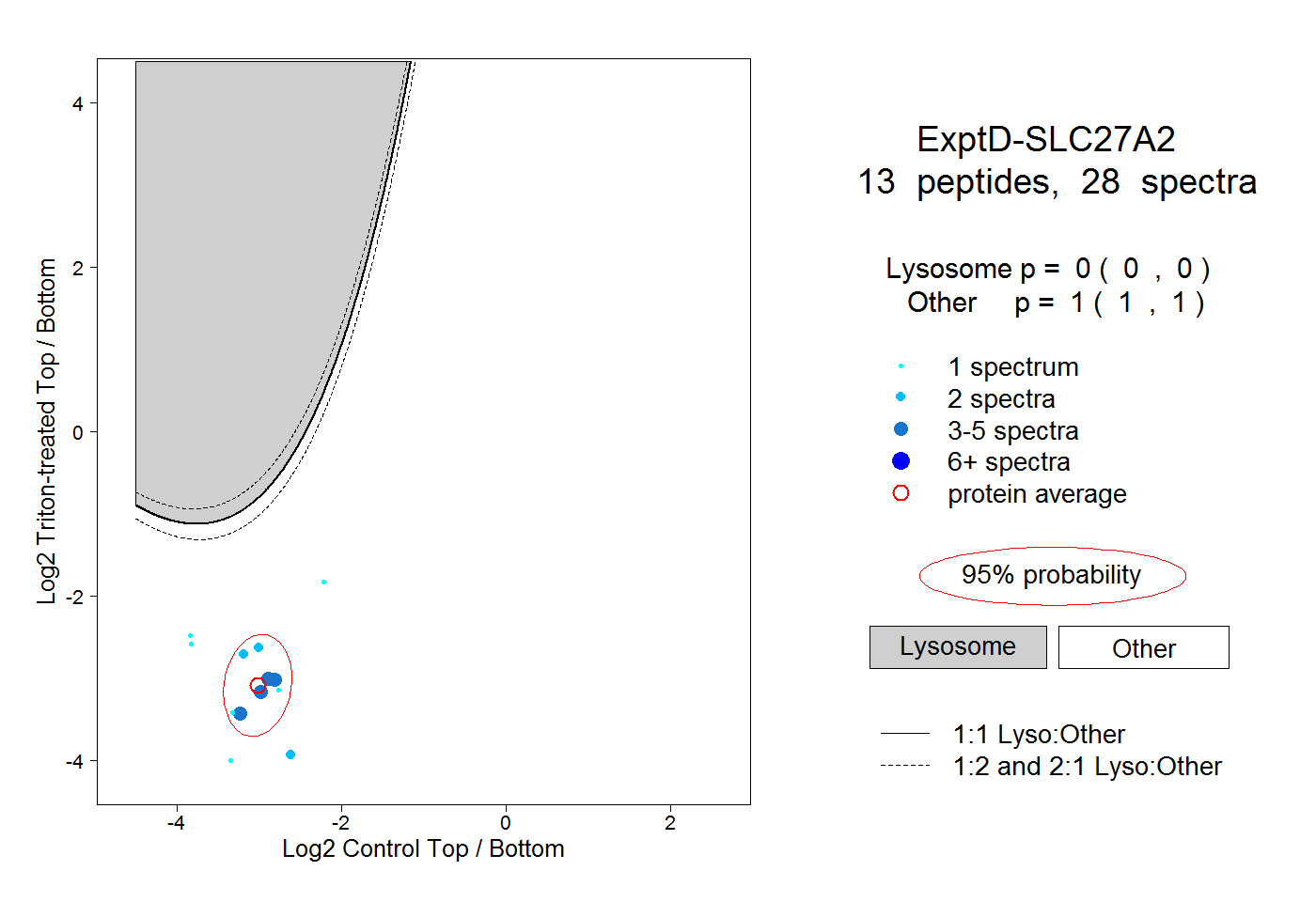 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |