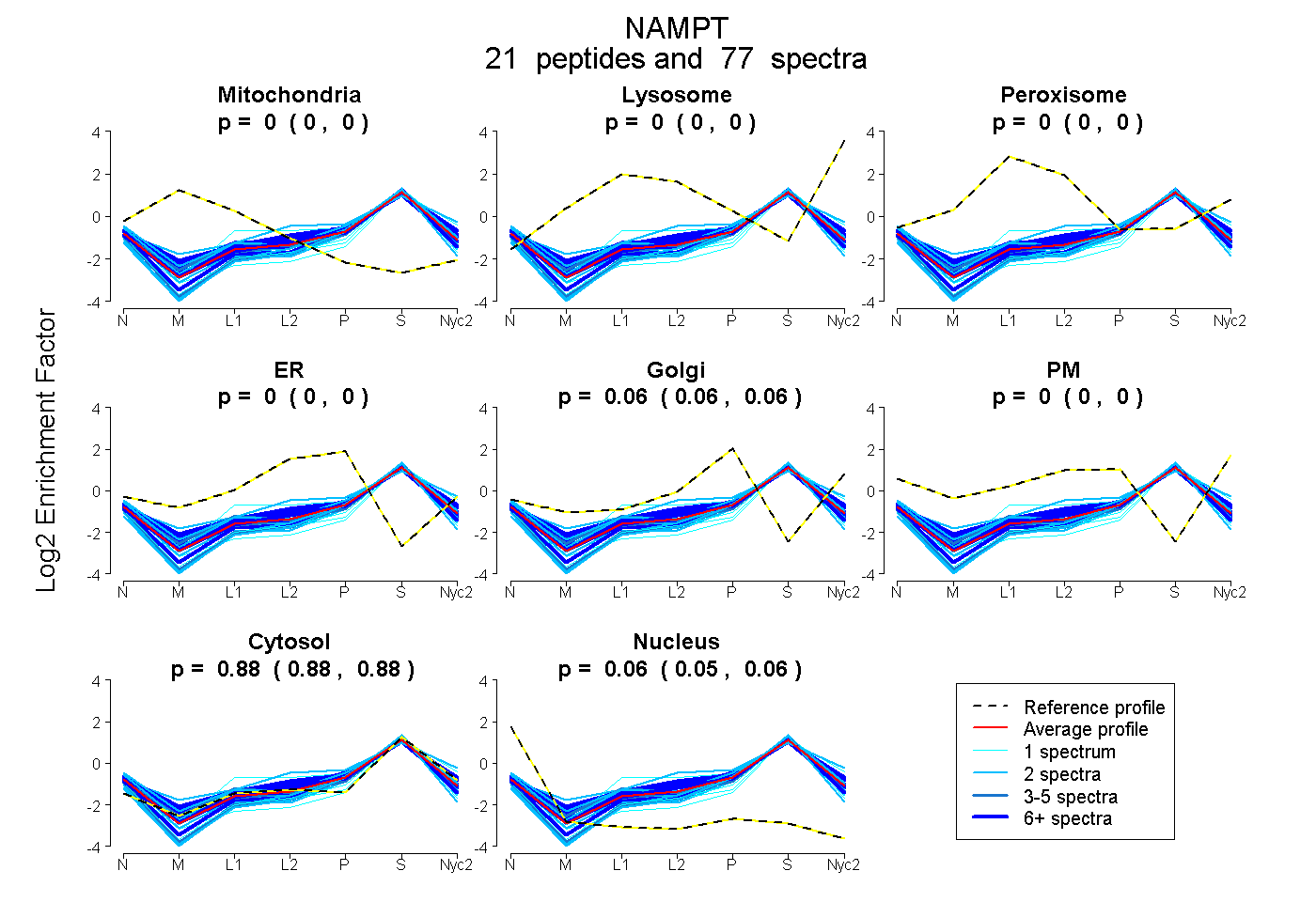
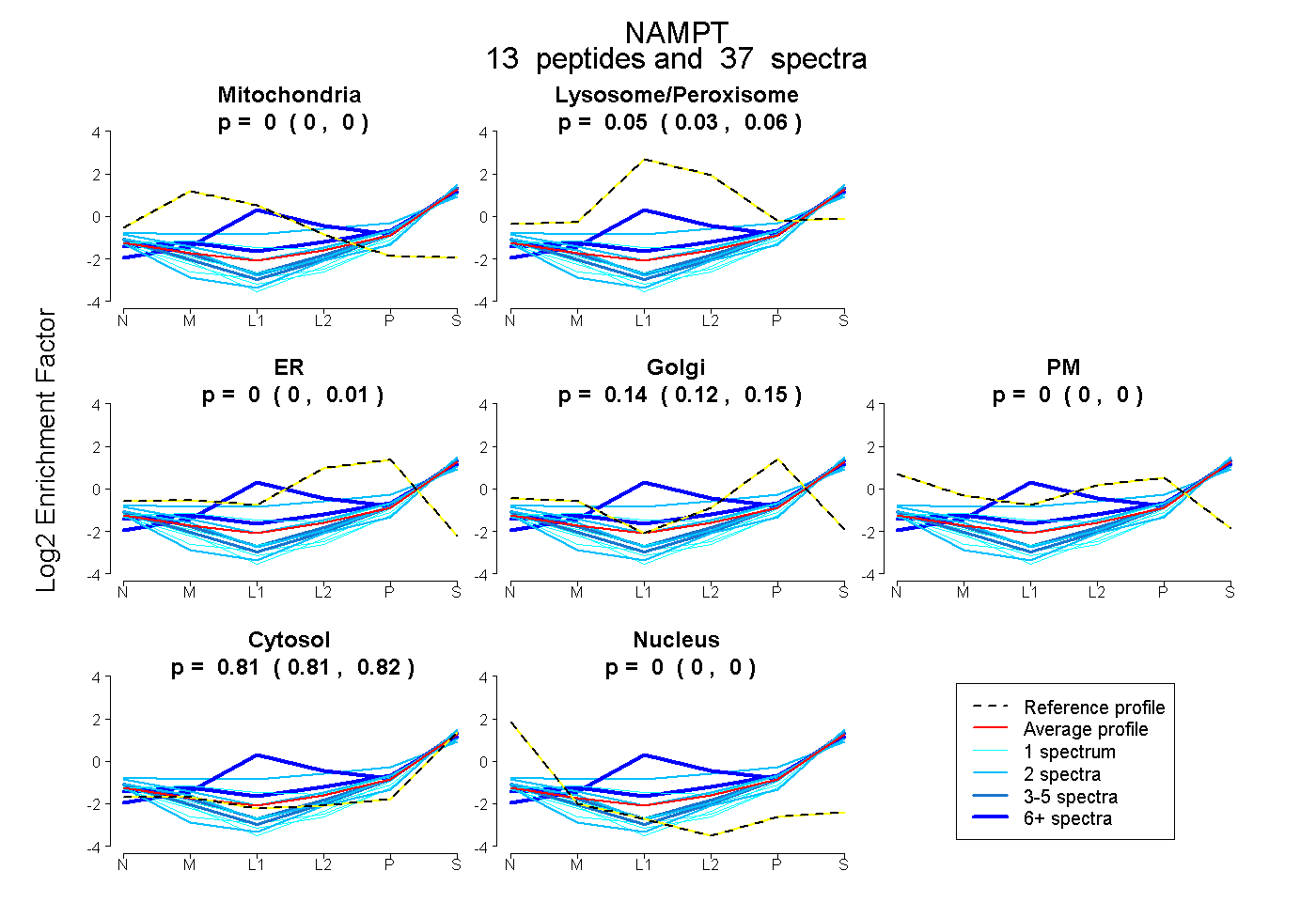
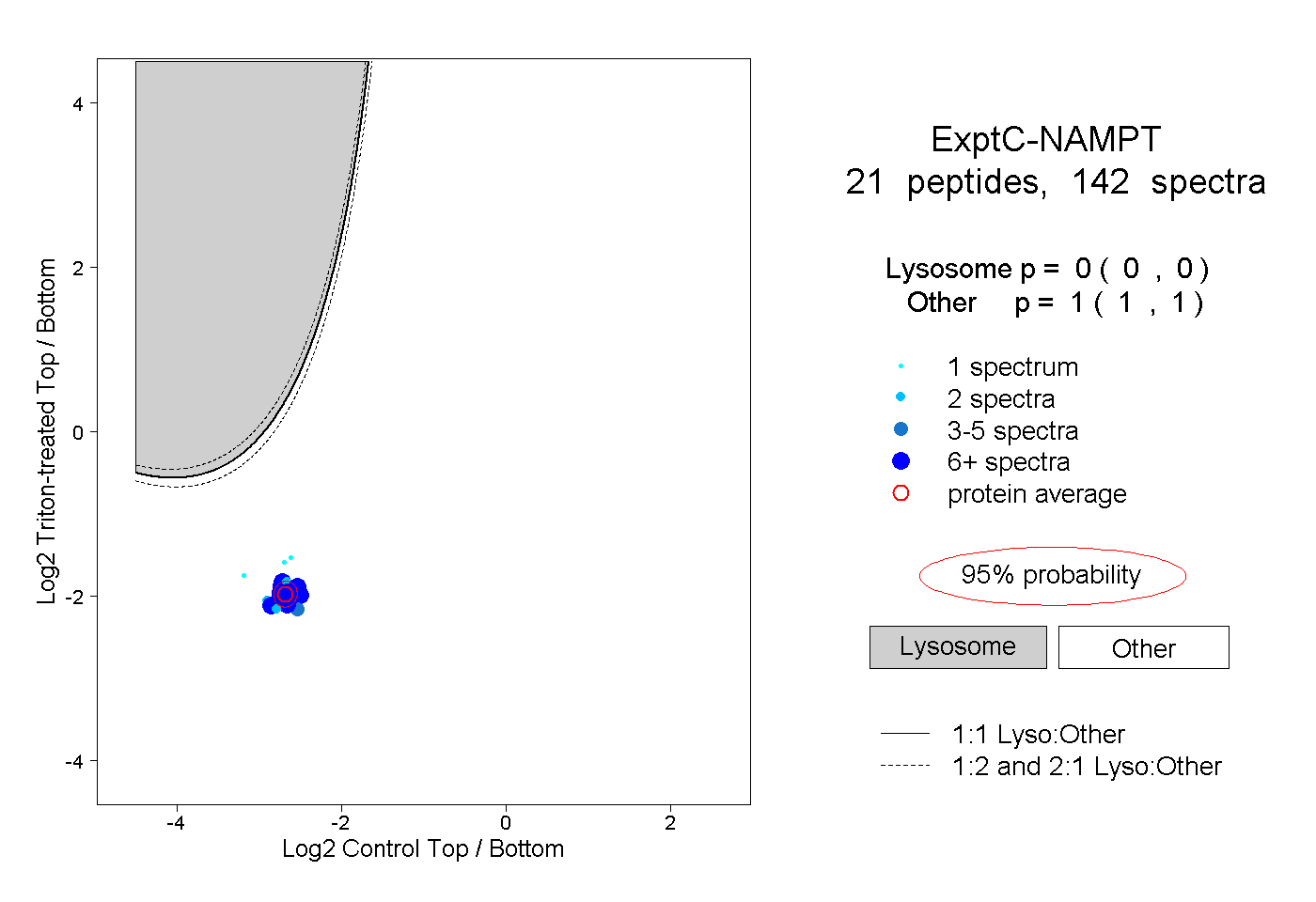
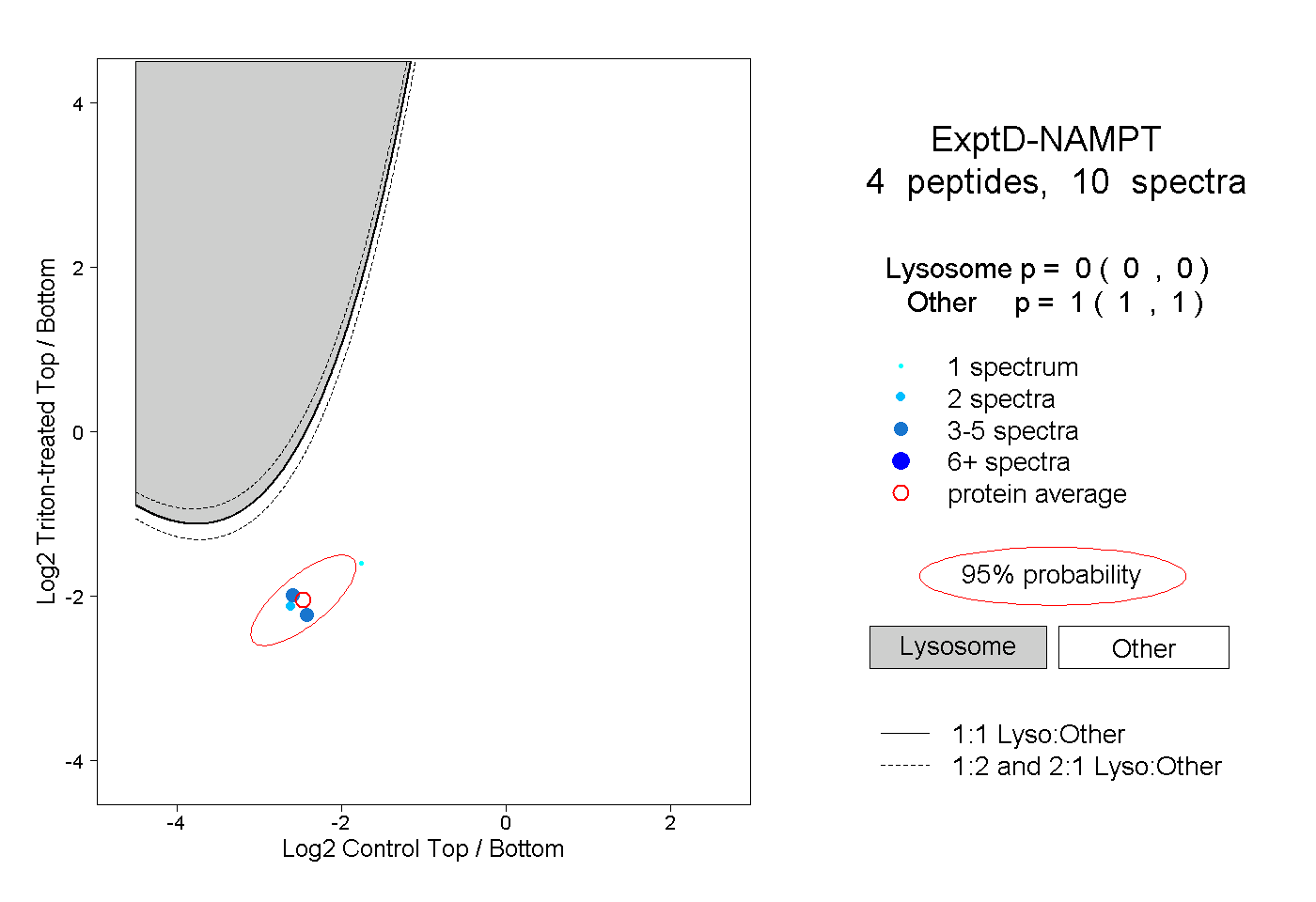
| 2 spectra, YYGTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DPVADPNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, VYSYFECR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, STEAPLIIRPDSGNPLDTVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FPVSENSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DLLNCSFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, YDGHLPIEVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VIQGDGVDINTLQEIVEGMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, IWGEDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, HLIVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GTDTVAGIALIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LLPPYLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, QYPPNTSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, AVPEGSVIPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, EHFQDDVFNER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, VLDILGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GWNYILEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, LHDFGYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, SYSFDEVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, NAQLNMEQDVAPH |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GDLEEYGHDLLHTVFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |