peptides
spectra
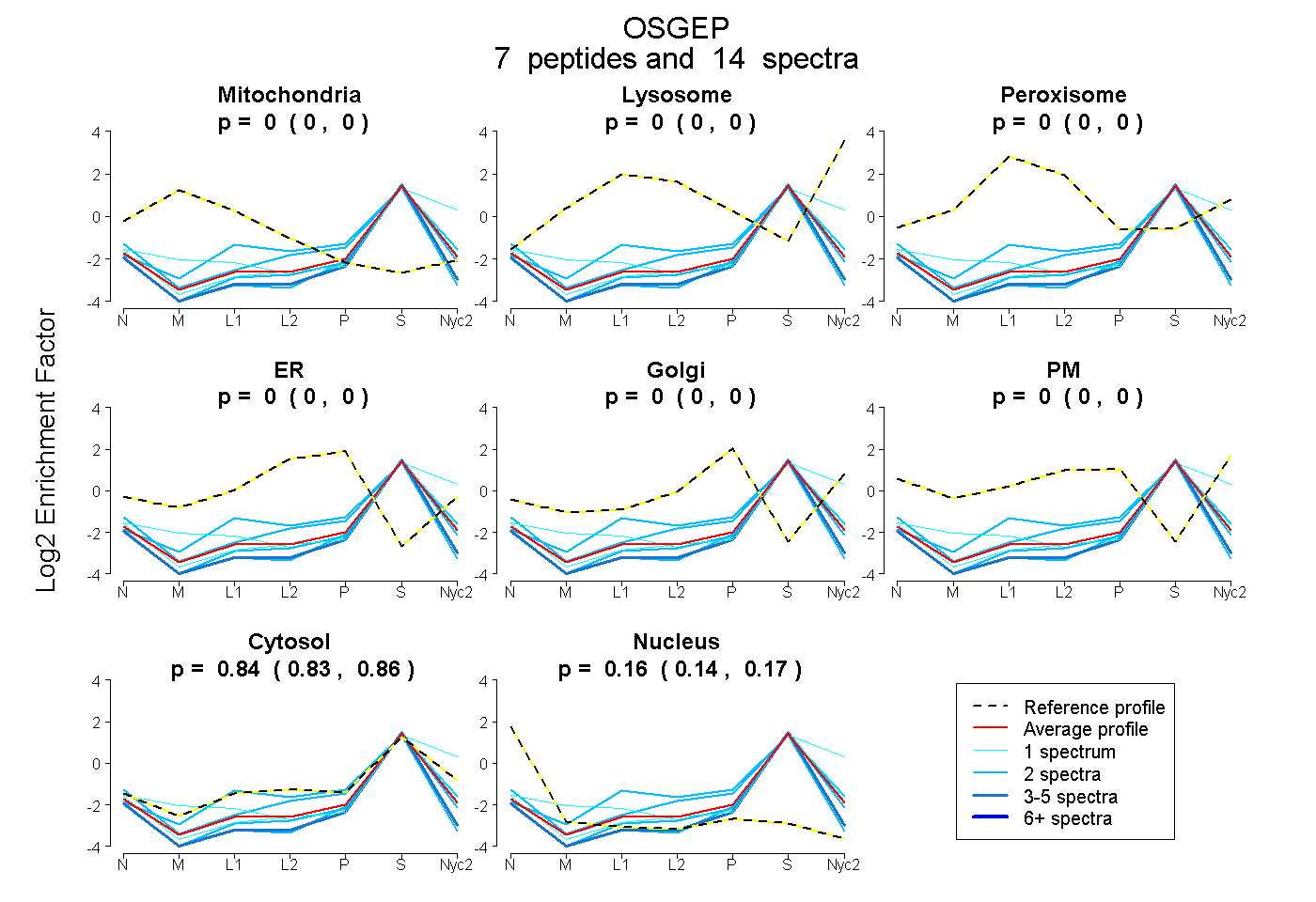
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.826 | 0.858
0.140 | 0.171
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.844 0.826 | 0.858 |
0.156 0.140 | 0.171 |
| 2 spectra, IGVGVVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.802 | 0.198 | ||
| 2 spectra, AMAHCGSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.766 | 0.234 | ||
| 1 spectrum, EALIVGGVGCNVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.979 | 0.021 | ||
| 2 spectra, DIDCIAYTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.982 | 0.018 | ||
| 4 spectra, TPLQDSGITQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.734 | 0.266 | ||
| 1 spectrum, TYVTAPGTGFLPGDTAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.833 | 0.167 | ||
| 2 spectra, GAQLFATDER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.822 | 0.178 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
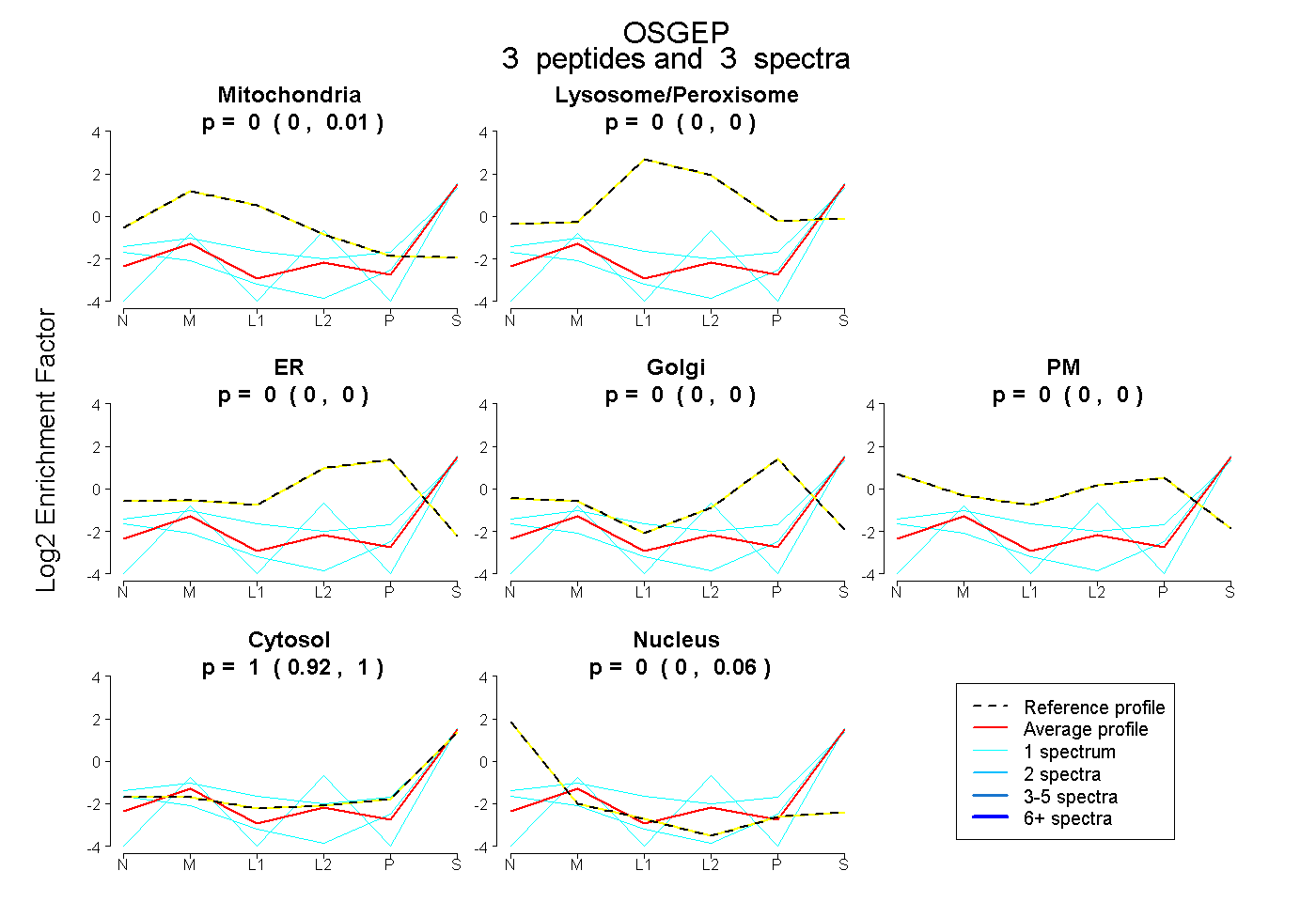 |
0.000 0.000 | 0.007 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 0.918 | 1.000 |
0.000 0.000 | 0.055 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3 spectra |
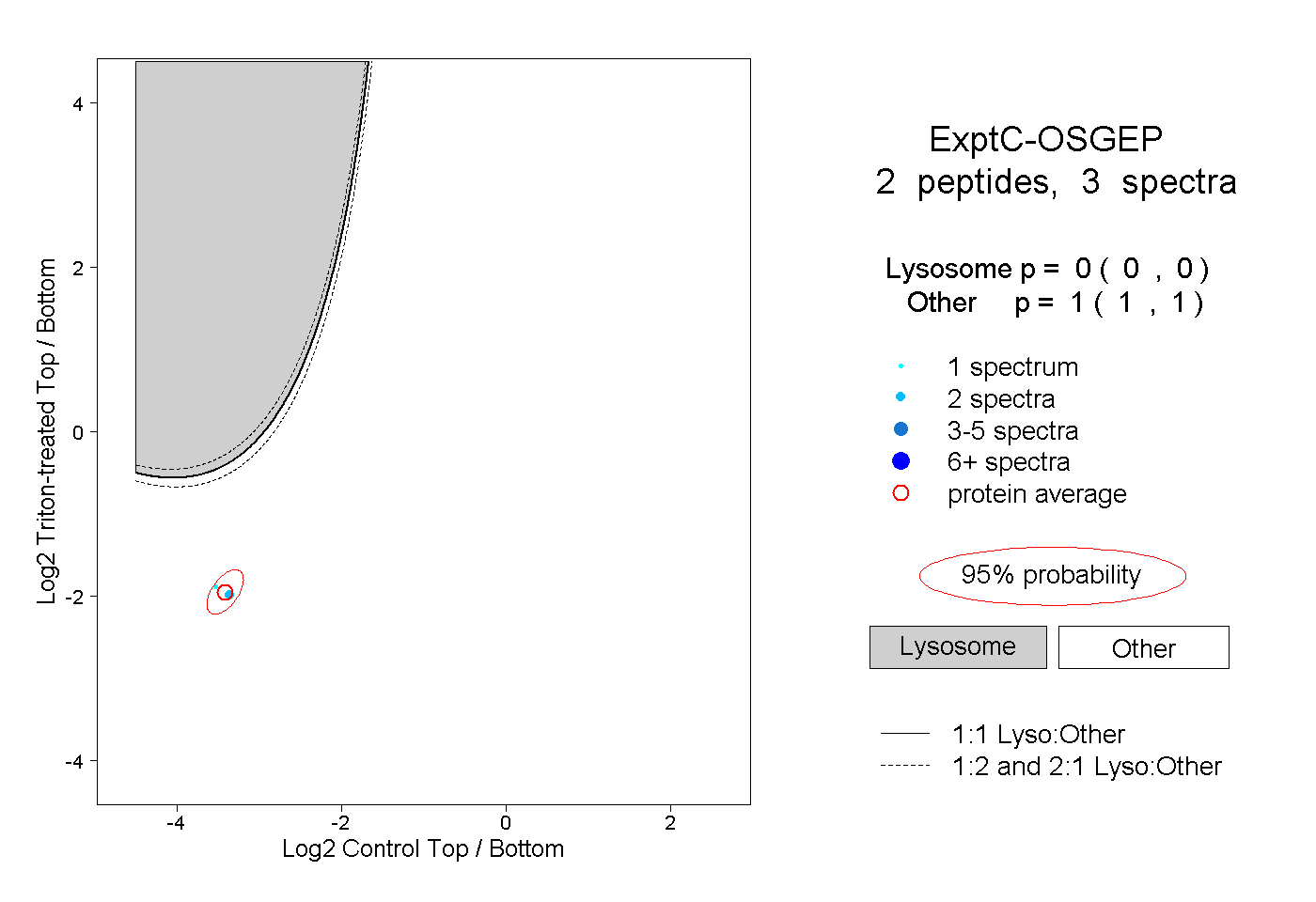 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |