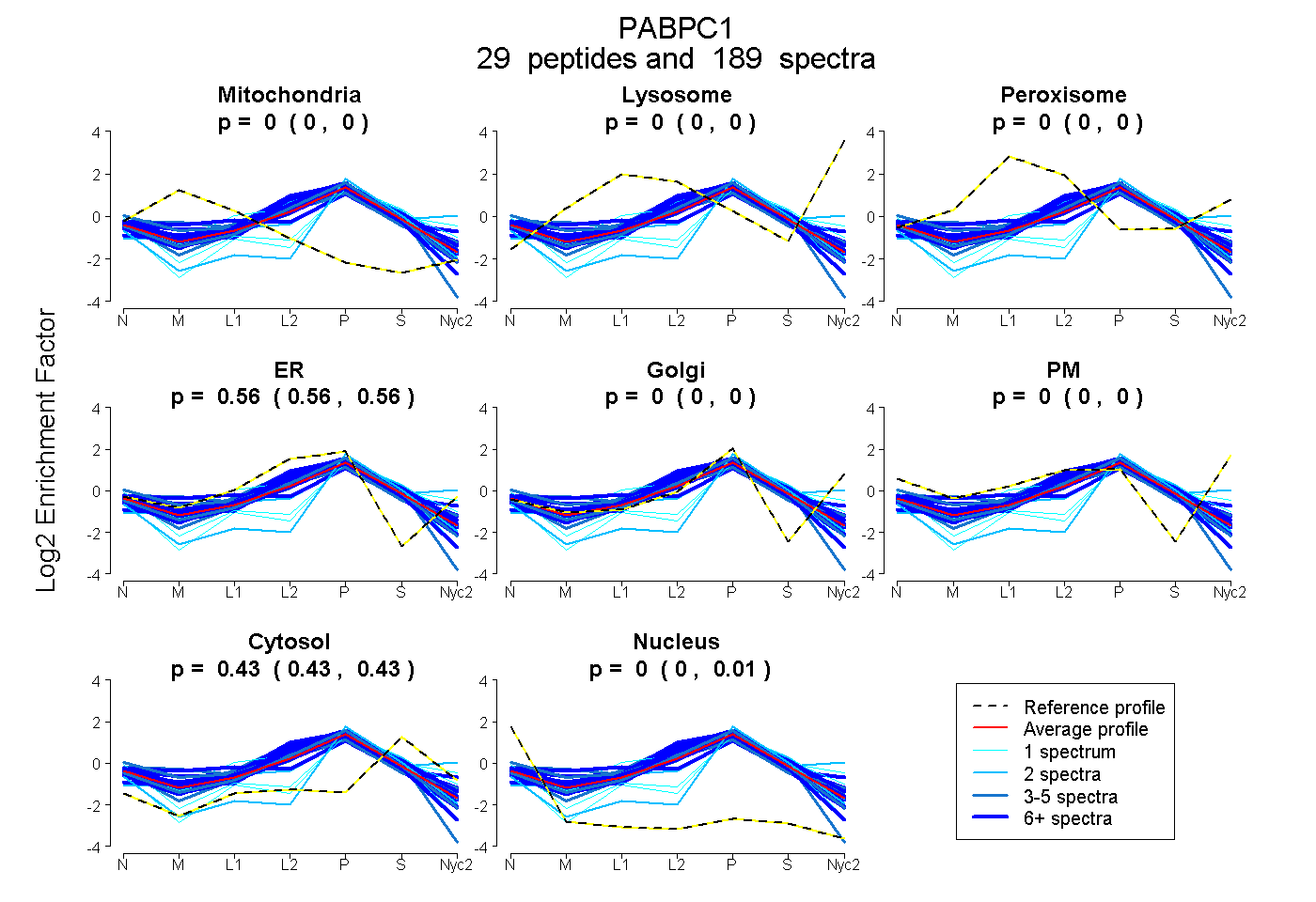
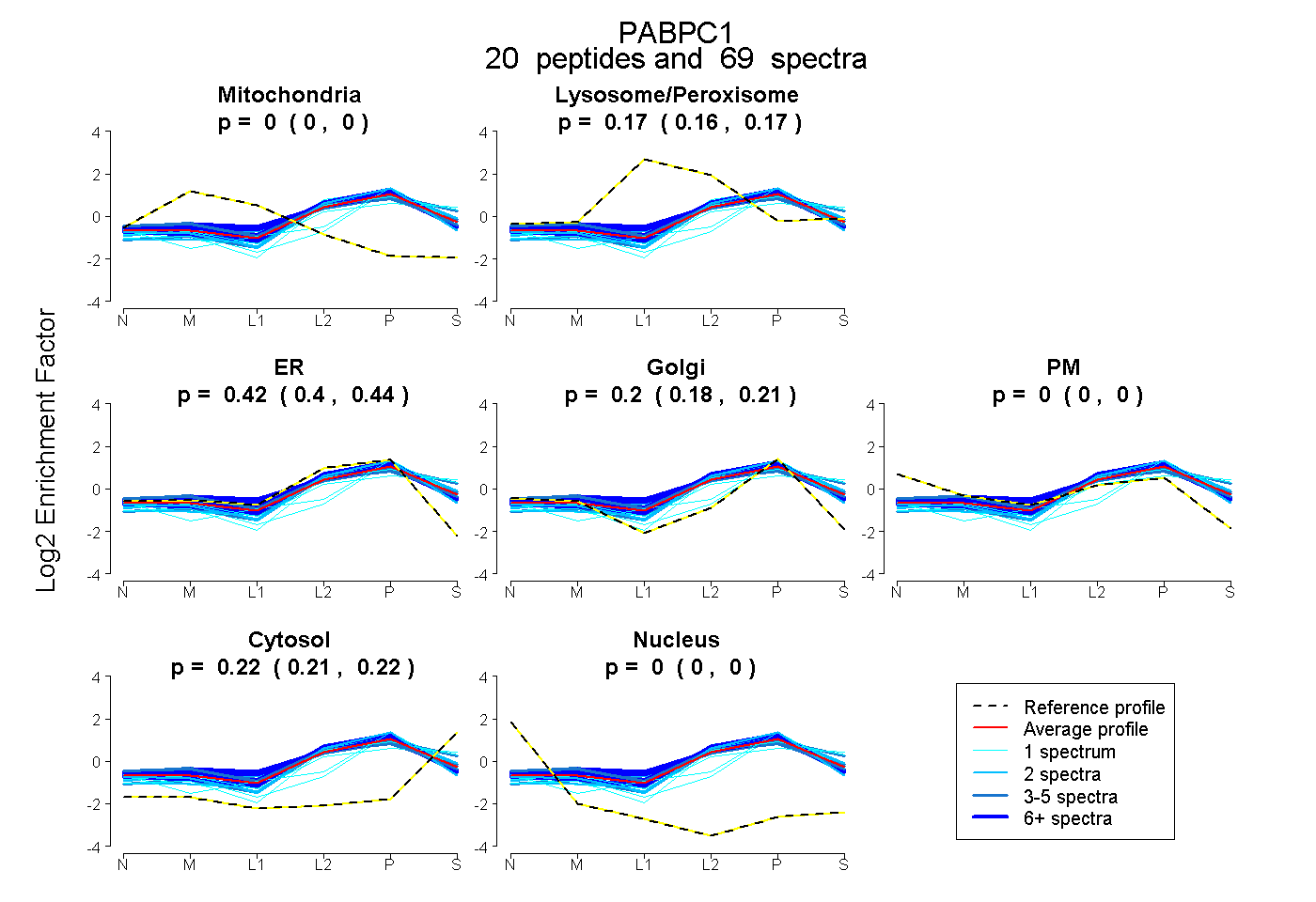
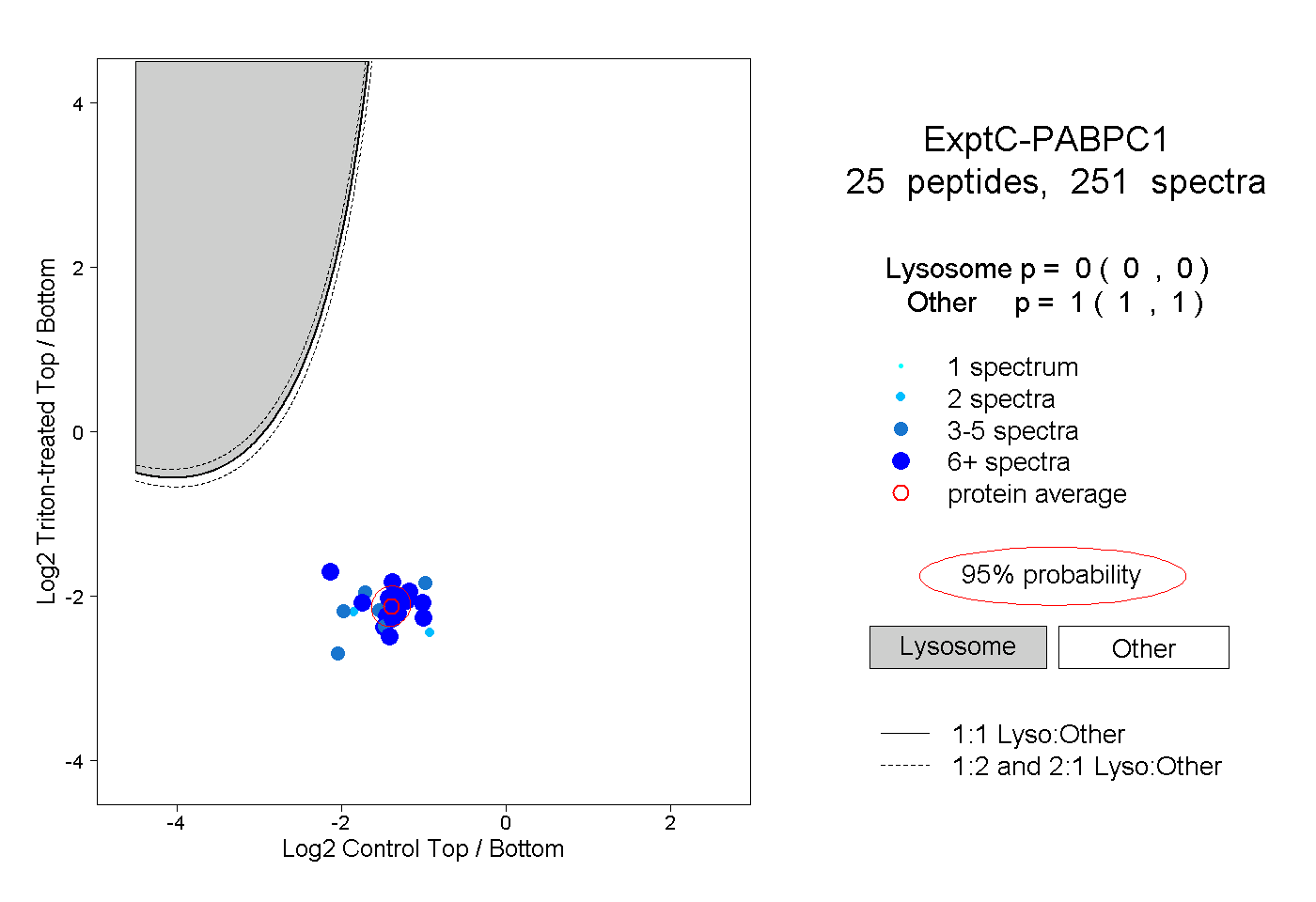
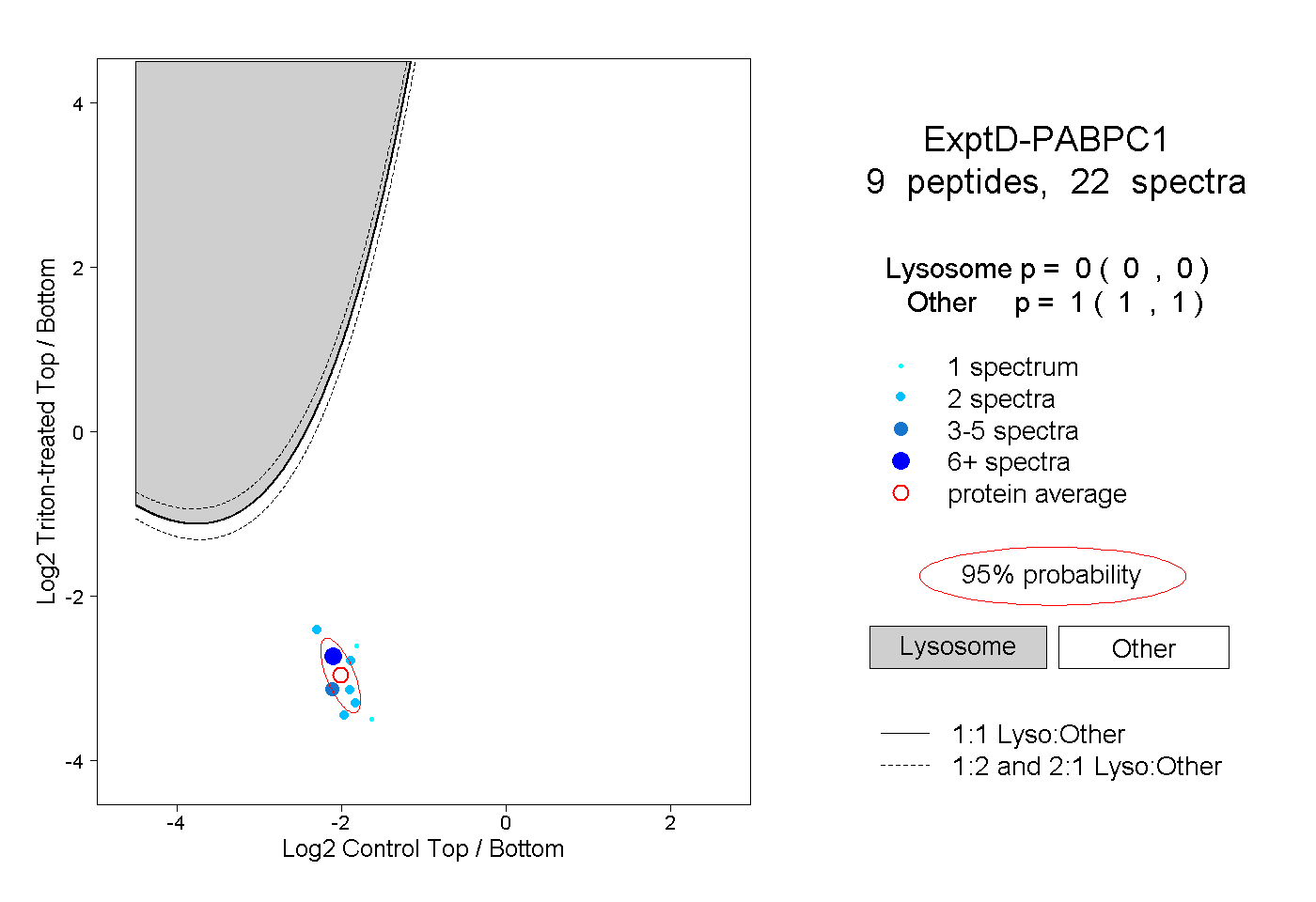
| 18 spectra, HEDAQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, AVDEMNGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LMWSQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, FSPAGPILSIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, NLDDGIDDER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GFGFVCFSSPEEATK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, MNGMLLNDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, SGVGNIFIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, ALDTMNFDVIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EFTNVYIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, IVATKPLYVALAQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, GFGFVSFER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, YQGVNLYVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, VMTDESGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, GYGFVHFETQEAAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VVCDENGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VMMEGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SLGYAYVNFQQPADAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, FGPALSVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, QIYVGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, EAELGAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, EFSPFGTITSAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QAHLTNQYMQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AVTEMNGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, NFGEDMDDER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |