peptides
spectra
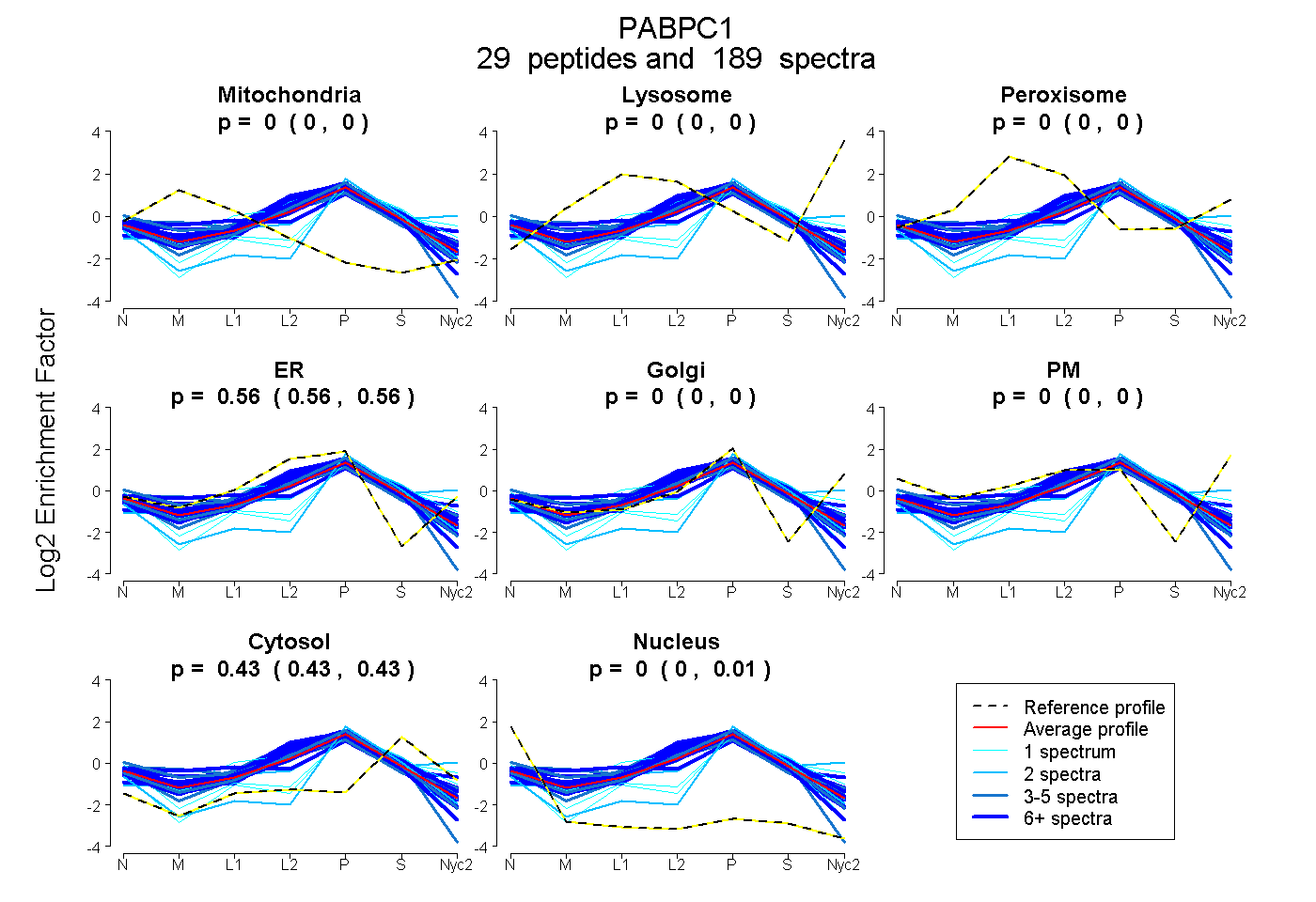
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.561 | 0.564
0.000 | 0.000
0.000 | 0.000
0.432 | 0.434
0.003 | 0.006
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
189 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.562 0.561 | 0.564 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.433 0.432 | 0.434 |
0.004 0.003 | 0.006 |
| 3 spectra, HEDAQK | 0.000 | 0.000 | 0.000 | 0.595 | 0.000 | 0.000 | 0.405 | 0.000 | ||
| 4 spectra, AVDEMNGK | 0.000 | 0.000 | 0.000 | 0.628 | 0.000 | 0.000 | 0.372 | 0.000 | ||
| 16 spectra, LMWSQR | 0.000 | 0.000 | 0.000 | 0.635 | 0.000 | 0.000 | 0.365 | 0.000 | ||
| 11 spectra, FSPAGPILSIR | 0.000 | 0.000 | 0.000 | 0.580 | 0.000 | 0.000 | 0.420 | 0.000 | ||
| 9 spectra, NLDDGIDDER | 0.000 | 0.000 | 0.000 | 0.552 | 0.000 | 0.000 | 0.429 | 0.019 | ||
| 1 spectrum, VDEAVAVLQAHQAK | 0.000 | 0.000 | 0.000 | 0.063 | 0.392 | 0.000 | 0.497 | 0.048 | ||
| 4 spectra, GFGFVCFSSPEEATK | 0.000 | 0.000 | 0.000 | 0.462 | 0.000 | 0.000 | 0.385 | 0.153 | ||
| 2 spectra, MNGMLLNDR | 0.000 | 0.000 | 0.000 | 0.525 | 0.000 | 0.000 | 0.475 | 0.000 | ||
| 5 spectra, SGVGNIFIK | 0.064 | 0.000 | 0.000 | 0.590 | 0.000 | 0.000 | 0.346 | 0.000 | ||
| 5 spectra, ALDTMNFDVIK | 0.000 | 0.000 | 0.000 | 0.611 | 0.000 | 0.000 | 0.389 | 0.000 | ||
| 3 spectra, EFTNVYIK | 0.000 | 0.000 | 0.000 | 0.496 | 0.000 | 0.000 | 0.480 | 0.024 | ||
| 7 spectra, IVATKPLYVALAQR | 0.000 | 0.000 | 0.000 | 0.633 | 0.000 | 0.000 | 0.367 | 0.000 | ||
| 3 spectra, GFGFVSFER | 0.000 | 0.000 | 0.000 | 0.567 | 0.000 | 0.000 | 0.433 | 0.000 | ||
| 4 spectra, YQGVNLYVK | 0.000 | 0.000 | 0.000 | 0.563 | 0.000 | 0.000 | 0.411 | 0.027 | ||
| 13 spectra, VMTDESGK | 0.000 | 0.000 | 0.000 | 0.577 | 0.000 | 0.000 | 0.408 | 0.015 | ||
| 10 spectra, GYGFVHFETQEAAER | 0.053 | 0.000 | 0.000 | 0.568 | 0.000 | 0.000 | 0.379 | 0.000 | ||
| 7 spectra, VVCDENGSK | 0.000 | 0.000 | 0.000 | 0.589 | 0.000 | 0.000 | 0.354 | 0.058 | ||
| 8 spectra, VMMEGGR | 0.000 | 0.000 | 0.000 | 0.526 | 0.000 | 0.000 | 0.474 | 0.000 | ||
| 1 spectrum, AAYYPPSQIAQLRPSPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.376 | 0.000 | 0.570 | 0.054 | ||
| 2 spectra, YAAGVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.368 | 0.000 | 0.486 | 0.147 | ||
| 2 spectra, AVNSATGVPTV | 0.000 | 0.000 | 0.160 | 0.000 | 0.520 | 0.000 | 0.321 | 0.000 | ||
| 1 spectrum, SLGYAYVNFQQPADAER | 0.000 | 0.000 | 0.000 | 0.528 | 0.000 | 0.000 | 0.417 | 0.055 | ||
| 4 spectra, FGPALSVK | 0.114 | 0.000 | 0.000 | 0.572 | 0.000 | 0.000 | 0.314 | 0.000 | ||
| 12 spectra, QIYVGR | 0.000 | 0.000 | 0.000 | 0.578 | 0.000 | 0.000 | 0.422 | 0.000 | ||
| 1 spectrum, EAELGAR | 0.000 | 0.000 | 0.165 | 0.420 | 0.051 | 0.000 | 0.363 | 0.000 | ||
| 4 spectra, EFSPFGTITSAK | 0.030 | 0.000 | 0.000 | 0.529 | 0.000 | 0.000 | 0.422 | 0.020 | ||
| 9 spectra, QAHLTNQYMQR | 0.202 | 0.000 | 0.000 | 0.461 | 0.000 | 0.000 | 0.337 | 0.000 | ||
| 17 spectra, NFGEDMDDER | 0.000 | 0.000 | 0.000 | 0.568 | 0.000 | 0.000 | 0.432 | 0.000 | ||
| 21 spectra, AVTEMNGR | 0.000 | 0.000 | 0.016 | 0.659 | 0.000 | 0.000 | 0.325 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
69 spectra |
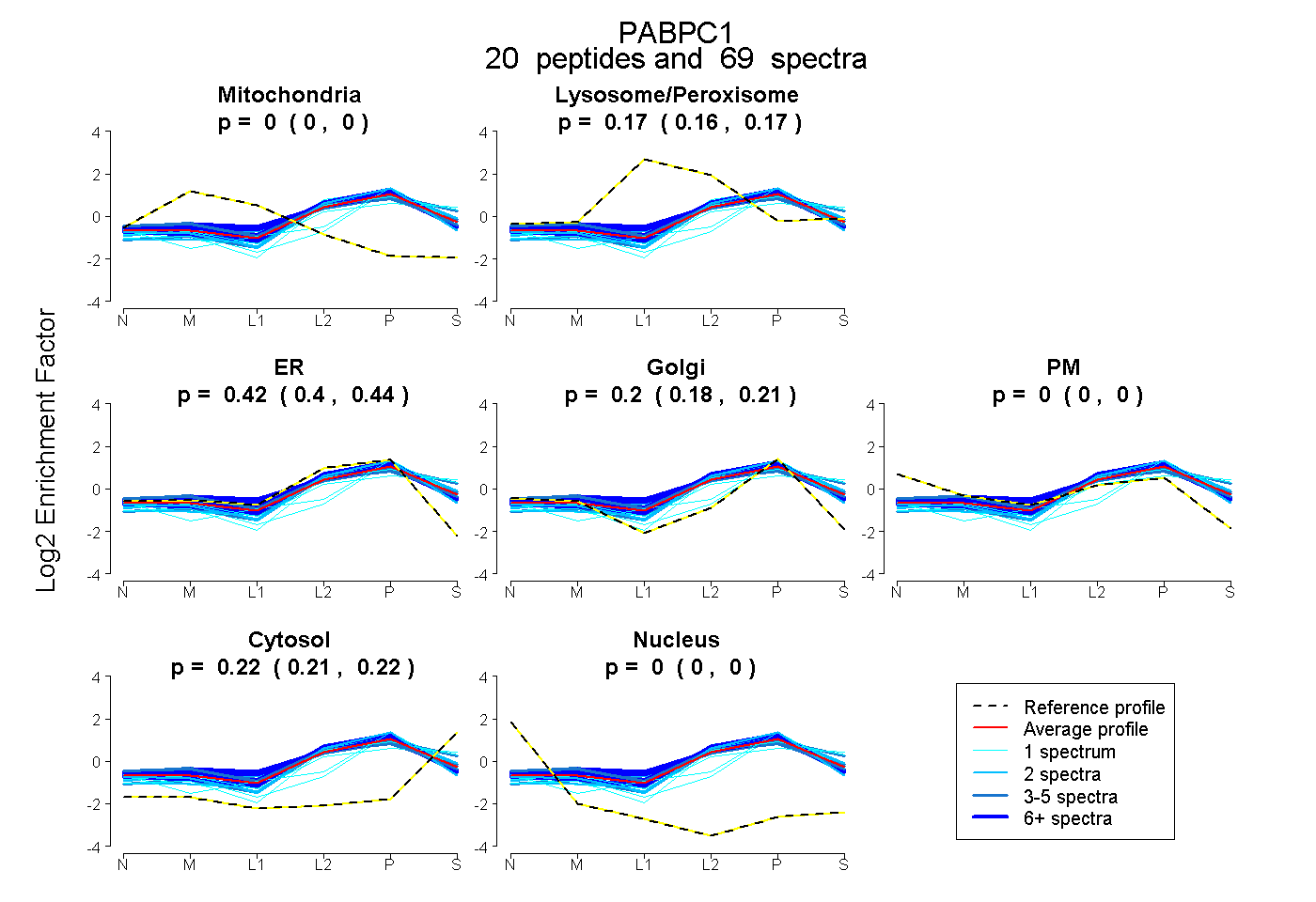 |
0.000 0.000 | 0.000 |
0.167 0.160 | 0.172 |
0.421 0.404 | 0.436 |
0.197 0.181 | 0.209 |
0.000 0.000 | 0.000 |
0.216 0.212 | 0.219 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
251 spectra |
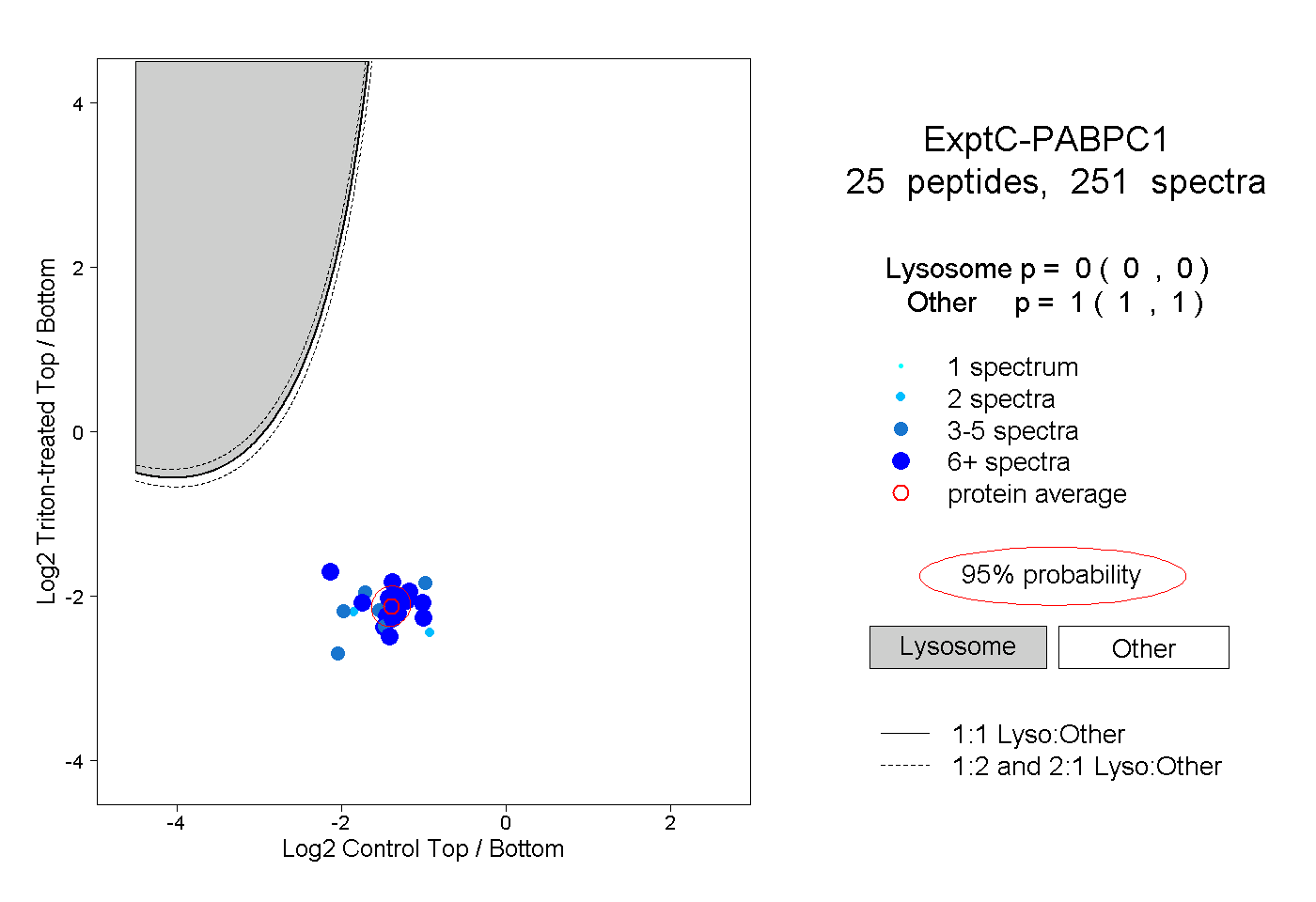 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
22 spectra |
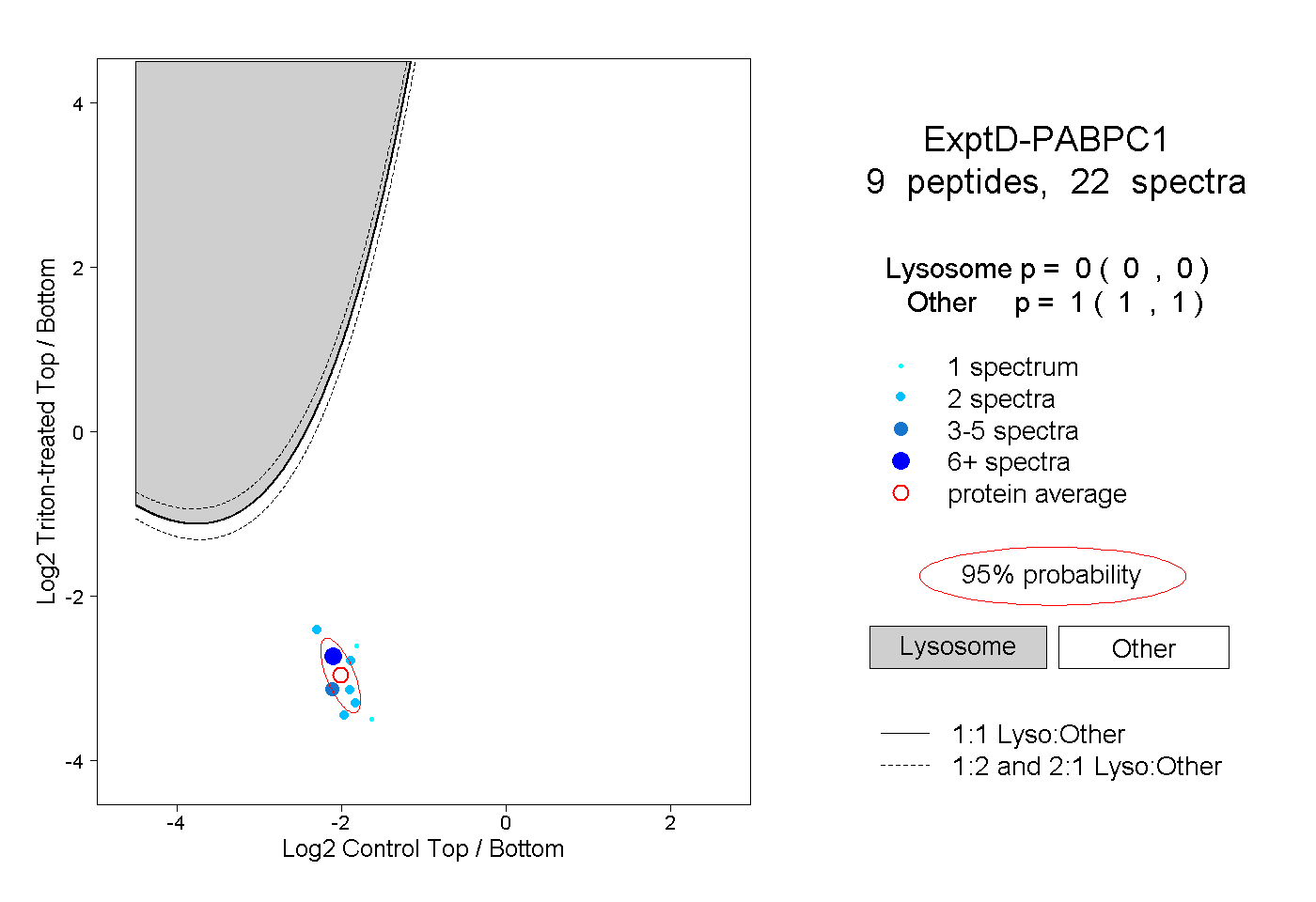 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |