peptides
spectra

0.000 | 0.000
0.256 | 0.260
0.000 | 0.000
0.232 | 0.239
0.075 | 0.082
0.014 | 0.023
0.407 | 0.410
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.220 | 0.225
0.383 | 0.394
0.007 | 0.016
0.000 | 0.000
0.375 | 0.378
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
480 spectra |
 |
0.000 0.000 | 0.000 |
0.258 0.256 | 0.260 |
0.000 0.000 | 0.000 |
0.236 0.232 | 0.239 |
0.079 0.075 | 0.082 |
0.019 0.014 | 0.023 |
0.409 0.407 | 0.410 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
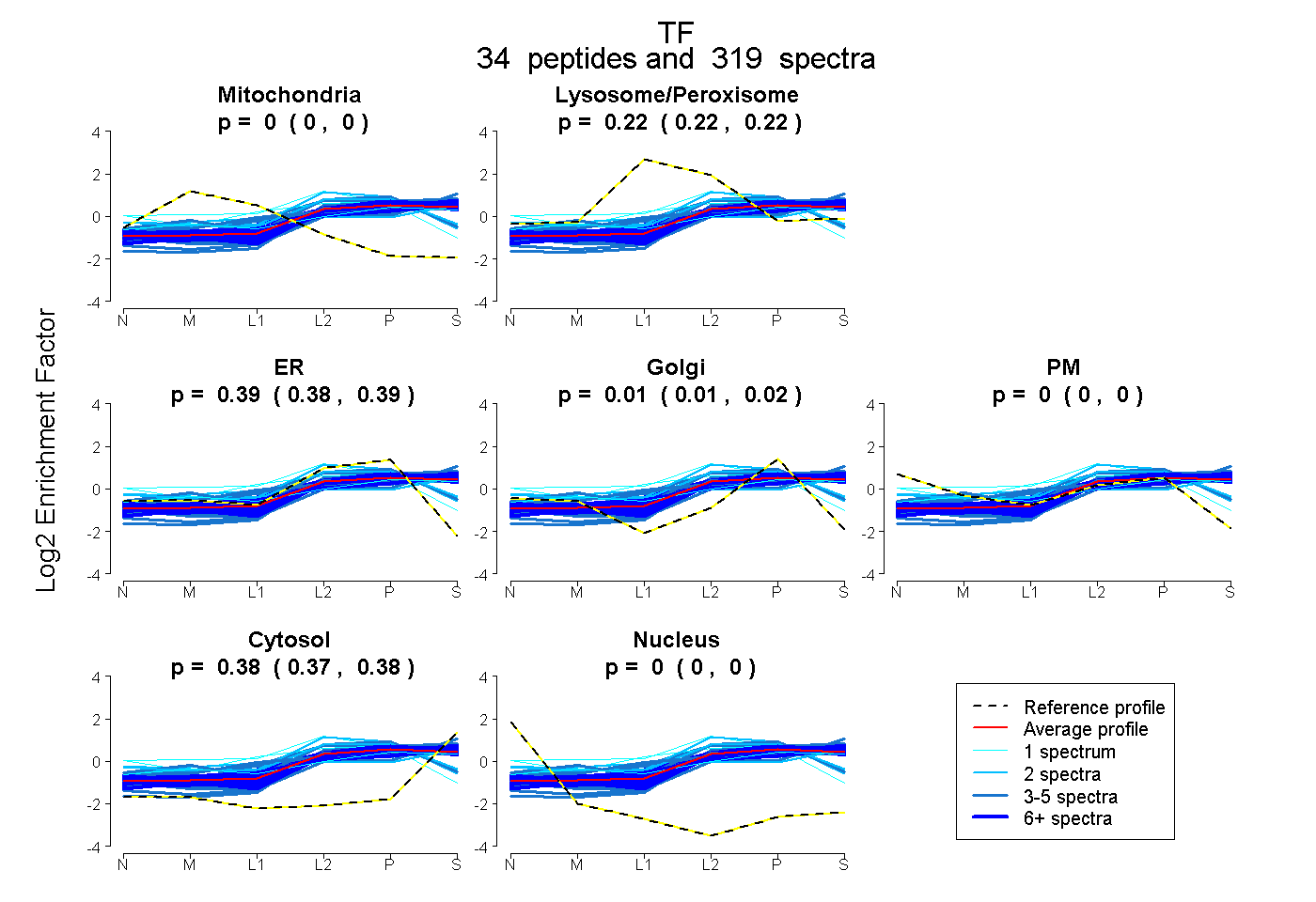
| Expt B |
peptides |
319 spectra |
 |
0.000 0.000 | 0.000 |
0.223 0.220 | 0.225 |
0.389 0.383 | 0.394 |
0.012 0.007 | 0.016 |
0.000 0.000 | 0.000 |
0.377 0.375 | 0.378 |
0.000 0.000 | 0.000 |
| 11 spectra, LLEACTFHK | 0.000 | 0.166 | 0.407 | 0.000 | 0.000 | 0.427 | 0.000 | |||
| 2 spectra, LLTGQYR | 0.000 | 0.281 | 0.473 | 0.072 | 0.073 | 0.101 | 0.000 | |||
| 4 spectra, DCTGNFCLFR | 0.000 | 0.189 | 0.363 | 0.000 | 0.000 | 0.447 | 0.000 | |||
| 1 spectrum, GDAGSADVQDLEK | 0.000 | 0.463 | 0.000 | 0.326 | 0.160 | 0.050 | 0.000 | |||
| 5 spectra, SCHTGVDR | 0.000 | 0.428 | 0.047 | 0.201 | 0.000 | 0.324 | 0.000 | |||
| 34 spectra, LYLGHSYVTAIR | 0.000 | 0.207 | 0.378 | 0.000 | 0.000 | 0.415 | 0.000 | |||
| 1 spectrum, GDVAFVK | 0.000 | 0.349 | 0.094 | 0.228 | 0.000 | 0.329 | 0.000 | |||
| 3 spectra, FDEFFSQGCAPGYK | 0.000 | 0.170 | 0.254 | 0.000 | 0.000 | 0.577 | 0.000 | |||
| 16 spectra, VAQEHFGK | 0.000 | 0.280 | 0.262 | 0.108 | 0.000 | 0.350 | 0.000 | |||
| 21 spectra, KPVDQYEDCYLAR | 0.000 | 0.226 | 0.394 | 0.000 | 0.000 | 0.380 | 0.000 | |||
| 4 spectra, DQYELLCLDNTR | 0.000 | 0.121 | 0.475 | 0.000 | 0.000 | 0.405 | 0.000 | |||
| 46 spectra, TVLPADGPR | 0.000 | 0.168 | 0.432 | 0.000 | 0.000 | 0.400 | 0.000 | |||
| 9 spectra, ASDSSINWNNLK | 0.000 | 0.131 | 0.441 | 0.016 | 0.000 | 0.412 | 0.000 | |||
| 4 spectra, TSYQDCIK | 0.000 | 0.463 | 0.000 | 0.255 | 0.000 | 0.281 | 0.000 | |||
| 1 spectrum, AVLFVGLCDSGK | 0.000 | 0.334 | 0.275 | 0.013 | 0.378 | 0.000 | 0.000 | |||
| 5 spectra, EGVCPEGSIDSAPVK | 0.000 | 0.426 | 0.000 | 0.288 | 0.000 | 0.285 | 0.000 | |||
| 26 spectra, DSAFGLLR | 0.000 | 0.198 | 0.368 | 0.048 | 0.000 | 0.386 | 0.000 | |||
| 6 spectra, DGGGDVAFVK | 0.000 | 0.249 | 0.286 | 0.120 | 0.000 | 0.345 | 0.000 | |||
| 3 spectra, EDLIWEILK | 0.000 | 0.104 | 0.418 | 0.000 | 0.000 | 0.478 | 0.000 | |||
| 5 spectra, DFQLFGSPLGK | 0.000 | 0.343 | 0.351 | 0.000 | 0.000 | 0.306 | 0.000 | |||
| 2 spectra, TLLFVR | 0.000 | 0.340 | 0.246 | 0.275 | 0.021 | 0.118 | 0.000 | |||
| 3 spectra, SAAPSTLDSSSTAPAQLGK | 0.000 | 0.237 | 0.437 | 0.187 | 0.000 | 0.139 | 0.000 | |||
| 40 spectra, IPSHAVVAR | 0.000 | 0.325 | 0.244 | 0.142 | 0.000 | 0.290 | 0.000 | |||
| 3 spectra, CAPNNR | 0.000 | 0.143 | 0.419 | 0.000 | 0.000 | 0.439 | 0.000 | |||
| 9 spectra, GYYAVAVVK | 0.000 | 0.262 | 0.286 | 0.122 | 0.000 | 0.330 | 0.000 | |||
| 4 spectra, GTDFQLNQLQGK | 0.000 | 0.114 | 0.456 | 0.000 | 0.000 | 0.431 | 0.000 | |||
| 6 spectra, EGYNGYTGAFQCLVEK | 0.000 | 0.154 | 0.393 | 0.000 | 0.000 | 0.453 | 0.000 | |||
| 2 spectra, HTTIFEVLPQK | 0.000 | 0.456 | 0.000 | 0.213 | 0.000 | 0.331 | 0.000 | |||
| 3 spectra, QEDFQLLCPDGTK | 0.000 | 0.257 | 0.289 | 0.000 | 0.000 | 0.454 | 0.000 | |||
| 4 spectra, KPVTEFATCHLAQAPNHVVVSR | 0.000 | 0.207 | 0.334 | 0.000 | 0.000 | 0.459 | 0.000 | |||
| 1 spectrum, WCAVSEHENTK | 0.000 | 0.370 | 0.000 | 0.360 | 0.000 | 0.270 | 0.000 | |||
| 10 spectra, WCALSHQER | 0.000 | 0.380 | 0.000 | 0.278 | 0.000 | 0.342 | 0.000 | |||
| 12 spectra, TAGWNIPMGLLFSR | 0.000 | 0.157 | 0.378 | 0.000 | 0.000 | 0.466 | 0.000 | |||
| 13 spectra, VSTVLTAQK | 0.000 | 0.256 | 0.249 | 0.126 | 0.000 | 0.369 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
843 spectra |
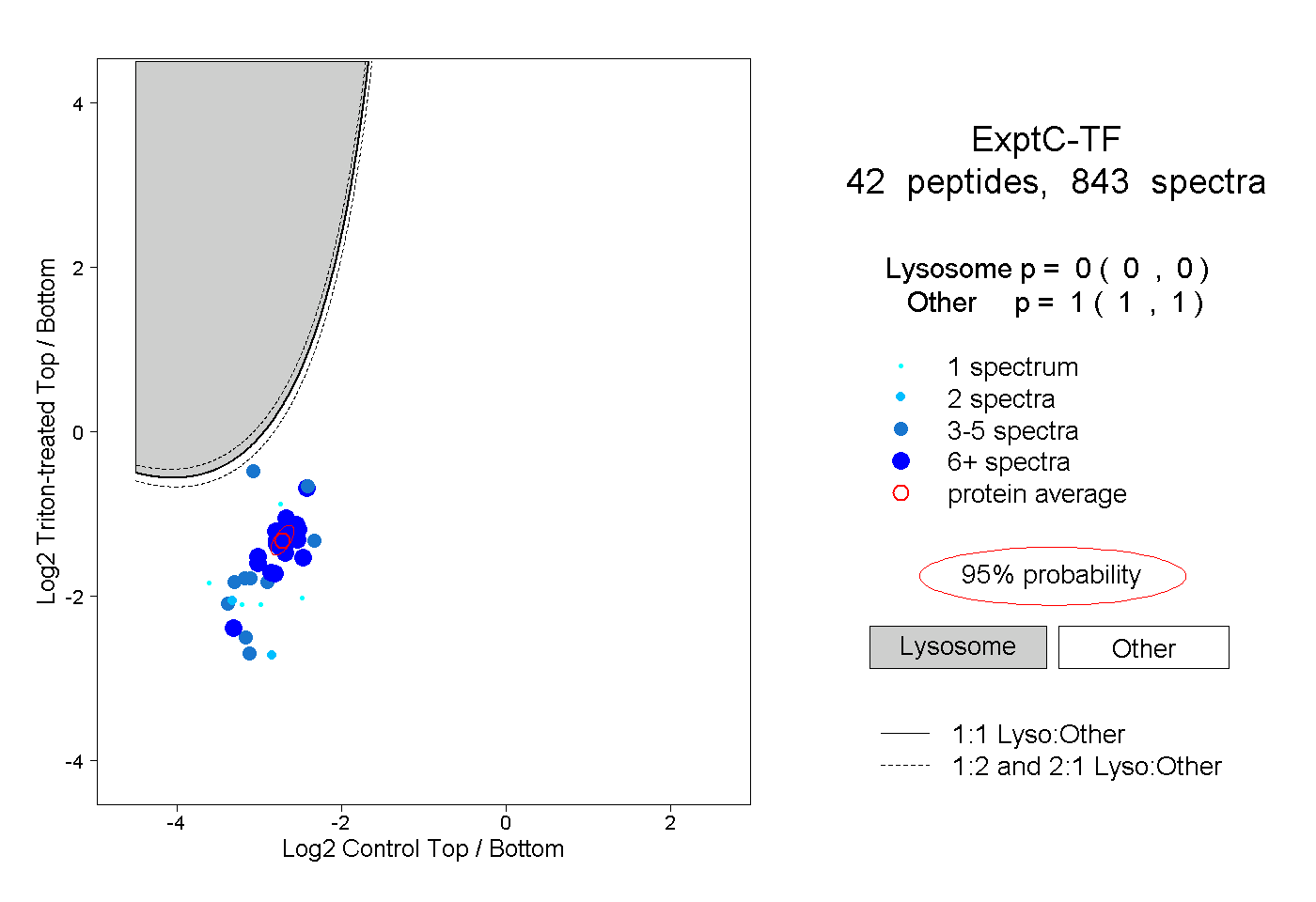 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
107 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |