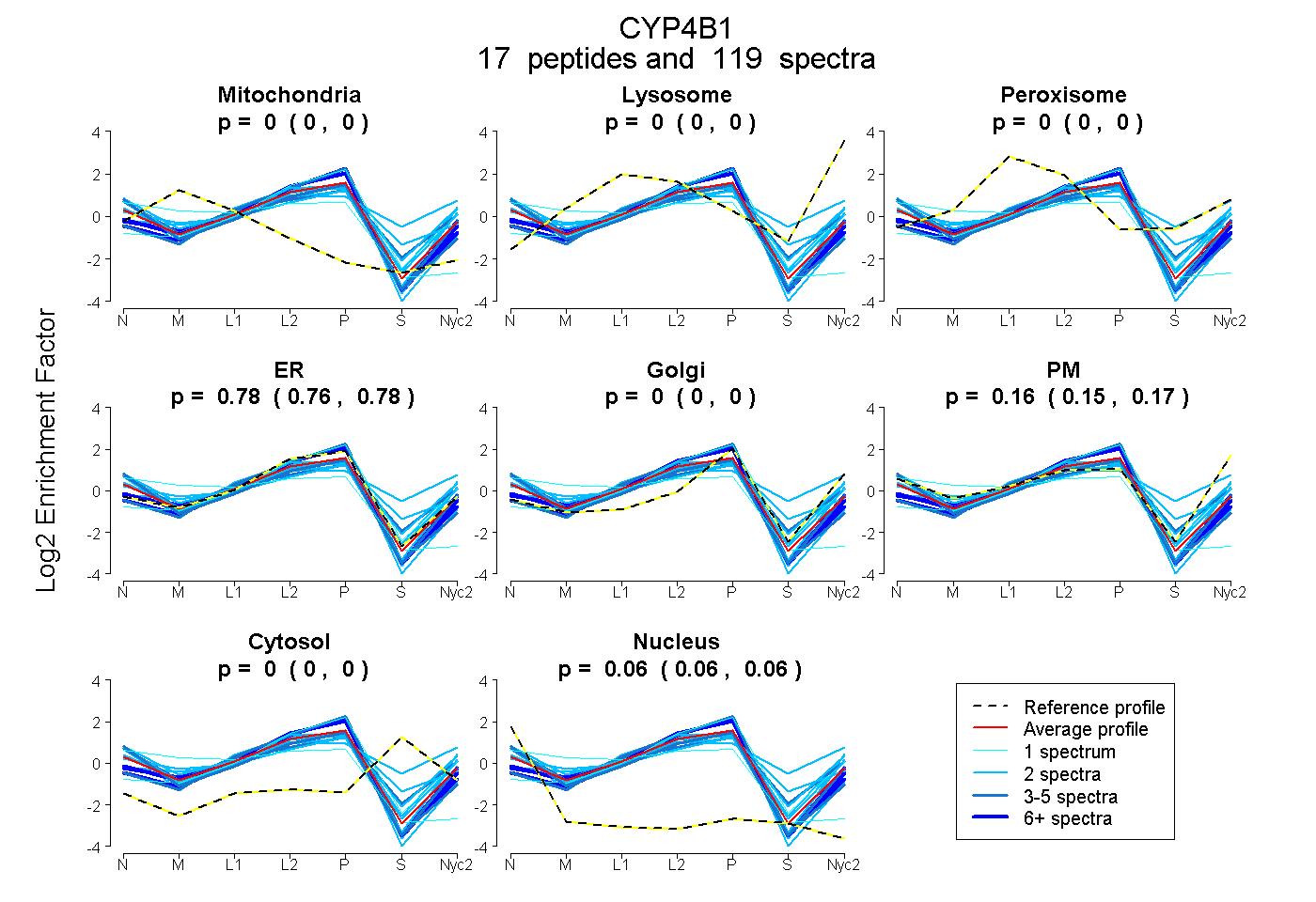
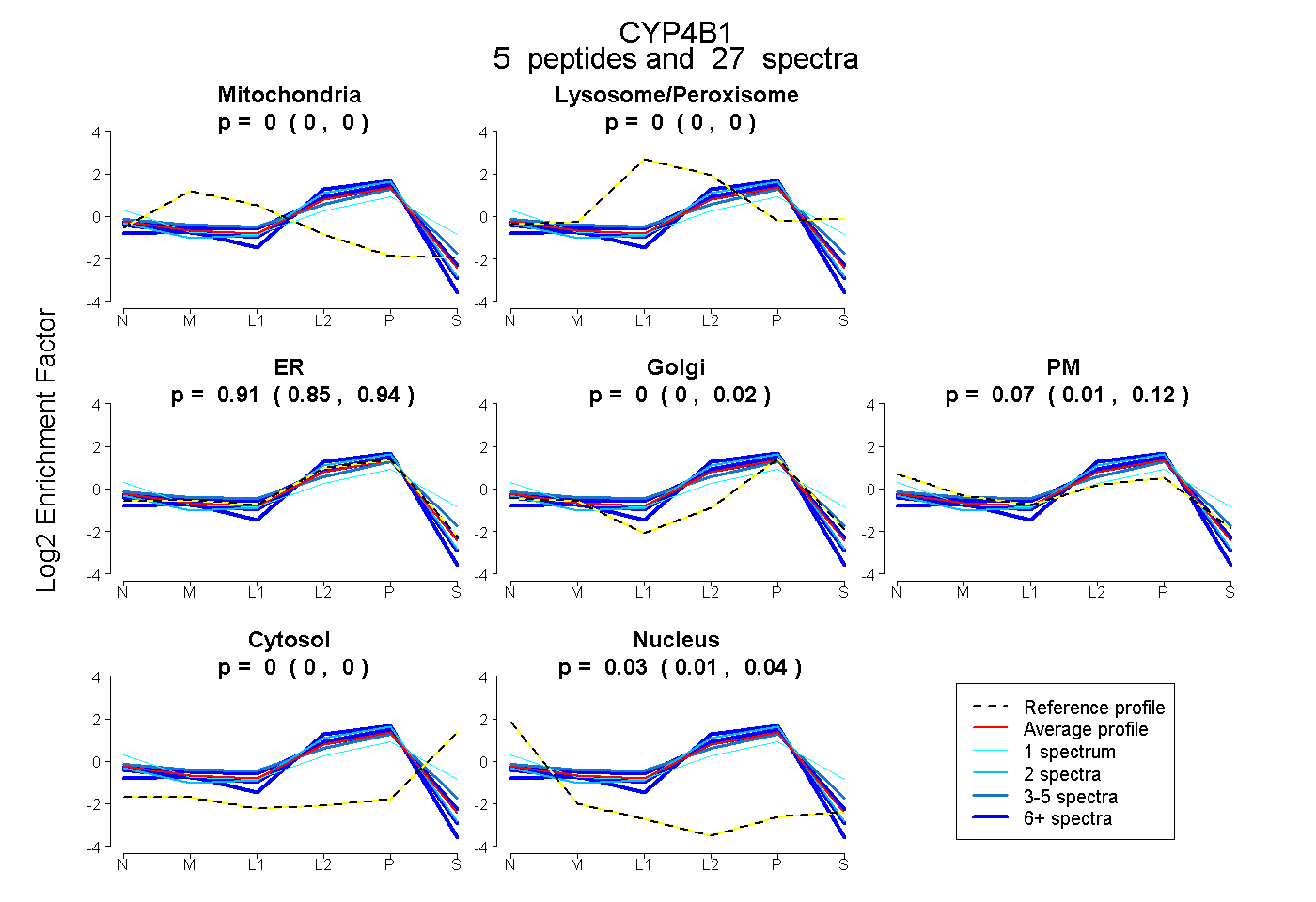
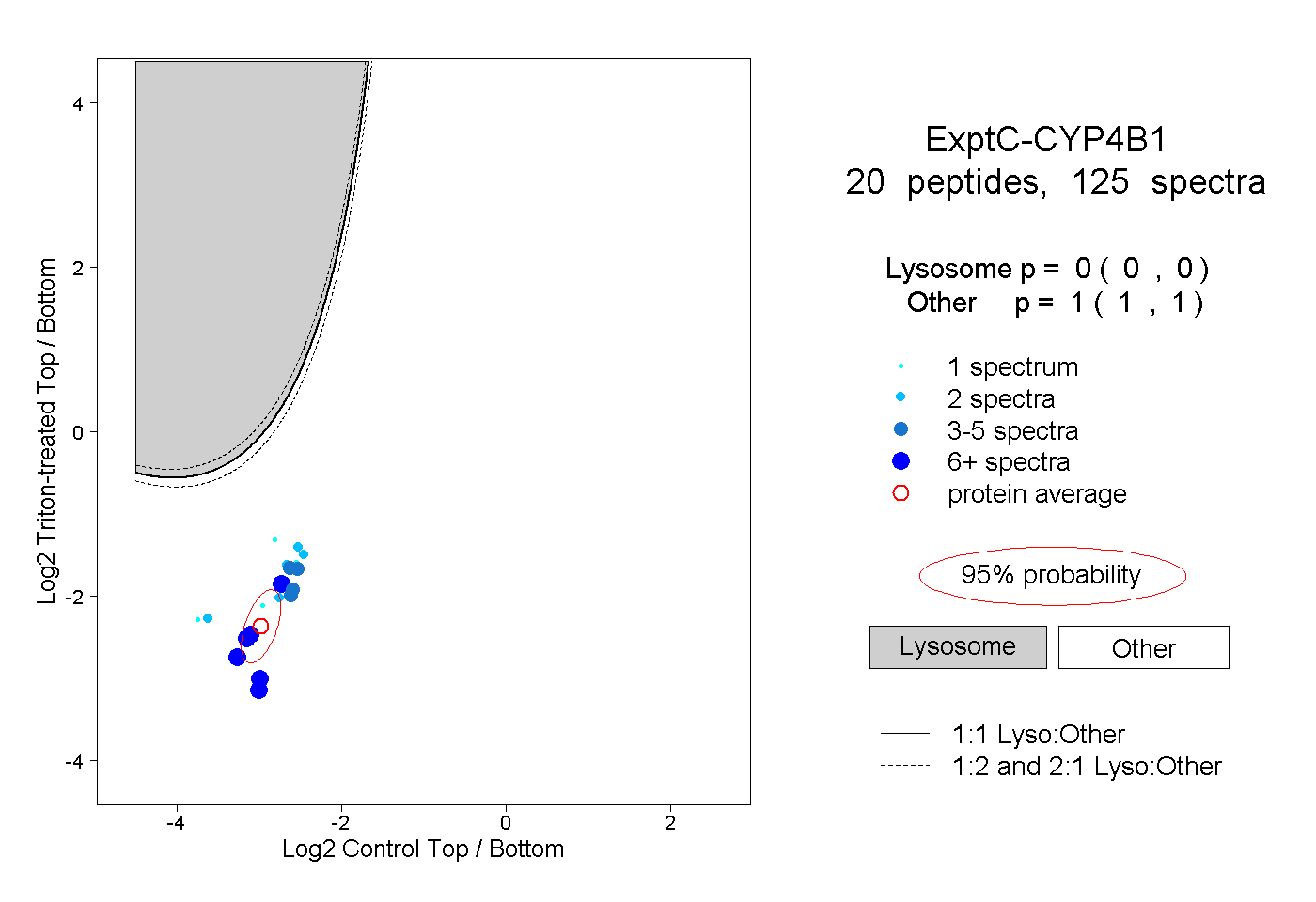
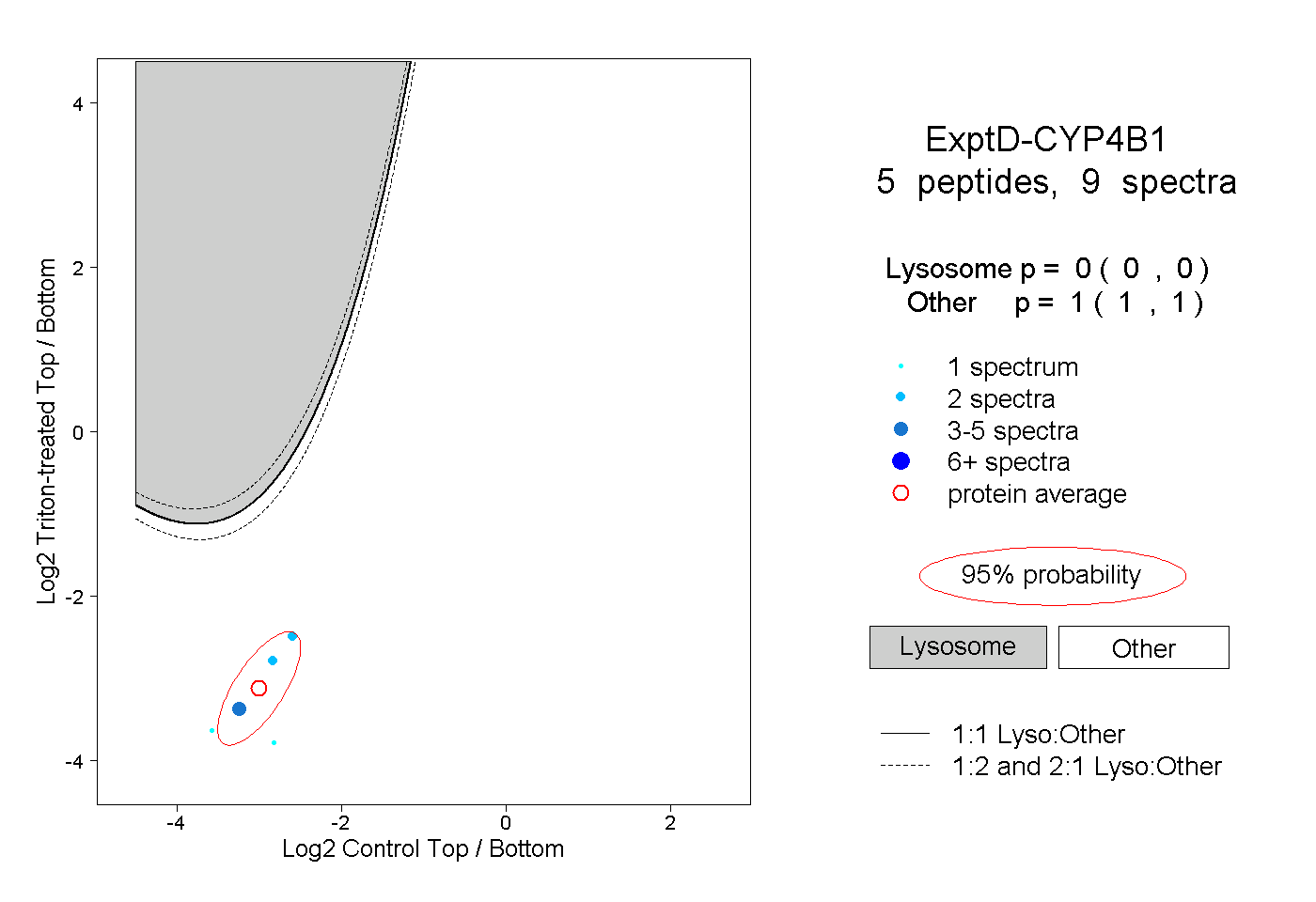
| 2 spectra, VVTALCLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, IPVPMAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VLNFLSPSLSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, NSTVWPDPEVFDPLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FEFSLDPSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, MTYLTMCMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QLNKPVTFVDGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GILGDQDSFQWDDLAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LYPPVPQVYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, FSPENAAGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LGSLDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, GFSVFTPTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HPFAFMPFSAGPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VPQLILR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, AVEDLNNLTFFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, LYPPVPSVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GLLVLDGPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DESGIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, LSDAELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, MLTPAFHYGILKPYVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |