peptides
spectra
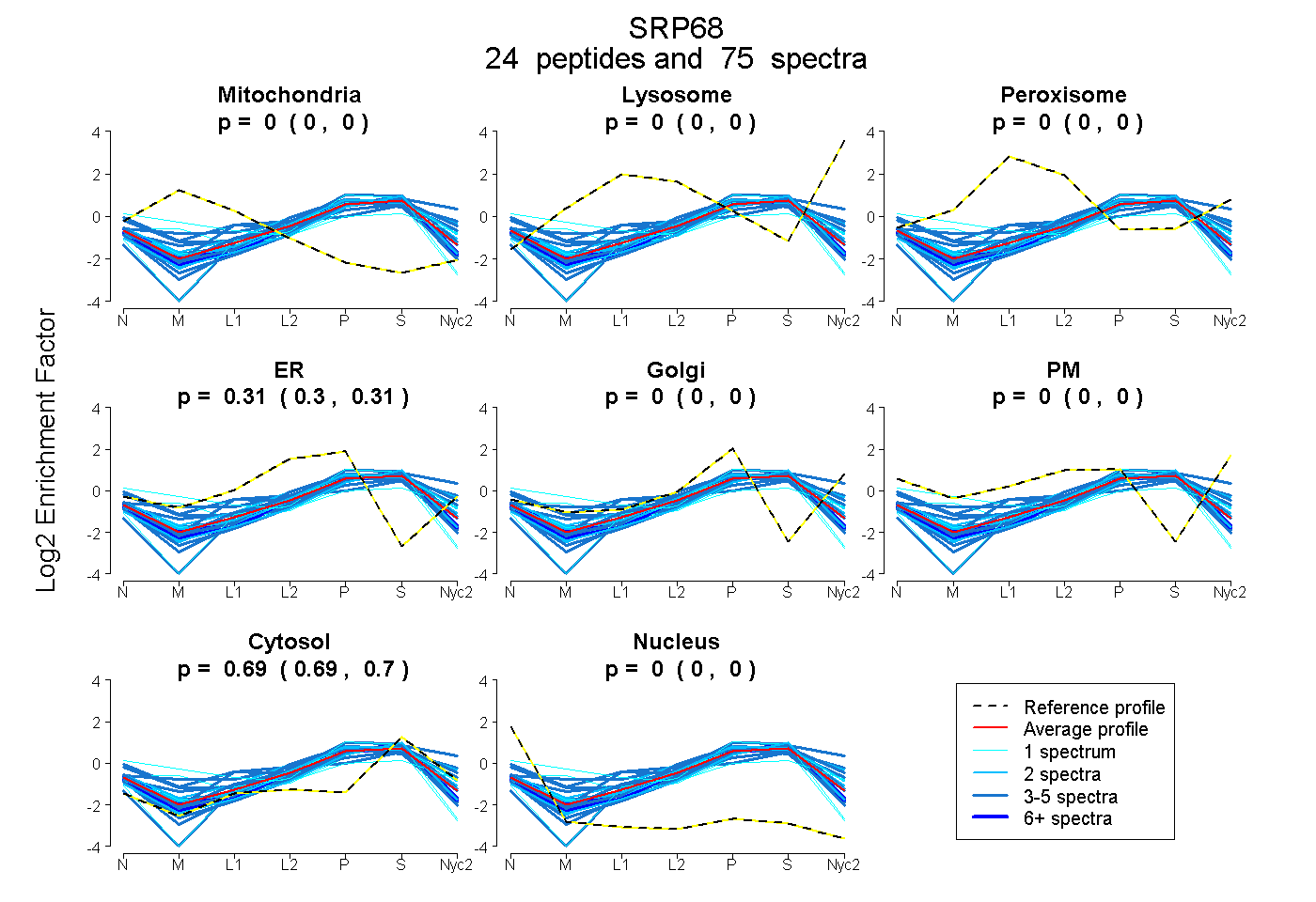
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.304 | 0.308
0.000 | 0.000
0.000 | 0.000
0.691 | 0.695
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
75 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.306 0.304 | 0.308 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.694 0.691 | 0.695 |
0.000 0.000 | 0.000 |
| 3 spectra, LFESMLSECR | 0.070 | 0.000 | 0.000 | 0.393 | 0.000 | 0.000 | 0.537 | 0.000 | ||
| 2 spectra, NENMAK | 0.000 | 0.000 | 0.012 | 0.259 | 0.160 | 0.000 | 0.569 | 0.000 | ||
| 4 spectra, AAIEAFNR | 0.000 | 0.000 | 0.000 | 0.262 | 0.000 | 0.000 | 0.704 | 0.034 | ||
| 3 spectra, DLPDVQELITQVR | 0.000 | 0.000 | 0.000 | 0.195 | 0.000 | 0.000 | 0.764 | 0.040 | ||
| 7 spectra, HAEELER | 0.000 | 0.000 | 0.000 | 0.263 | 0.000 | 0.000 | 0.714 | 0.023 | ||
| 1 spectrum, SGGTEGLLAEK | 0.224 | 0.000 | 0.045 | 0.000 | 0.169 | 0.121 | 0.442 | 0.000 | ||
| 2 spectra, FEHQEWK | 0.000 | 0.000 | 0.000 | 0.299 | 0.000 | 0.000 | 0.680 | 0.021 | ||
| 1 spectrum, LASAFTEEQAVLYNQR | 0.000 | 0.000 | 0.000 | 0.215 | 0.144 | 0.000 | 0.641 | 0.000 | ||
| 4 spectra, QEANTEPR | 0.000 | 0.000 | 0.000 | 0.327 | 0.000 | 0.000 | 0.650 | 0.023 | ||
| 4 spectra, AWSYAMQLK | 0.000 | 0.000 | 0.000 | 0.259 | 0.147 | 0.000 | 0.594 | 0.000 | ||
| 3 spectra, GIFGFR | 0.000 | 0.000 | 0.000 | 0.229 | 0.000 | 0.000 | 0.771 | 0.000 | ||
| 2 spectra, DNTPLVER | 0.000 | 0.000 | 0.000 | 0.264 | 0.039 | 0.000 | 0.696 | 0.000 | ||
| 2 spectra, WSEALVLYDR | 0.000 | 0.000 | 0.000 | 0.192 | 0.000 | 0.000 | 0.776 | 0.032 | ||
| 1 spectrum, SGLTGYIK | 0.000 | 0.000 | 0.000 | 0.194 | 0.000 | 0.000 | 0.754 | 0.052 | ||
| 2 spectra, HGDFQR | 0.000 | 0.000 | 0.000 | 0.155 | 0.165 | 0.000 | 0.680 | 0.000 | ||
| 2 spectra, YLLLVLMDAER | 0.000 | 0.000 | 0.000 | 0.316 | 0.024 | 0.000 | 0.660 | 0.000 | ||
| 3 spectra, SPRPQDLIR | 0.000 | 0.121 | 0.037 | 0.000 | 0.249 | 0.000 | 0.593 | 0.000 | ||
| 4 spectra, DALQAVR | 0.000 | 0.000 | 0.000 | 0.246 | 0.000 | 0.000 | 0.730 | 0.024 | ||
| 3 spectra, LCESSR | 0.024 | 0.000 | 0.000 | 0.331 | 0.000 | 0.000 | 0.615 | 0.031 | ||
| 4 spectra, VTEELLTDSR | 0.000 | 0.000 | 0.000 | 0.189 | 0.009 | 0.000 | 0.760 | 0.043 | ||
| 8 spectra, FHLLSR | 0.000 | 0.000 | 0.000 | 0.291 | 0.000 | 0.000 | 0.673 | 0.036 | ||
| 1 spectrum, FETFCLDPSLVTK | 0.190 | 0.000 | 0.000 | 0.186 | 0.000 | 0.000 | 0.567 | 0.057 | ||
| 5 spectra, QAATMSEVEWR | 0.000 | 0.000 | 0.000 | 0.162 | 0.182 | 0.000 | 0.656 | 0.000 | ||
| 4 spectra, ESQQQHGLR | 0.000 | 0.000 | 0.134 | 0.072 | 0.000 | 0.235 | 0.558 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
32 spectra |
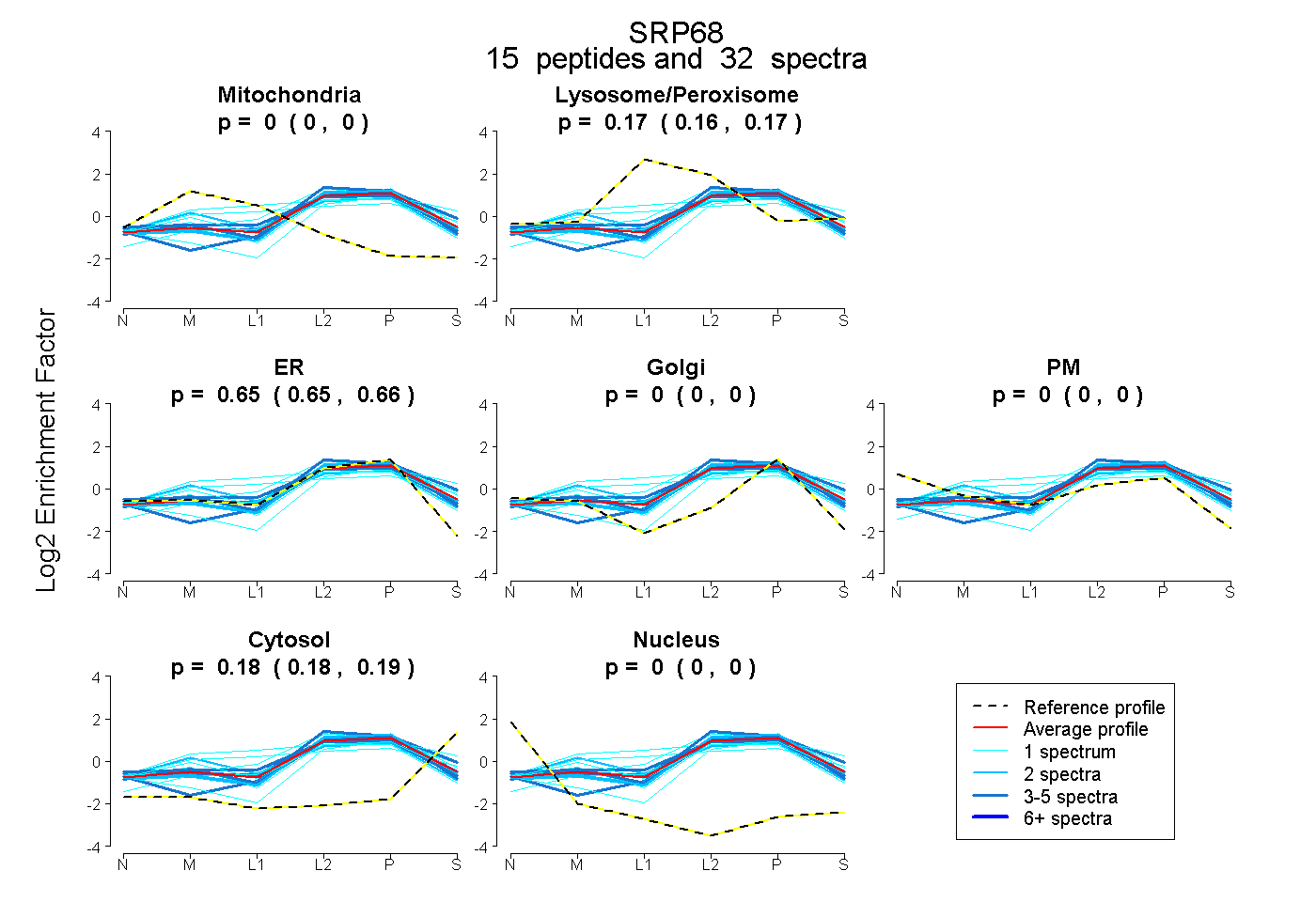 |
0.000 0.000 | 0.000 |
0.166 0.157 | 0.172 |
0.653 0.645 | 0.660 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.181 0.177 | 0.185 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
54 spectra |
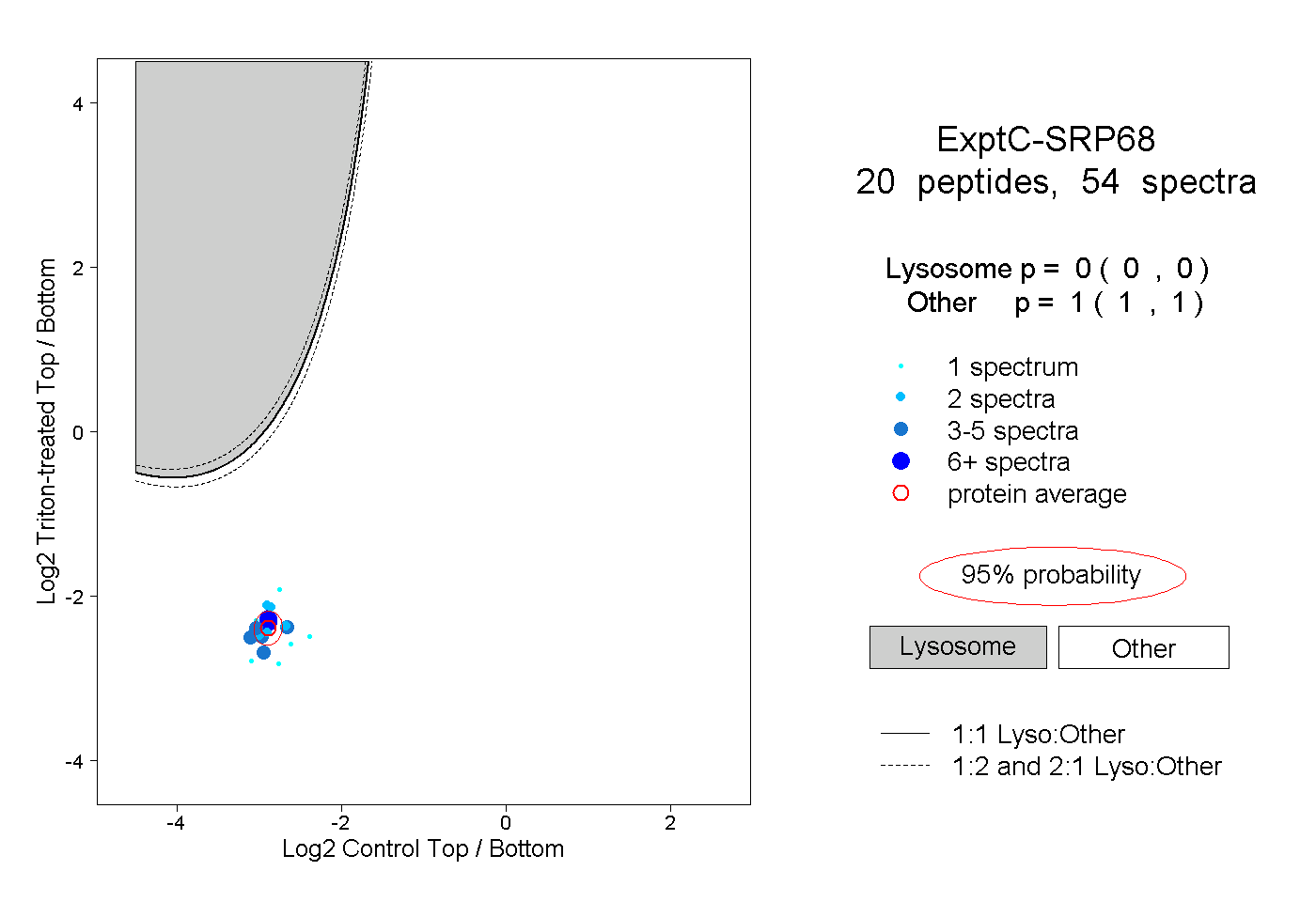 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
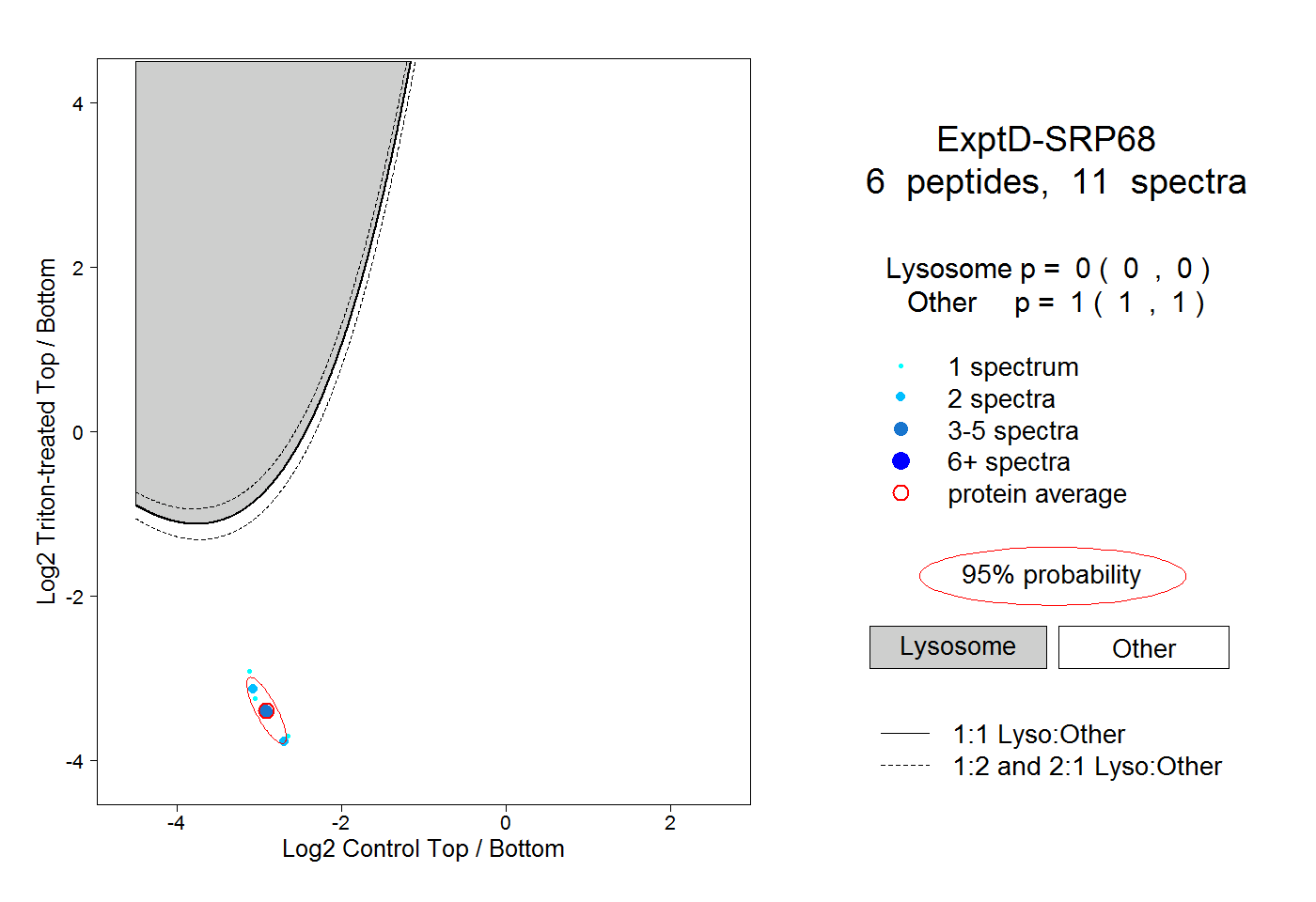 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |