peptides
spectra
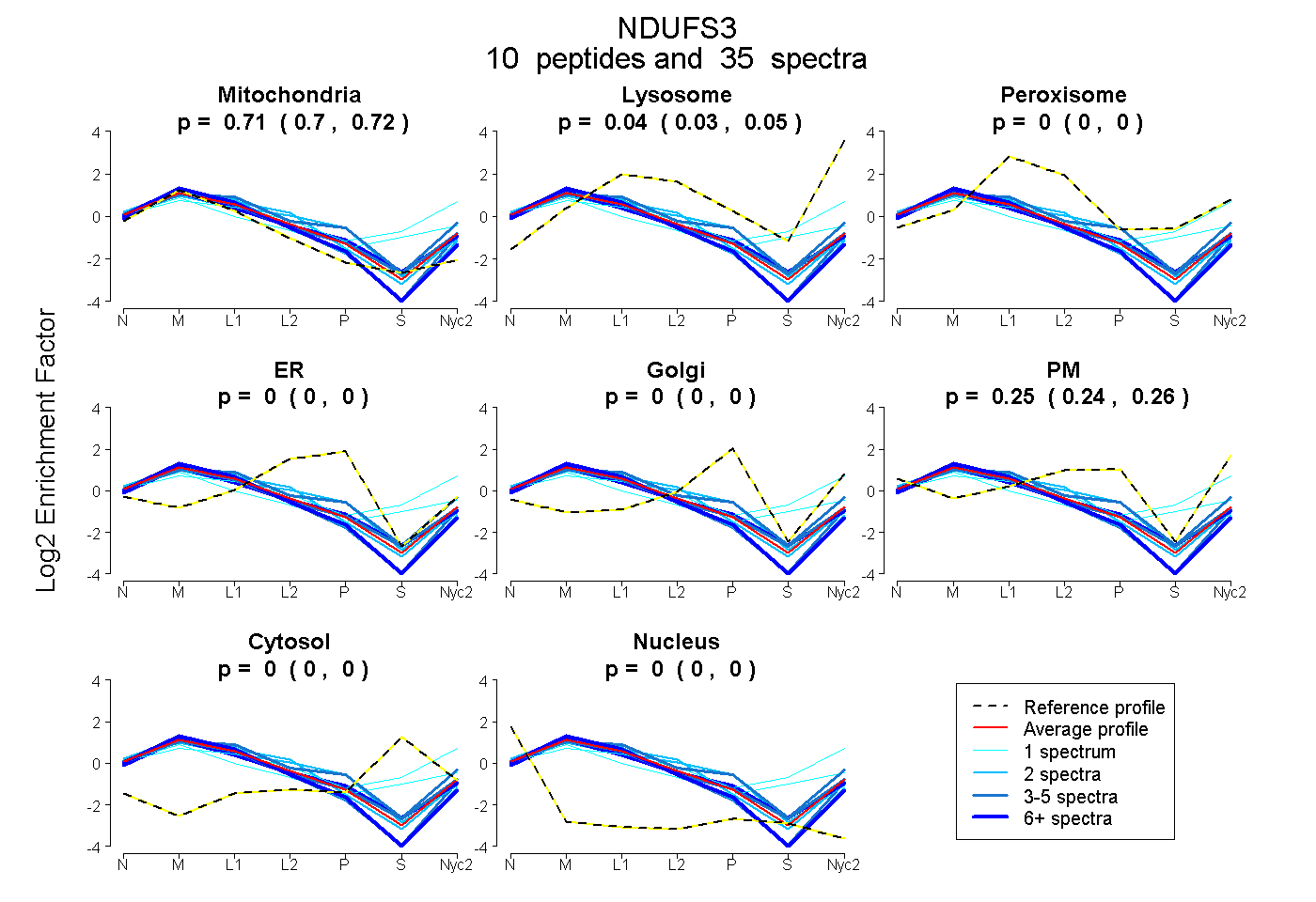
0.702 | 0.717
0.027 | 0.049
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.237 | 0.262
0.000 | 0.000
0.000 | 0.000
peptides
spectra
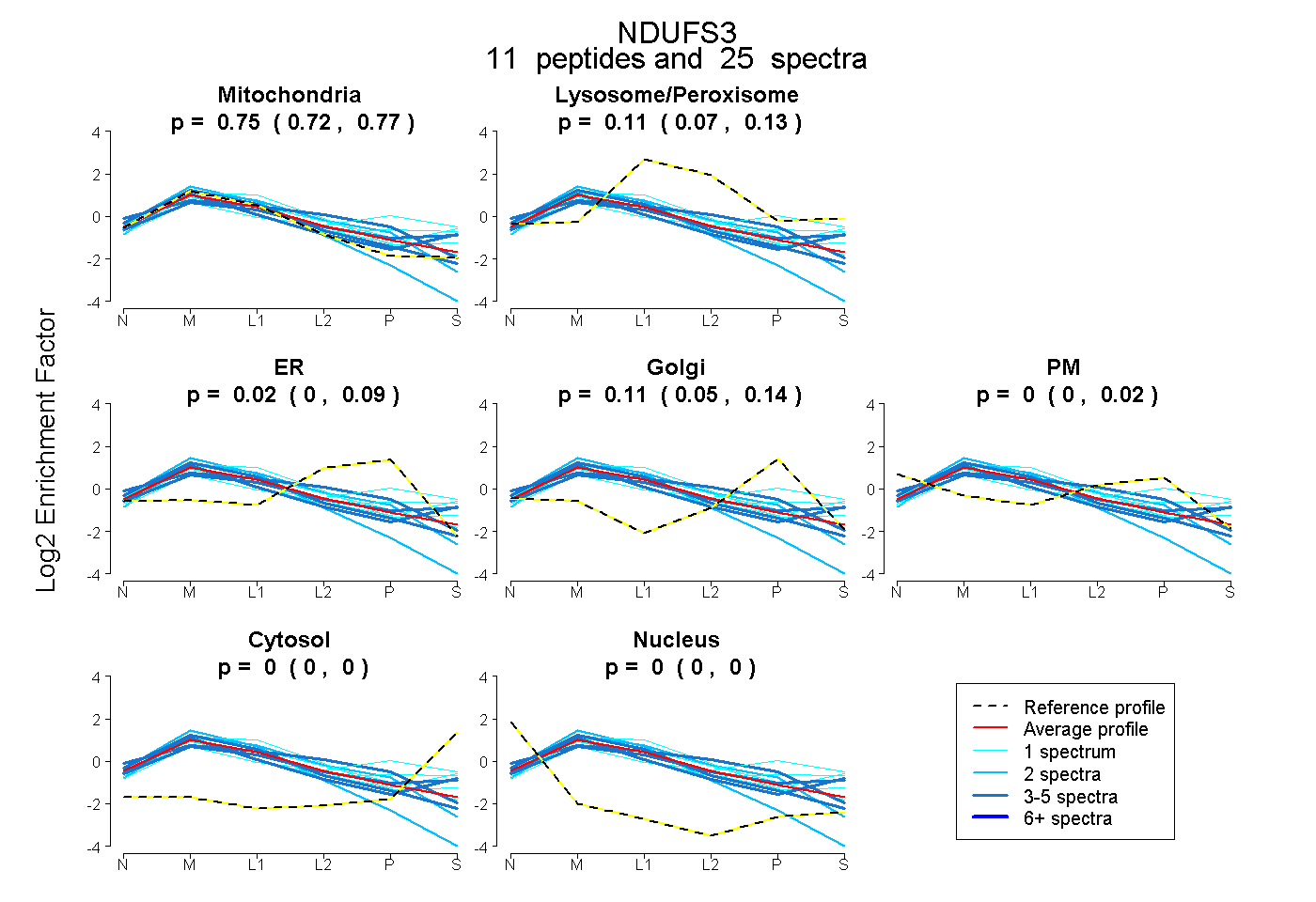
0.725 | 0.770
0.068 | 0.134
0.000 | 0.087
0.048 | 0.138
0.000 | 0.022
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
35 spectra |
 |
0.710 0.702 | 0.717 |
0.039 0.027 | 0.049 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.251 0.237 | 0.262 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.747 0.725 | 0.770 |
0.115 0.068 | 0.134 |
0.023 0.000 | 0.087 |
0.115 0.048 | 0.138 |
0.000 0.000 | 0.022 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, EVWDMFGVFFFNHPDLR | 0.735 | 0.259 | 0.000 | 0.004 | 0.000 | 0.002 | 0.000 | |||
| 2 spectra, DHTNAQFK | 0.741 | 0.023 | 0.236 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DFPLTGYVELR | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | |||
| 5 spectra, QPPEHLK | 0.885 | 0.000 | 0.044 | 0.000 | 0.071 | 0.000 | 0.000 | |||
| 1 spectrum, ESAAADK | 0.718 | 0.094 | 0.100 | 0.000 | 0.088 | 0.000 | 0.000 | |||
| 5 spectra, ILTDYGFEGHPFR | 0.510 | 0.121 | 0.156 | 0.000 | 0.213 | 0.000 | 0.000 | |||
| 1 spectrum, LEAGDK | 0.622 | 0.203 | 0.000 | 0.000 | 0.016 | 0.159 | 0.000 | |||
| 1 spectrum, FDLNSPWEAFPAYR | 0.527 | 0.167 | 0.000 | 0.173 | 0.000 | 0.133 | 0.000 | |||
| 3 spectra, SLADLTAVDVPTR | 0.747 | 0.071 | 0.000 | 0.000 | 0.004 | 0.178 | 0.000 | |||
| 1 spectrum, LSAFGEYVAEILPK | 0.296 | 0.270 | 0.000 | 0.308 | 0.000 | 0.126 | 0.000 | |||
| 3 spectra, VVAEPVELAQEFR | 0.566 | 0.201 | 0.000 | 0.106 | 0.000 | 0.126 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
275 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |