peptides
spectra
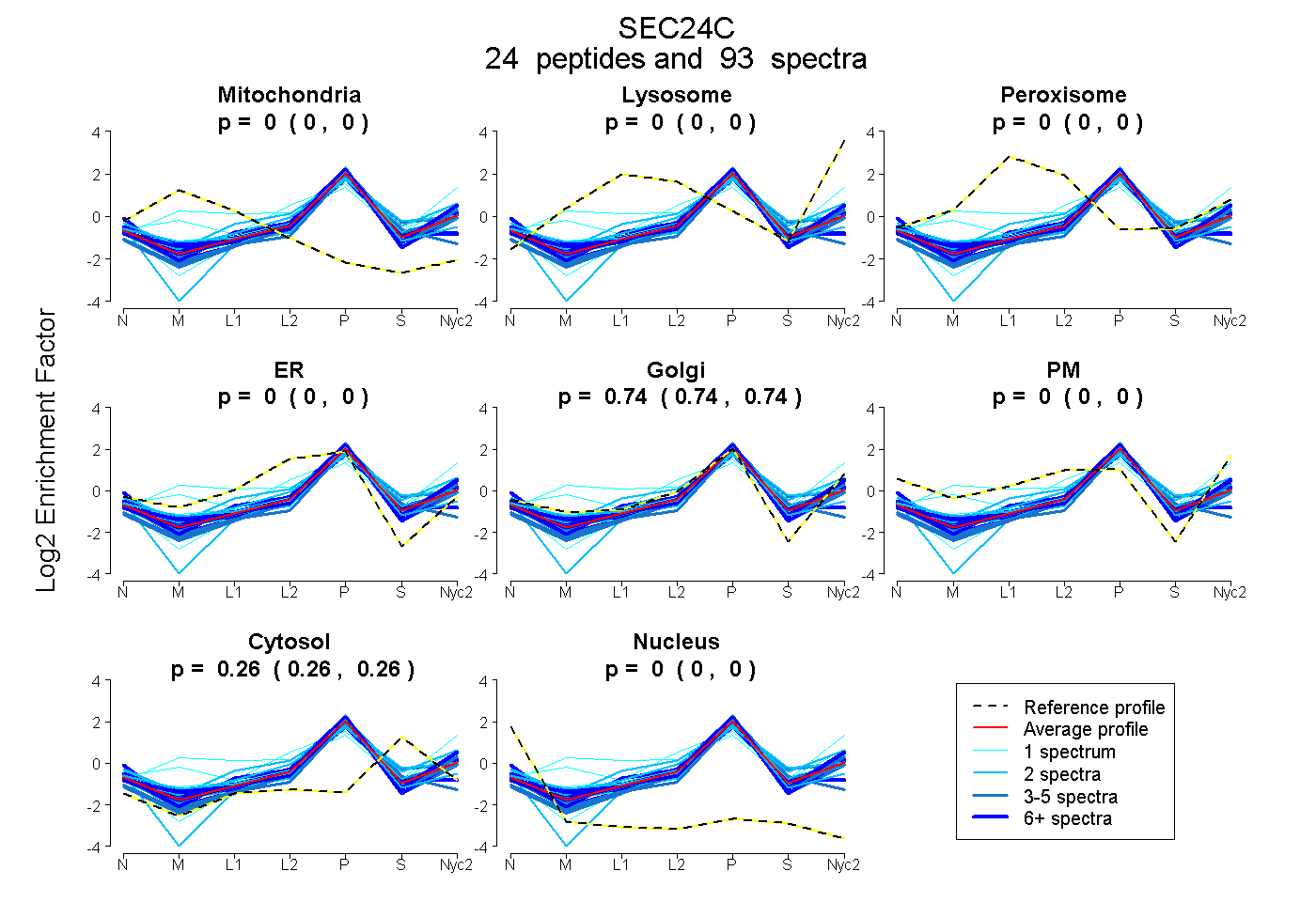
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.739 | 0.743
0.000 | 0.000
0.256 | 0.261
0.000 | 0.000
peptides
spectra
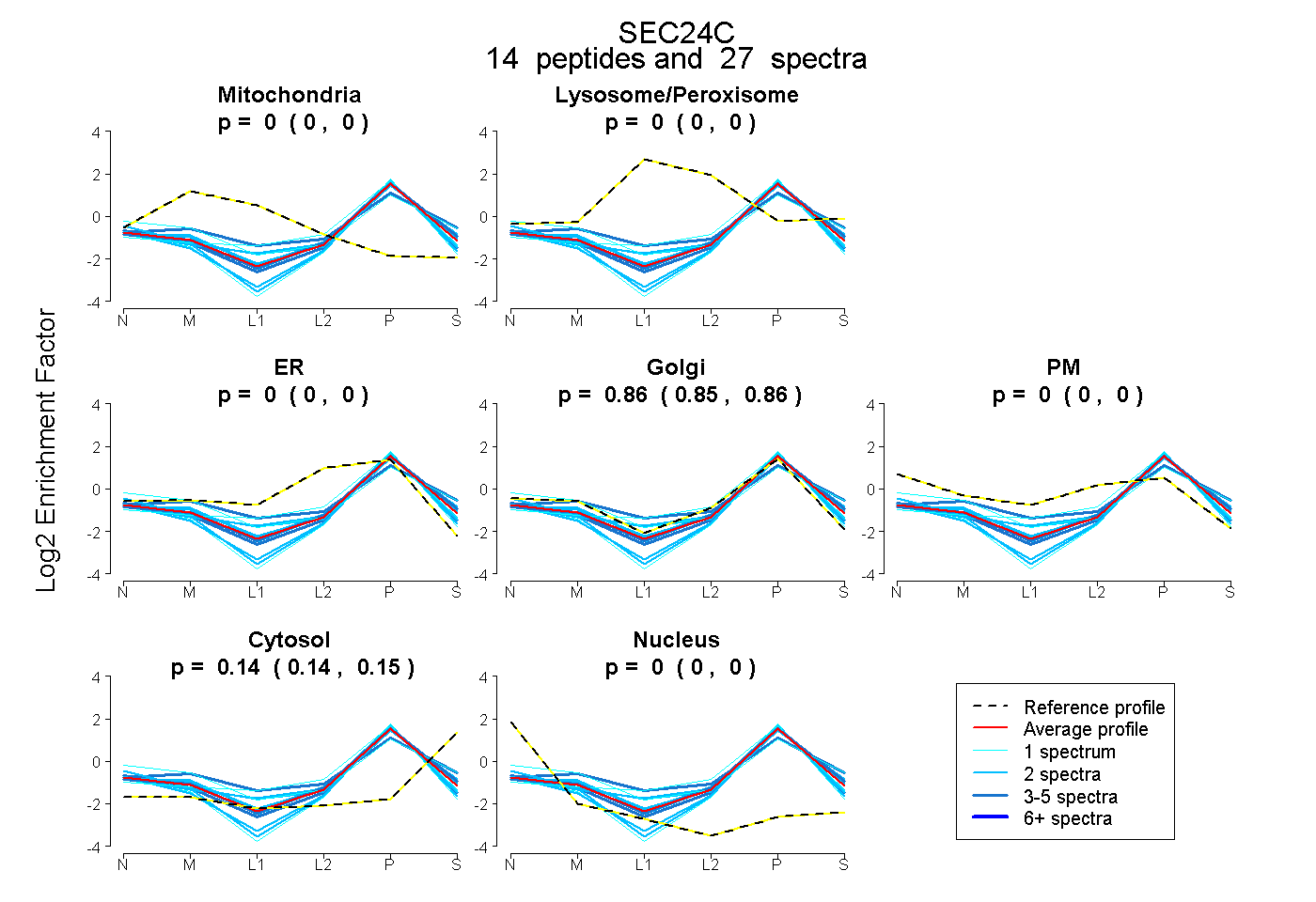
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.853 | 0.863
0.000 | 0.000
0.135 | 0.146
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
93 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.741 0.739 | 0.743 |
0.000 0.000 | 0.000 |
0.259 0.256 | 0.261 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.859 0.853 | 0.863 |
0.000 0.000 | 0.000 |
0.141 0.135 | 0.146 |
0.000 0.000 | 0.000 |
| 3 spectra, EGGAEESAIR | 0.000 | 0.000 | 0.000 | 0.898 | 0.000 | 0.102 | 0.000 | |||
| 1 spectrum, VLHFYNVK | 0.000 | 0.074 | 0.047 | 0.808 | 0.000 | 0.070 | 0.000 | |||
| 3 spectra, GQVPPLVTTNFLVK | 0.000 | 0.123 | 0.000 | 0.675 | 0.000 | 0.202 | 0.000 | |||
| 2 spectra, AVVSSPVK | 0.000 | 0.000 | 0.000 | 0.849 | 0.000 | 0.151 | 0.000 | |||
| 2 spectra, SLLDYLPR | 0.000 | 0.000 | 0.000 | 0.898 | 0.000 | 0.082 | 0.020 | |||
| 1 spectrum, GLIDTLR | 0.000 | 0.000 | 0.000 | 0.885 | 0.000 | 0.115 | 0.000 | |||
| 2 spectra, GSEPFVTGVR | 0.000 | 0.001 | 0.000 | 0.906 | 0.000 | 0.093 | 0.000 | |||
| 3 spectra, VVGFDAVMR | 0.000 | 0.000 | 0.000 | 0.829 | 0.000 | 0.171 | 0.000 | |||
| 2 spectra, LPPEEASPYVVDHGESGPLR | 0.000 | 0.000 | 0.000 | 0.861 | 0.000 | 0.139 | 0.000 | |||
| 1 spectrum, YACFQVENDQER | 0.000 | 0.019 | 0.000 | 0.669 | 0.086 | 0.226 | 0.000 | |||
| 2 spectra, VGFVTYNK | 0.000 | 0.000 | 0.000 | 0.836 | 0.000 | 0.164 | 0.000 | |||
| 2 spectra, HFLVEDK | 0.000 | 0.000 | 0.000 | 0.897 | 0.000 | 0.103 | 0.000 | |||
| 1 spectrum, SPLDSTTEPPAVR | 0.000 | 0.000 | 0.000 | 0.906 | 0.000 | 0.057 | 0.036 | |||
| 2 spectra, LICEELK | 0.000 | 0.013 | 0.000 | 0.802 | 0.000 | 0.185 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
108 spectra |
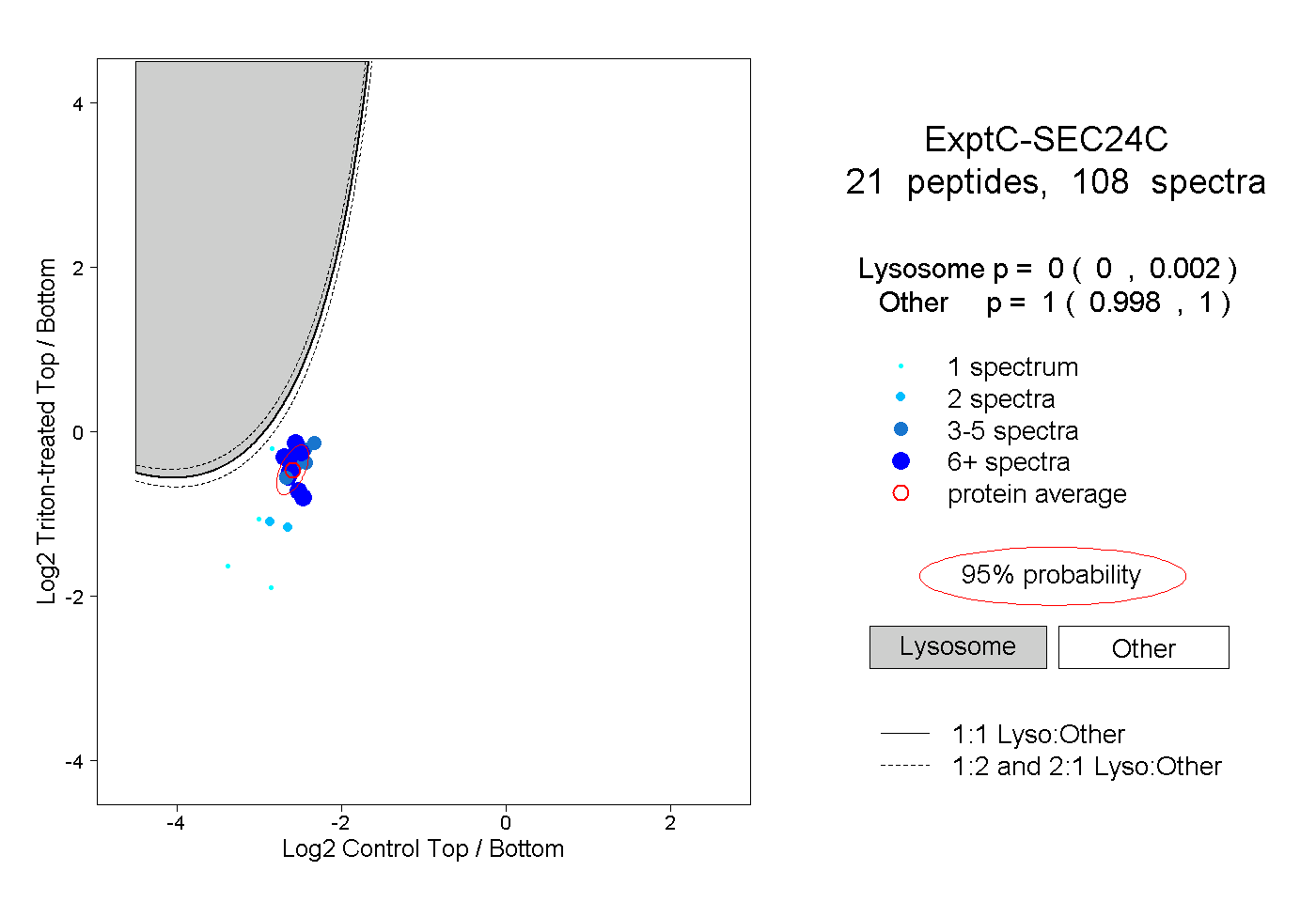 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
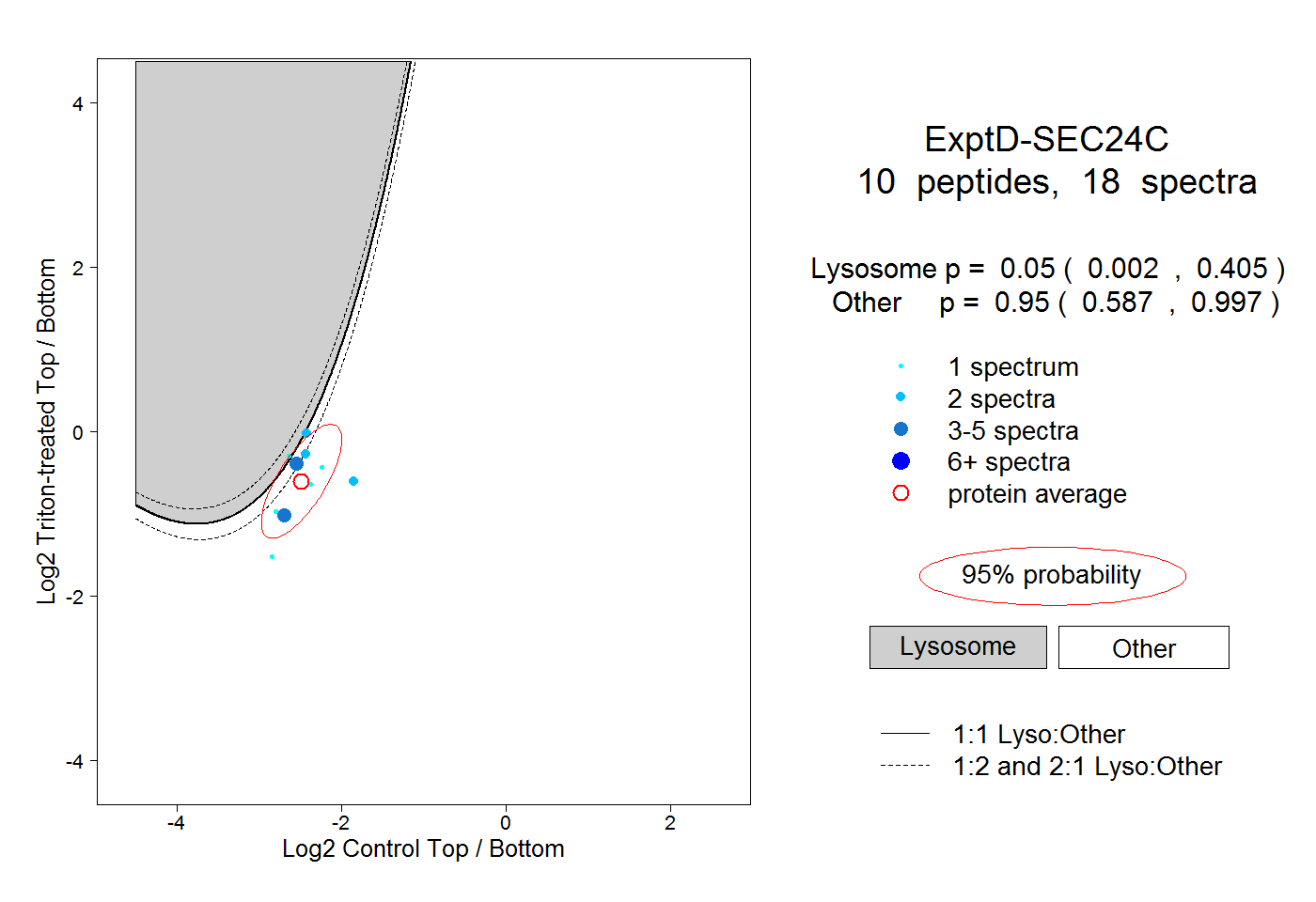 |
0.050 0.002 | 0.405 |
0.950 0.587 | 0.997 |