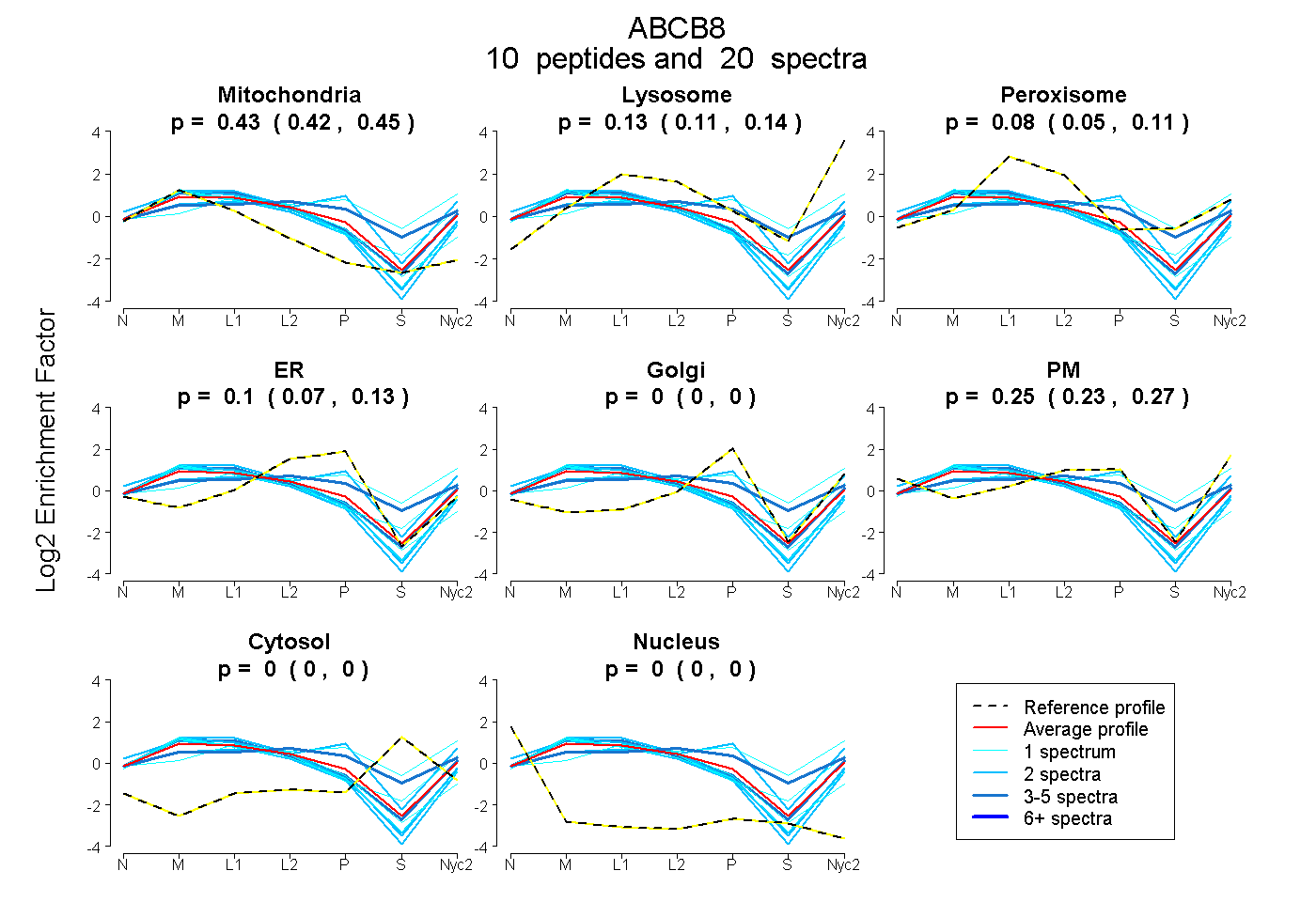
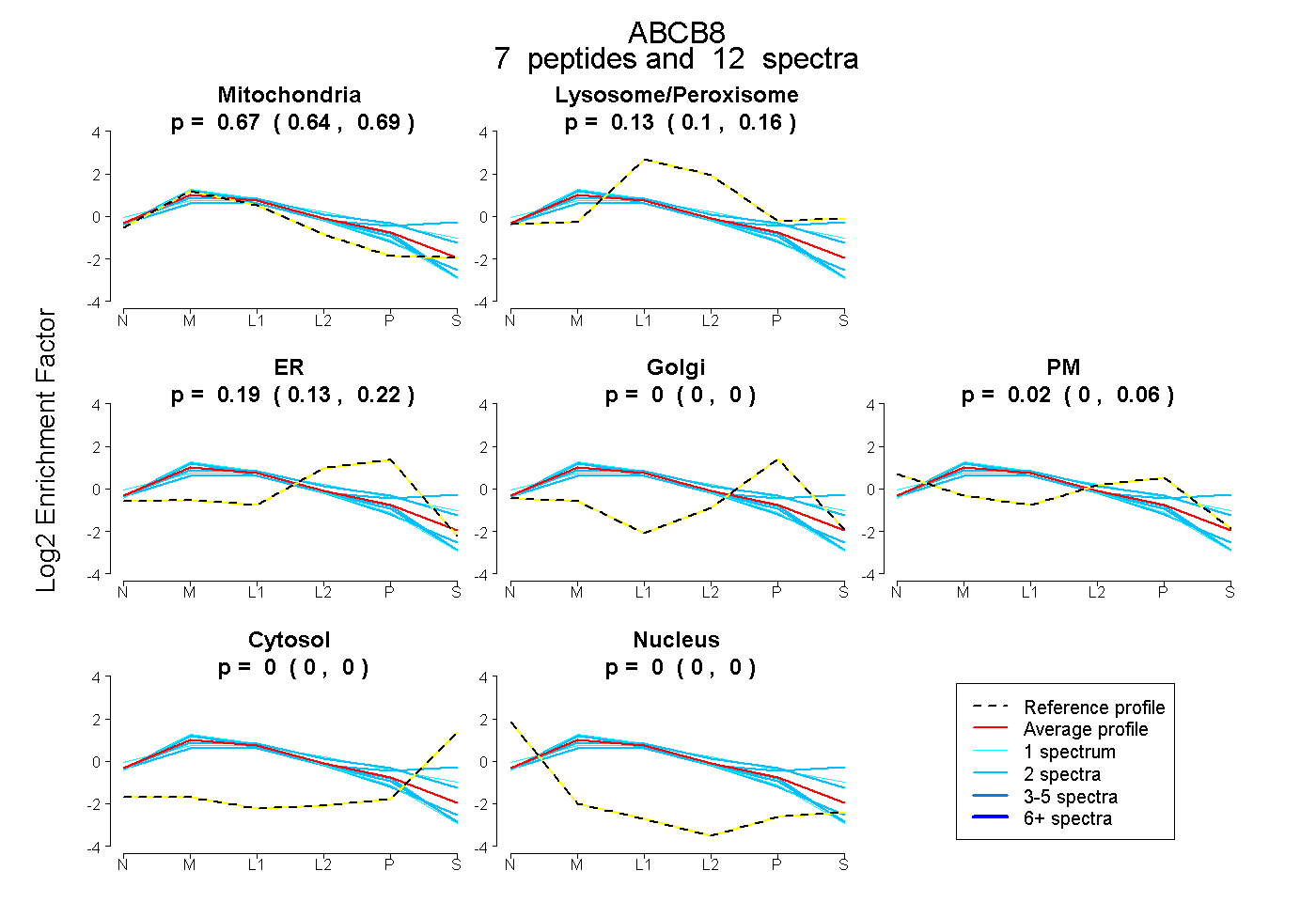
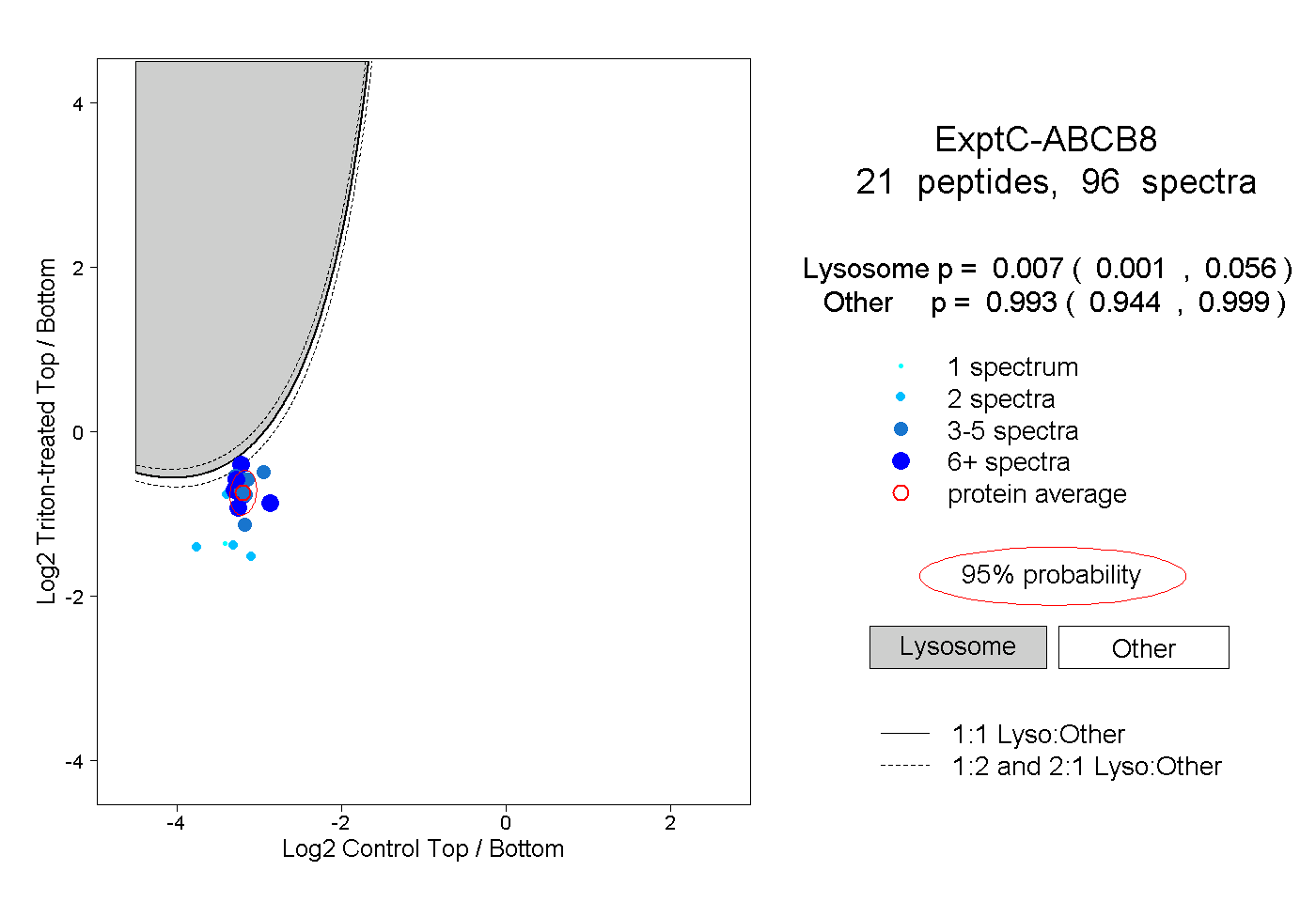
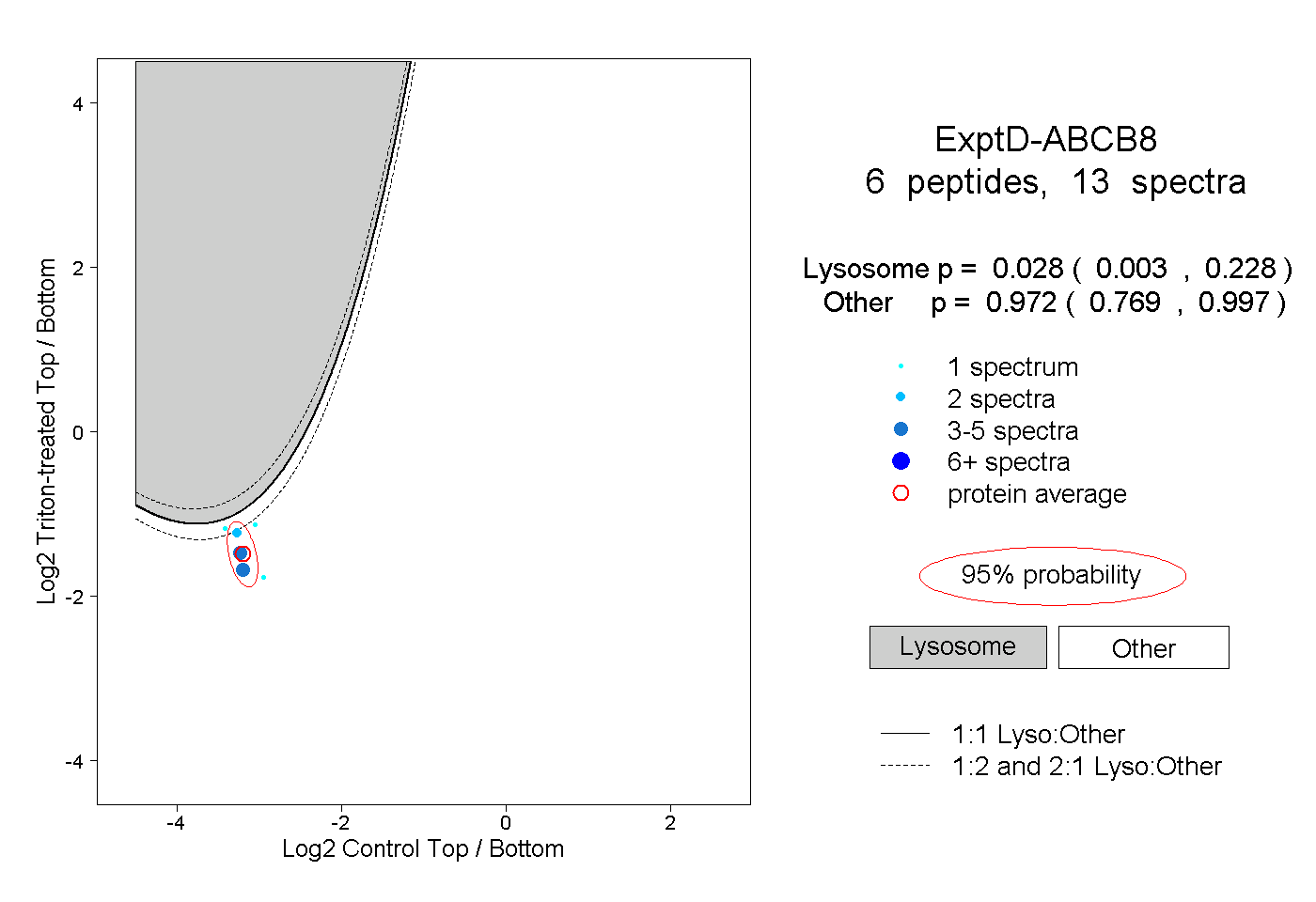
| 6 spectra, TTVASLLER |
|
0.061 |
|
|
|
|
|
|
|
0.939 |
| 4 spectra, GLSAGAR |
|
0.011 |
|
|
|
|
|
|
|
0.989 |
| 2 spectra, AFAMEK |
|
0.017 |
|
|
|
|
|
|
|
0.983 |
| 4 spectra, TLDPSWLR |
|
0.103 |
|
|
|
|
|
|
|
0.897 |
| 6 spectra, GTTLSGGQK |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 3 spectra, QDIAFFDAK |
|
0.036 |
|
|
|
|
|
|
|
0.964 |
| 12 spectra, GSPPAQPTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, IVALVGQSGGGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ALFSSLLR |
|
0.018 |
|
|
|
|
|
|
|
0.982 |
| 2 spectra, ATGVADEALGSVR |
|
0.012 |
|
|
|
|
|
|
|
0.988 |
| 2 spectra, RPTVLILDEATSALDAESER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GGLYAELIR |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 4 spectra, LTTDVQEFK |
|
0.011 |
|
|
|
|
|
|
|
0.989 |
| 4 spectra, TGQLVSR |
|
0.033 |
|
|
|
|
|
|
|
0.967 |
| 2 spectra, FYDPTAGVVTLDGHDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GGDLMSFLVASQTVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YQAELESCCCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, IVQEALDR |
|
0.229 |
|
|
|
|
|
|
|
0.771 |
| 3 spectra, LVISQGLR |
|
0.004 |
|
|
|
|
|
|
|
0.996 |
| 4 spectra, QCQEQIAR |
|
0.025 |
|
|
|
|
|
|
|
0.975 |
| 6 spectra, LDASDEEVYTAAR |
|
0.065 |
|
|
|
|
|
|
|
0.935 |