peptides
spectra

0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.959 | 0.968
0.023 | 0.032
0.000 | 0.008
0.000 | 0.000
0.003 | 0.005
peptides
spectra
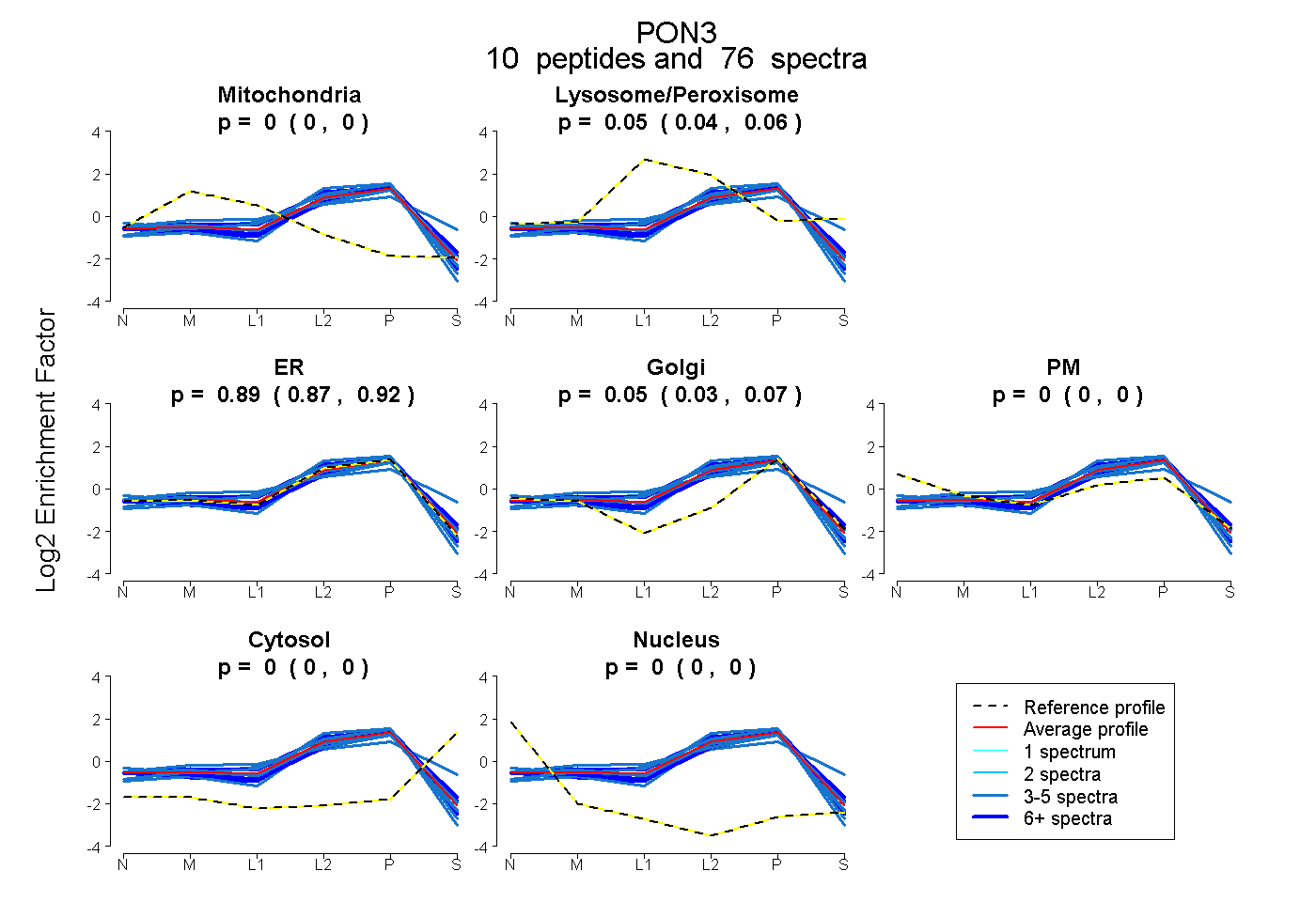
0.000 | 0.004
0.039 | 0.060
0.872 | 0.916
0.034 | 0.065
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
128 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.964 0.959 | 0.968 |
0.027 0.023 | 0.032 |
0.005 0.000 | 0.008 |
0.000 0.000 | 0.000 |
0.004 0.003 | 0.005 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
76 spectra |
 |
0.000 0.000 | 0.004 |
0.052 0.039 | 0.060 |
0.894 0.872 | 0.916 |
0.054 0.034 | 0.065 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, YPGMPSFAPDKPGR | 0.065 | 0.132 | 0.697 | 0.106 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LLIYNPEDPPGSEVLR | 0.000 | 0.066 | 0.793 | 0.132 | 0.009 | 0.000 | 0.000 | |||
| 3 spectra, IFLMDLNEPYPK | 0.000 | 0.000 | 0.907 | 0.093 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, HNNWDLTPVK | 0.000 | 0.396 | 0.086 | 0.473 | 0.000 | 0.045 | 0.000 | |||
| 5 spectra, NIHIMK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, IQDPLSDNPR | 0.000 | 0.074 | 0.703 | 0.183 | 0.000 | 0.039 | 0.000 | |||
| 4 spectra, YVYVADVTAK | 0.048 | 0.000 | 0.920 | 0.000 | 0.032 | 0.000 | 0.000 | |||
| 5 spectra, SLVHLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, FEEQPR | 0.000 | 0.000 | 0.944 | 0.022 | 0.000 | 0.034 | 0.000 | |||
| 24 spectra, MLIGTIFHK | 0.000 | 0.041 | 0.959 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
155 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |