peptides
spectra
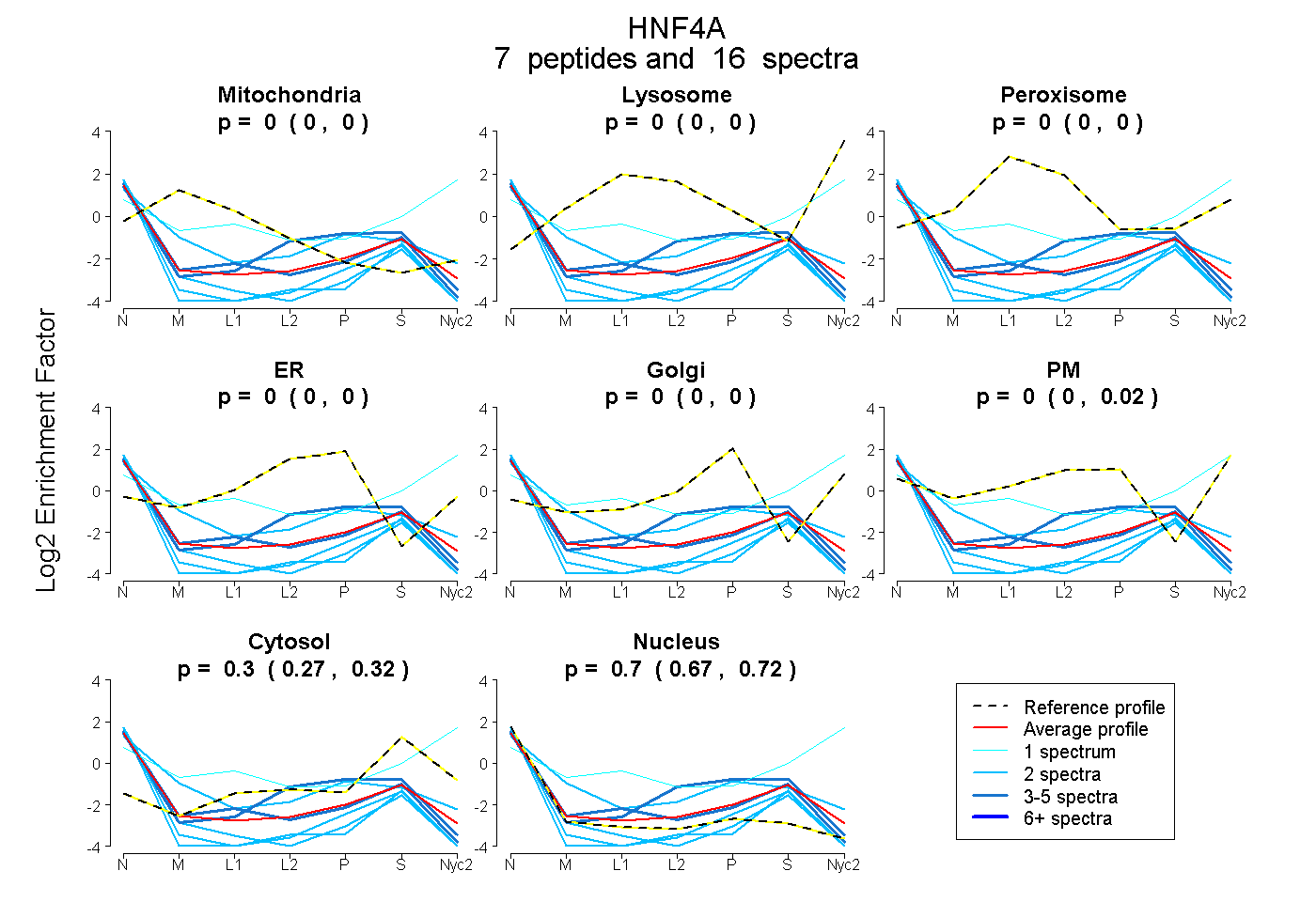
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.018
0.274 | 0.319
0.665 | 0.718
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.018 |
0.305 0.274 | 0.319 |
0.695 0.665 | 0.718 |
| 2 spectra, AHAGEHLLLGATK | 0.147 | 0.000 | 0.000 | 0.000 | 0.172 | 0.042 | 0.183 | 0.456 | ||
| 3 spectra, HCPELAEMSR | 0.000 | 0.000 | 0.000 | 0.157 | 0.000 | 0.000 | 0.267 | 0.576 | ||
| 4 spectra, AIIFFDPDAK | 0.000 | 0.000 | 0.001 | 0.000 | 0.000 | 0.000 | 0.257 | 0.742 | ||
| 1 spectrum, SQVQVSLEDYINDR | 0.000 | 0.405 | 0.000 | 0.000 | 0.000 | 0.106 | 0.291 | 0.199 | ||
| 2 spectra, DVLLLGNDYIVPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.056 | 0.944 | ||
| 2 spectra, EAVQNER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.045 | 0.955 | ||
| 2 spectra, LFGMAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.074 | 0.926 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
1.000 NA | NA |