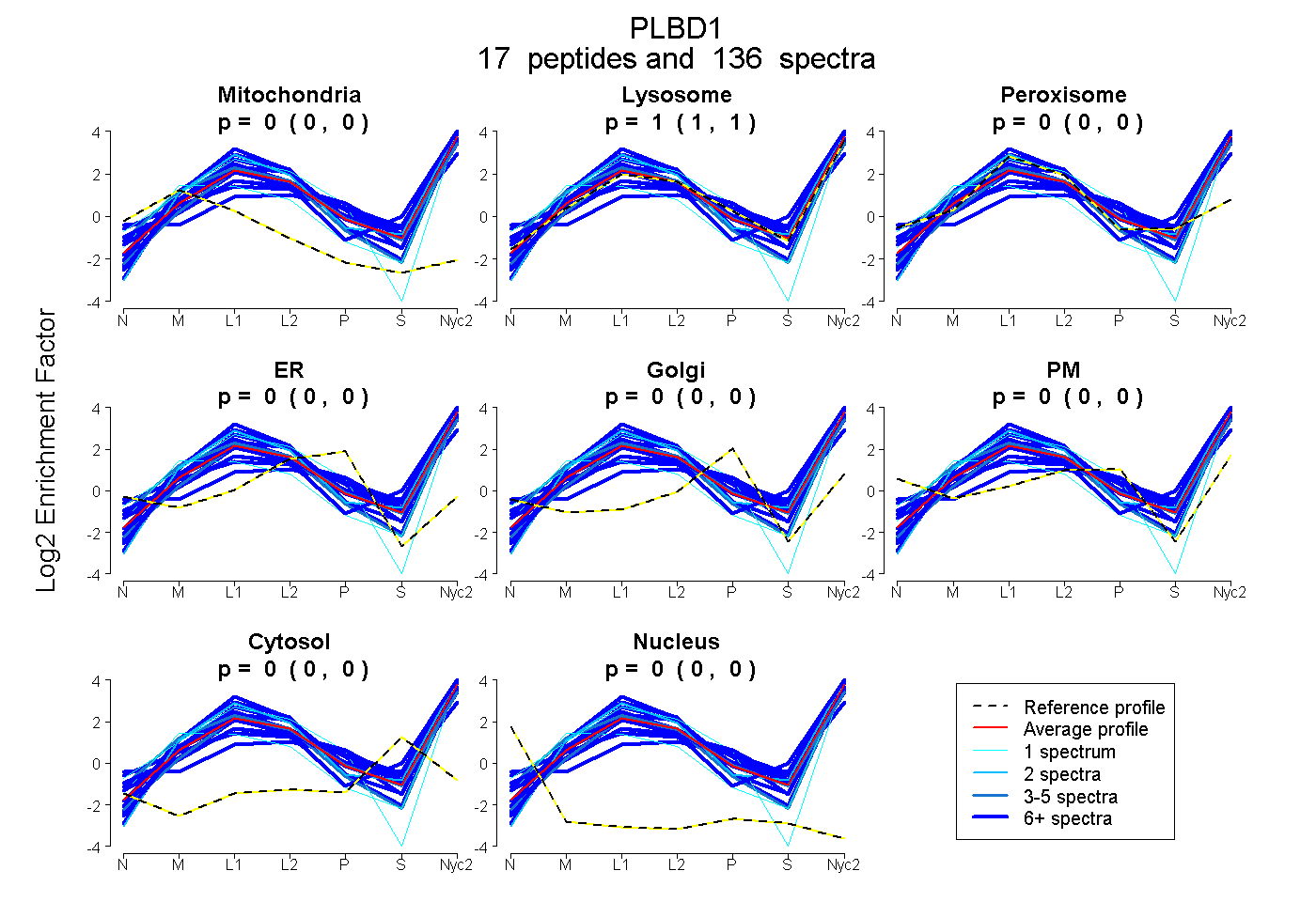
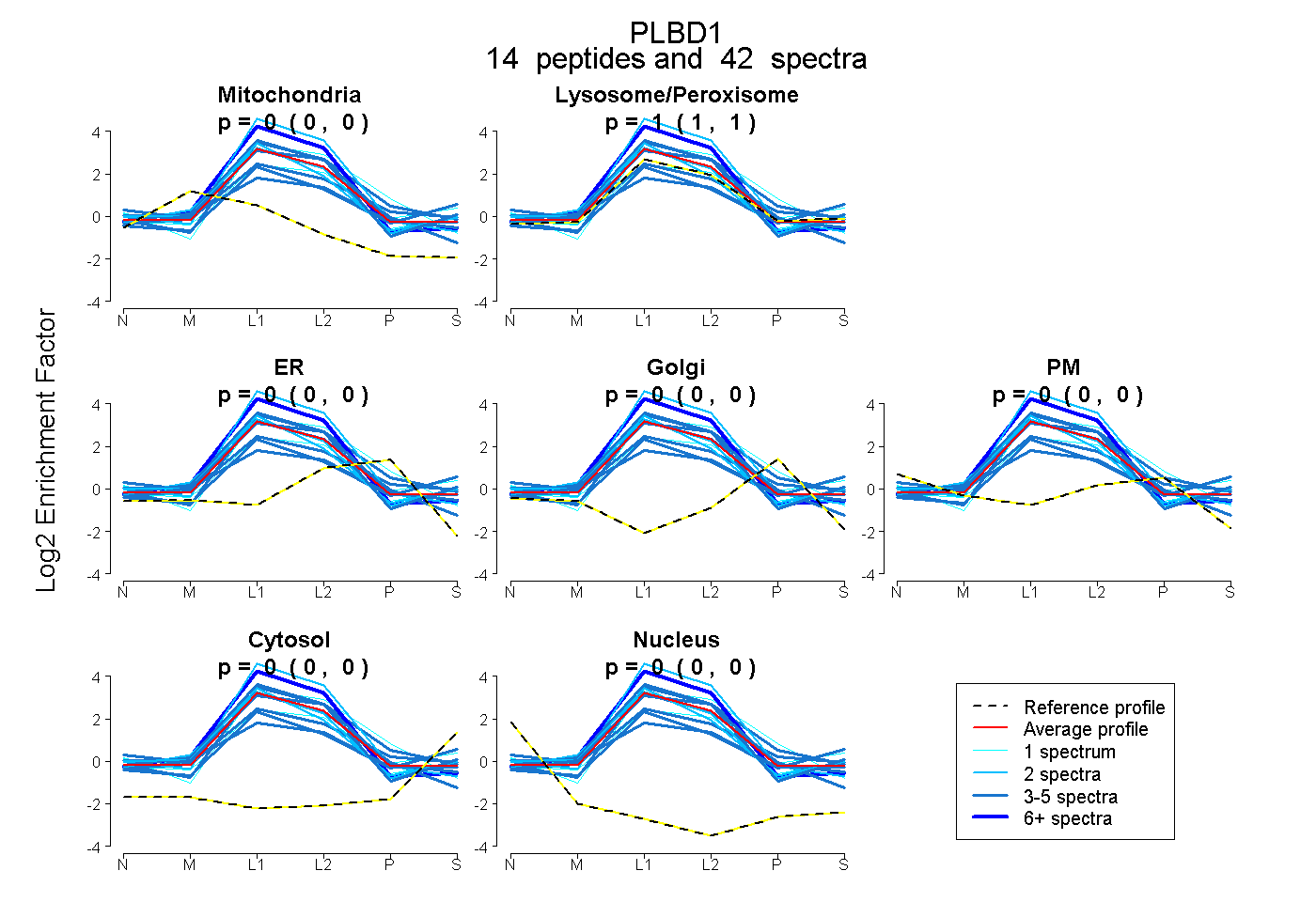
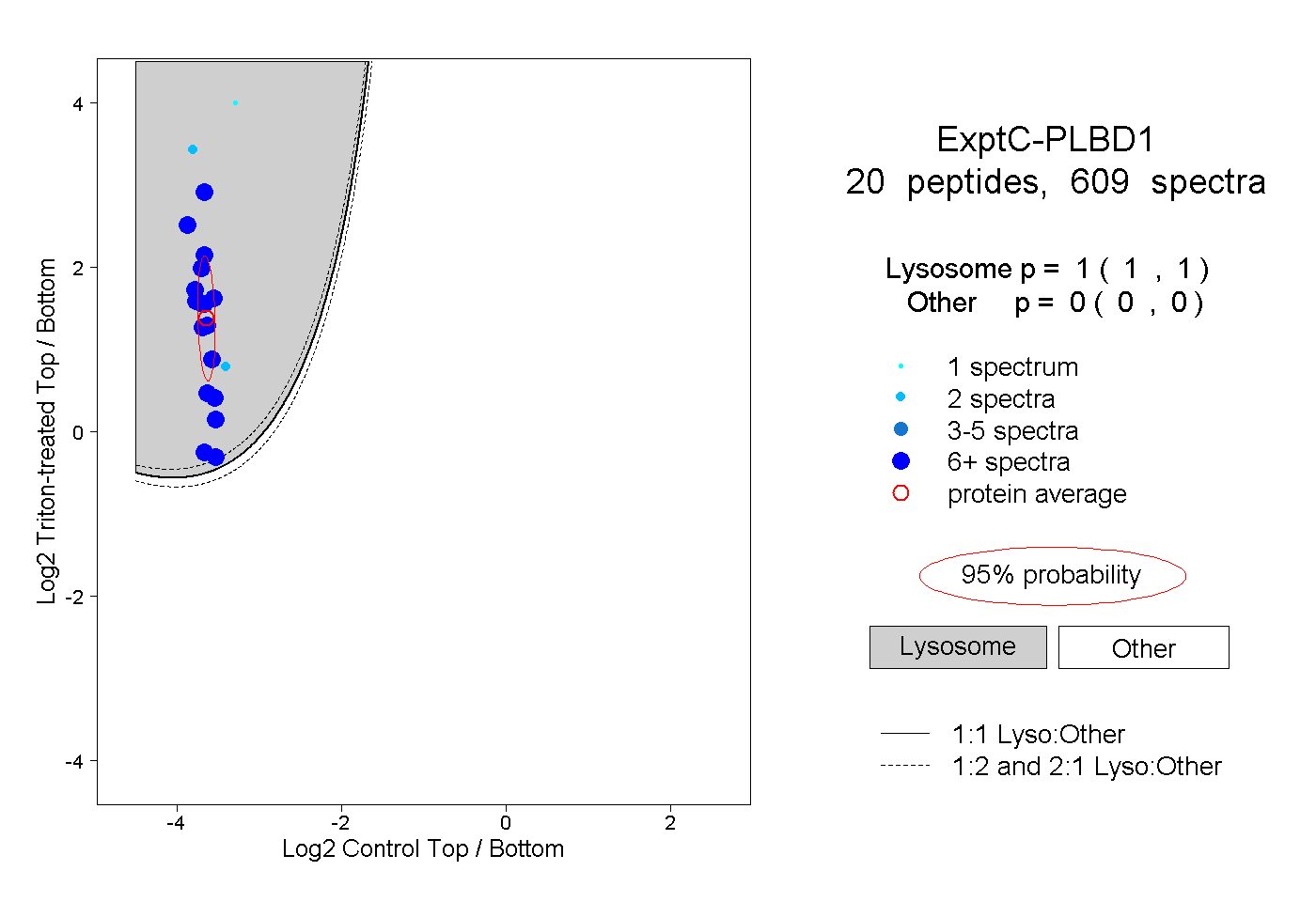
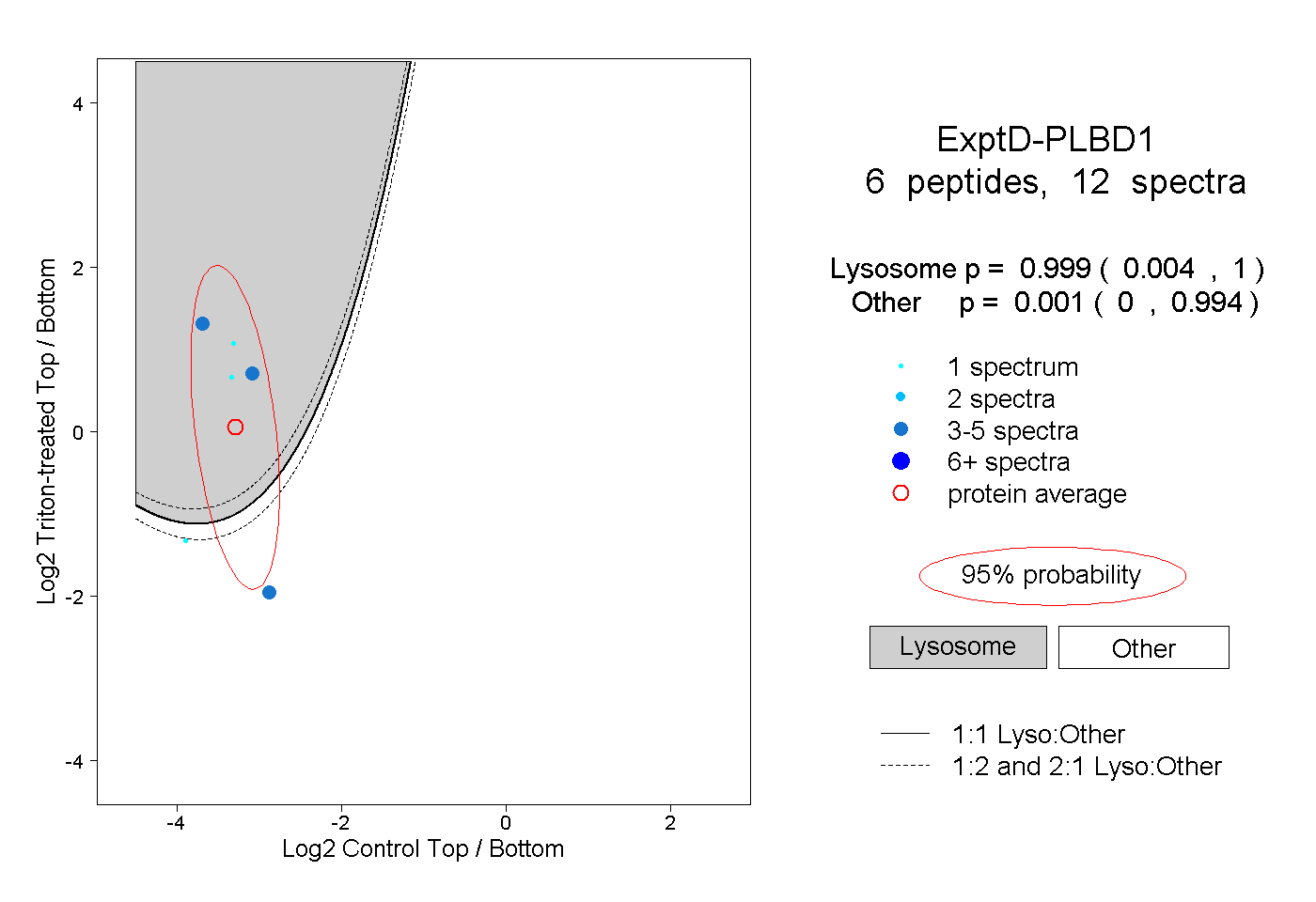
| 40 spectra, NPSIVK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 8 spectra, EDLNEASPSPGGCYDTK |
|
0.851 |
|
|
|
|
|
|
|
0.149 |
| 15 spectra, HTGYVVSQLDGMYLGAQK |
|
0.953 |
|
|
|
|
|
|
|
0.047 |
| 28 spectra, DDPFWR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 25 spectra, LVVPESLLAWQR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 50 spectra, GDPCSTICCR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 32 spectra, GYWASYNIPFHK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 118 spectra, DQGTVTDMASMK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 33 spectra, HWDFNIK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 9 spectra, MVLDK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 12 spectra, VQDFMEK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 65 spectra, VDPYSK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 37 spectra, LGLDYSYDLAPR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, AYAISGPTVQNGLPPFNWNR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 18 spectra, QELWTR |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 65 spectra, VANMMAQGGK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, YTASNR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, GALYVVEQIPTYVEYSDQTNILR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 16 spectra, TVYNWSGYPLLVHK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 33 spectra, VADIFLASQYK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |