peptides
spectra
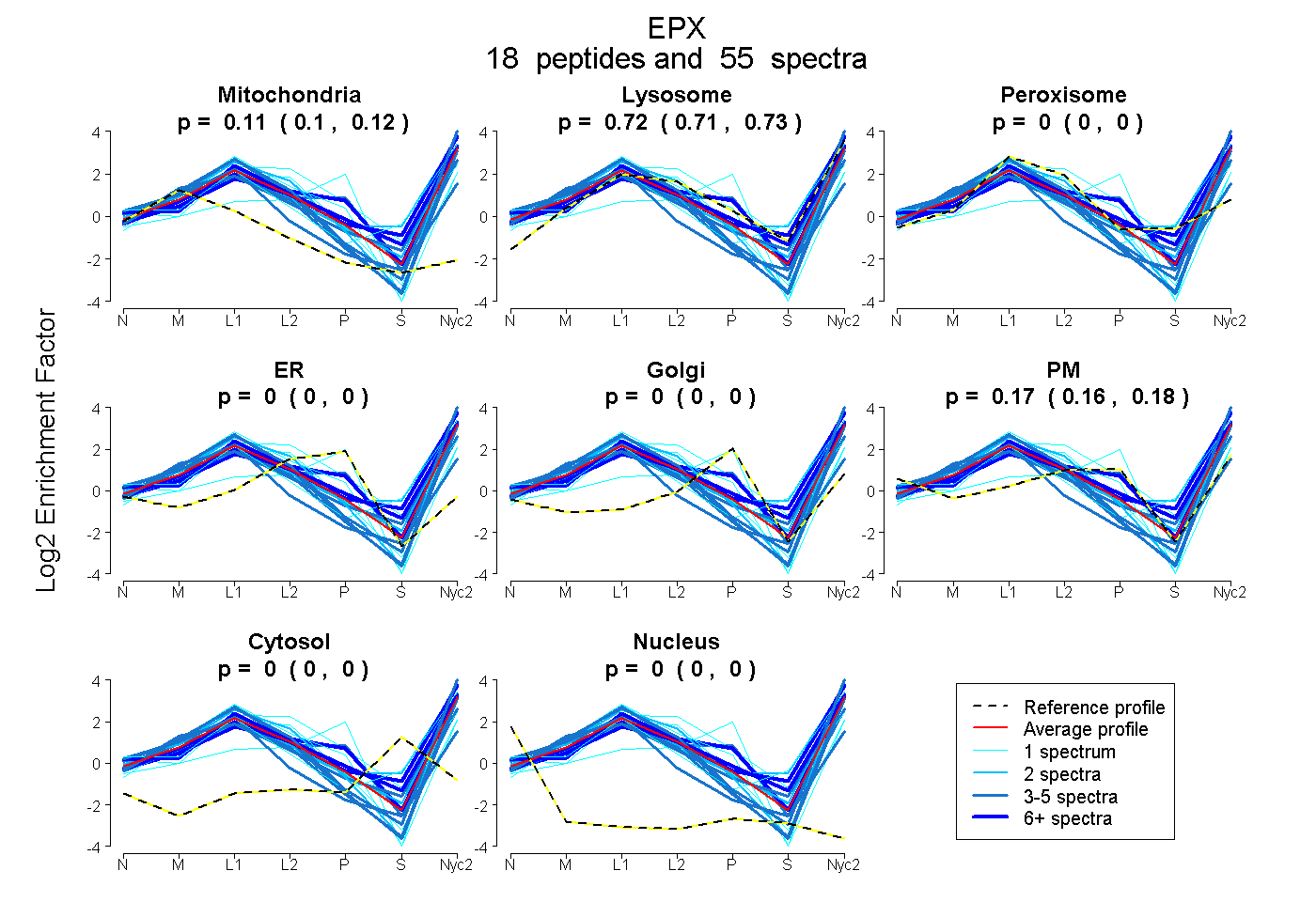
0.105 | 0.119
0.706 | 0.725
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.157 | 0.182
0.000 | 0.000
0.000 | 0.000
peptides
spectra
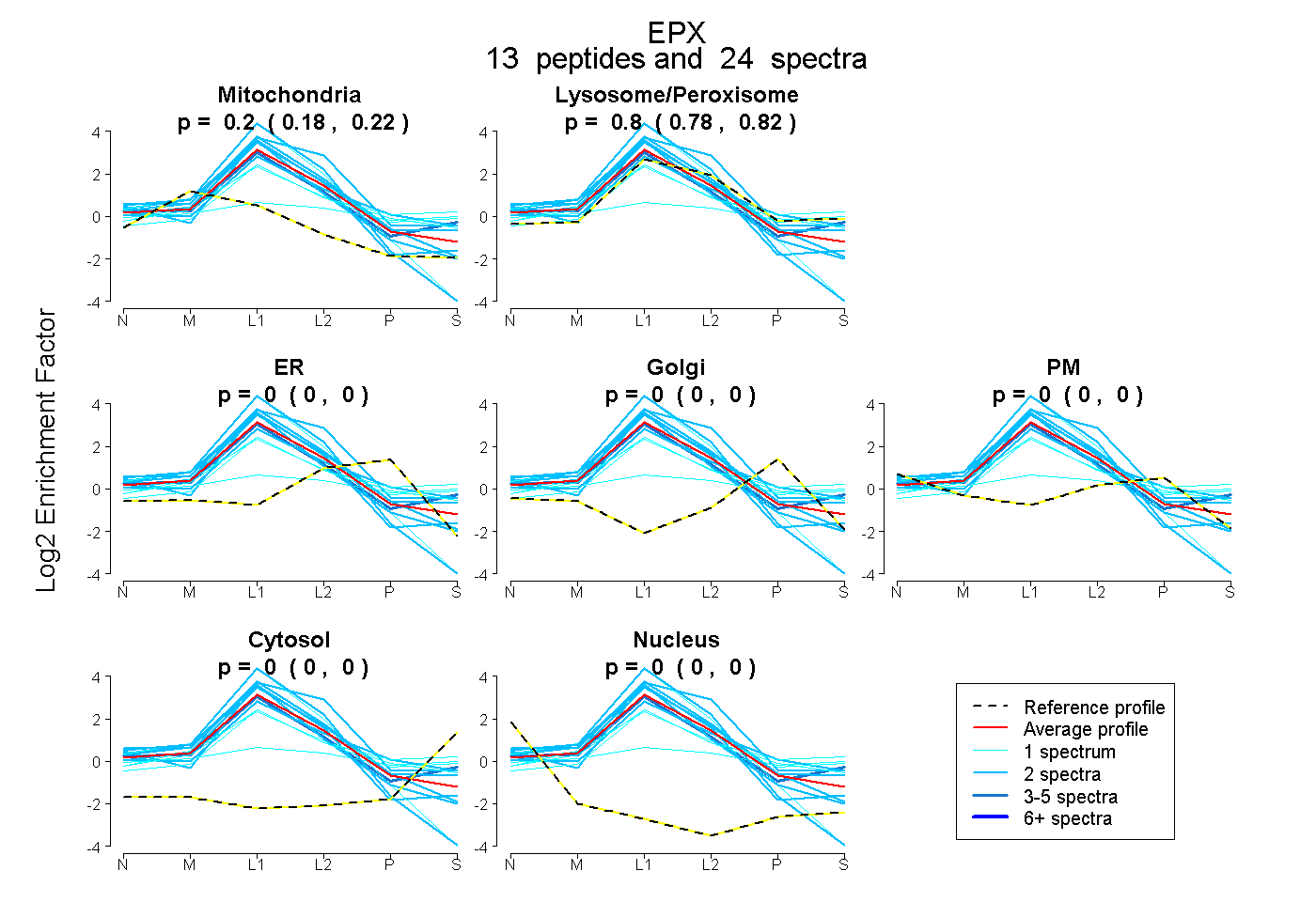
0.180 | 0.219
0.776 | 0.816
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
55 spectra |
 |
0.112 0.105 | 0.119 |
0.716 0.706 | 0.725 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.171 0.157 | 0.182 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
24 spectra |
 |
0.202 0.180 | 0.219 |
0.798 0.776 | 0.816 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, NGFLLPLVR | 0.310 | 0.690 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, IPCFLAGDSR | 0.290 | 0.710 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DCIPFFR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, NLAQLSR | 0.016 | 0.864 | 0.000 | 0.033 | 0.000 | 0.087 | 0.000 | |||
| 2 spectra, LFQQVR | 0.084 | 0.916 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DHGLPGYNAWR | 0.081 | 0.470 | 0.000 | 0.000 | 0.273 | 0.176 | 0.000 | |||
| 2 spectra, VANVFTLAFR | 0.321 | 0.679 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, ALLPFDNLHEDPCLLTNR | 0.181 | 0.819 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TIGLMR | 0.200 | 0.783 | 0.000 | 0.000 | 0.000 | 0.017 | 0.000 | |||
| 2 spectra, SAPACPQNR | 0.321 | 0.679 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FCGLSQPR | 0.052 | 0.882 | 0.000 | 0.000 | 0.066 | 0.000 | 0.000 | |||
| 1 spectrum, RPWLGASNQALAR | 0.221 | 0.746 | 0.000 | 0.033 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AVSNQIVR | 0.164 | 0.836 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
89 spectra |
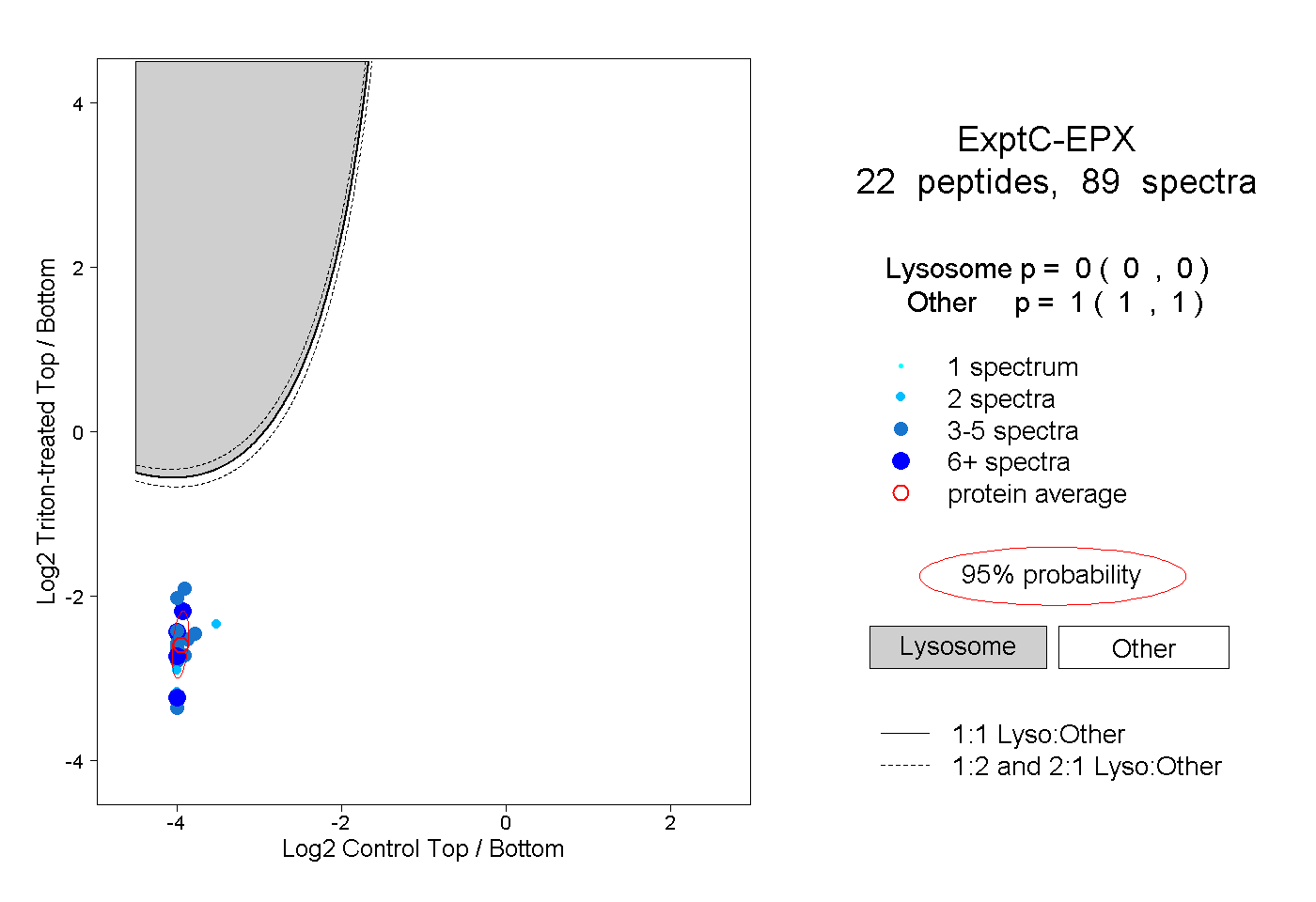 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
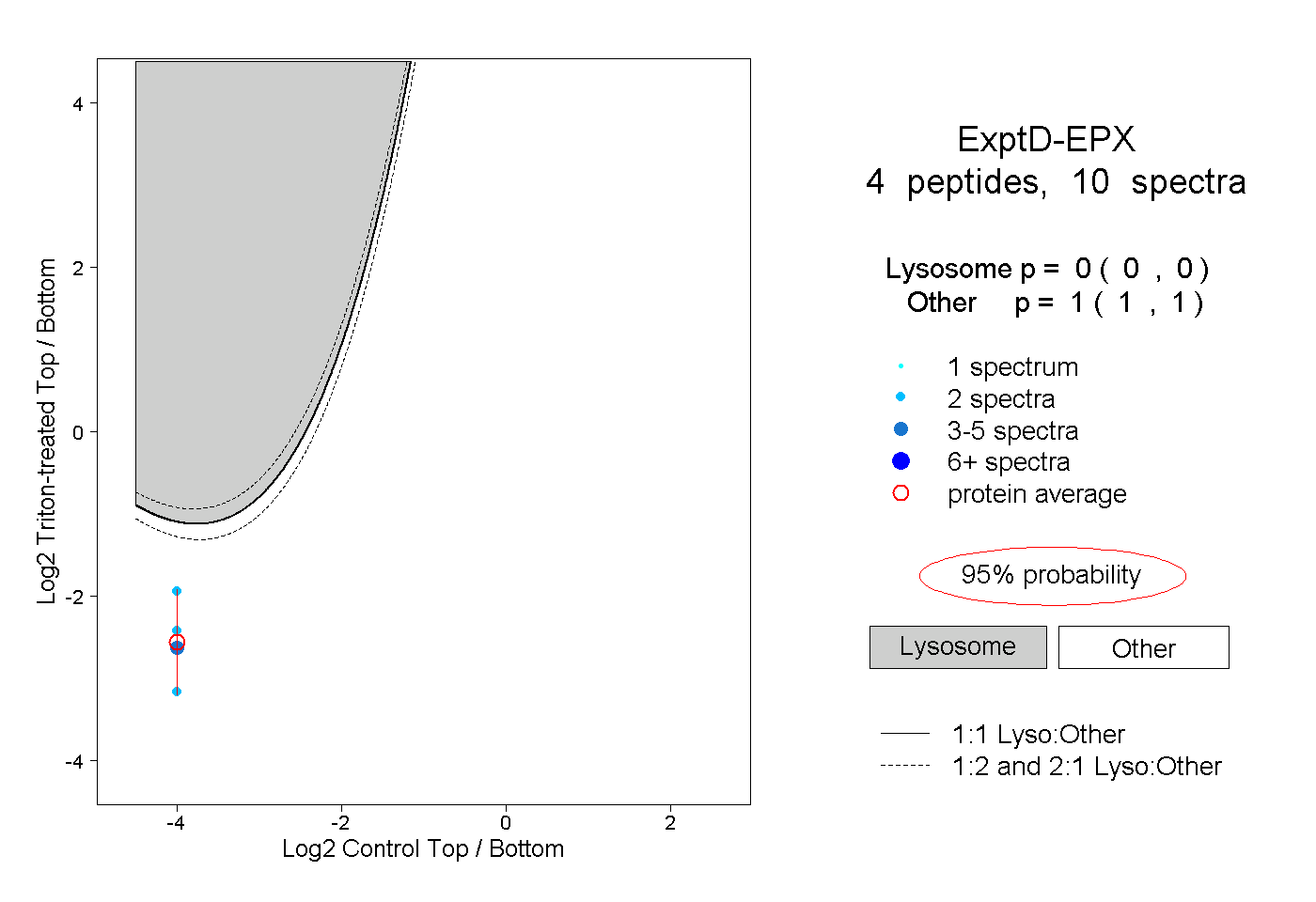 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |