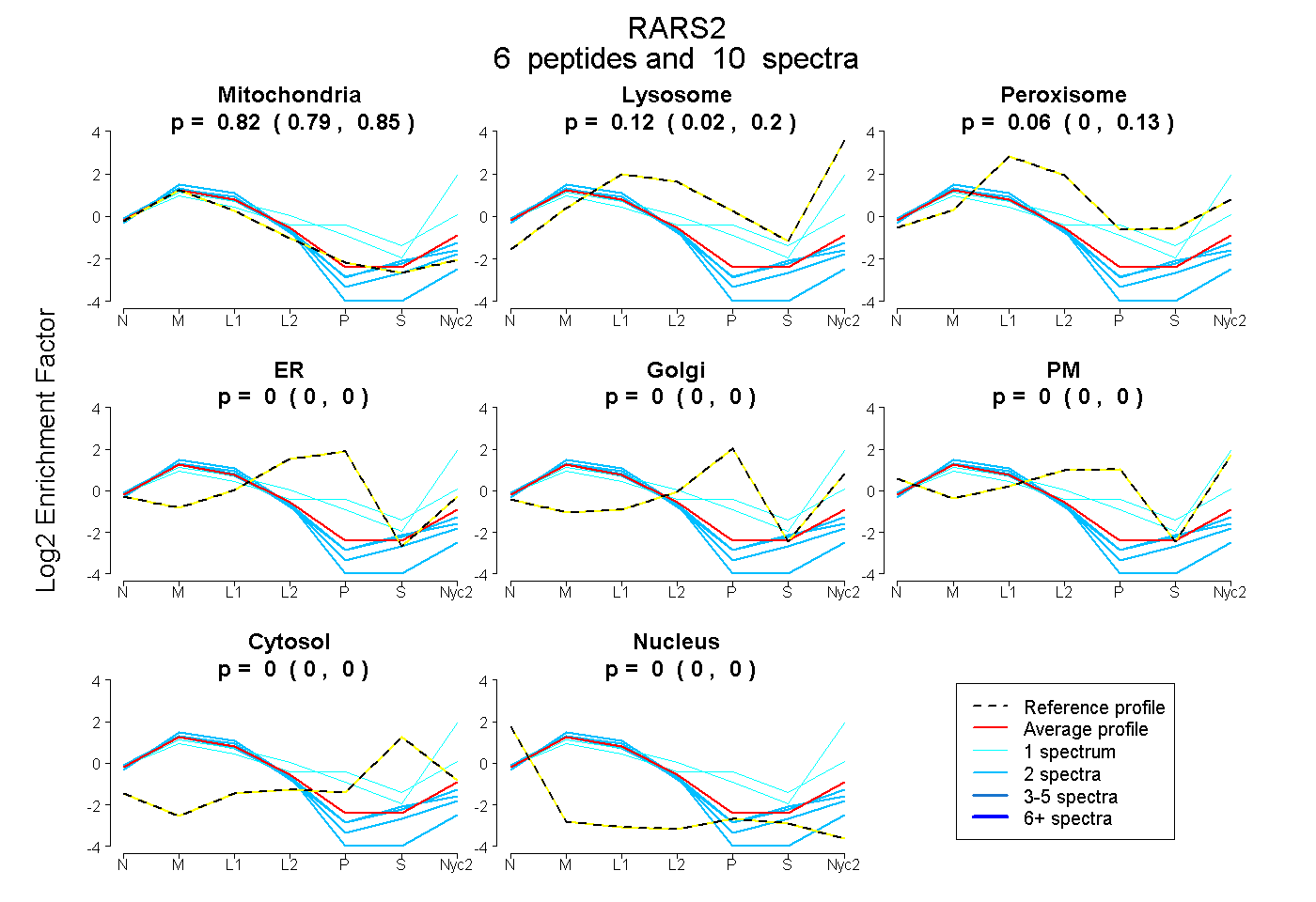
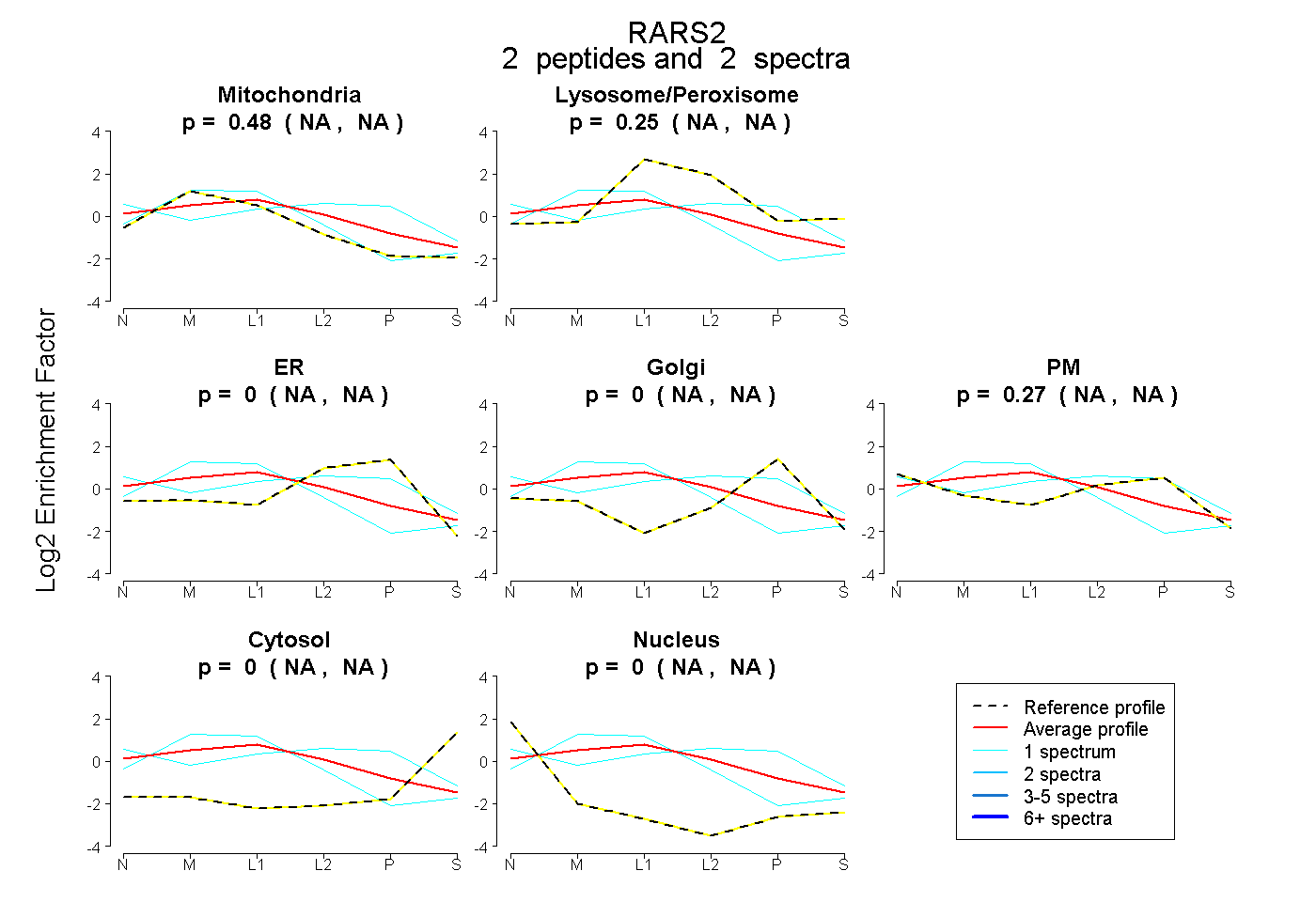
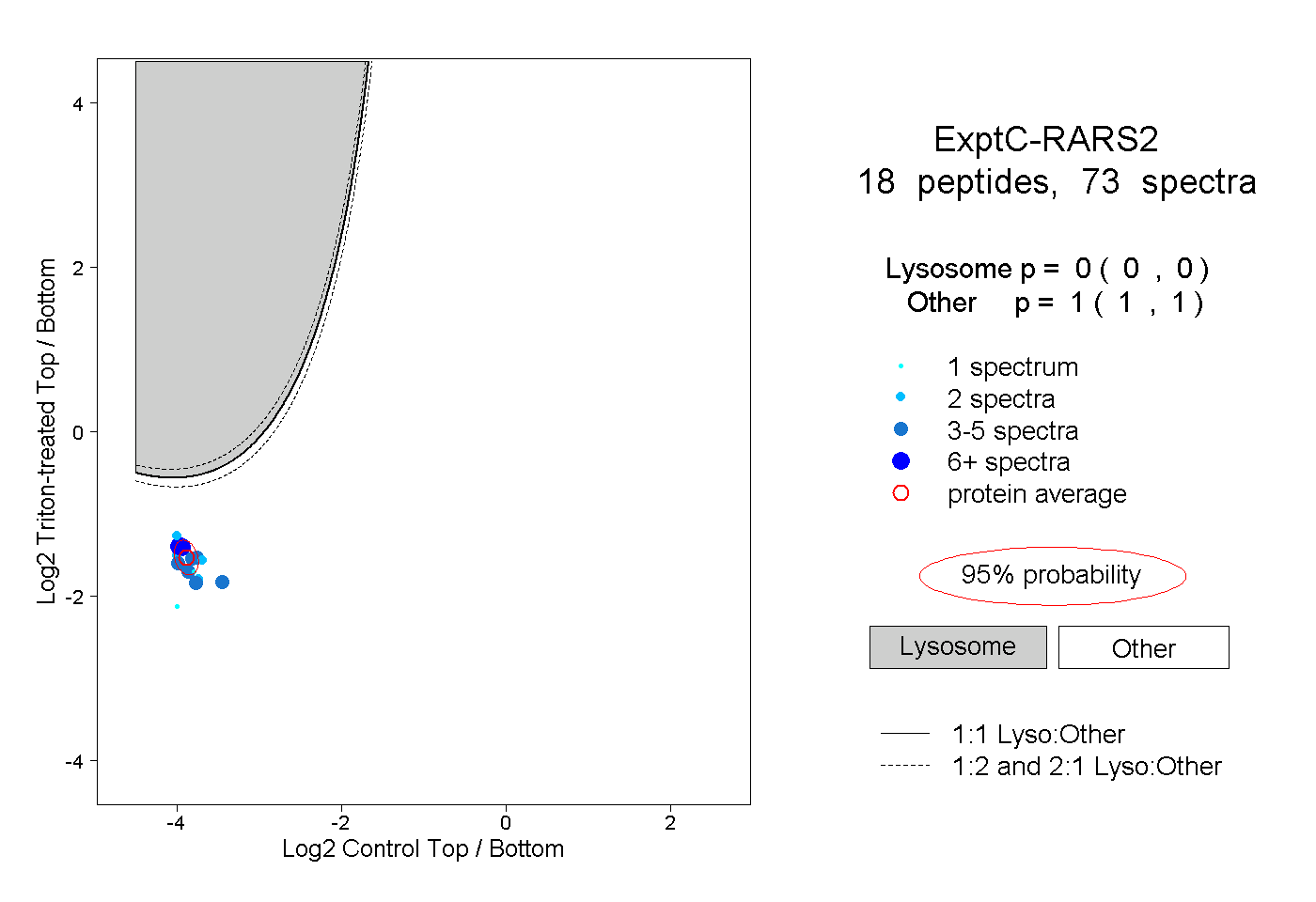
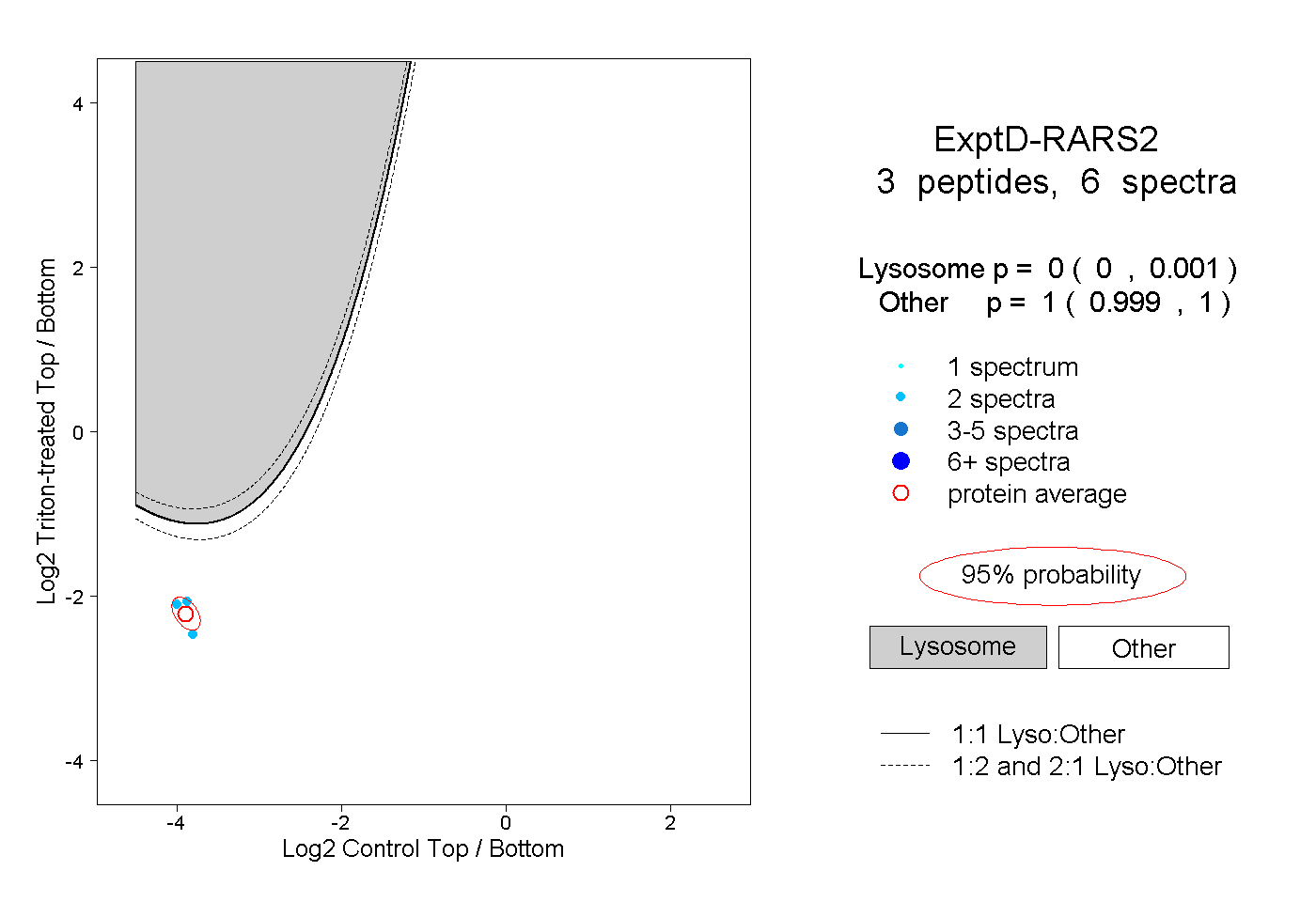
| 5 spectra, SISAVPVSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LELGDTQALALWQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DSPPEVAGAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, AVLQQVTEDGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GEVTFLEDVLNEVQSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SVLANGMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LGIYFDEYSGESFYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VGLAALIIQDFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DLAAAIHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, SQLDTQDQAQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, EALGHQVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GLLLSDYQFSWDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LAHEFFHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IMGHEWAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LLGITPVCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, SDGTSLYATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VLALPPESLIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SIACQLSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |