peptides
spectra
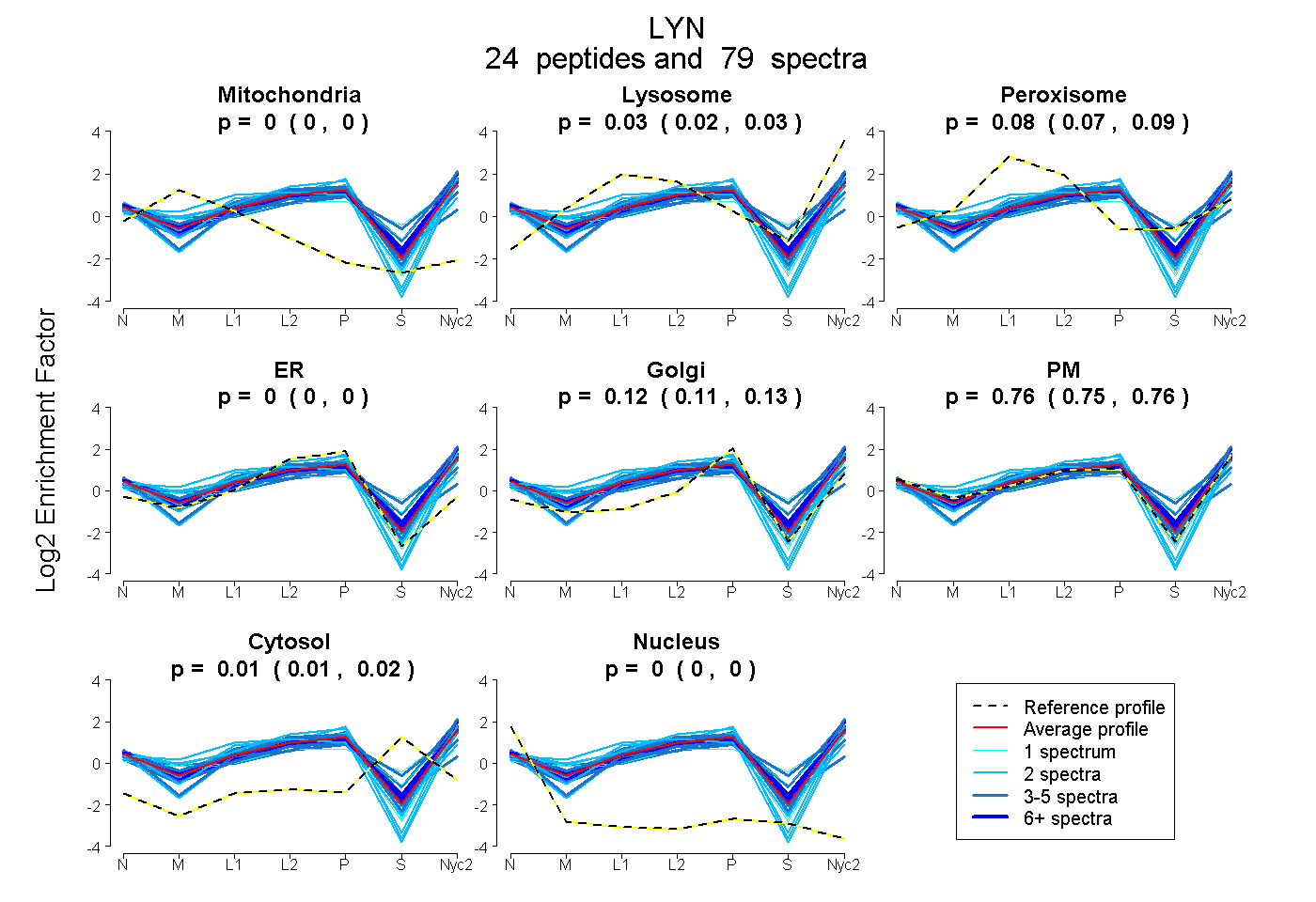
0.000 | 0.000
0.023 | 0.034
0.074 | 0.088
0.000 | 0.005
0.111 | 0.127
0.748 | 0.763
0.009 | 0.016
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
79 spectra |
 |
0.000 0.000 | 0.000 |
0.029 0.023 | 0.034 |
0.082 0.074 | 0.088 |
0.000 0.000 | 0.005 |
0.120 0.111 | 0.127 |
0.756 0.748 | 0.763 |
0.013 0.009 | 0.016 |
0.000 0.000 | 0.000 |
| 5 spectra, AANVLVSESLMCK | 0.000 | 0.000 | 0.074 | 0.423 | 0.072 | 0.314 | 0.117 | 0.000 | ||
| 2 spectra, DPTSNK | 0.000 | 0.000 | 0.000 | 0.187 | 0.193 | 0.620 | 0.000 | 0.000 | ||
| 4 spectra, MENCPDELYDIMK | 0.000 | 0.131 | 0.078 | 0.112 | 0.082 | 0.597 | 0.000 | 0.000 | ||
| 2 spectra, TIYVR | 0.000 | 0.000 | 0.000 | 0.165 | 0.000 | 0.835 | 0.000 | 0.000 | ||
| 4 spectra, DNLNDDGVDMK | 0.000 | 0.141 | 0.000 | 0.157 | 0.000 | 0.629 | 0.073 | 0.000 | ||
| 5 spectra, TNADVMTALSQGYR | 0.000 | 0.085 | 0.000 | 0.000 | 0.000 | 0.915 | 0.000 | 0.000 | ||
| 5 spectra, DAWEIPR | 0.000 | 0.183 | 0.000 | 0.000 | 0.027 | 0.680 | 0.110 | 0.000 | ||
| 1 spectrum, EGFIPSNYVAK | 0.000 | 0.018 | 0.000 | 0.000 | 0.000 | 0.982 | 0.000 | 0.000 | ||
| 2 spectra, QLLAPGNSAGAFLIR | 0.015 | 0.000 | 0.000 | 0.069 | 0.000 | 0.916 | 0.000 | 0.000 | ||
| 4 spectra, DYDPMHGDVIK | 0.014 | 0.080 | 0.005 | 0.000 | 0.022 | 0.758 | 0.120 | 0.000 | ||
| 3 spectra, VLEEHGEWWK | 0.000 | 0.103 | 0.014 | 0.092 | 0.020 | 0.770 | 0.000 | 0.000 | ||
| 1 spectrum, LGAGQFGEVWMGYYNNSTK | 0.000 | 0.186 | 0.049 | 0.000 | 0.000 | 0.527 | 0.239 | 0.000 | ||
| 2 spectra, SLDNGGYYISPR | 0.000 | 0.007 | 0.000 | 0.000 | 0.000 | 0.993 | 0.000 | 0.000 | ||
| 4 spectra, QQRPVPESQLLPGQR | 0.000 | 0.000 | 0.000 | 0.119 | 0.117 | 0.649 | 0.115 | 0.000 | ||
| 1 spectrum, LYAVVTK | 0.000 | 0.084 | 0.016 | 0.000 | 0.000 | 0.748 | 0.152 | 0.000 | ||
| 2 spectra, QSDGLCR | 0.029 | 0.000 | 0.151 | 0.204 | 0.112 | 0.503 | 0.000 | 0.000 | ||
| 3 spectra, GSFSLSVR | 0.000 | 0.021 | 0.081 | 0.000 | 0.012 | 0.851 | 0.035 | 0.000 | ||
| 1 spectrum, ITFPCISDMIK | 0.000 | 0.055 | 0.000 | 0.001 | 0.000 | 0.944 | 0.000 | 0.000 | ||
| 6 spectra, GSLLDFLK | 0.000 | 0.068 | 0.000 | 0.000 | 0.000 | 0.836 | 0.096 | 0.000 | ||
| 3 spectra, SDEGSK | 0.000 | 0.100 | 0.024 | 0.000 | 0.000 | 0.660 | 0.216 | 0.000 | ||
| 4 spectra, EEPIYIITEFMAK | 0.000 | 0.045 | 0.064 | 0.001 | 0.060 | 0.800 | 0.030 | 0.000 | ||
| 6 spectra, LADFGLAR | 0.000 | 0.098 | 0.000 | 0.000 | 0.000 | 0.892 | 0.011 | 0.000 | ||
| 7 spectra, VIEDNEYTAR | 0.000 | 0.044 | 0.068 | 0.000 | 0.020 | 0.820 | 0.047 | 0.000 | ||
| 2 spectra, VNTLETEEWFFK | 0.009 | 0.103 | 0.102 | 0.003 | 0.000 | 0.783 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
15 spectra |
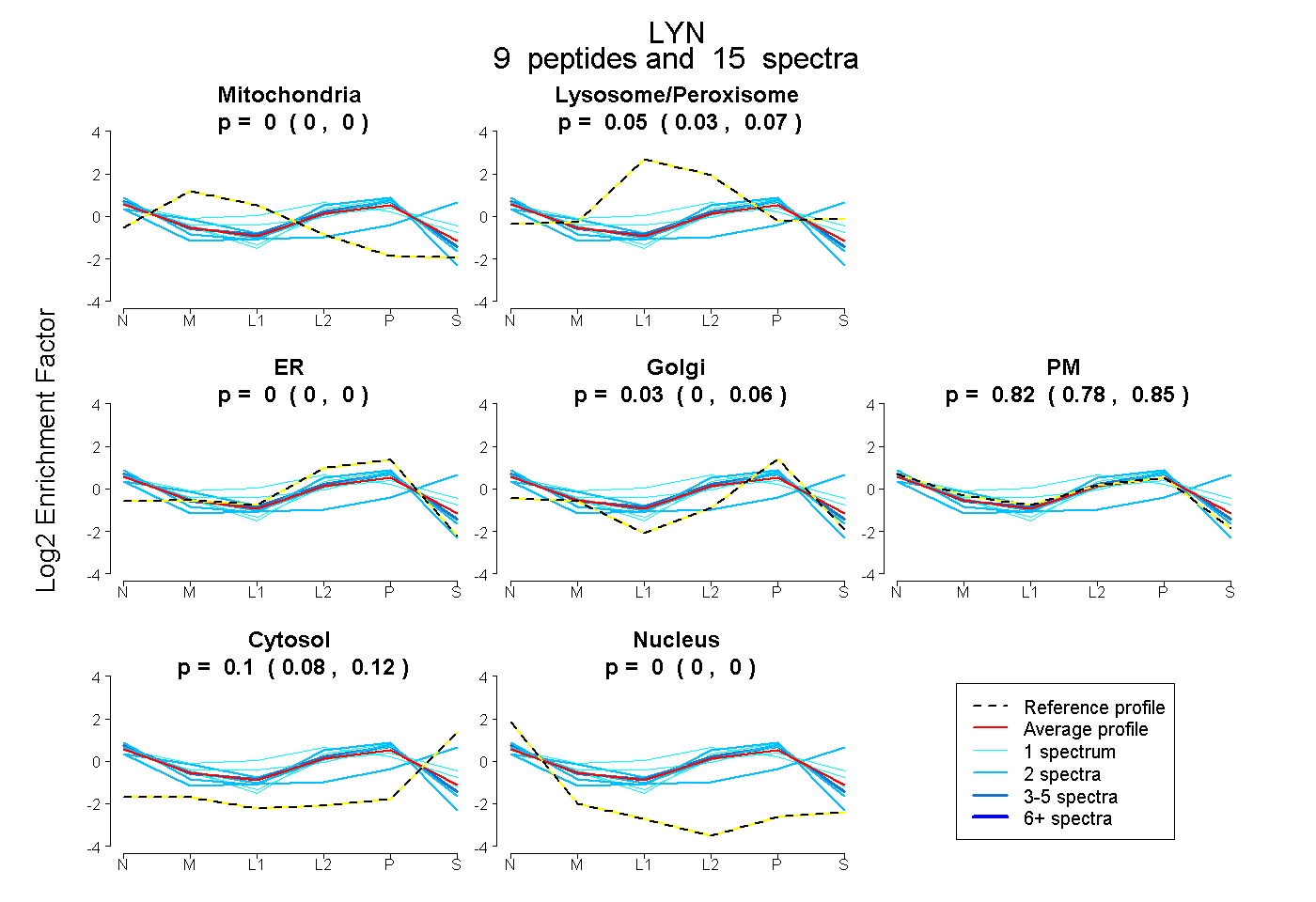 |
0.000 0.000 | 0.000 |
0.048 0.027 | 0.066 |
0.000 0.000 | 0.000 |
0.033 0.000 | 0.062 |
0.819 0.776 | 0.853 |
0.100 0.081 | 0.116 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
137 spectra |
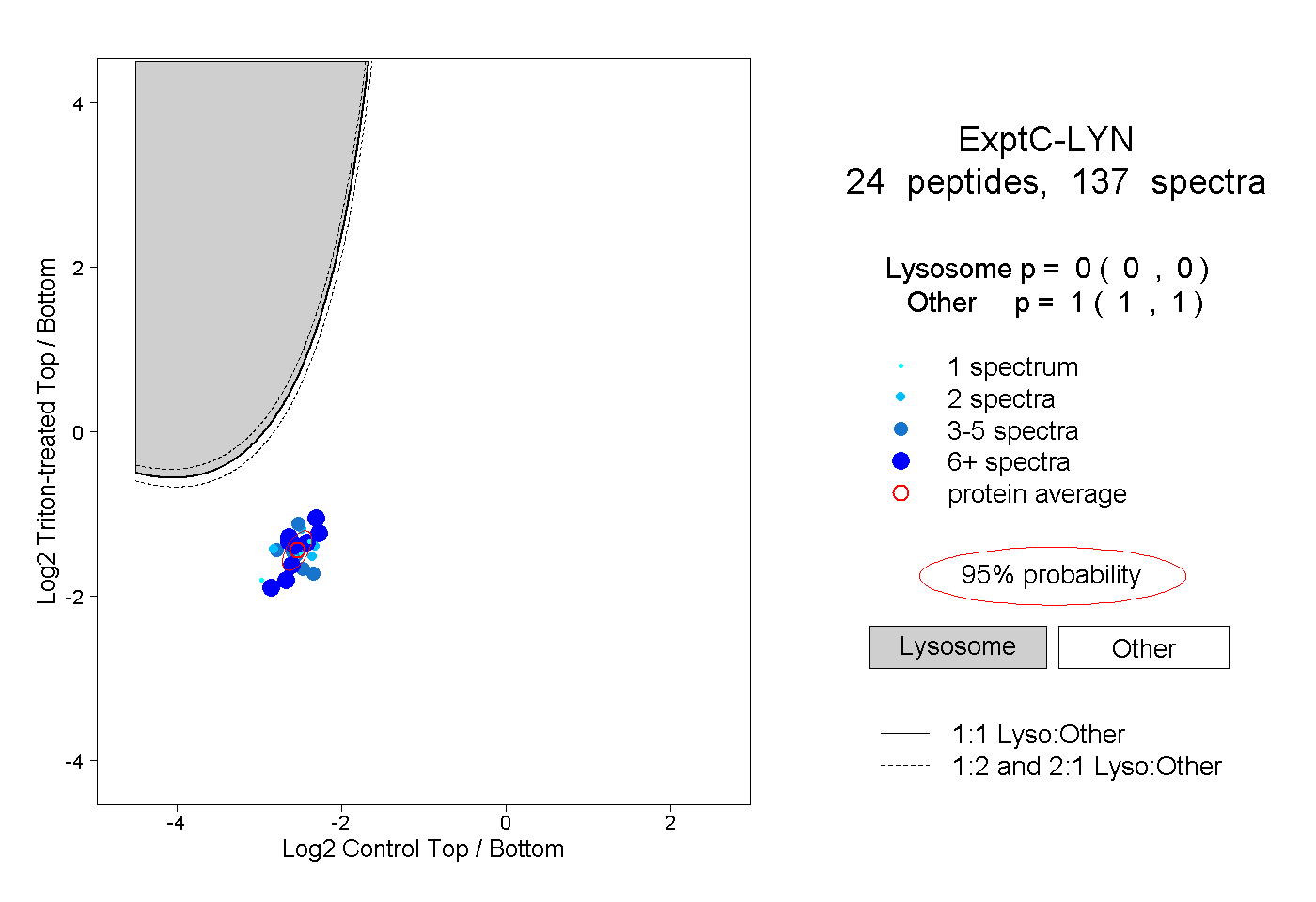 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
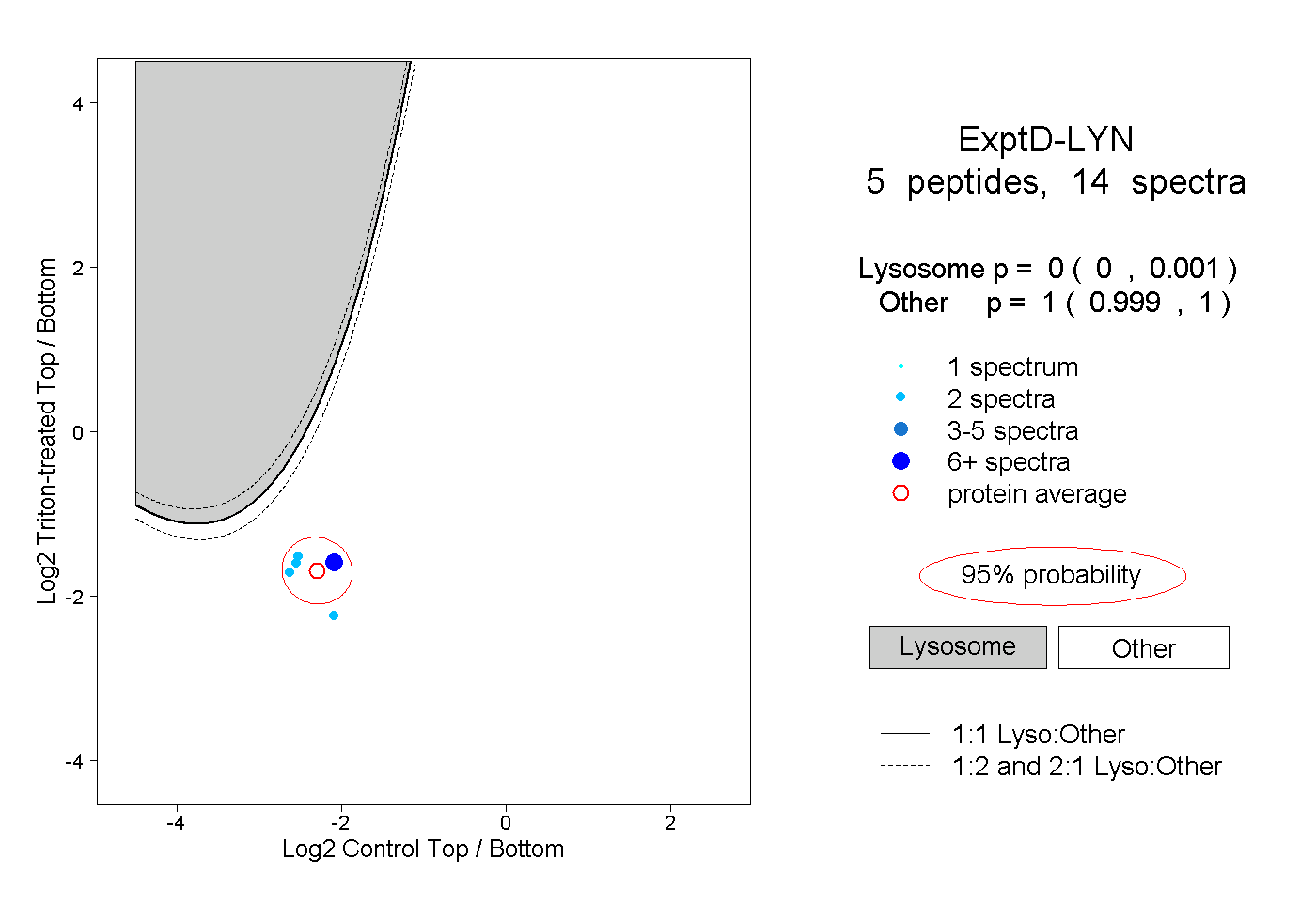 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |