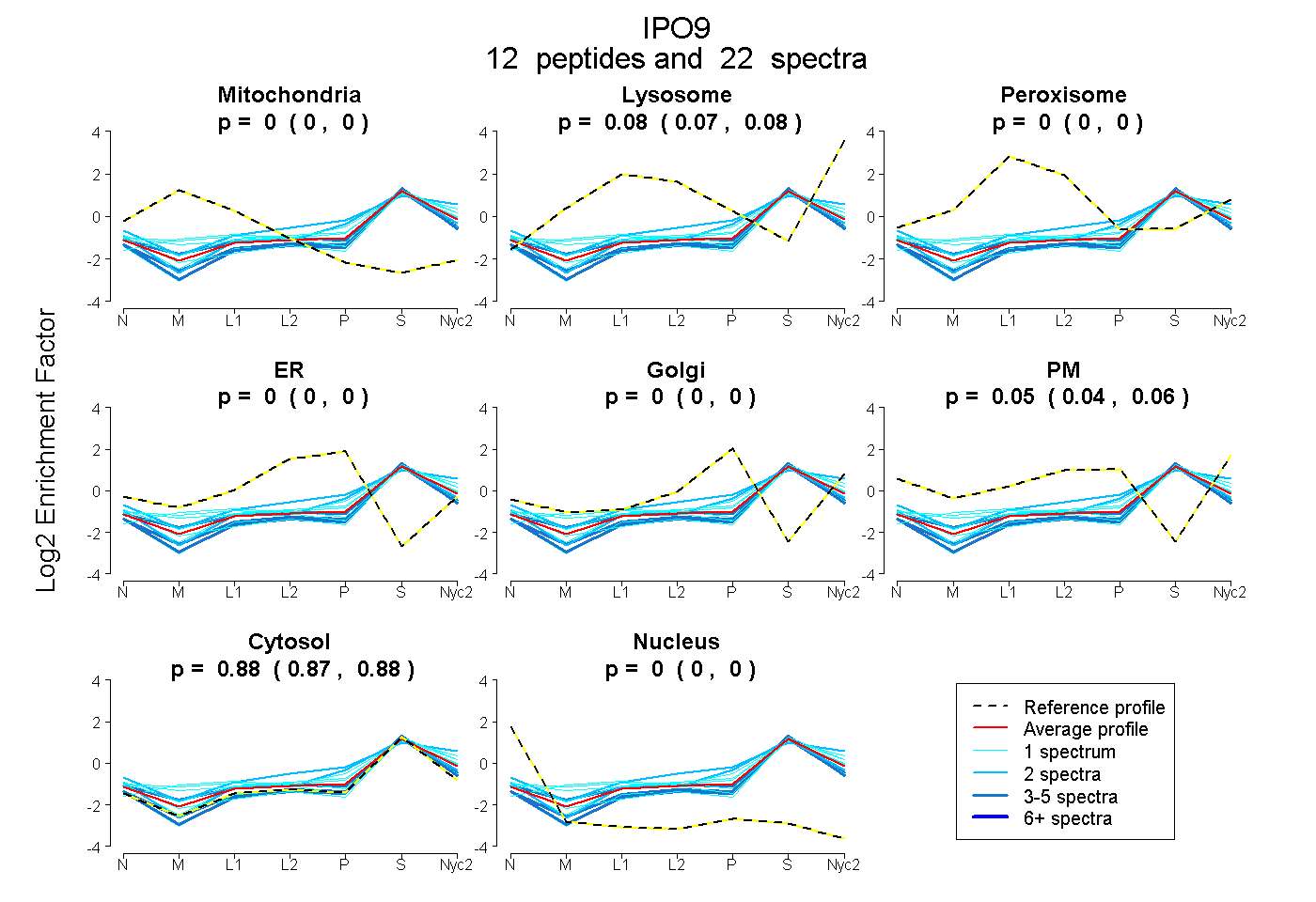
peptides
spectra
0.000 | 0.000
0.065 | 0.084
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.038 | 0.057
0.869 | 0.881
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.075 0.065 | 0.084 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.049 0.038 | 0.057 |
0.876 0.869 | 0.881 |
0.000 0.000 | 0.000 |
| 2 spectra, FRPPETTER | 0.000 | 0.000 | 0.000 | 0.000 | 0.167 | 0.000 | 0.833 | 0.000 | ||
| 1 spectrum, LIPTLVSIMQAPADK | 0.000 | 0.234 | 0.000 | 0.000 | 0.032 | 0.000 | 0.734 | 0.000 | ||
| 2 spectra, HLQEAEQTK | 0.000 | 0.129 | 0.000 | 0.000 | 0.025 | 0.162 | 0.684 | 0.000 | ||
| 1 spectrum, VLTEFTR | 0.063 | 0.146 | 0.000 | 0.000 | 0.000 | 0.000 | 0.791 | 0.000 | ||
| 1 spectrum, TSEFTAAFVGR | 0.093 | 0.146 | 0.000 | 0.000 | 0.000 | 0.000 | 0.761 | 0.000 | ||
| 1 spectrum, AVTALVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 4 spectra, AAAEEQIK | 0.000 | 0.021 | 0.000 | 0.000 | 0.000 | 0.000 | 0.979 | 0.000 | ||
| 1 spectrum, ELSQIEACQGPMQMR | 0.000 | 0.029 | 0.000 | 0.000 | 0.004 | 0.081 | 0.886 | 0.000 | ||
| 4 spectra, ALWAASR | 0.028 | 0.029 | 0.039 | 0.000 | 0.000 | 0.040 | 0.864 | 0.000 | ||
| 3 spectra, ELGENLDQILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, WTNIPLLVK | 0.000 | 0.069 | 0.000 | 0.000 | 0.000 | 0.000 | 0.919 | 0.013 | ||
| 1 spectrum, QLASVILK | 0.000 | 0.105 | 0.000 | 0.000 | 0.000 | 0.097 | 0.799 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
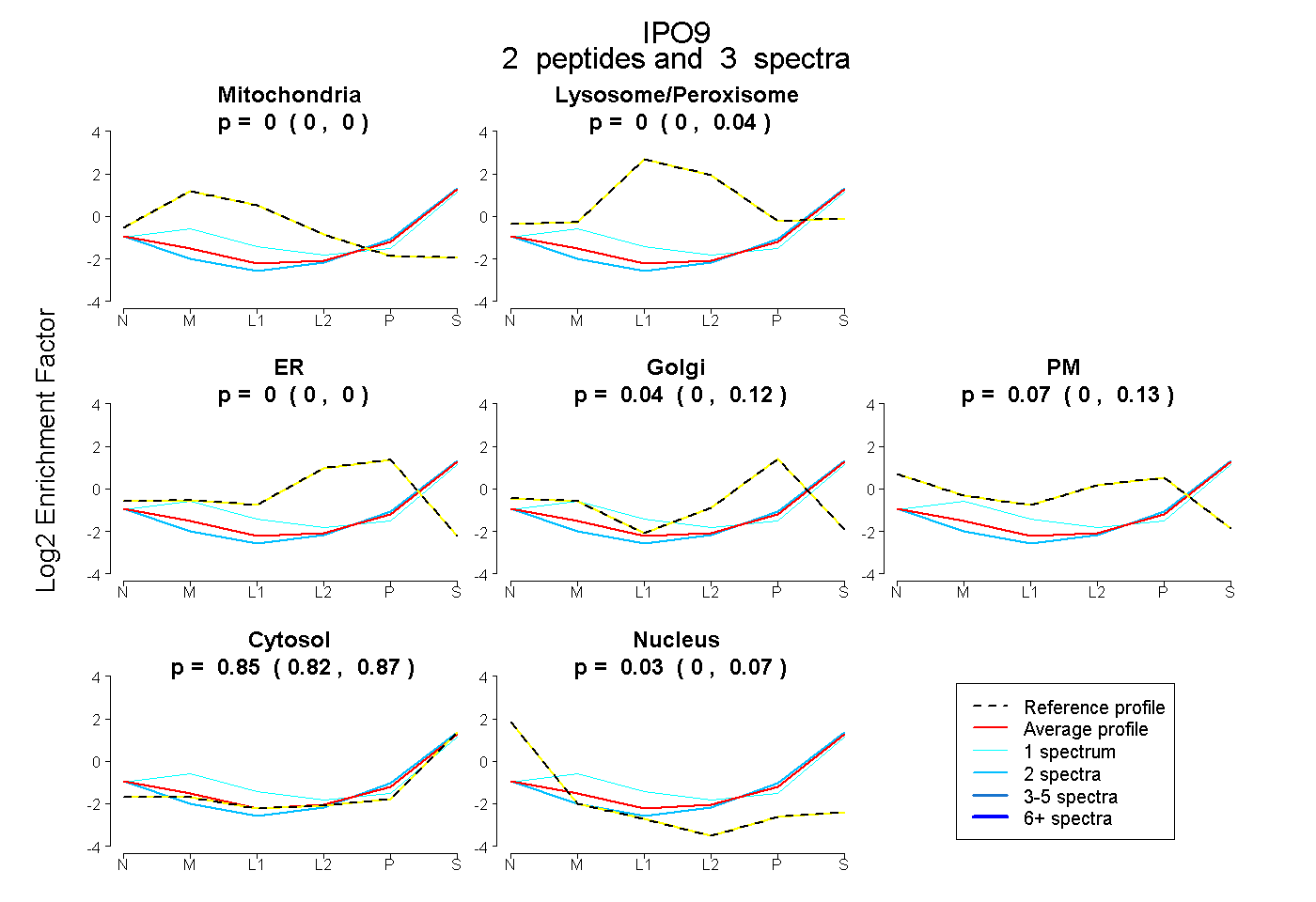 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.041 |
0.000 0.000 | 0.000 |
0.041 0.000 | 0.120 |
0.071 0.000 | 0.133 |
0.855 0.822 | 0.872 |
0.033 0.000 | 0.066 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
10 spectra |
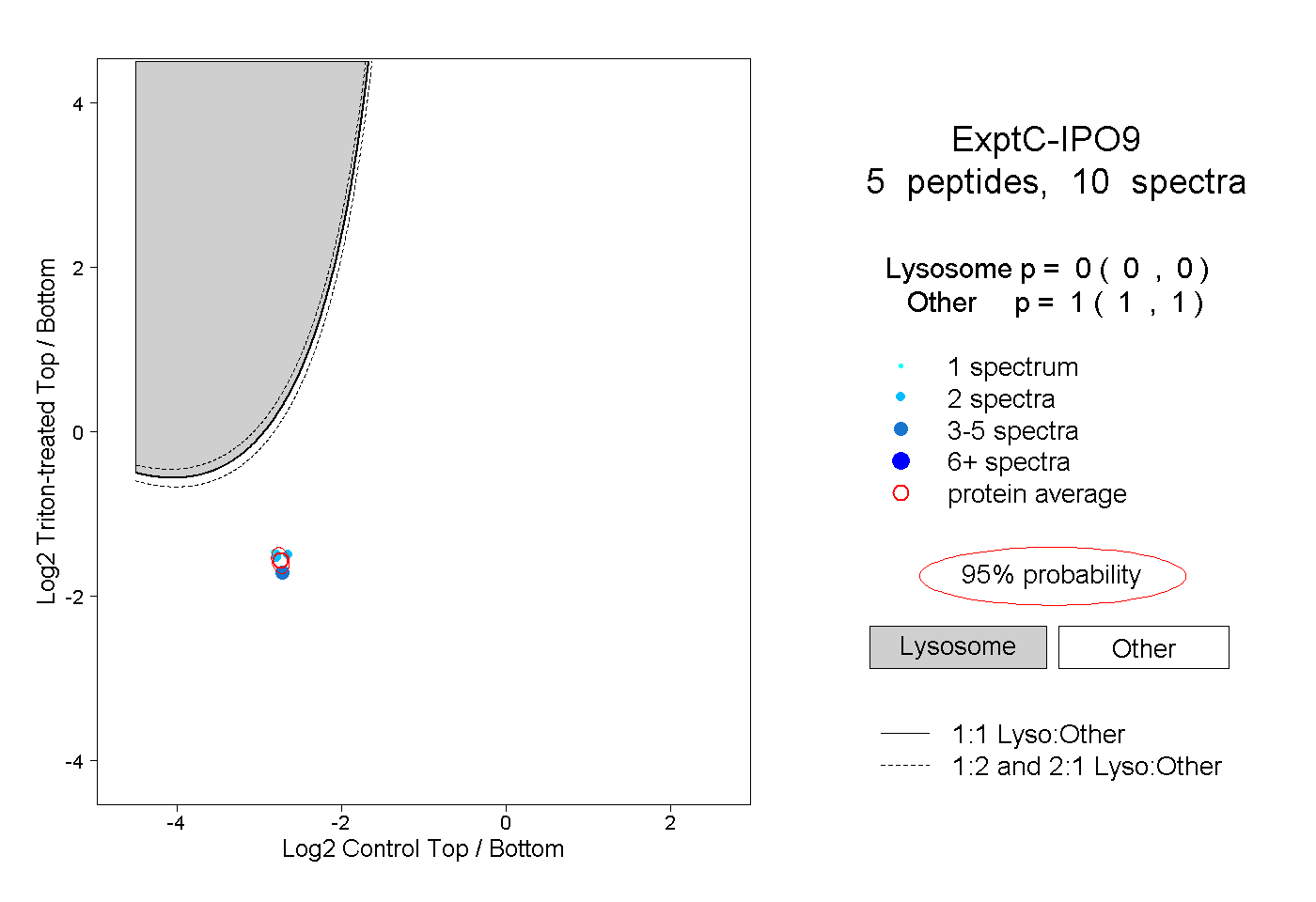 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |