peptides
spectra
0.000 | 0.000
0.011 | 0.014
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.986 | 0.989
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
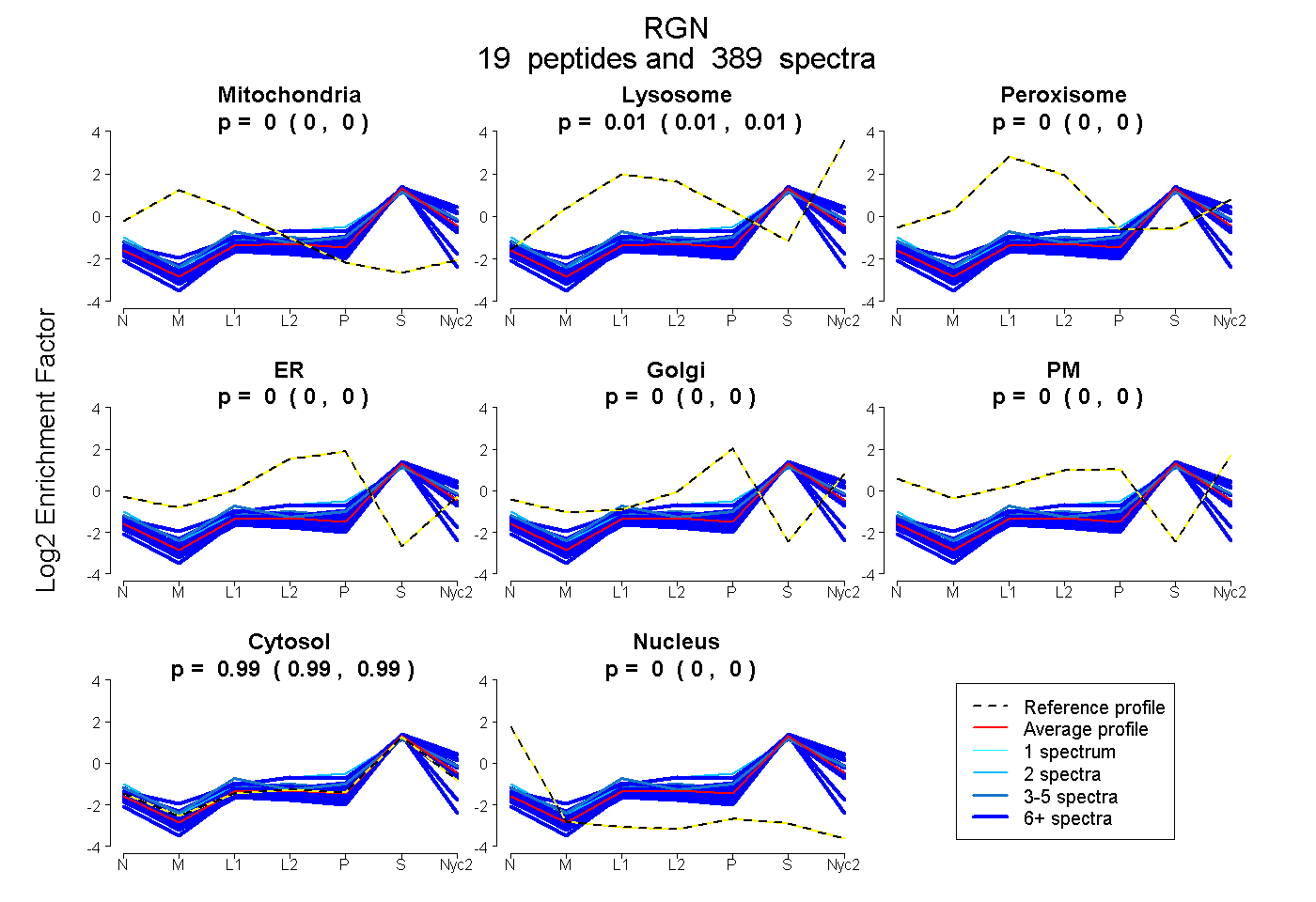
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
389 spectra |
 |
0.000 0.000 | 0.000 |
0.013 0.011 | 0.014 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.987 0.986 | 0.989 |
0.000 0.000 | 0.000 |
||
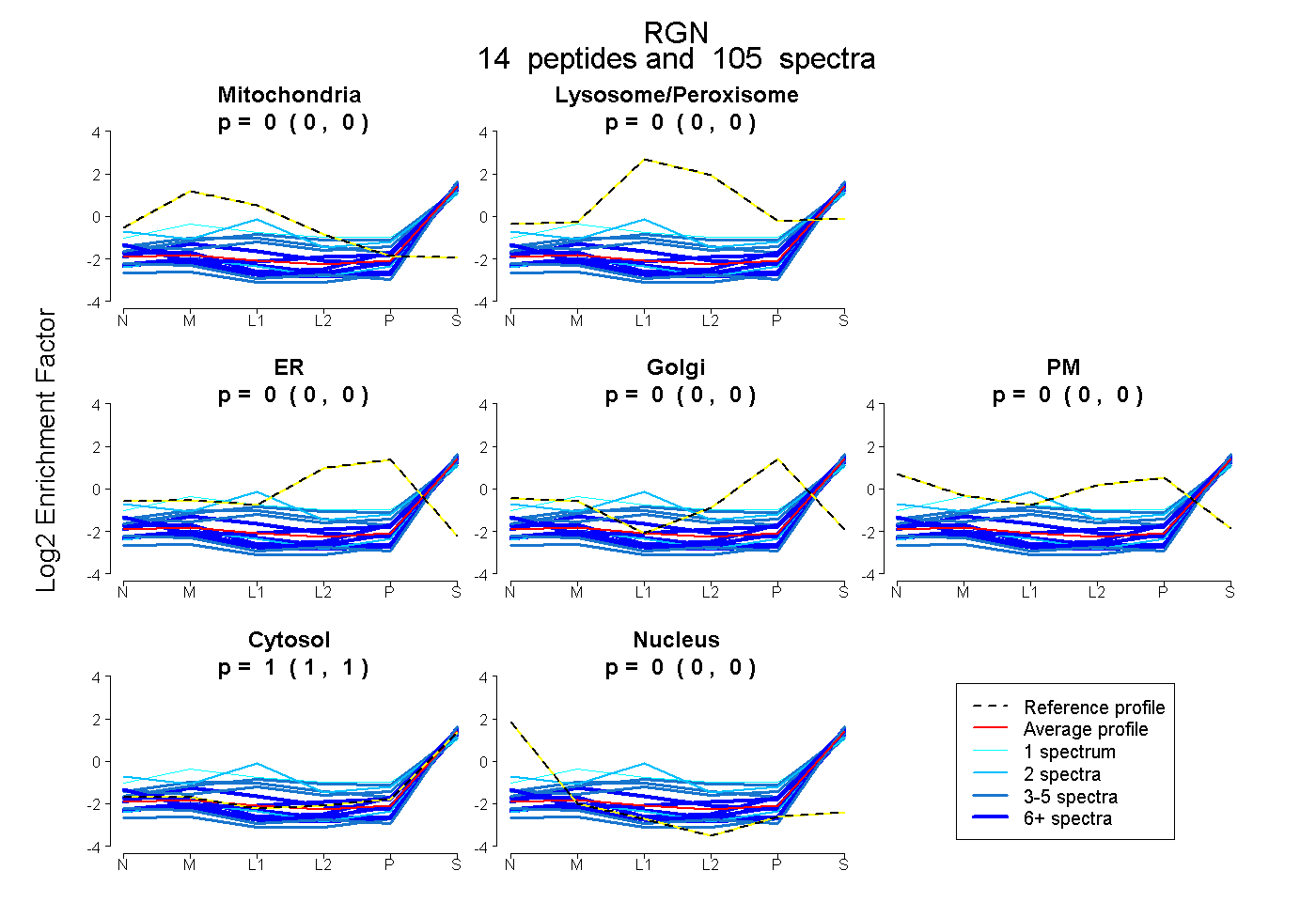
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
105 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 4 spectra, QSGGYVATIGTK | 0.000 | 0.169 | 0.000 | 0.000 | 0.000 | 0.831 | 0.000 | |||
| 7 spectra, IECVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, HQGSLYSLFPDHSVK | 0.000 | 0.259 | 0.000 | 0.000 | 0.000 | 0.741 | 0.000 | |||
| 26 spectra, VGVDAPVSSVALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 8 spectra, CGESPVWEEASK | 0.098 | 0.000 | 0.000 | 0.000 | 0.000 | 0.902 | 0.000 | |||
| 2 spectra, VDPAGR | 0.000 | 0.333 | 0.000 | 0.000 | 0.000 | 0.615 | 0.052 | |||
| 7 spectra, WDSISNR | 0.000 | 0.019 | 0.000 | 0.000 | 0.000 | 0.955 | 0.026 | |||
| 5 spectra, CLLFVDIPSK | 0.093 | 0.157 | 0.000 | 0.000 | 0.000 | 0.750 | 0.000 | |||
| 5 spectra, DYSEMYVTCAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, QPDAGNIFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, GIAPYSYAG | 0.100 | 0.252 | 0.000 | 0.048 | 0.000 | 0.600 | 0.000 | |||
| 3 spectra, YFDQVDISNGLDWSLDHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 17 spectra, DGMSAEGLLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.980 | 0.020 | |||
| 15 spectra, LWVACYNGGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
481 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
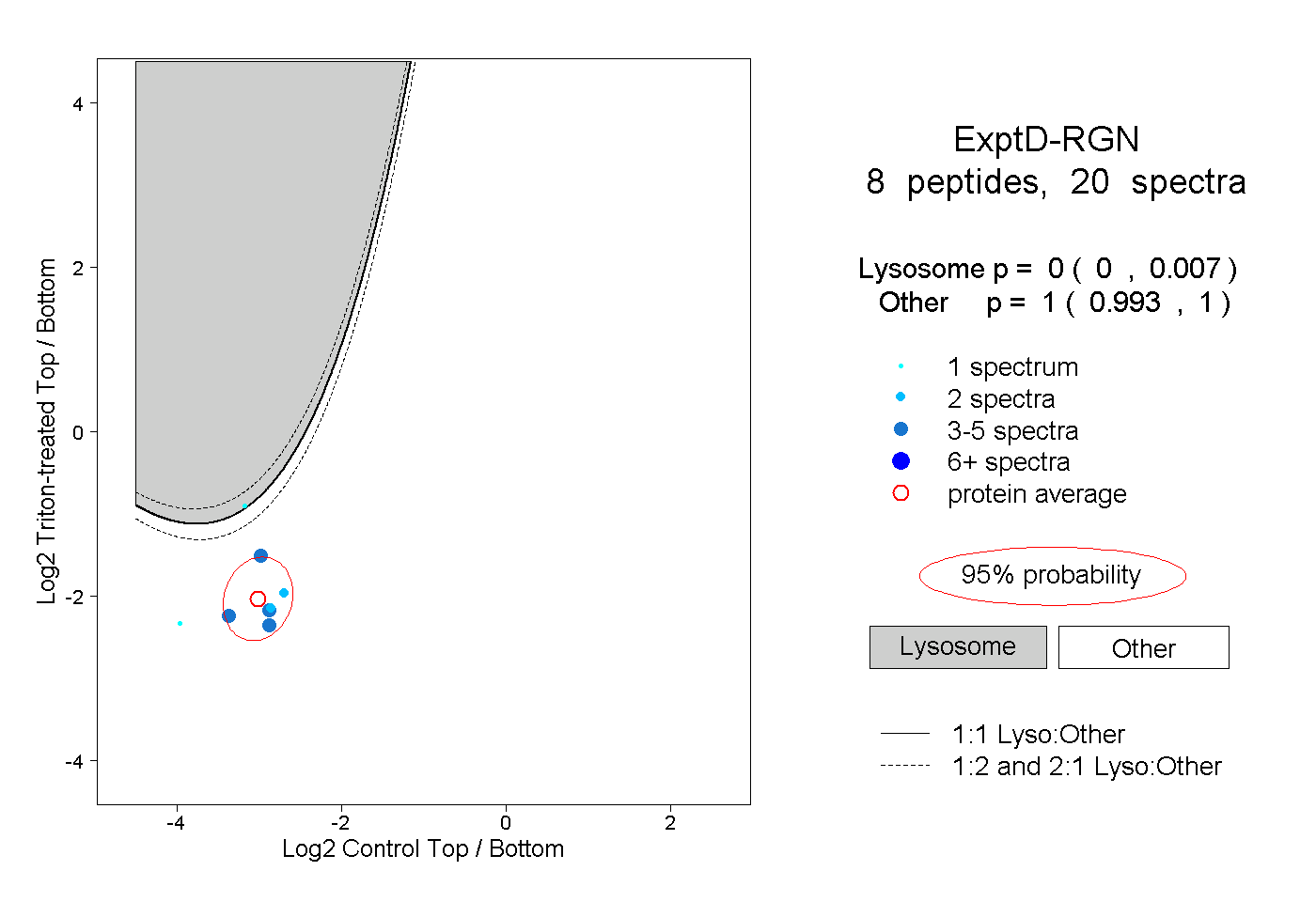 |
0.000 0.000 | 0.007 |
1.000 0.993 | 1.000 |