peptides
spectra
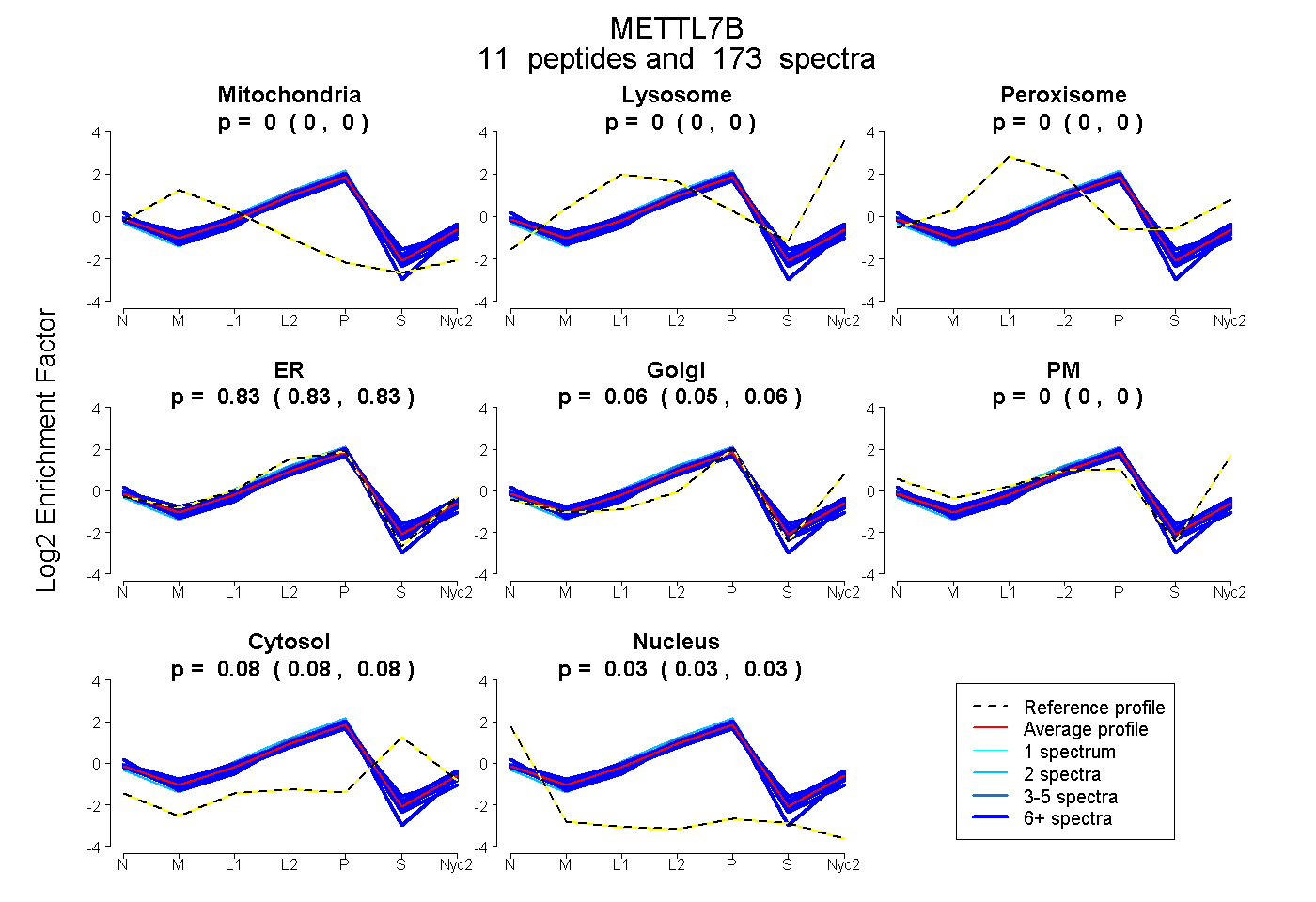
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.828 | 0.834
0.051 | 0.059
0.000 | 0.000
0.079 | 0.084
0.030 | 0.033
peptides
spectra
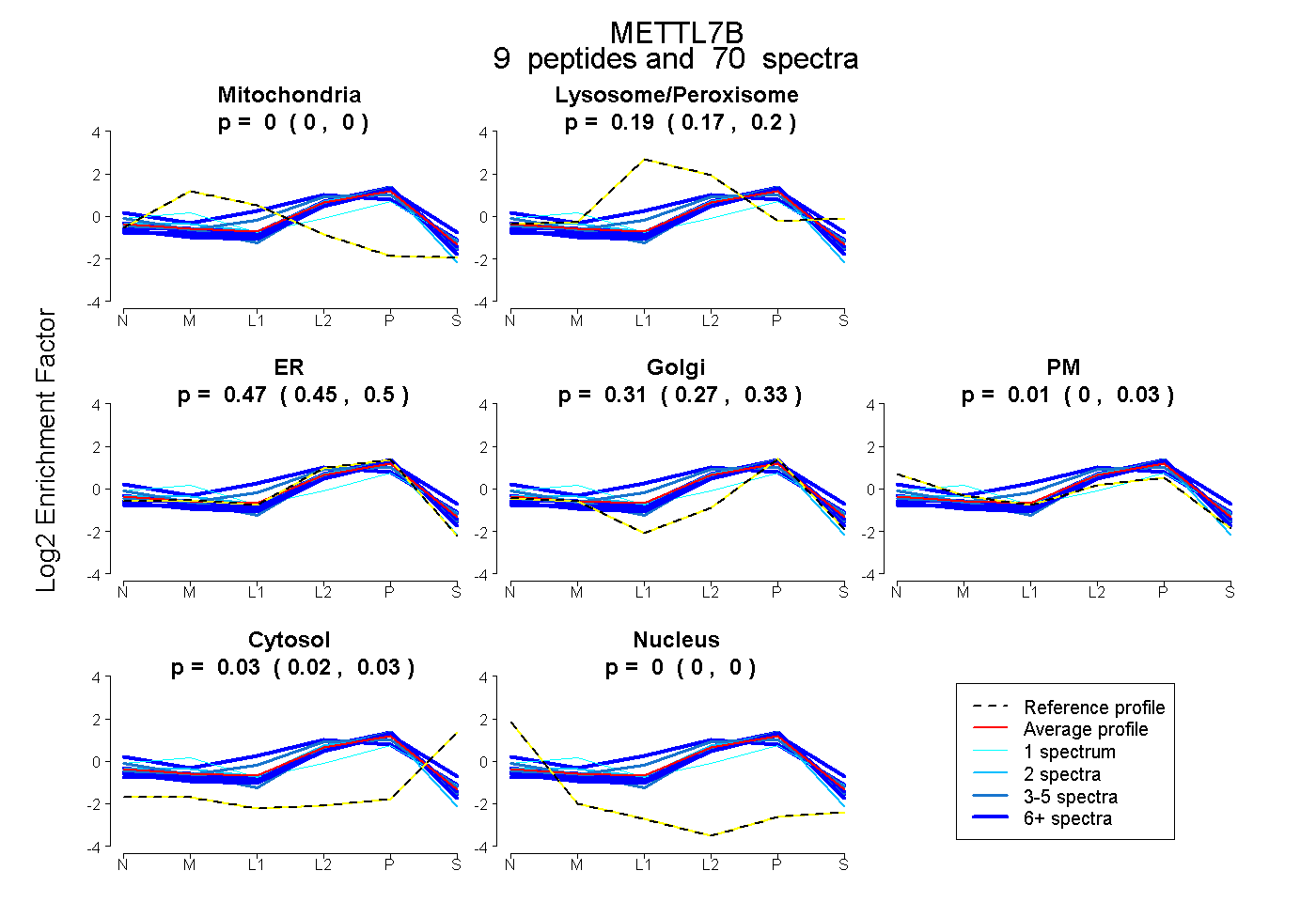
0.000 | 0.000
0.172 | 0.200
0.446 | 0.495
0.275 | 0.327
0.000 | 0.026
0.017 | 0.032
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
173 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.831 0.828 | 0.834 |
0.055 0.051 | 0.059 |
0.000 0.000 | 0.000 |
0.082 0.079 | 0.084 |
0.032 0.030 | 0.033 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
70 spectra |
 |
0.000 0.000 | 0.000 |
0.188 0.172 | 0.200 |
0.472 0.446 | 0.495 |
0.306 0.275 | 0.327 |
0.009 0.000 | 0.026 |
0.025 0.017 | 0.032 |
0.000 0.000 | 0.000 |
| 4 spectra, VTCVDPNPNFEK | 0.000 | 0.267 | 0.403 | 0.159 | 0.158 | 0.013 | 0.000 | |||
| 2 spectra, VLEPTWK | 0.019 | 0.002 | 0.801 | 0.039 | 0.139 | 0.000 | 0.000 | |||
| 14 spectra, ELFSQIK | 0.000 | 0.070 | 0.672 | 0.196 | 0.050 | 0.011 | 0.000 | |||
| 15 spectra, VLQEVQR | 0.000 | 0.100 | 0.558 | 0.170 | 0.000 | 0.172 | 0.000 | |||
| 7 spectra, FIVAYGENMK | 0.000 | 0.117 | 0.633 | 0.226 | 0.000 | 0.023 | 0.000 | |||
| 1 spectrum, HLQYER | 0.084 | 0.203 | 0.000 | 0.487 | 0.209 | 0.018 | 0.000 | |||
| 12 spectra, HIGDGCHLTR | 0.000 | 0.333 | 0.231 | 0.033 | 0.404 | 0.000 | 0.000 | |||
| 5 spectra, TYFPYLMATLTAR | 0.000 | 0.018 | 0.716 | 0.197 | 0.000 | 0.069 | 0.000 | |||
| 10 spectra, WLPVGPHIMGK | 0.000 | 0.060 | 0.685 | 0.160 | 0.000 | 0.095 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
178 spectra |
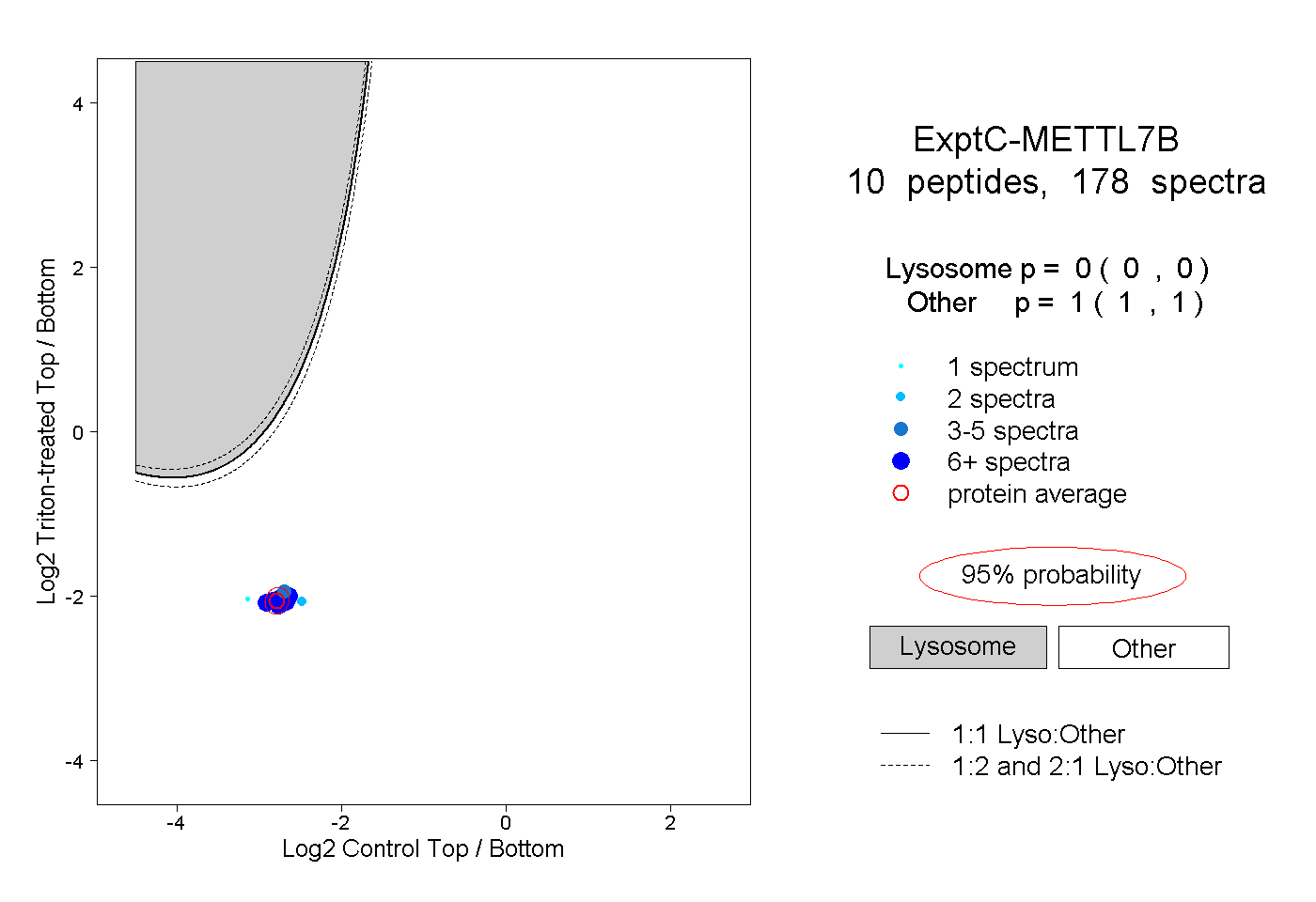 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
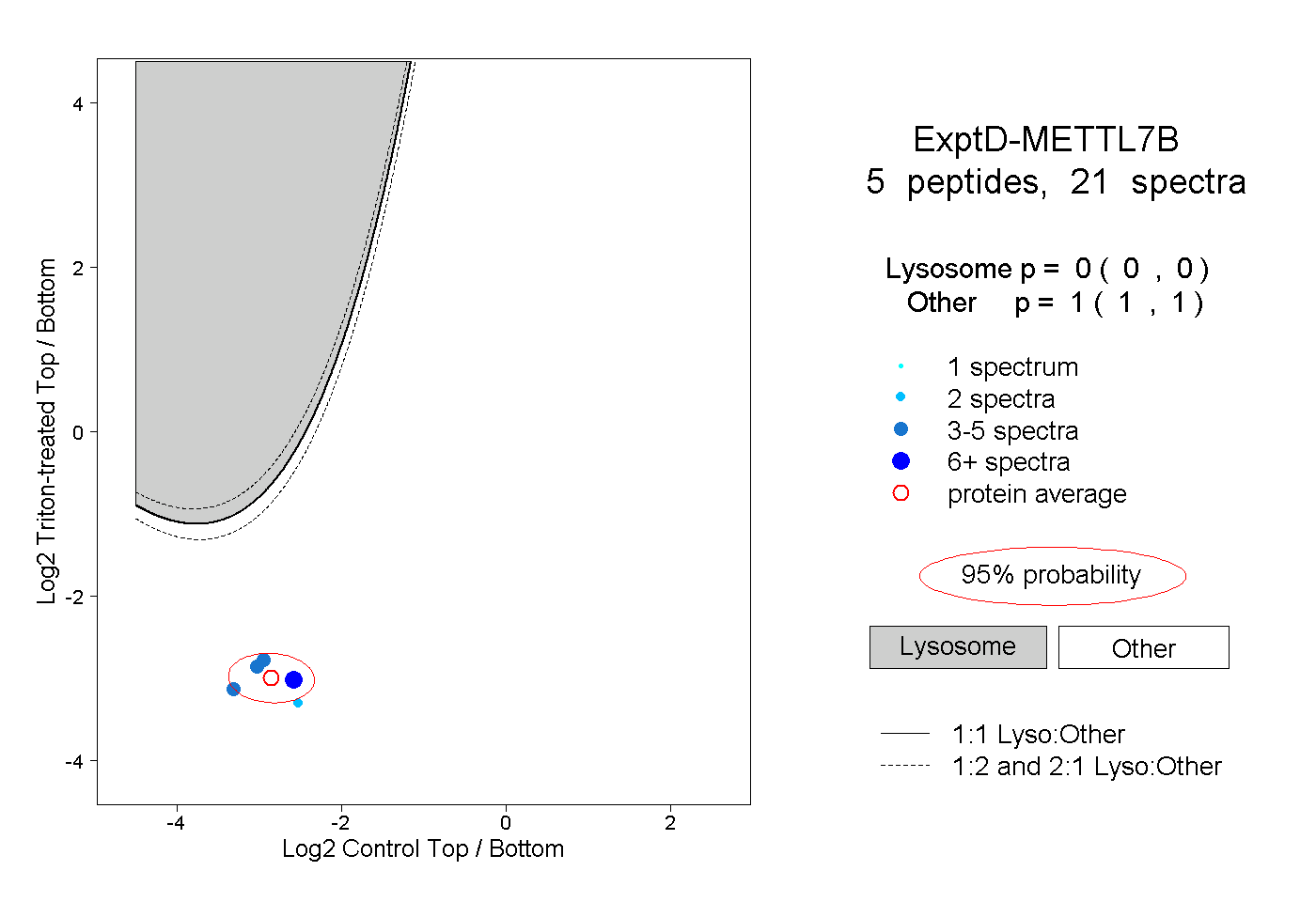 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |