peptides
spectra
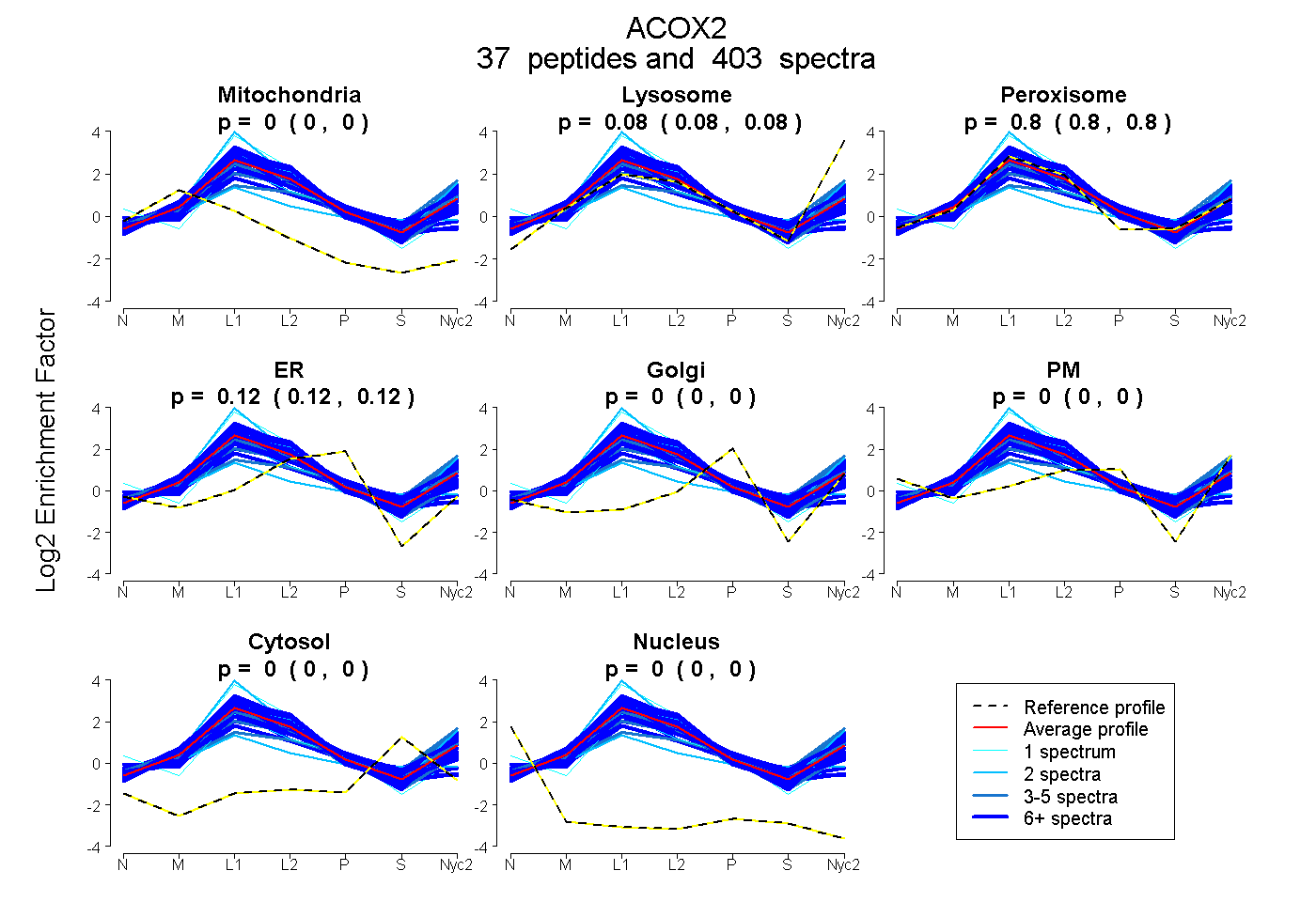
0.000 | 0.000
0.078 | 0.083
0.799 | 0.803
0.117 | 0.119
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
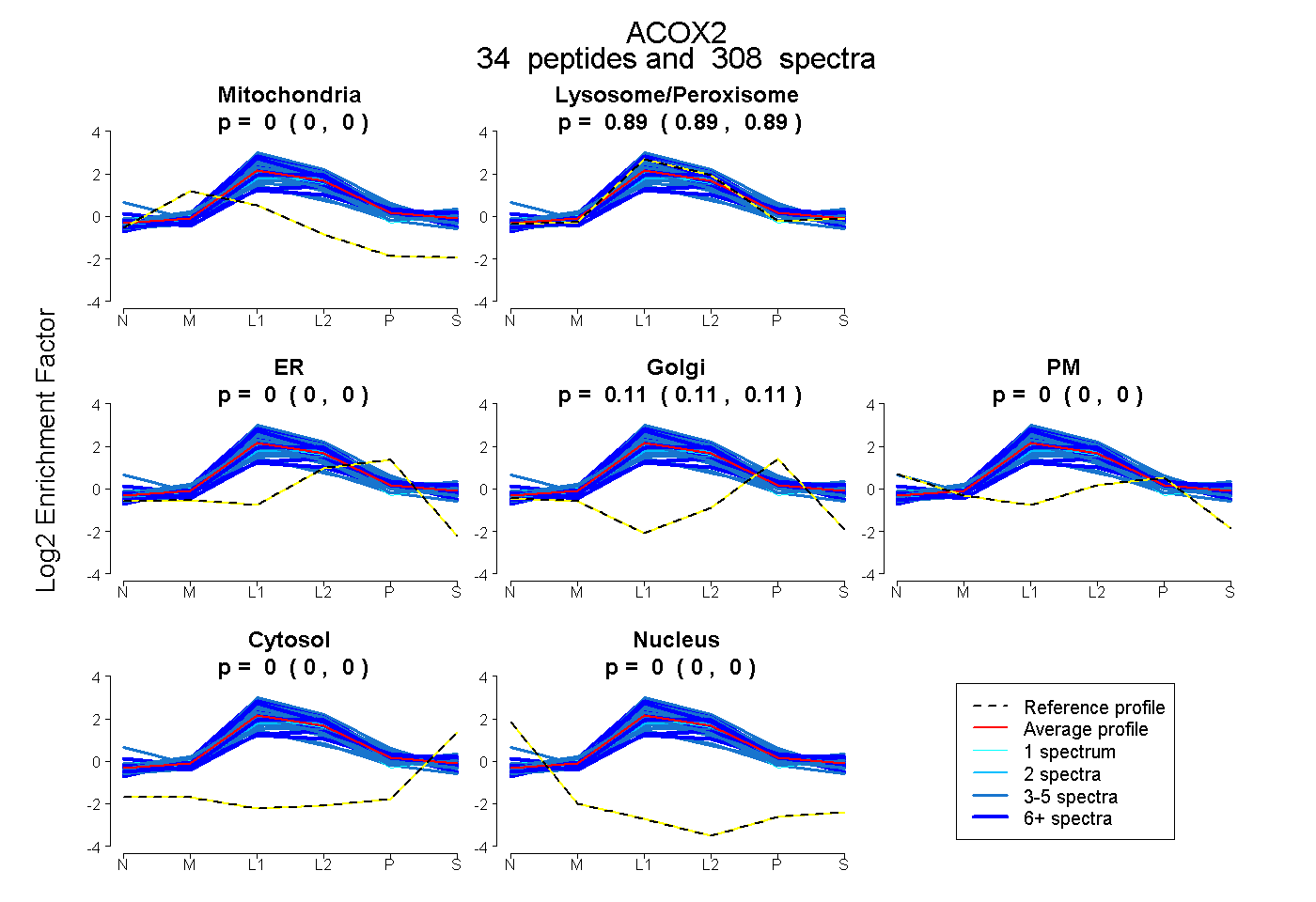
0.000 | 0.000
0.891 | 0.893
0.000 | 0.000
0.106 | 0.109
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
403 spectra |
 |
0.000 0.000 | 0.000 |
0.081 0.078 | 0.083 |
0.801 0.799 | 0.803 |
0.118 0.117 | 0.119 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
308 spectra |
 |
0.000 0.000 | 0.000 |
0.892 0.891 | 0.893 |
0.000 0.000 | 0.000 |
0.108 0.106 | 0.109 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, TQTLMK | 0.000 | 0.835 | 0.052 | 0.065 | 0.000 | 0.047 | 0.000 | |||
| 24 spectra, HGMHAFIVPIR | 0.000 | 0.831 | 0.000 | 0.143 | 0.000 | 0.026 | 0.000 | |||
| 24 spectra, ACIIATR | 0.034 | 0.901 | 0.000 | 0.047 | 0.019 | 0.000 | 0.000 | |||
| 4 spectra, LGTPQSNYLGMLVTR | 0.007 | 0.829 | 0.000 | 0.110 | 0.000 | 0.054 | 0.000 | |||
| 16 spectra, LRPSDPEAK | 0.007 | 0.875 | 0.000 | 0.118 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, LTNILDGGLPNTVLR | 0.000 | 0.912 | 0.088 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, DFSLLPELHALSTGMK | 0.000 | 0.870 | 0.000 | 0.123 | 0.000 | 0.007 | 0.000 | |||
| 4 spectra, SPANTQENPAYK | 0.000 | 0.844 | 0.156 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, MGLEHIDNGFLQLNHVR | 0.000 | 0.700 | 0.000 | 0.146 | 0.053 | 0.101 | 0.000 | |||
| 10 spectra, LAWSLGWSEDGPER | 0.000 | 0.906 | 0.000 | 0.094 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, VESIIQSDPVFNLK | 0.007 | 0.760 | 0.054 | 0.180 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, CSAQTAADFR | 0.000 | 0.945 | 0.055 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ILEYQTQQQK | 0.000 | 0.930 | 0.034 | 0.036 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, SLEDHTPLPGITVGDIGPK | 0.000 | 0.932 | 0.068 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, SLGSDEQIAK | 0.083 | 0.781 | 0.000 | 0.078 | 0.057 | 0.000 | 0.000 | |||
| 4 spectra, ATFADFCAQGAEICR | 0.000 | 0.820 | 0.000 | 0.000 | 0.054 | 0.126 | 0.000 | |||
| 9 spectra, VQLLCK | 0.000 | 0.971 | 0.029 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, YIRPLMLGWR | 0.000 | 0.861 | 0.092 | 0.000 | 0.000 | 0.047 | 0.000 | |||
| 4 spectra, WGQLCK | 0.083 | 0.834 | 0.000 | 0.034 | 0.000 | 0.050 | 0.000 | |||
| 16 spectra, LYFMTR | 0.000 | 0.940 | 0.043 | 0.000 | 0.000 | 0.017 | 0.000 | |||
| 5 spectra, EELYEDAIQK | 0.000 | 0.873 | 0.000 | 0.081 | 0.000 | 0.046 | 0.000 | |||
| 7 spectra, VSLGDTWSWQVHPDIDSER | 0.000 | 0.744 | 0.000 | 0.206 | 0.000 | 0.050 | 0.000 | |||
| 3 spectra, HSPSFSVER | 0.024 | 0.674 | 0.000 | 0.087 | 0.119 | 0.097 | 0.000 | |||
| 16 spectra, LFEWAQK | 0.000 | 0.990 | 0.010 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 41 spectra, LSGLPTLVAR | 0.000 | 0.952 | 0.048 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, FAEVLPDGTYQR | 0.000 | 0.650 | 0.000 | 0.000 | 0.256 | 0.000 | 0.094 | |||
| 8 spectra, AYCYFITVK | 0.000 | 0.948 | 0.000 | 0.011 | 0.000 | 0.041 | 0.000 | |||
| 11 spectra, EAFLDLLPLIR | 0.000 | 0.969 | 0.031 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, GILPSLQK | 0.048 | 0.822 | 0.000 | 0.113 | 0.017 | 0.000 | 0.000 | |||
| 17 spectra, ACGGHGYSK | 0.000 | 0.766 | 0.000 | 0.000 | 0.234 | 0.000 | 0.000 | |||
| 3 spectra, VLDGNVNLSLHGVAMNAIR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SGVDQHDAWNQTTVIHLQAAK | 0.034 | 0.851 | 0.000 | 0.000 | 0.061 | 0.054 | 0.000 | |||
| 3 spectra, EPEIQR | 0.000 | 0.969 | 0.031 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, QEFVIHSPTMTSTK | 0.000 | 0.825 | 0.078 | 0.000 | 0.000 | 0.096 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1982 spectra |
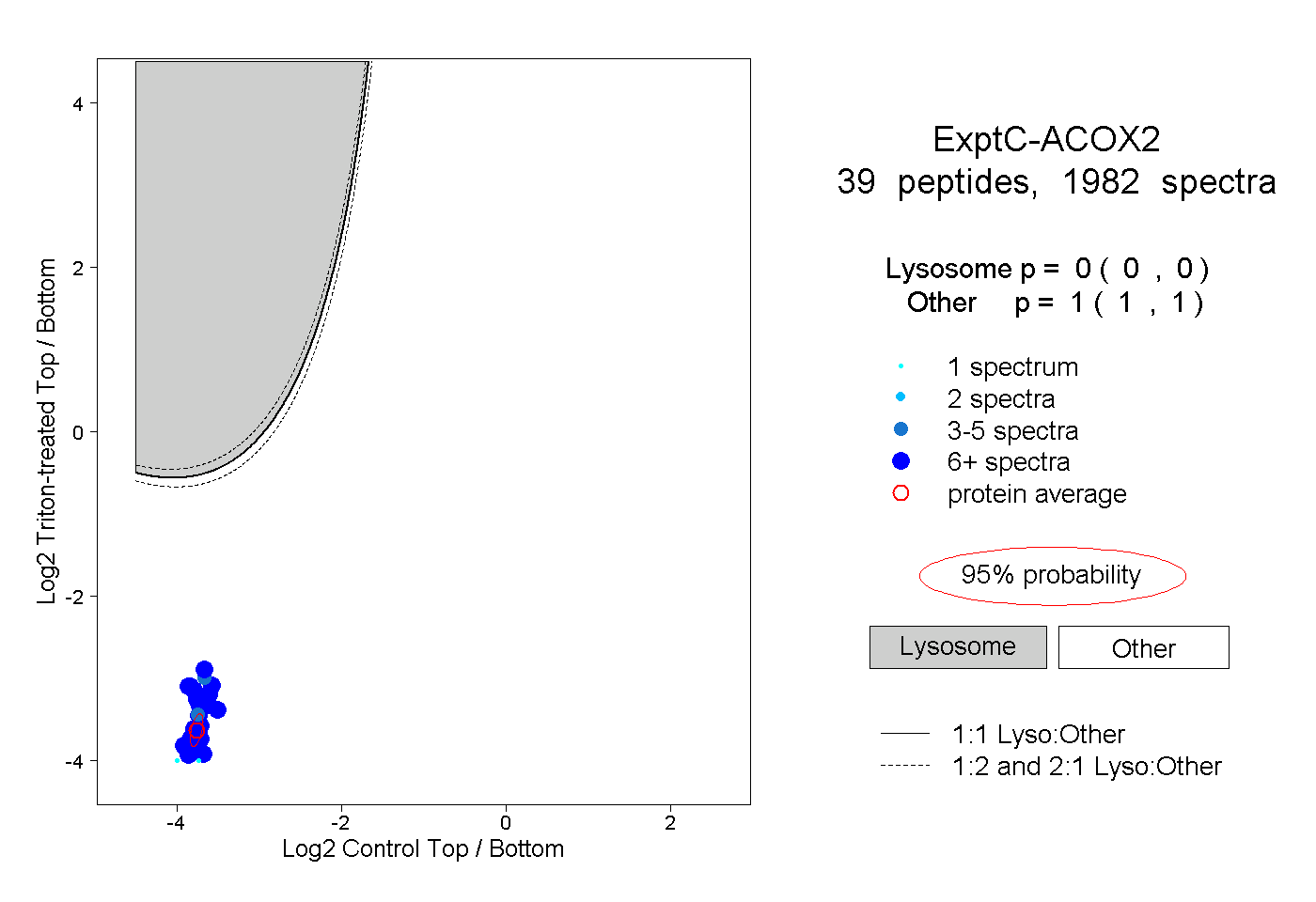 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
174 spectra |
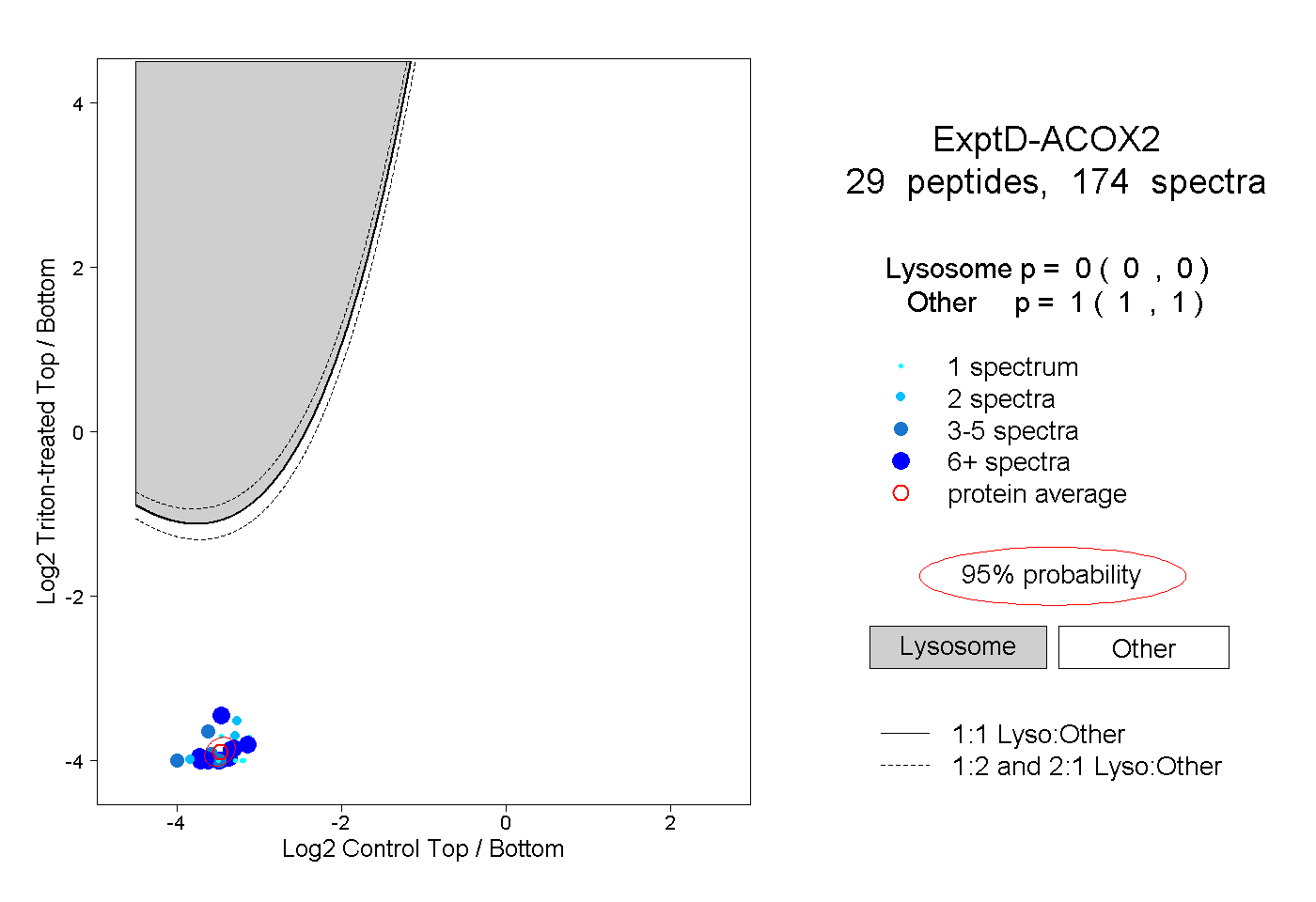 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |