peptides
spectra
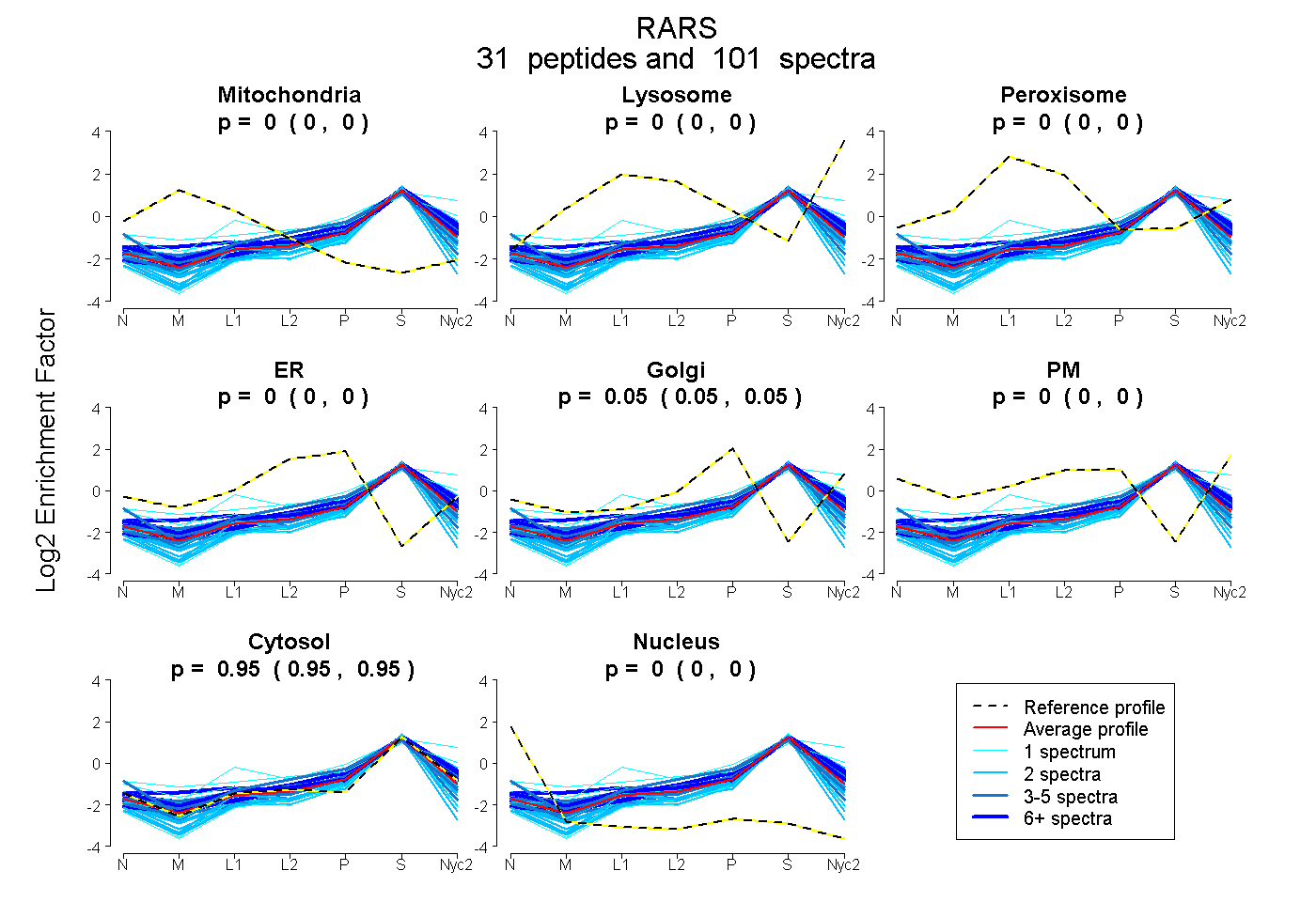
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.047 | 0.050
0.000 | 0.000
0.949 | 0.953
0.000 | 0.000
peptides
spectra
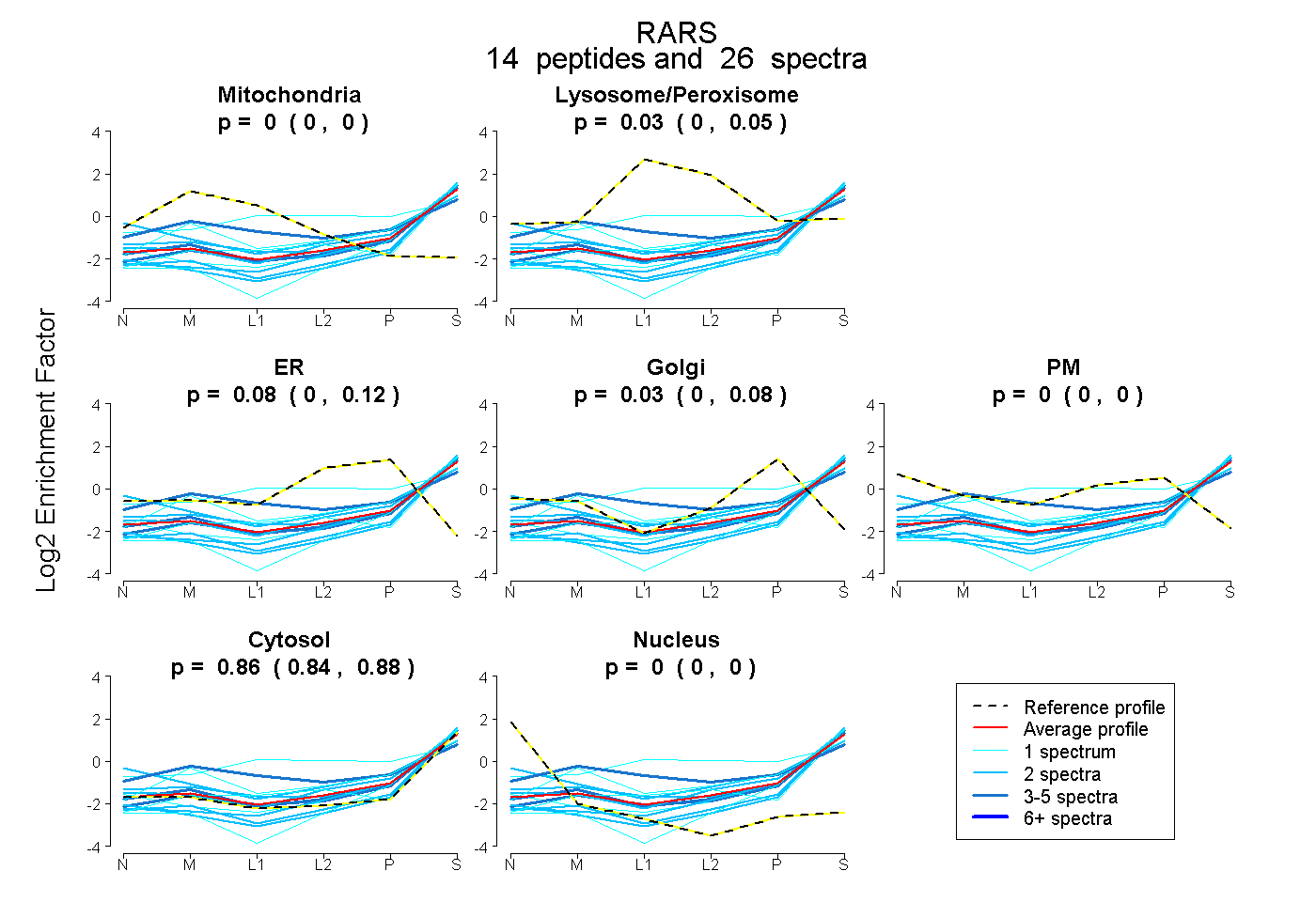
0.000 | 0.000
0.000 | 0.052
0.004 | 0.119
0.000 | 0.083
0.000 | 0.000
0.844 | 0.878
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
101 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.049 0.047 | 0.050 |
0.000 0.000 | 0.000 |
0.951 0.949 | 0.953 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
0.027 0.000 | 0.052 |
0.078 0.004 | 0.119 |
0.031 0.000 | 0.083 |
0.000 0.000 | 0.000 |
0.864 0.844 | 0.878 |
0.000 0.000 | 0.000 |
| 2 spectra, LNDYVFSFDK | 0.000 | 0.000 | 0.152 | 0.015 | 0.000 | 0.833 | 0.000 | |||
| 3 spectra, VEIAGPGFINVHLR | 0.102 | 0.251 | 0.000 | 0.125 | 0.000 | 0.522 | 0.000 | |||
| 1 spectrum, AYECVVLLQSK | 0.000 | 0.000 | 0.000 | 0.078 | 0.000 | 0.922 | 0.000 | |||
| 2 spectra, EMHVGHLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, LQELFGCAIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, YADLSHNR | 0.023 | 0.157 | 0.000 | 0.157 | 0.000 | 0.663 | 0.000 | |||
| 1 spectrum, GESFYQDR | 0.000 | 0.475 | 0.000 | 0.164 | 0.000 | 0.361 | 0.000 | |||
| 3 spectra, LANIDEEMLQR | 0.000 | 0.027 | 0.000 | 0.100 | 0.000 | 0.873 | 0.000 | |||
| 1 spectrum, VAHVGFGVVLGEDK | 0.000 | 0.102 | 0.000 | 0.000 | 0.000 | 0.898 | 0.000 | |||
| 3 spectra, LFEFAGYNVLR | 0.000 | 0.010 | 0.053 | 0.000 | 0.000 | 0.937 | 0.000 | |||
| 2 spectra, HLPNNEYIDR | 0.000 | 0.023 | 0.000 | 0.000 | 0.329 | 0.647 | 0.000 | |||
| 2 spectra, SLTAEIDR | 0.000 | 0.000 | 0.000 | 0.033 | 0.000 | 0.967 | 0.000 | |||
| 1 spectrum, VLTEEELK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, AAQTSVAYGCIK | 0.000 | 0.112 | 0.000 | 0.073 | 0.000 | 0.816 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
61 spectra |
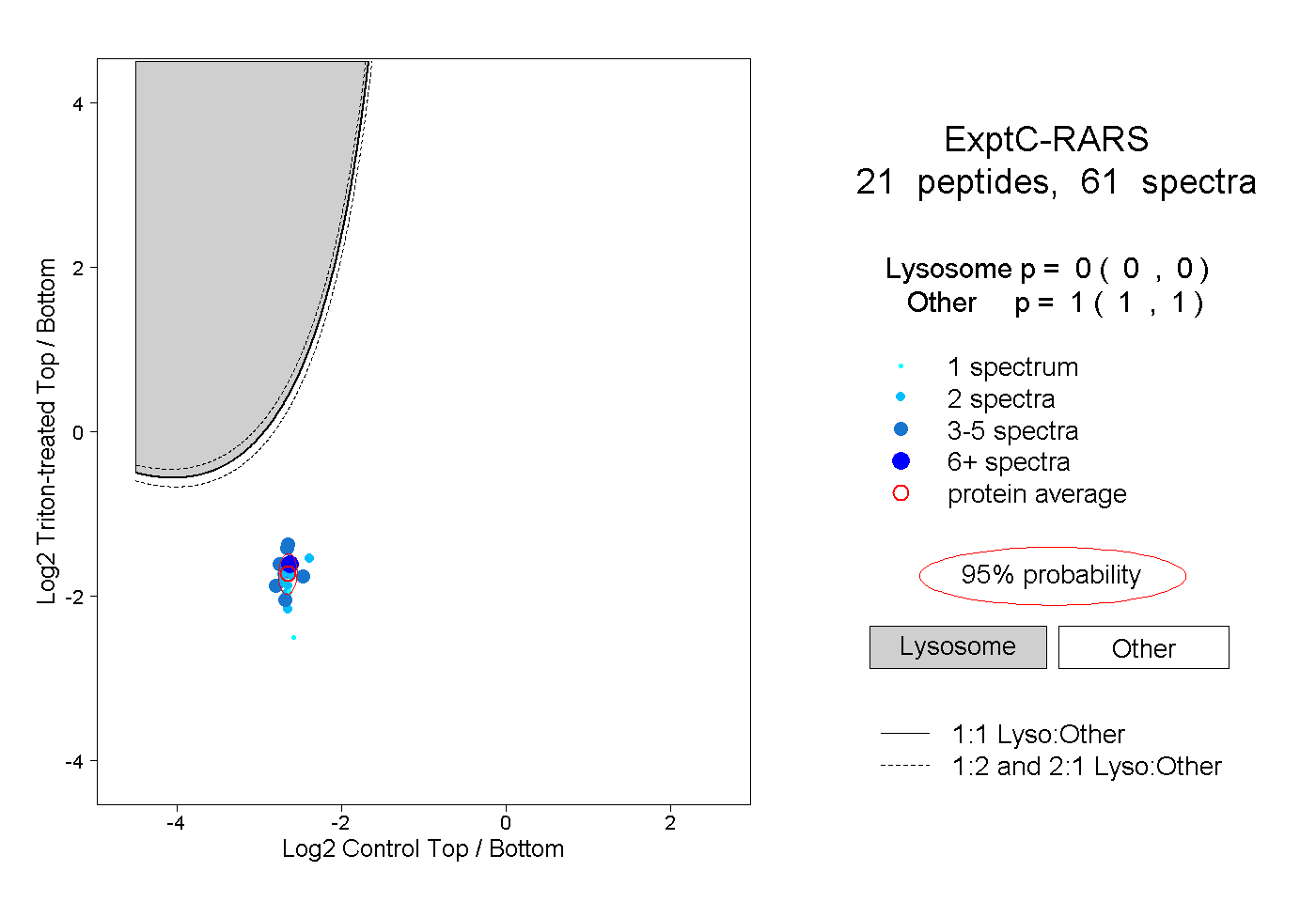 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
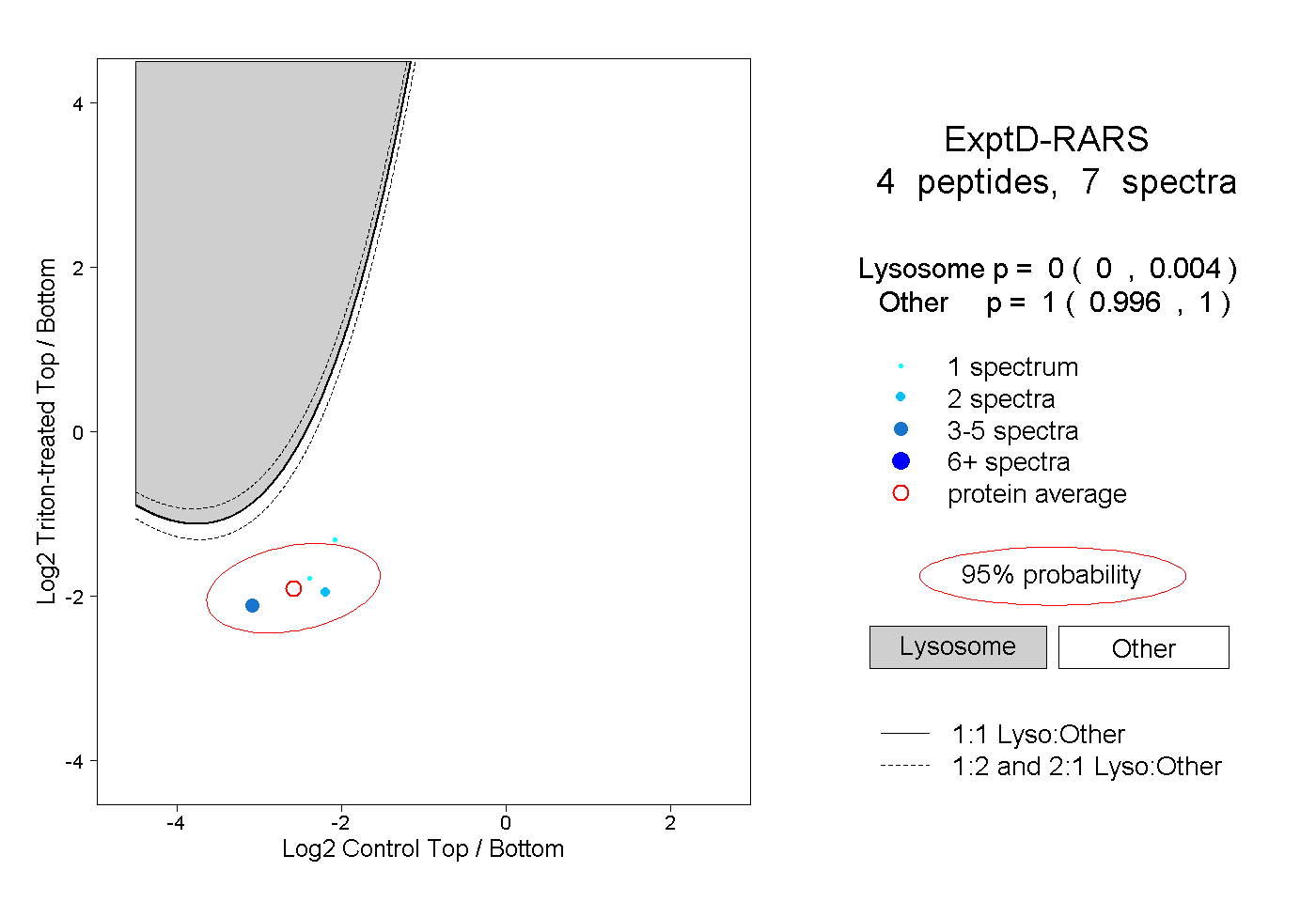 |
0.000 0.000 | 0.004 |
1.000 0.996 | 1.000 |