peptides
spectra
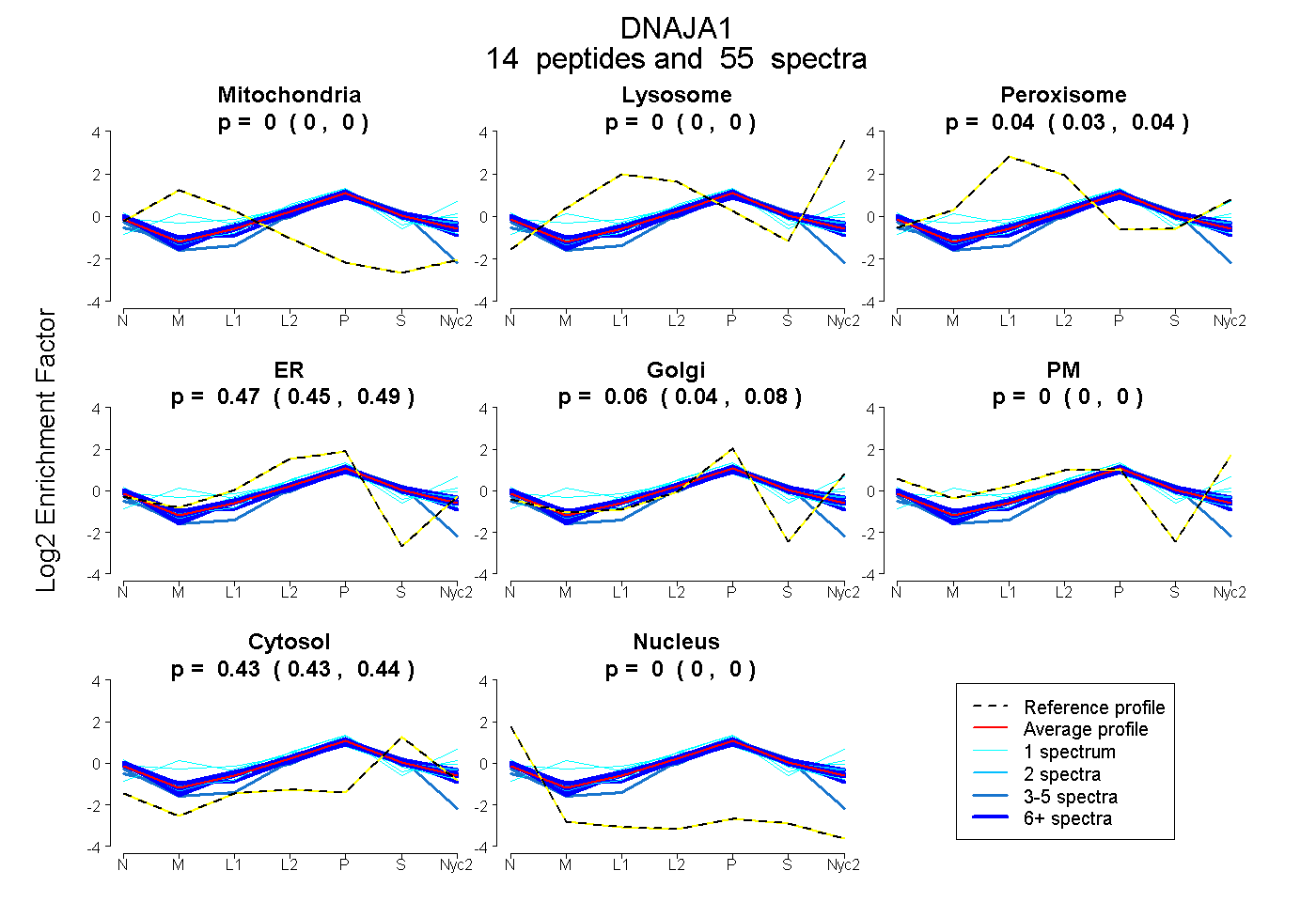
0.000 | 0.000
0.000 | 0.000
0.029 | 0.044
0.448 | 0.487
0.040 | 0.076
0.000 | 0.000
0.428 | 0.439
0.000 | 0.000
peptides
spectra
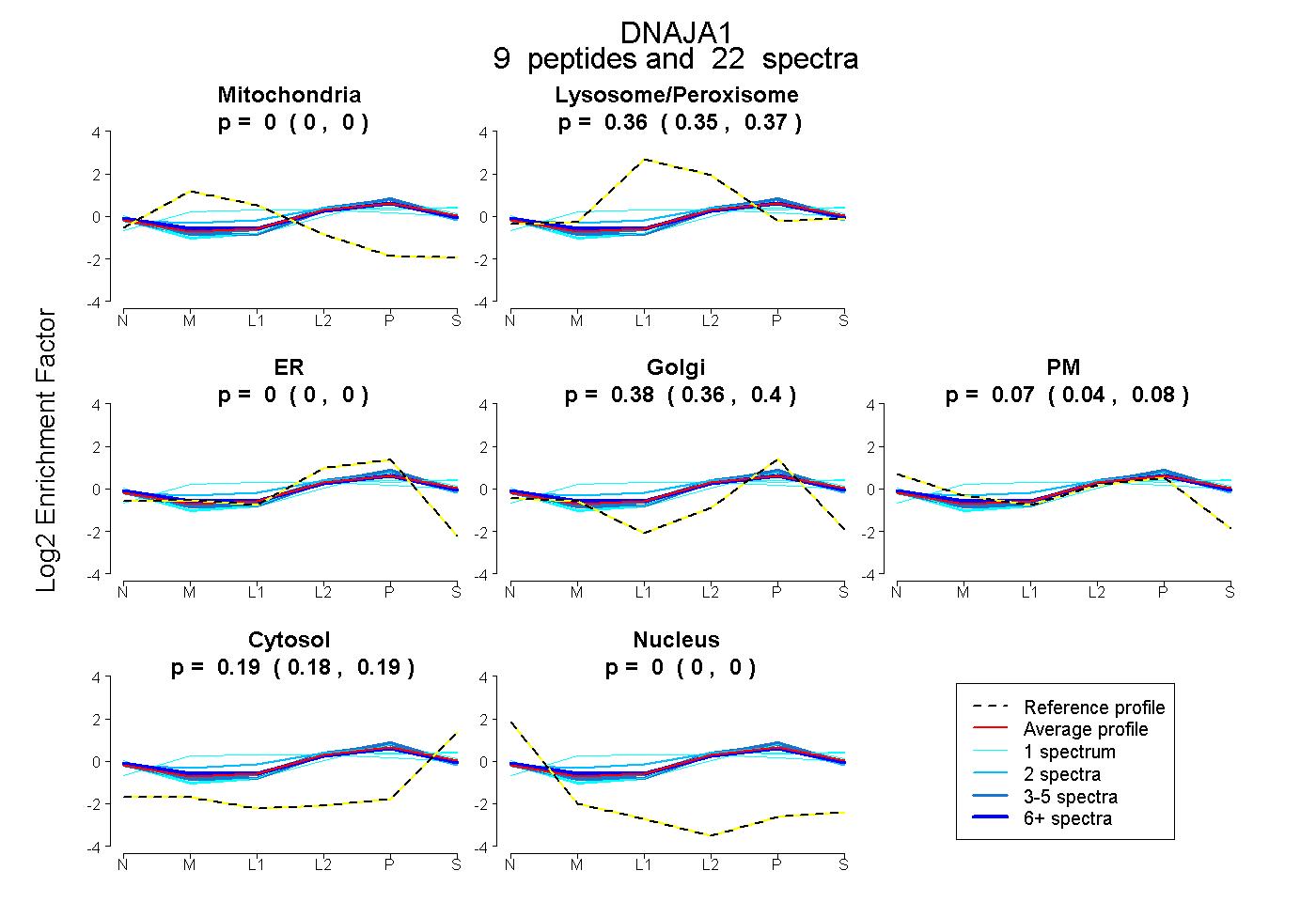
0.000 | 0.000
0.353 | 0.371
0.000 | 0.000
0.365 | 0.400
0.043 | 0.085
0.181 | 0.193
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
55 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.037 0.029 | 0.044 |
0.469 0.448 | 0.487 |
0.060 0.040 | 0.076 |
0.000 0.000 | 0.000 |
0.434 0.428 | 0.439 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.363 0.353 | 0.371 |
0.000 0.000 | 0.000 |
0.383 0.365 | 0.400 |
0.066 0.043 | 0.085 |
0.187 0.181 | 0.193 |
0.000 0.000 | 0.000 |
| 1 spectrum, DHAVFTR | 0.062 | 0.493 | 0.000 | 0.283 | 0.000 | 0.162 | 0.000 | |||
| 1 spectrum, CVLNEGMPIYR | 0.000 | 0.327 | 0.041 | 0.436 | 0.006 | 0.190 | 0.000 | |||
| 8 spectra, TIVITSHPGQIVK | 0.000 | 0.335 | 0.000 | 0.352 | 0.138 | 0.175 | 0.000 | |||
| 1 spectrum, GAVECCPNCR | 0.000 | 0.231 | 0.130 | 0.000 | 0.309 | 0.330 | 0.000 | |||
| 1 spectrum, ITFHGEGDQEPGLEPGDIIIVLDQK | 0.000 | 0.317 | 0.000 | 0.465 | 0.000 | 0.218 | 0.000 | |||
| 1 spectrum, NVICDK | 0.000 | 0.260 | 0.119 | 0.079 | 0.236 | 0.305 | 0.000 | |||
| 2 spectra, QISQAYEVLADSK | 0.000 | 0.432 | 0.000 | 0.402 | 0.051 | 0.114 | 0.000 | |||
| 3 spectra, LLLEFK | 0.000 | 0.334 | 0.010 | 0.491 | 0.002 | 0.163 | 0.000 | |||
| 4 spectra, ILEVHIDK | 0.000 | 0.353 | 0.000 | 0.416 | 0.077 | 0.154 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
91 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
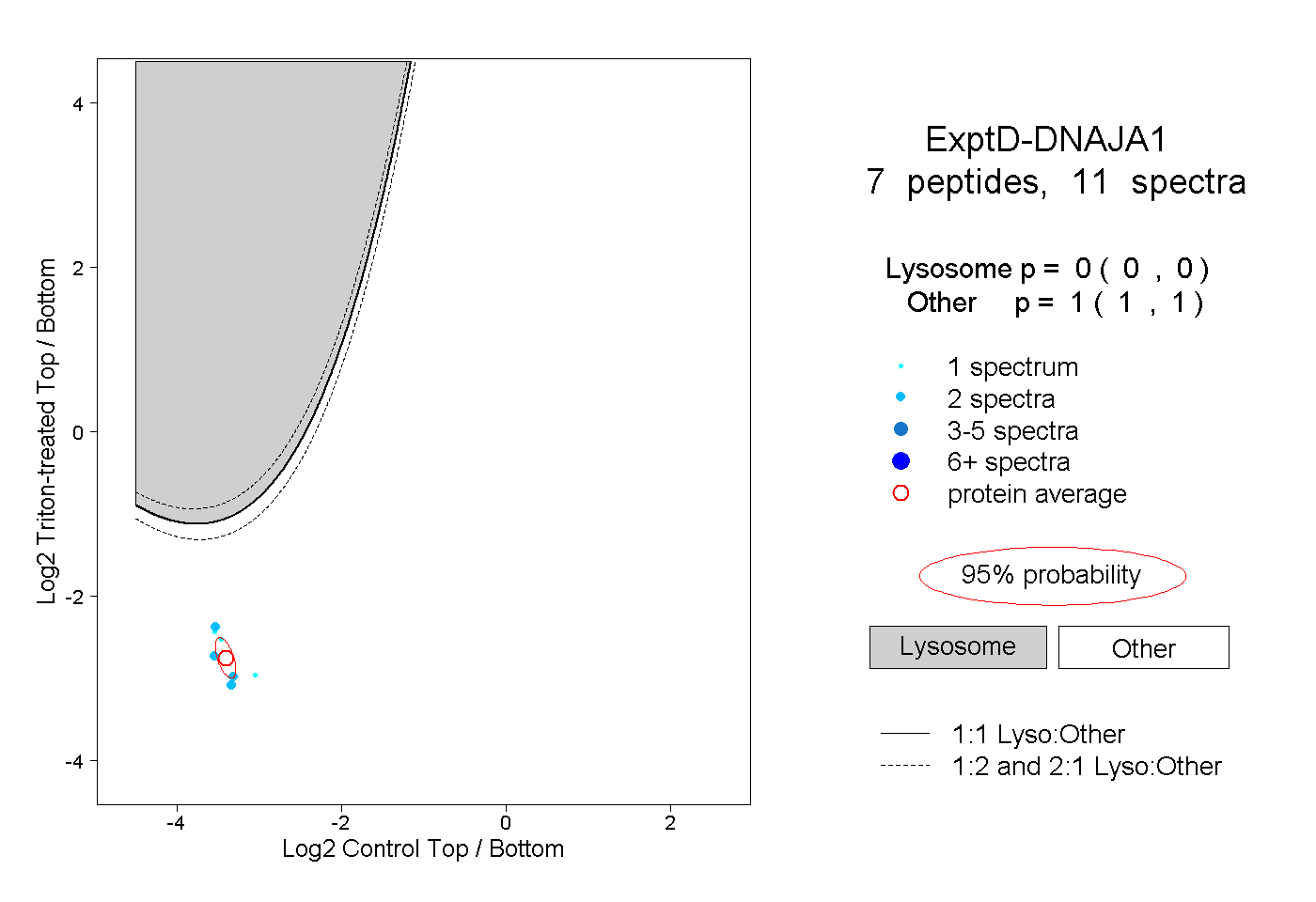 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |