peptides
spectra
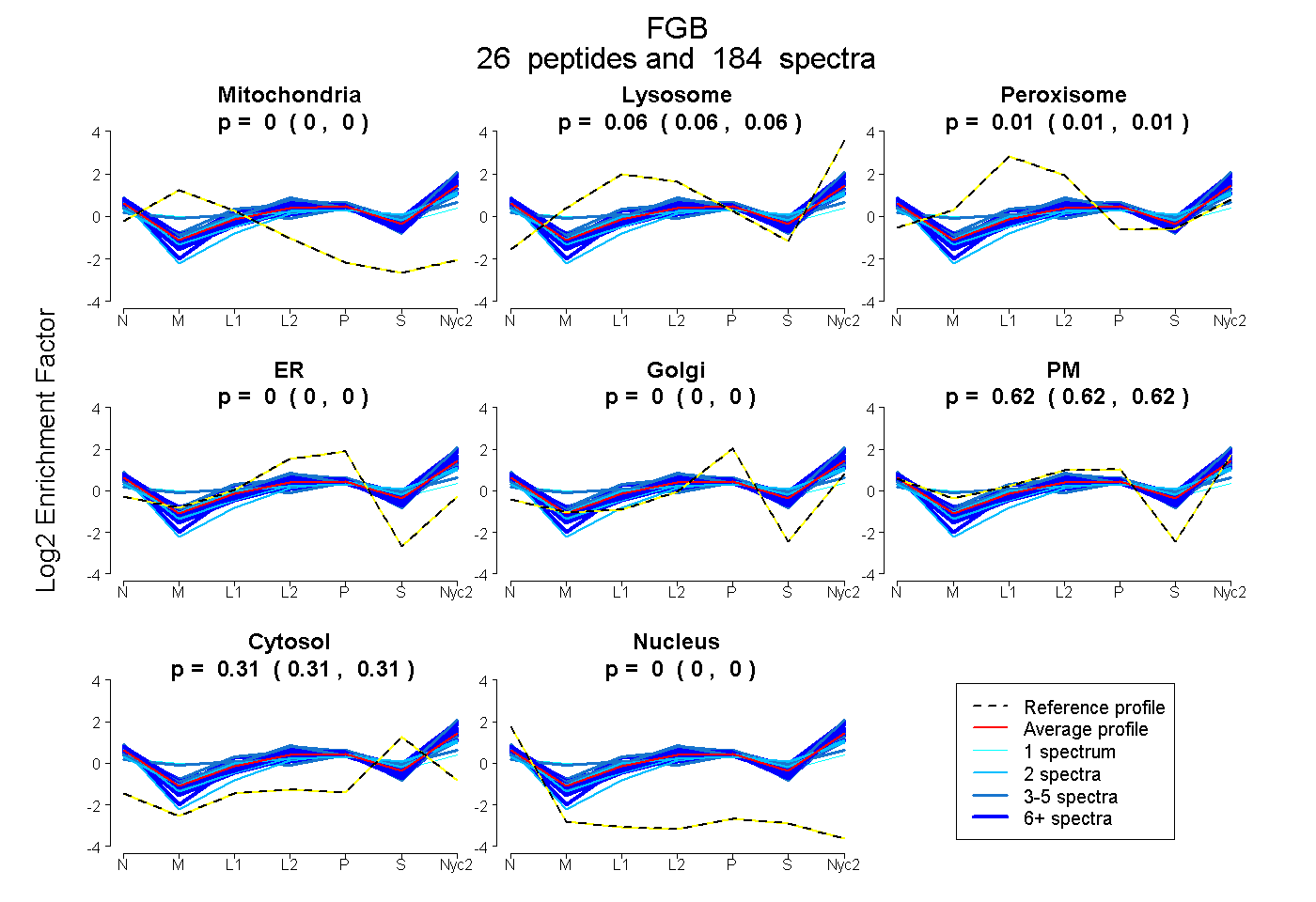
0.000 | 0.000
0.057 | 0.063
0.006 | 0.011
0.000 | 0.000
0.000 | 0.000
0.621 | 0.624
0.307 | 0.309
0.000 | 0.000
peptides
spectra
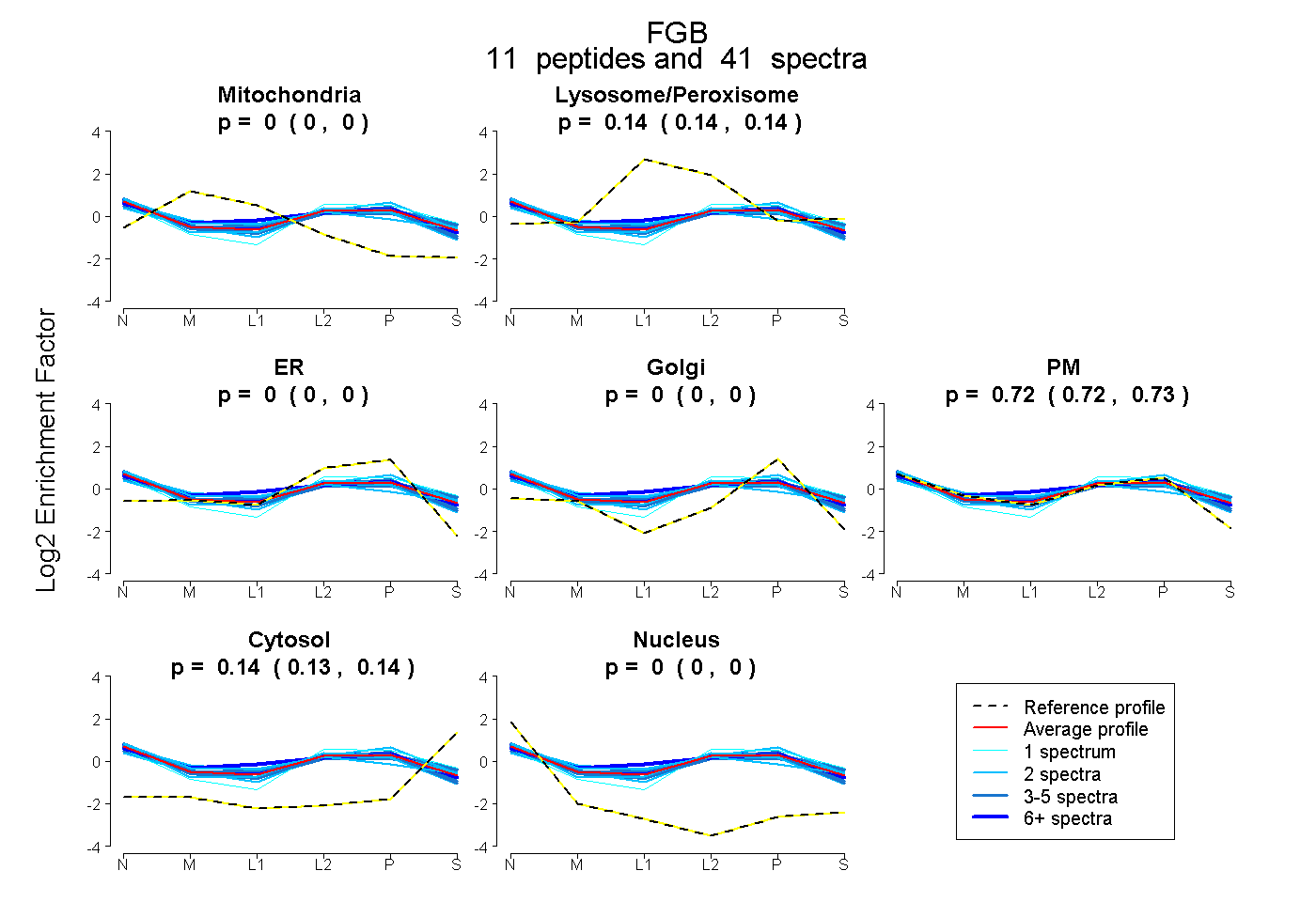
0.000 | 0.000
0.135 | 0.145
0.000 | 0.000
0.000 | 0.000
0.718 | 0.729
0.132 | 0.139
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
184 spectra |
 |
0.000 0.000 | 0.000 |
0.060 0.057 | 0.063 |
0.009 0.006 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.623 0.621 | 0.624 |
0.309 0.307 | 0.309 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
41 spectra |
 |
0.000 0.000 | 0.000 |
0.140 0.135 | 0.145 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.724 0.718 | 0.729 |
0.136 0.132 | 0.139 |
0.000 0.000 | 0.000 |
| 4 spectra, SLLEDIR | 0.000 | 0.080 | 0.000 | 0.000 | 0.823 | 0.097 | 0.000 | |||
| 9 spectra, QTLLNHERPIK | 0.000 | 0.214 | 0.000 | 0.000 | 0.684 | 0.101 | 0.000 | |||
| 2 spectra, ISQLTR | 0.000 | 0.158 | 0.000 | 0.000 | 0.758 | 0.074 | 0.010 | |||
| 2 spectra, YCGLPGEYWLGNDK | 0.000 | 0.143 | 0.000 | 0.000 | 0.708 | 0.149 | 0.000 | |||
| 2 spectra, TENGGWTVIQNR | 0.000 | 0.244 | 0.000 | 0.000 | 0.580 | 0.117 | 0.059 | |||
| 4 spectra, QDGSVDFGR | 0.000 | 0.081 | 0.000 | 0.000 | 0.810 | 0.109 | 0.000 | |||
| 7 spectra, ECEEIIR | 0.000 | 0.146 | 0.000 | 0.000 | 0.741 | 0.113 | 0.000 | |||
| 4 spectra, EEPPSLRPAPPPISGGGYR | 0.000 | 0.203 | 0.000 | 0.000 | 0.616 | 0.181 | 0.000 | |||
| 1 spectrum, IGPTELLIEMEDWK | 0.000 | 0.072 | 0.093 | 0.000 | 0.637 | 0.199 | 0.000 | |||
| 2 spectra, GHRPVDR | 0.000 | 0.139 | 0.000 | 0.155 | 0.574 | 0.131 | 0.000 | |||
| 4 spectra, EDGGGWWYNR | 0.000 | 0.136 | 0.000 | 0.000 | 0.673 | 0.191 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
420 spectra |
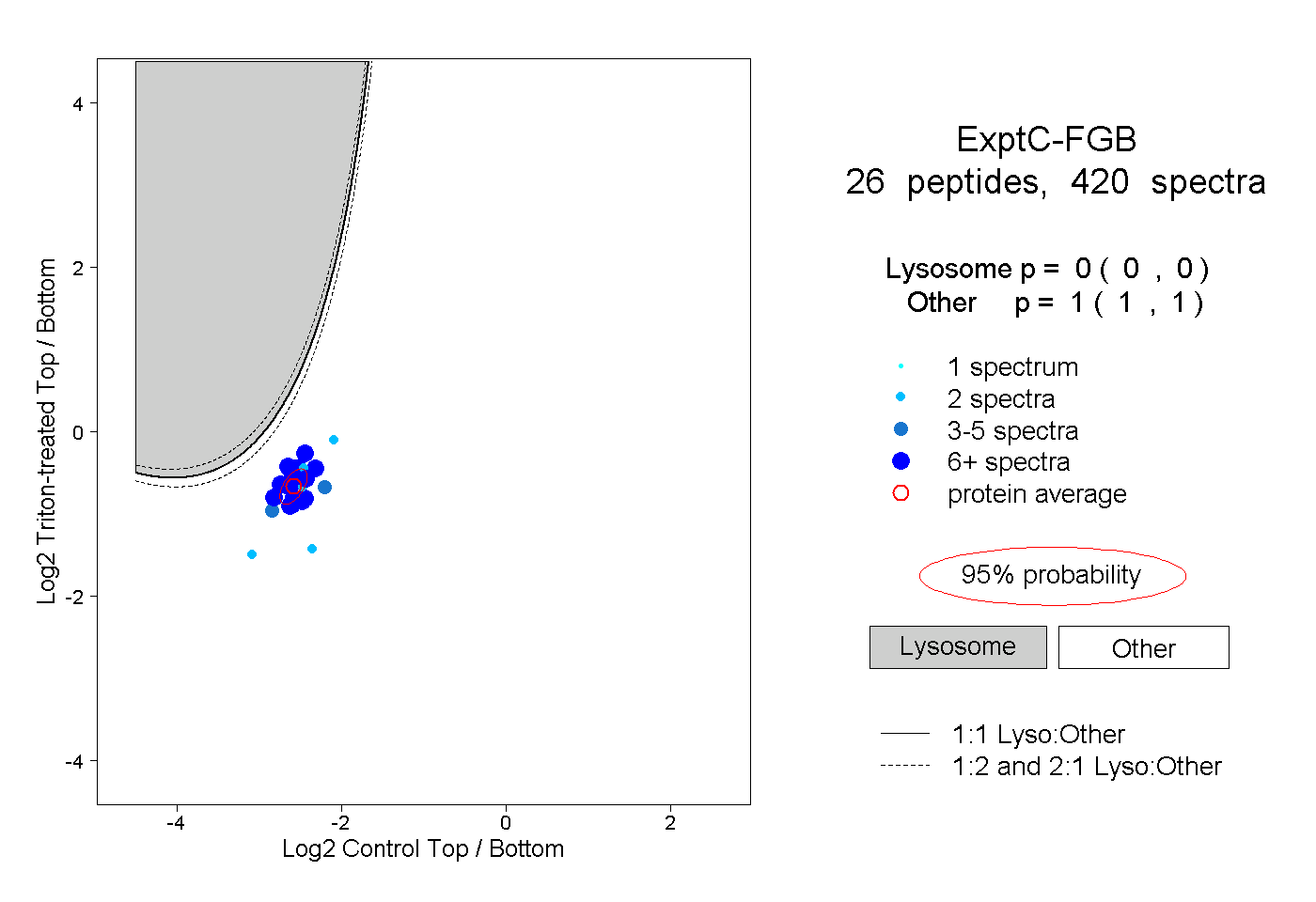 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
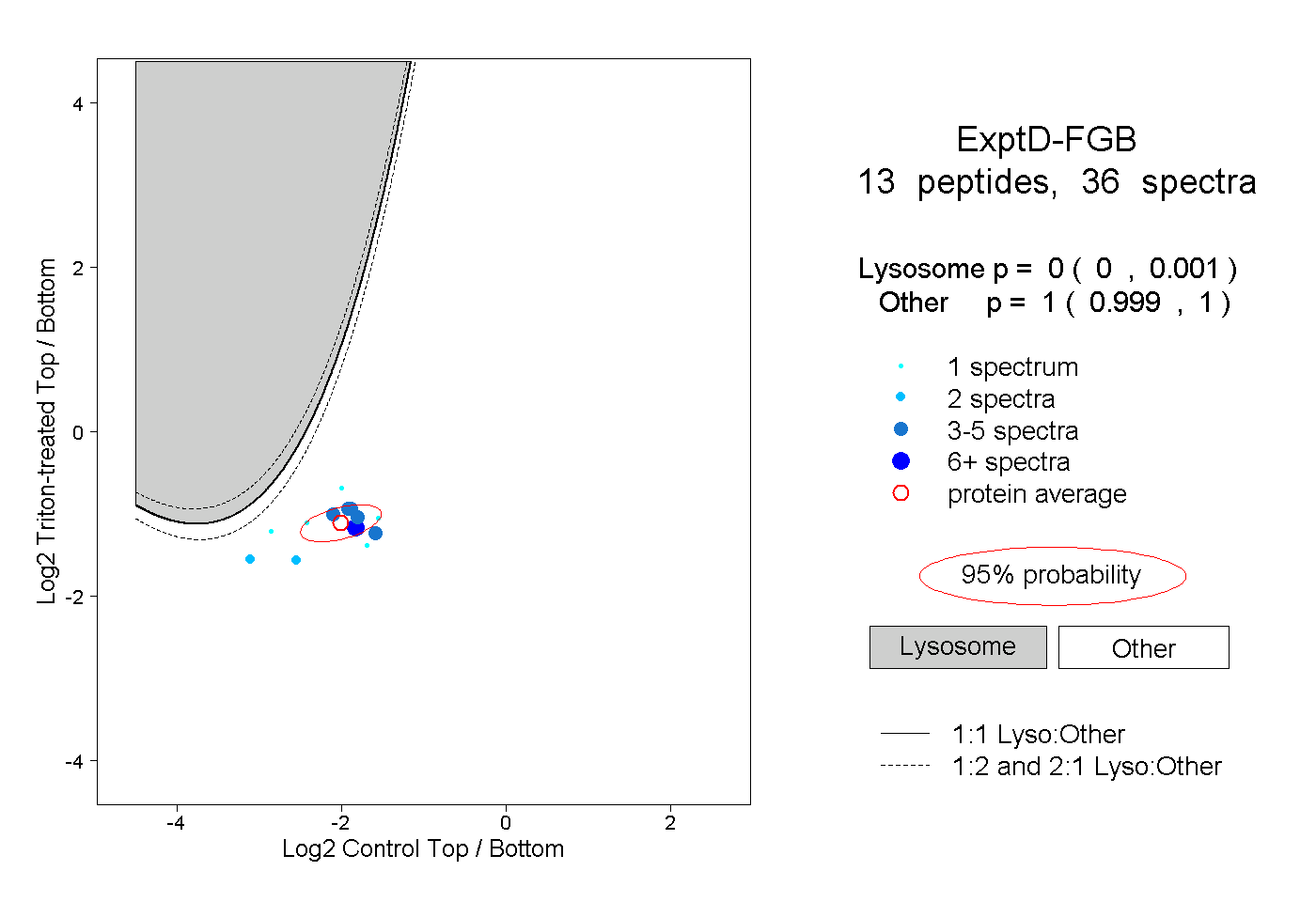 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |