peptides
spectra
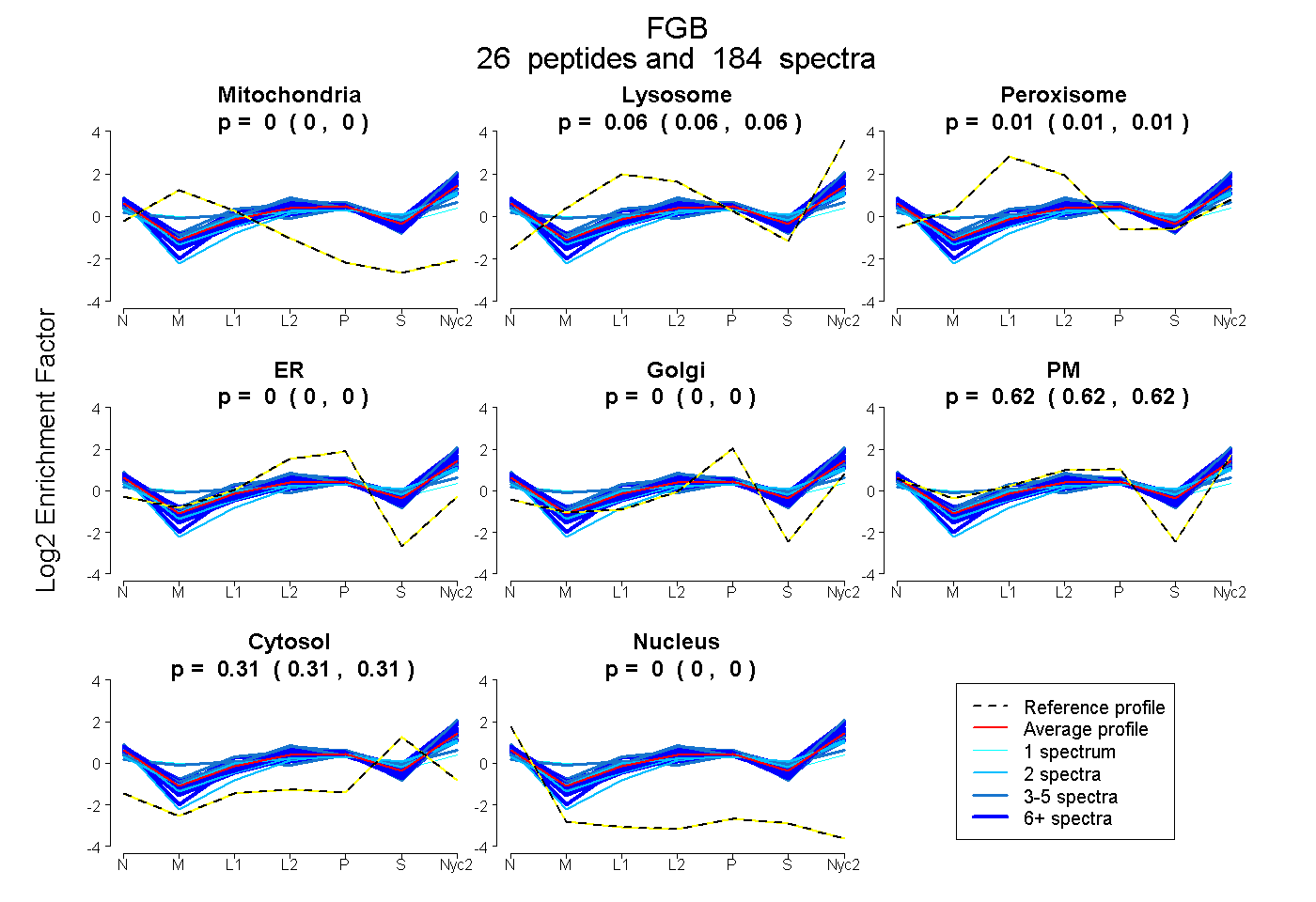
0.000 | 0.000
0.057 | 0.063
0.006 | 0.011
0.000 | 0.000
0.000 | 0.000
0.621 | 0.624
0.307 | 0.309
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
184 spectra |
 |
0.000 0.000 | 0.000 |
0.060 0.057 | 0.063 |
0.009 0.006 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.623 0.621 | 0.624 |
0.309 0.307 | 0.309 |
0.000 0.000 | 0.000 |
| 2 spectra, AHYGGFTVQTEANK | 0.000 | 0.128 | 0.000 | 0.000 | 0.000 | 0.554 | 0.318 | 0.000 | ||
| 9 spectra, QTLLNHERPIK | 0.000 | 0.022 | 0.000 | 0.000 | 0.000 | 0.695 | 0.283 | 0.000 | ||
| 20 spectra, ISQLTR | 0.000 | 0.072 | 0.000 | 0.000 | 0.000 | 0.705 | 0.224 | 0.000 | ||
| 3 spectra, HGTDDGVVWMNWK | 0.000 | 0.118 | 0.112 | 0.000 | 0.000 | 0.504 | 0.266 | 0.000 | ||
| 6 spectra, YQVSVNK | 0.000 | 0.024 | 0.000 | 0.000 | 0.000 | 0.681 | 0.296 | 0.000 | ||
| 4 spectra, TMTIHNGMFFSTYDR | 0.032 | 0.142 | 0.037 | 0.000 | 0.000 | 0.506 | 0.282 | 0.000 | ||
| 3 spectra, KPPDAGGCVHGDGDMGVLCPTGCELR | 0.000 | 0.000 | 0.123 | 0.000 | 0.000 | 0.580 | 0.297 | 0.000 | ||
| 9 spectra, VDAGQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.603 | 0.397 | 0.000 | ||
| 4 spectra, TENGGWTVIQNR | 0.000 | 0.182 | 0.000 | 0.000 | 0.000 | 0.580 | 0.238 | 0.000 | ||
| 1 spectrum, CHAANPNGR | 0.076 | 0.000 | 0.159 | 0.000 | 0.000 | 0.465 | 0.299 | 0.000 | ||
| 3 spectra, GGETSEMYLIQPDTSSKPYR | 0.000 | 0.029 | 0.000 | 0.000 | 0.000 | 0.740 | 0.231 | 0.000 | ||
| 15 spectra, IRPVFPQQ | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.678 | 0.322 | 0.000 | ||
| 23 spectra, ECEEIIR | 0.000 | 0.000 | 0.081 | 0.000 | 0.000 | 0.602 | 0.316 | 0.000 | ||
| 6 spectra, EEPPSLRPAPPPISGGGYR | 0.000 | 0.009 | 0.000 | 0.000 | 0.000 | 0.609 | 0.382 | 0.000 | ||
| 5 spectra, IGPTELLIEMEDWK | 0.000 | 0.082 | 0.000 | 0.000 | 0.000 | 0.607 | 0.311 | 0.000 | ||
| 14 spectra, EDGGGWWYNR | 0.000 | 0.102 | 0.017 | 0.000 | 0.000 | 0.610 | 0.271 | 0.000 | ||
| 6 spectra, GFGNIATNEDTK | 0.000 | 0.039 | 0.022 | 0.000 | 0.000 | 0.700 | 0.239 | 0.000 | ||
| 2 spectra, YYWGGLYSWDMSK | 0.000 | 0.030 | 0.118 | 0.000 | 0.000 | 0.472 | 0.380 | 0.000 | ||
| 12 spectra, SLLEDIR | 0.000 | 0.060 | 0.000 | 0.000 | 0.000 | 0.639 | 0.301 | 0.000 | ||
| 2 spectra, YCGLPGEYWLGNDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.623 | 0.377 | 0.000 | ||
| 10 spectra, GSWYSMR | 0.000 | 0.206 | 0.000 | 0.000 | 0.000 | 0.505 | 0.289 | 0.000 | ||
| 10 spectra, QDGSVDFGR | 0.000 | 0.075 | 0.000 | 0.000 | 0.000 | 0.695 | 0.230 | 0.000 | ||
| 3 spectra, VYCDMK | 0.000 | 0.000 | 0.155 | 0.000 | 0.000 | 0.481 | 0.365 | 0.000 | ||
| 6 spectra, DNDGWVTTDPR | 0.000 | 0.176 | 0.000 | 0.000 | 0.000 | 0.502 | 0.322 | 0.000 | ||
| 2 spectra, VDLSIAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.547 | 0.453 | 0.000 | ||
| 4 spectra, GHRPVDR | 0.000 | 0.000 | 0.062 | 0.000 | 0.000 | 0.665 | 0.273 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
41 spectra |
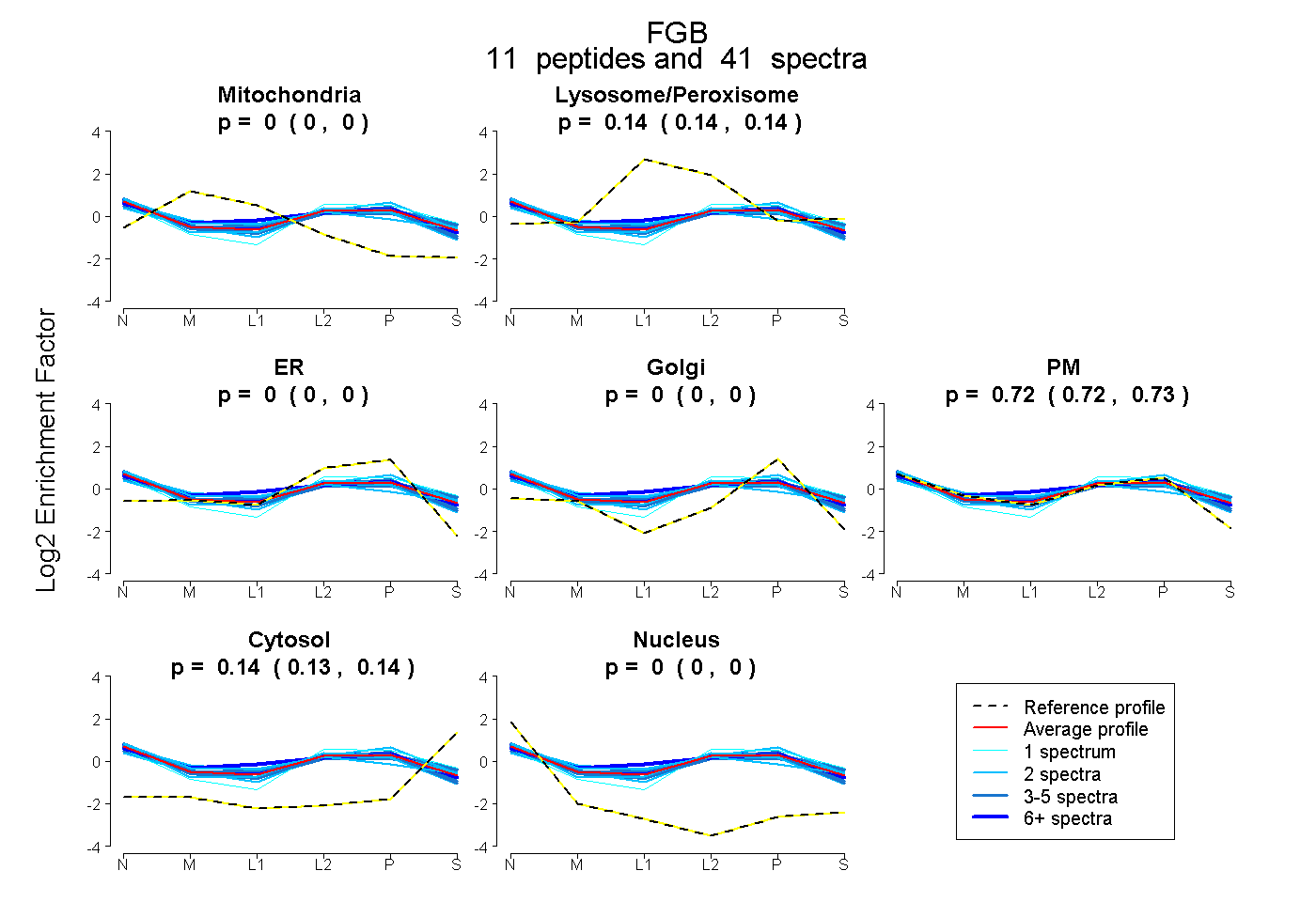 |
0.000 0.000 | 0.000 |
0.140 0.135 | 0.145 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.724 0.718 | 0.729 |
0.136 0.132 | 0.139 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
420 spectra |
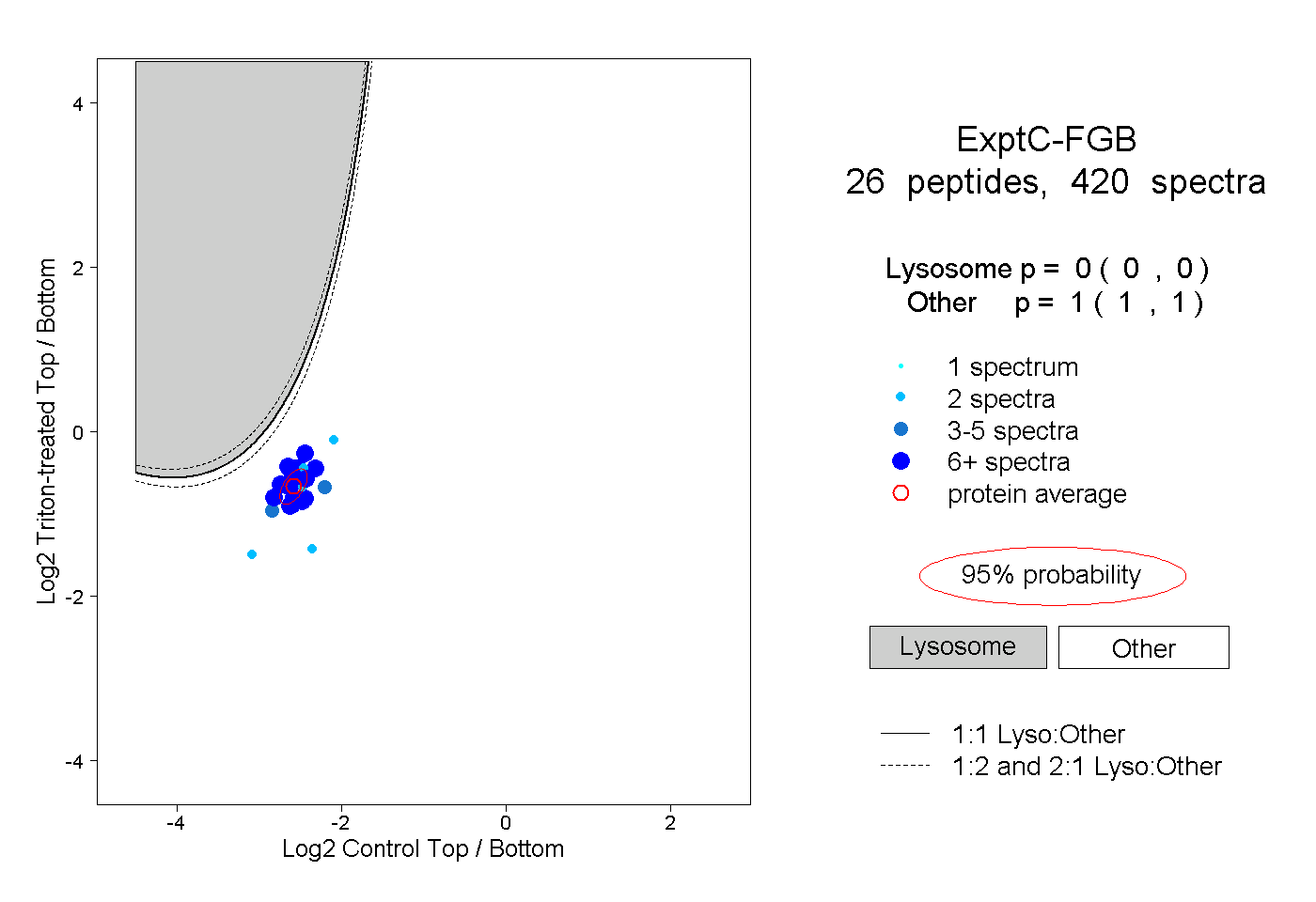 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
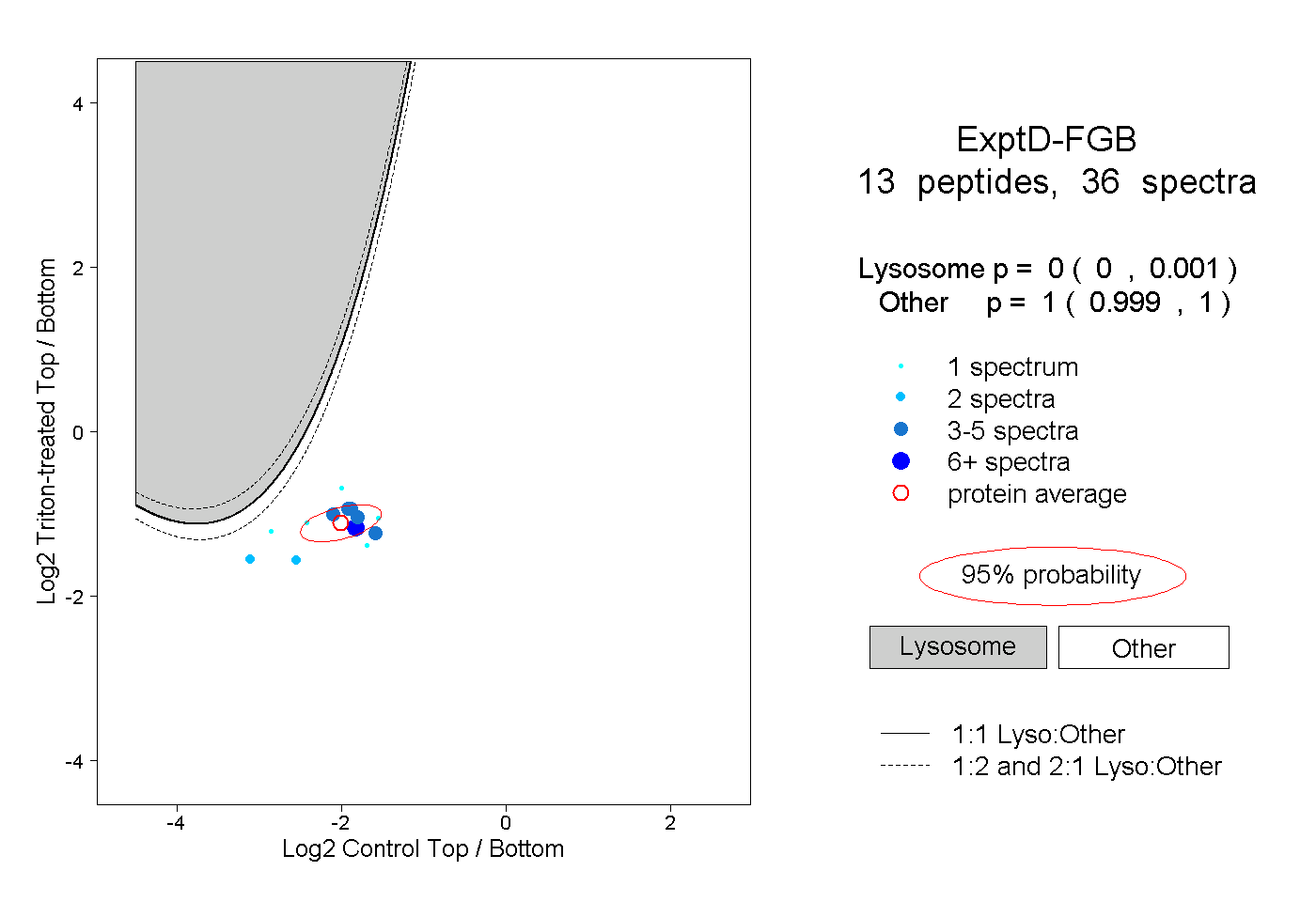 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |