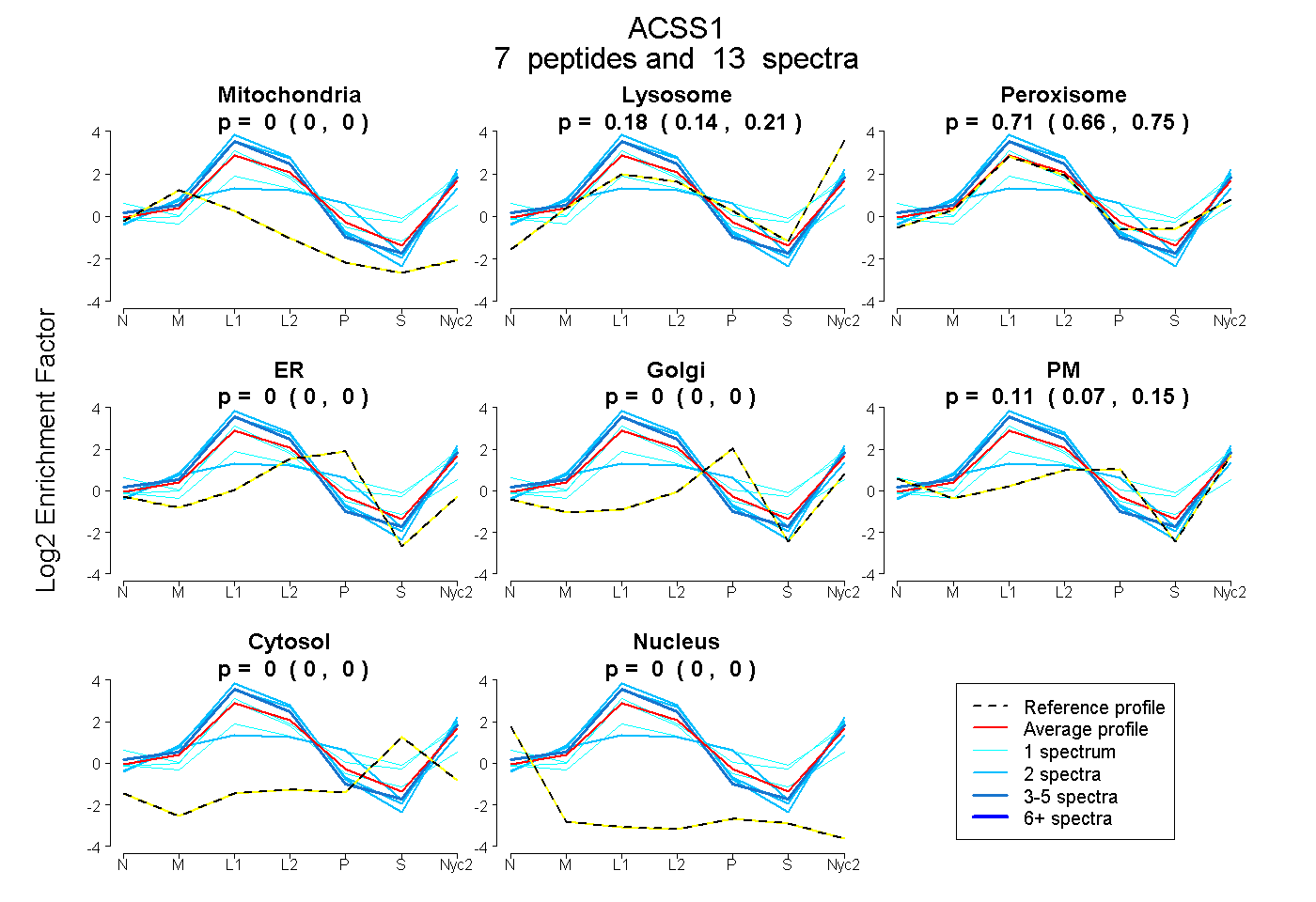
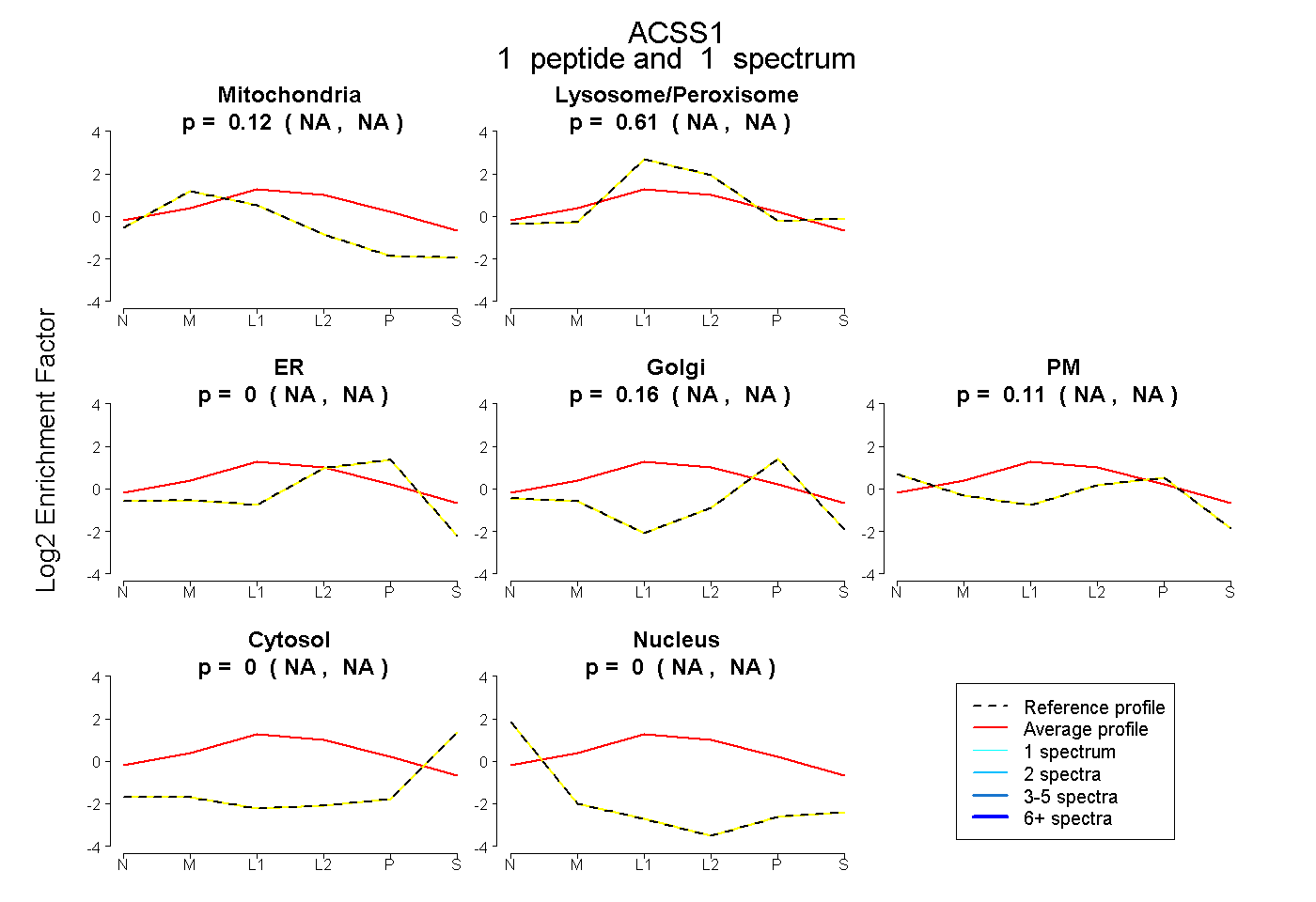
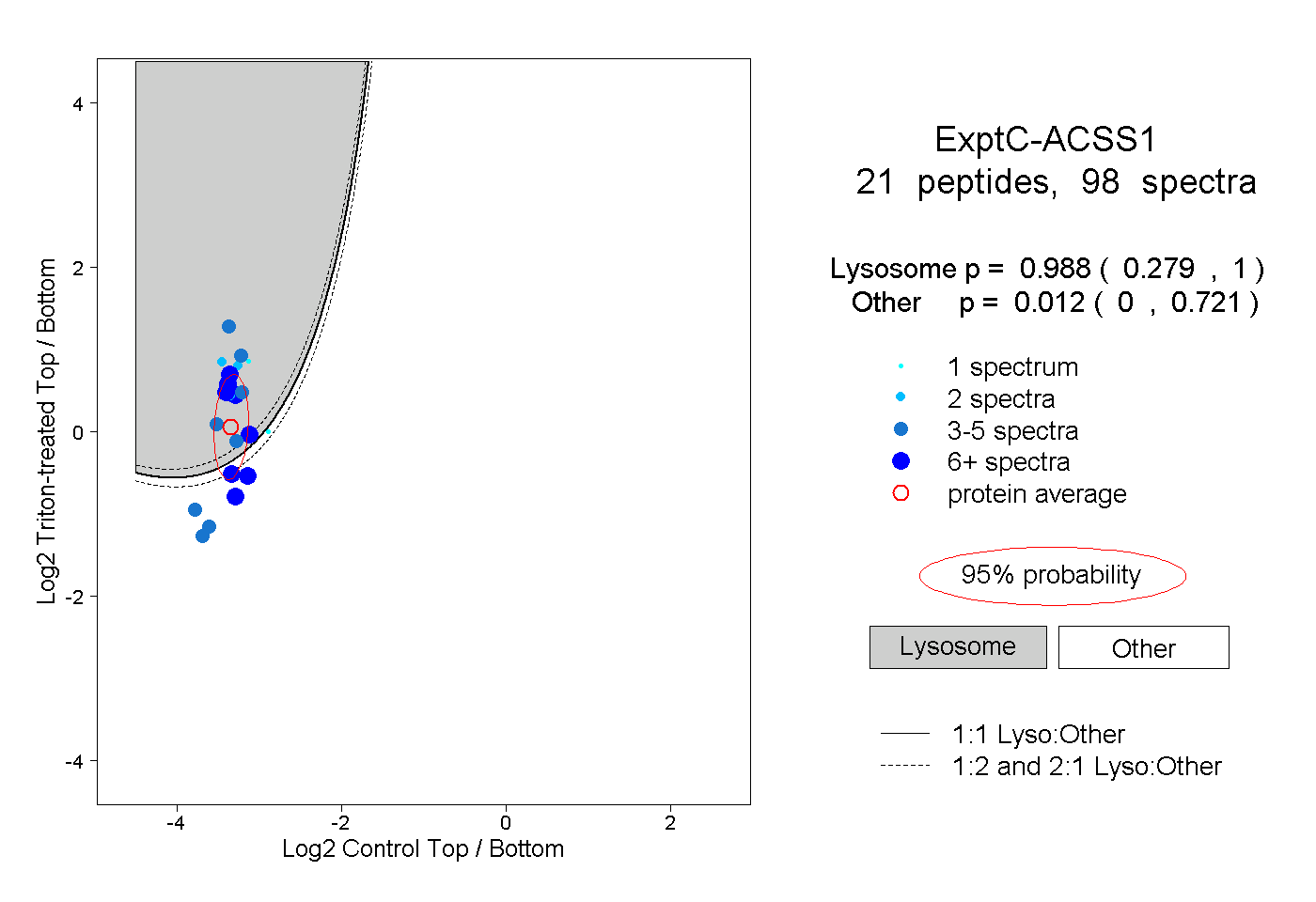
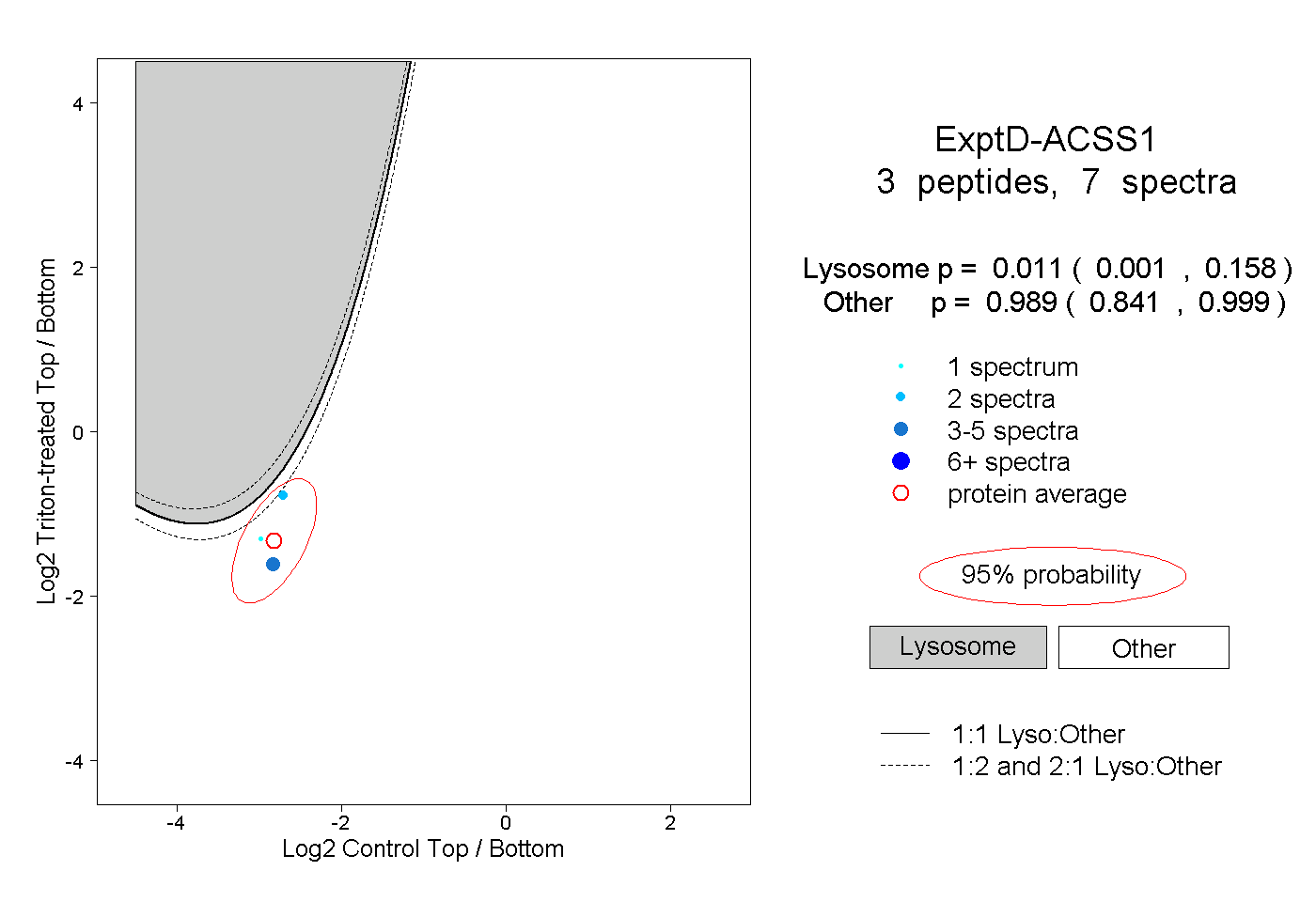
| 7 spectra, TEGGYYQITGR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, LAVATK |
|
0.039 |
|
|
|
|
|
|
|
0.961 |
| 1 spectrum, VVELK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, MDDVINISGHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, LANTLK |
|
0.153 |
|
|
|
|
|
|
|
0.847 |
| 6 spectra, ELLETTCR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, FGDAWVK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, VVITFNQGLR |
|
0.816 |
|
|
|
|
|
|
|
0.184 |
| 3 spectra, YWETVQR |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 4 spectra, TIYGDHQR |
|
0.007 |
|
|
|
|
|
|
|
0.993 |
| 2 spectra, VVGDGR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 8 spectra, TYPGYYFTGDGAHR |
|
0.008 |
|
|
|
|
|
|
|
0.992 |
| 2 spectra, IVDEAVK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 5 spectra, GLVHTQAGYLLYAAMTHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DEPGTEVR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 5 spectra, INQFYGAPTAVR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, TLGSVGEPINHEAWEWLHK |
|
0.359 |
|
|
|
|
|
|
|
0.641 |
| 5 spectra, YAVPDQILVVK |
|
0.893 |
|
|
|
|
|
|
|
0.107 |
| 2 spectra, DANVVVNELK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 12 spectra, FVDAYFR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, SPDTIALIWER |
|
0.998 |
|
|
|
|
|
|
|
0.002 |