peptides
spectra
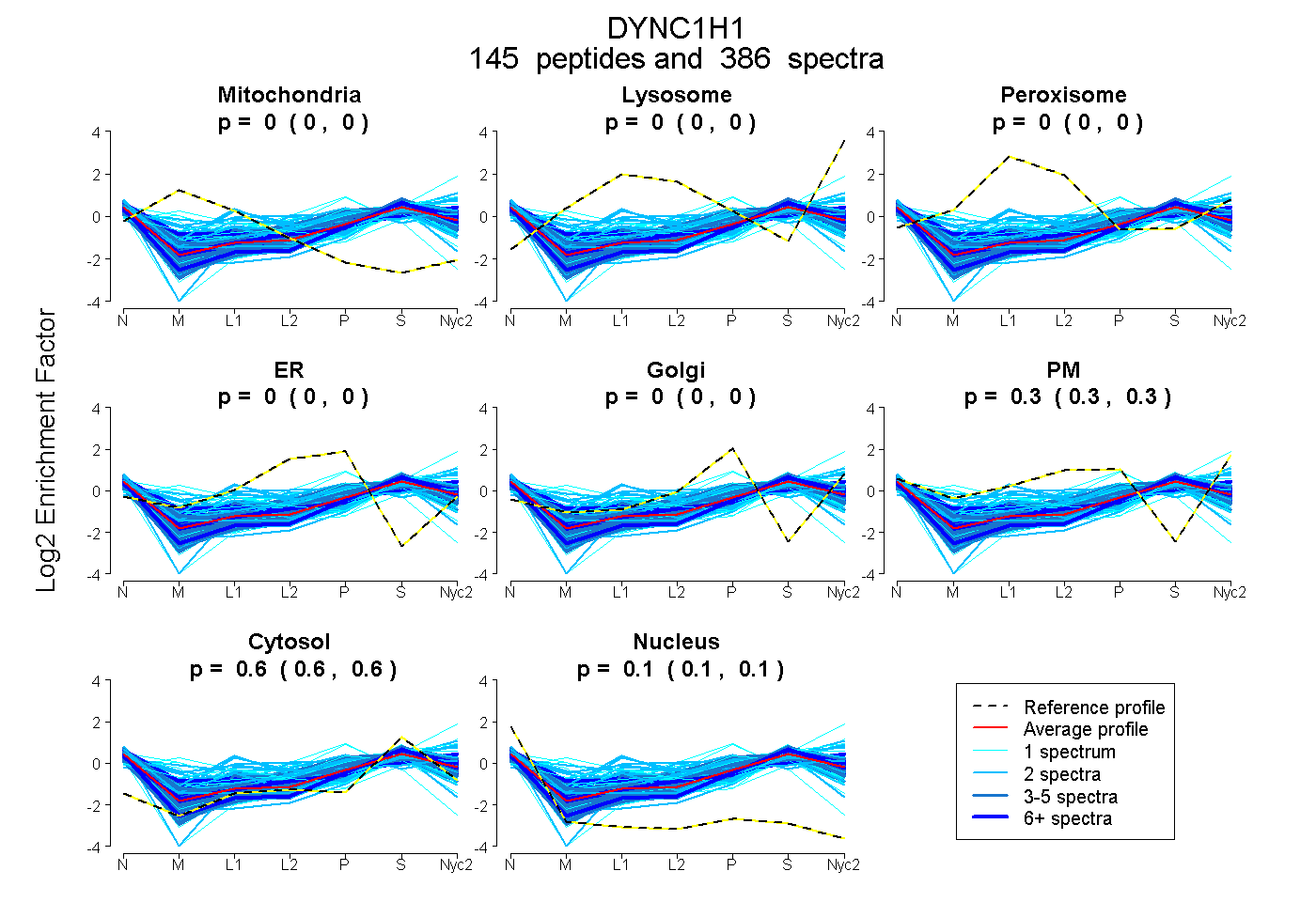
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.299 | 0.300
0.604 | 0.605
0.095 | 0.096
peptides
spectra
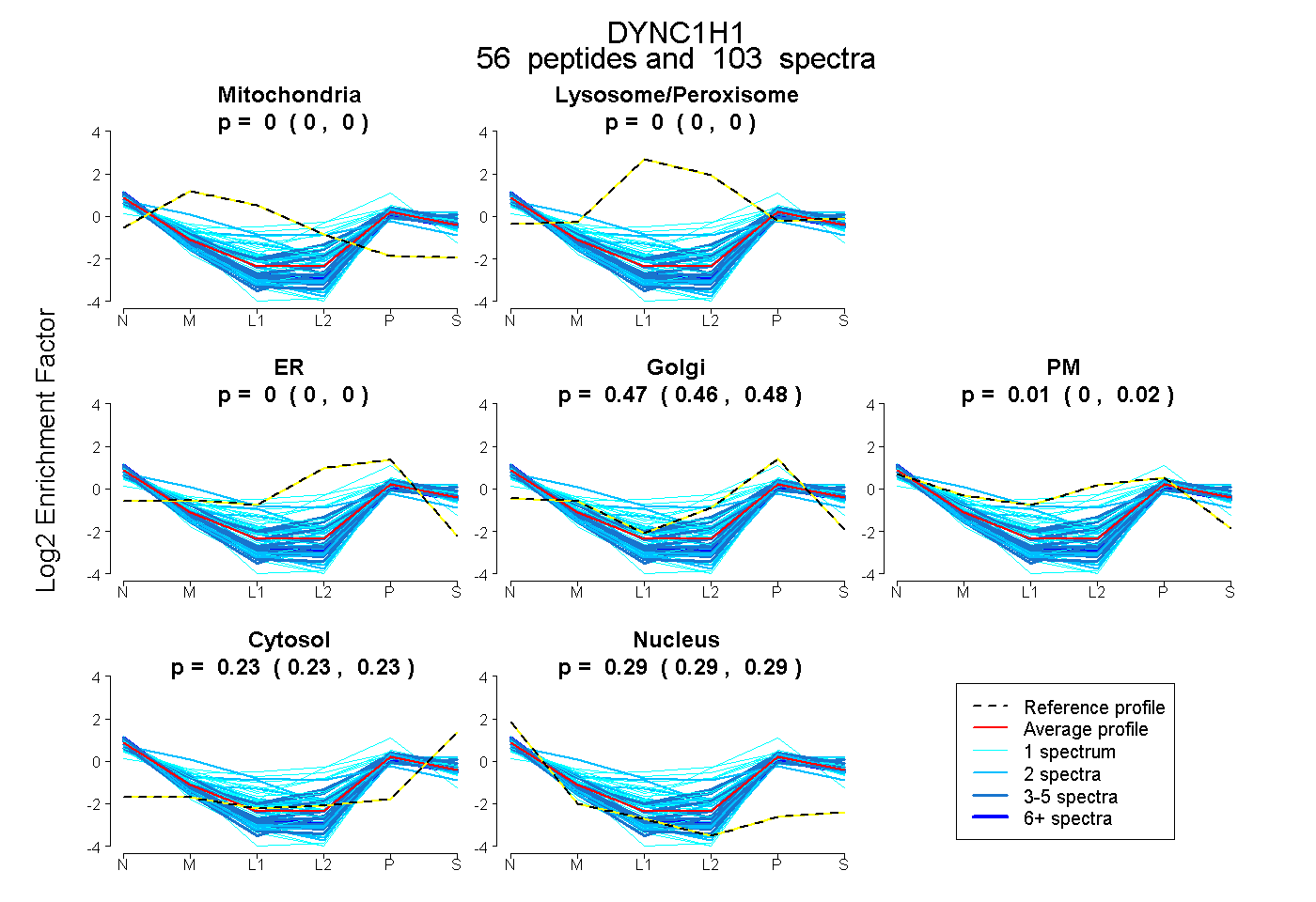
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.464 | 0.477
0.003 | 0.019
0.228 | 0.230
0.286 | 0.291
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
386 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.300 0.299 | 0.300 |
0.604 0.604 | 0.605 |
0.096 0.095 | 0.096 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
103 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.471 0.464 | 0.477 |
0.011 0.003 | 0.019 |
0.229 0.228 | 0.230 |
0.289 0.286 | 0.291 |
| 1 spectrum, SFDSEFK | 0.000 | 0.000 | 0.000 | 0.474 | 0.000 | 0.186 | 0.340 | |||
| 1 spectrum, NTISLLVAGLK | 0.000 | 0.000 | 0.000 | 0.419 | 0.017 | 0.330 | 0.235 | |||
| 1 spectrum, TPNGVVLAPVQLGK | 0.000 | 0.000 | 0.000 | 0.066 | 0.447 | 0.350 | 0.137 | |||
| 1 spectrum, GVWSELSK | 0.000 | 0.173 | 0.000 | 0.106 | 0.430 | 0.291 | 0.000 | |||
| 1 spectrum, SLLQALNEVK | 0.000 | 0.000 | 0.000 | 0.341 | 0.000 | 0.176 | 0.483 | |||
| 1 spectrum, LVEDEER | 0.000 | 0.000 | 0.000 | 0.475 | 0.445 | 0.071 | 0.008 | |||
| 1 spectrum, LDPYVQR | 0.000 | 0.016 | 0.000 | 0.169 | 0.416 | 0.261 | 0.138 | |||
| 1 spectrum, TLINELVK | 0.000 | 0.000 | 0.000 | 0.375 | 0.000 | 0.167 | 0.458 | |||
| 3 spectra, SIPLDEGEDEAQR | 0.000 | 0.000 | 0.000 | 0.429 | 0.000 | 0.214 | 0.357 | |||
| 1 spectrum, LADLLGK | 0.000 | 0.000 | 0.000 | 0.398 | 0.000 | 0.170 | 0.432 | |||
| 4 spectra, VPVNLLR | 0.000 | 0.000 | 0.000 | 0.368 | 0.000 | 0.202 | 0.429 | |||
| 1 spectrum, DYIPVDQEELR | 0.000 | 0.000 | 0.000 | 0.449 | 0.000 | 0.269 | 0.282 | |||
| 1 spectrum, IIDNVR | 0.000 | 0.000 | 0.000 | 0.297 | 0.276 | 0.224 | 0.202 | |||
| 4 spectra, YATLATVSR | 0.000 | 0.000 | 0.000 | 0.387 | 0.000 | 0.224 | 0.389 | |||
| 4 spectra, LVQTPLTDR | 0.000 | 0.000 | 0.000 | 0.398 | 0.000 | 0.182 | 0.420 | |||
| 1 spectrum, TSAPITCELLNK | 0.000 | 0.000 | 0.000 | 0.113 | 0.631 | 0.202 | 0.055 | |||
| 2 spectra, EWTDGLFTHVLR | 0.000 | 0.000 | 0.000 | 0.238 | 0.234 | 0.398 | 0.130 | |||
| 3 spectra, LAETVFNFQEK | 0.000 | 0.000 | 0.000 | 0.320 | 0.269 | 0.259 | 0.153 | |||
| 1 spectrum, LVEAISR | 0.000 | 0.000 | 0.000 | 0.407 | 0.104 | 0.165 | 0.325 | |||
| 1 spectrum, AERPDVDEK | 0.000 | 0.000 | 0.000 | 0.248 | 0.279 | 0.206 | 0.266 | |||
| 3 spectra, VLSFIR | 0.000 | 0.000 | 0.000 | 0.499 | 0.000 | 0.195 | 0.305 | |||
| 1 spectrum, VQYPQSQACK | 0.000 | 0.000 | 0.000 | 0.045 | 0.525 | 0.265 | 0.166 | |||
| 1 spectrum, ANEVEQMIR | 0.000 | 0.000 | 0.000 | 0.300 | 0.163 | 0.347 | 0.190 | |||
| 2 spectra, VQGLTVEQAEAVAR | 0.163 | 0.001 | 0.000 | 0.000 | 0.618 | 0.155 | 0.064 | |||
| 2 spectra, IFTIESAR | 0.000 | 0.000 | 0.000 | 0.402 | 0.000 | 0.203 | 0.395 | |||
| 3 spectra, TFSSIPVSR | 0.000 | 0.000 | 0.000 | 0.176 | 0.402 | 0.250 | 0.172 | |||
| 2 spectra, MIVLSLPR | 0.000 | 0.000 | 0.000 | 0.406 | 0.000 | 0.227 | 0.367 | |||
| 1 spectrum, FNYGFEYLGVQDK | 0.000 | 0.000 | 0.000 | 0.314 | 0.210 | 0.252 | 0.224 | |||
| 2 spectra, FQSISTEFLALMK | 0.000 | 0.000 | 0.000 | 0.443 | 0.000 | 0.253 | 0.304 | |||
| 2 spectra, IDLEVR | 0.000 | 0.000 | 0.000 | 0.447 | 0.000 | 0.187 | 0.366 | |||
| 1 spectrum, INEWLTLVEK | 0.000 | 0.000 | 0.000 | 0.357 | 0.000 | 0.283 | 0.360 | |||
| 1 spectrum, GWENHVEGQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.654 | 0.346 | 0.000 | |||
| 3 spectra, VDDLLIIEEK | 0.000 | 0.000 | 0.000 | 0.420 | 0.000 | 0.282 | 0.298 | |||
| 1 spectrum, LLAESVTEVEIFGK | 0.000 | 0.000 | 0.000 | 0.318 | 0.000 | 0.188 | 0.494 | |||
| 2 spectra, ALGHQLGR | 0.000 | 0.159 | 0.000 | 0.277 | 0.149 | 0.140 | 0.275 | |||
| 1 spectrum, AINTAVK | 0.000 | 0.000 | 0.000 | 0.013 | 0.755 | 0.210 | 0.021 | |||
| 2 spectra, NLESALR | 0.000 | 0.000 | 0.000 | 0.276 | 0.000 | 0.292 | 0.431 | |||
| 2 spectra, FNALFVRPHIR | 0.000 | 0.000 | 0.000 | 0.247 | 0.293 | 0.258 | 0.202 | |||
| 4 spectra, EAAEVTR | 0.000 | 0.000 | 0.000 | 0.402 | 0.052 | 0.219 | 0.327 | |||
| 1 spectrum, GIFEALRPLETLPVEGLIR | 0.000 | 0.000 | 0.000 | 0.299 | 0.000 | 0.206 | 0.495 | |||
| 2 spectra, DLEASIAR | 0.000 | 0.000 | 0.000 | 0.470 | 0.000 | 0.189 | 0.340 | |||
| 2 spectra, NVVHELR | 0.000 | 0.000 | 0.000 | 0.543 | 0.000 | 0.229 | 0.228 | |||
| 2 spectra, AATSPALFNR | 0.000 | 0.000 | 0.000 | 0.282 | 0.232 | 0.301 | 0.185 | |||
| 1 spectrum, LSLPPNVR | 0.000 | 0.000 | 0.000 | 0.389 | 0.160 | 0.193 | 0.258 | |||
| 2 spectra, VTFVNFTVTR | 0.000 | 0.000 | 0.000 | 0.408 | 0.000 | 0.180 | 0.412 | |||
| 2 spectra, EYQTQLIQR | 0.000 | 0.000 | 0.000 | 0.375 | 0.171 | 0.212 | 0.242 | |||
| 6 spectra, LLNTFLER | 0.000 | 0.000 | 0.000 | 0.390 | 0.000 | 0.203 | 0.407 | |||
| 2 spectra, VDNEFDQR | 0.000 | 0.000 | 0.000 | 0.366 | 0.000 | 0.171 | 0.463 | |||
| 1 spectrum, QDLADVVQVCEGK | 0.000 | 0.000 | 0.000 | 0.224 | 0.356 | 0.285 | 0.136 | |||
| 1 spectrum, FTQDTQPHYIYSPR | 0.000 | 0.151 | 0.000 | 0.000 | 0.632 | 0.217 | 0.000 | |||
| 1 spectrum, WFTSQVIR | 0.000 | 0.000 | 0.000 | 0.364 | 0.040 | 0.245 | 0.351 | |||
| 2 spectra, VQVALEELQDLK | 0.000 | 0.000 | 0.000 | 0.397 | 0.000 | 0.215 | 0.388 | |||
| 1 spectrum, TLMAQSIYGGR | 0.000 | 0.000 | 0.000 | 0.370 | 0.000 | 0.359 | 0.272 | |||
| 2 spectra, ALGEYLER | 0.000 | 0.000 | 0.000 | 0.454 | 0.000 | 0.192 | 0.353 | |||
| 2 spectra, DLFQVAFNR | 0.000 | 0.002 | 0.000 | 0.069 | 0.488 | 0.243 | 0.198 | |||
| 3 spectra, TMTLFSALR | 0.000 | 0.000 | 0.000 | 0.294 | 0.165 | 0.366 | 0.175 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
306 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
35 spectra |
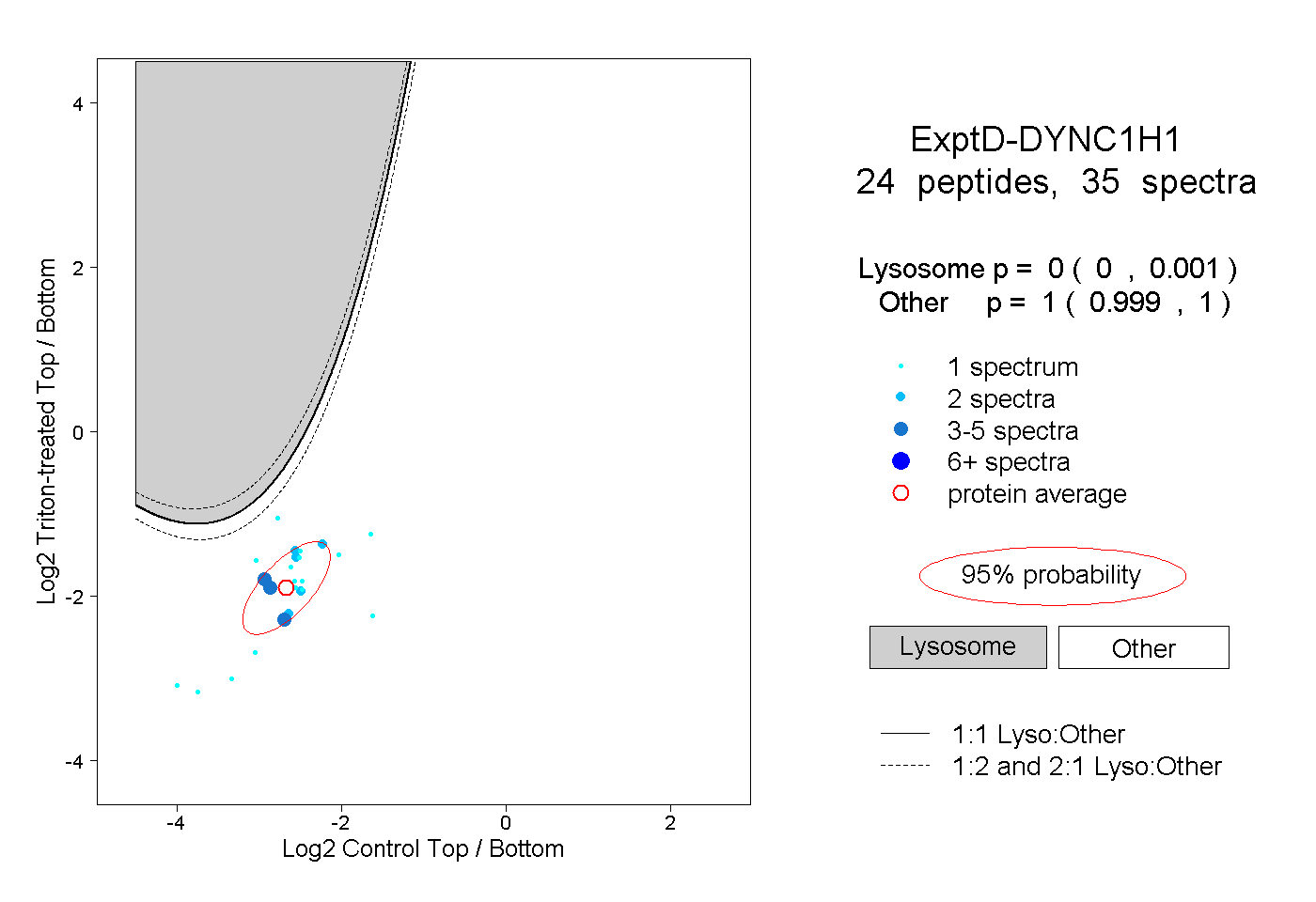 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |