peptides
spectra
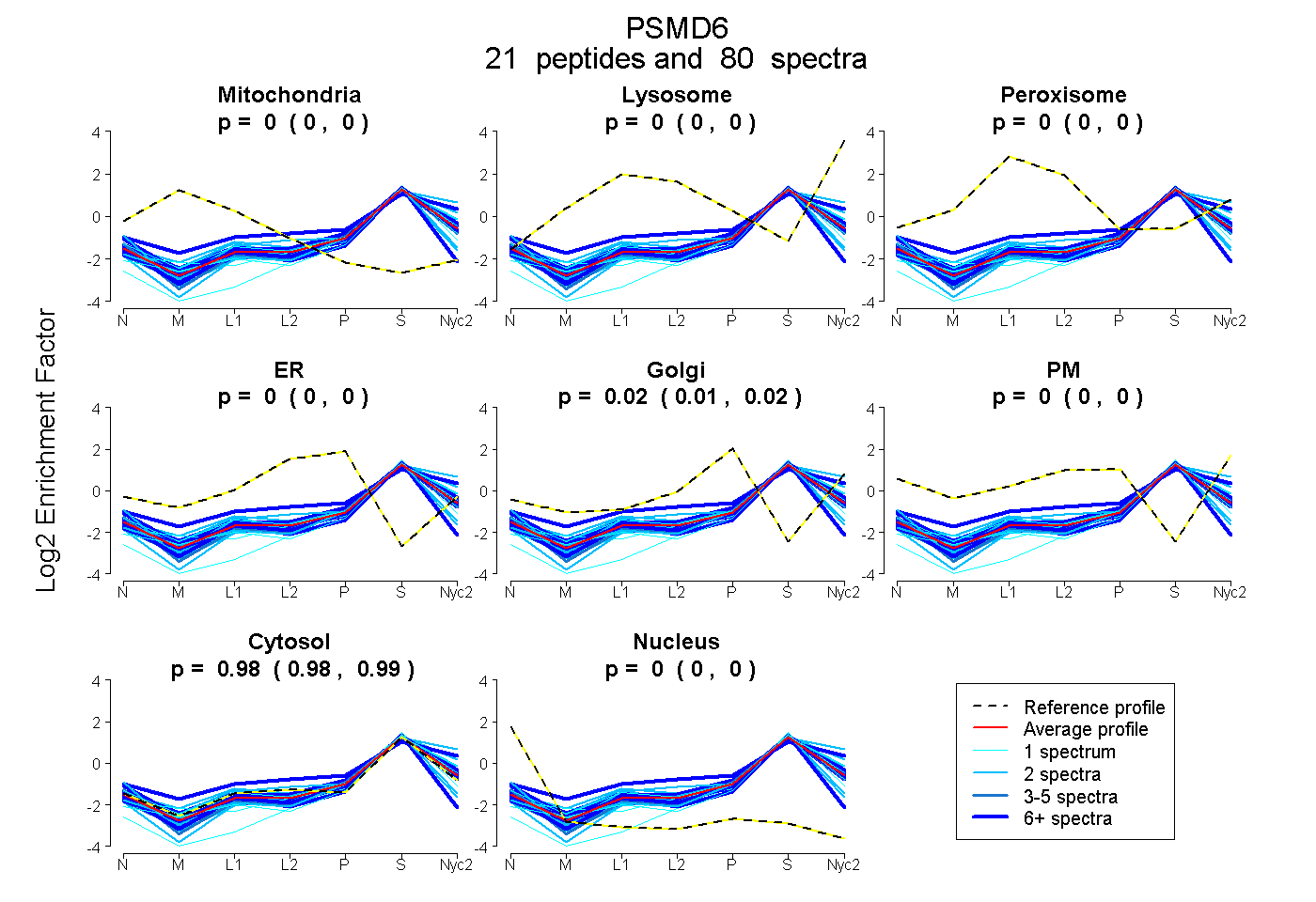
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.014 | 0.018
0.000 | 0.000
0.981 | 0.986
0.000 | 0.000
peptides
spectra
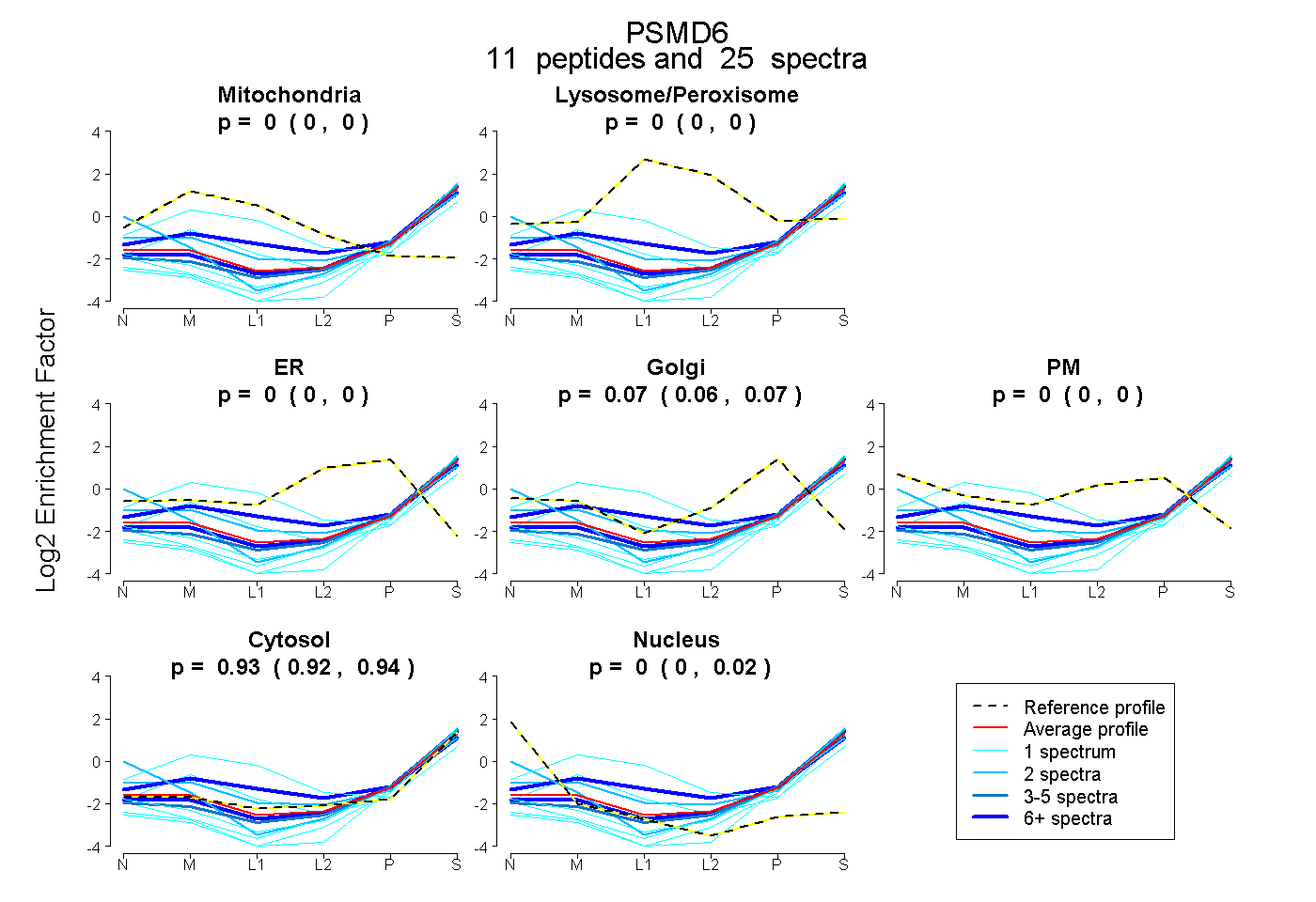
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.056 | 0.073
0.000 | 0.000
0.919 | 0.938
0.000 | 0.015
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
80 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.016 0.014 | 0.018 |
0.000 0.000 | 0.000 |
0.984 0.981 | 0.986 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.066 0.056 | 0.073 |
0.000 0.000 | 0.000 |
0.930 0.919 | 0.938 |
0.003 0.000 | 0.015 |
| 1 spectrum, FIAAGR | 0.128 | 0.000 | 0.000 | 0.000 | 0.000 | 0.872 | 0.000 | |||
| 1 spectrum, SLIEEGGDWDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | |||
| 6 spectra, GAEILEVLHSLPAVR | 0.099 | 0.111 | 0.000 | 0.040 | 0.000 | 0.750 | 0.000 | |||
| 2 spectra, DWLFAPHYR | 0.049 | 0.000 | 0.000 | 0.000 | 0.102 | 0.845 | 0.004 | |||
| 3 spectra, NLGESEIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, GDLLLNR | 0.000 | 0.000 | 0.000 | 0.053 | 0.000 | 0.701 | 0.246 | |||
| 1 spectrum, PLENLEEEGLPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 6 spectra, FLLSLPEHR | 0.000 | 0.000 | 0.000 | 0.036 | 0.000 | 0.964 | 0.000 | |||
| 1 spectrum, IGLFYMDNDLITR | 0.381 | 0.134 | 0.000 | 0.000 | 0.000 | 0.485 | 0.000 | |||
| 1 spectrum, EGALTAFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.999 | 0.001 | |||
| 1 spectrum, LDEELEDAEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
47 spectra |
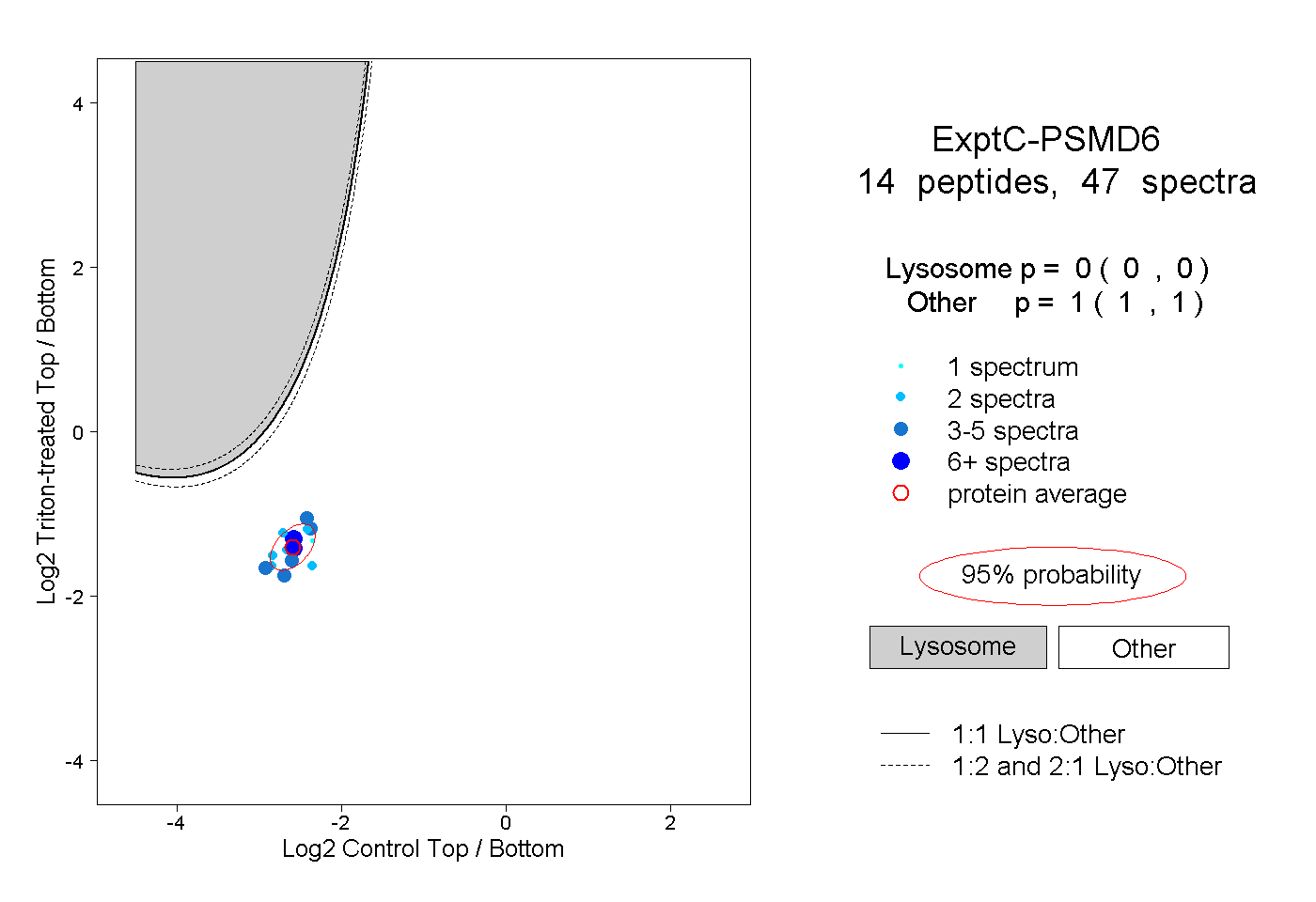 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
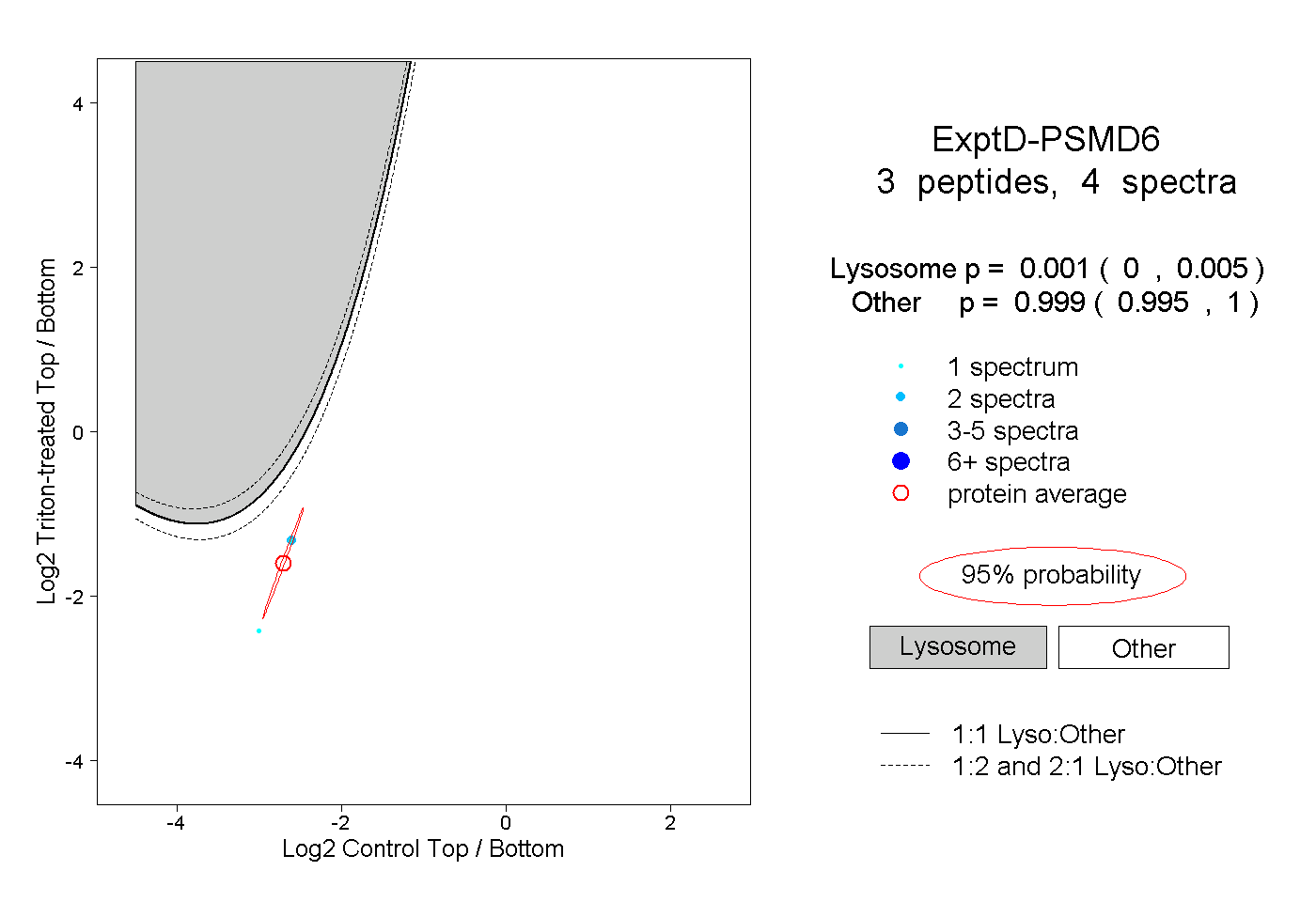 |
0.001 0.000 | 0.005 |
0.999 0.995 | 1.000 |