peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.097 | 0.134
0.000 | 0.019
0.000 | 0.000
0.727 | 0.745
0.126 | 0.148
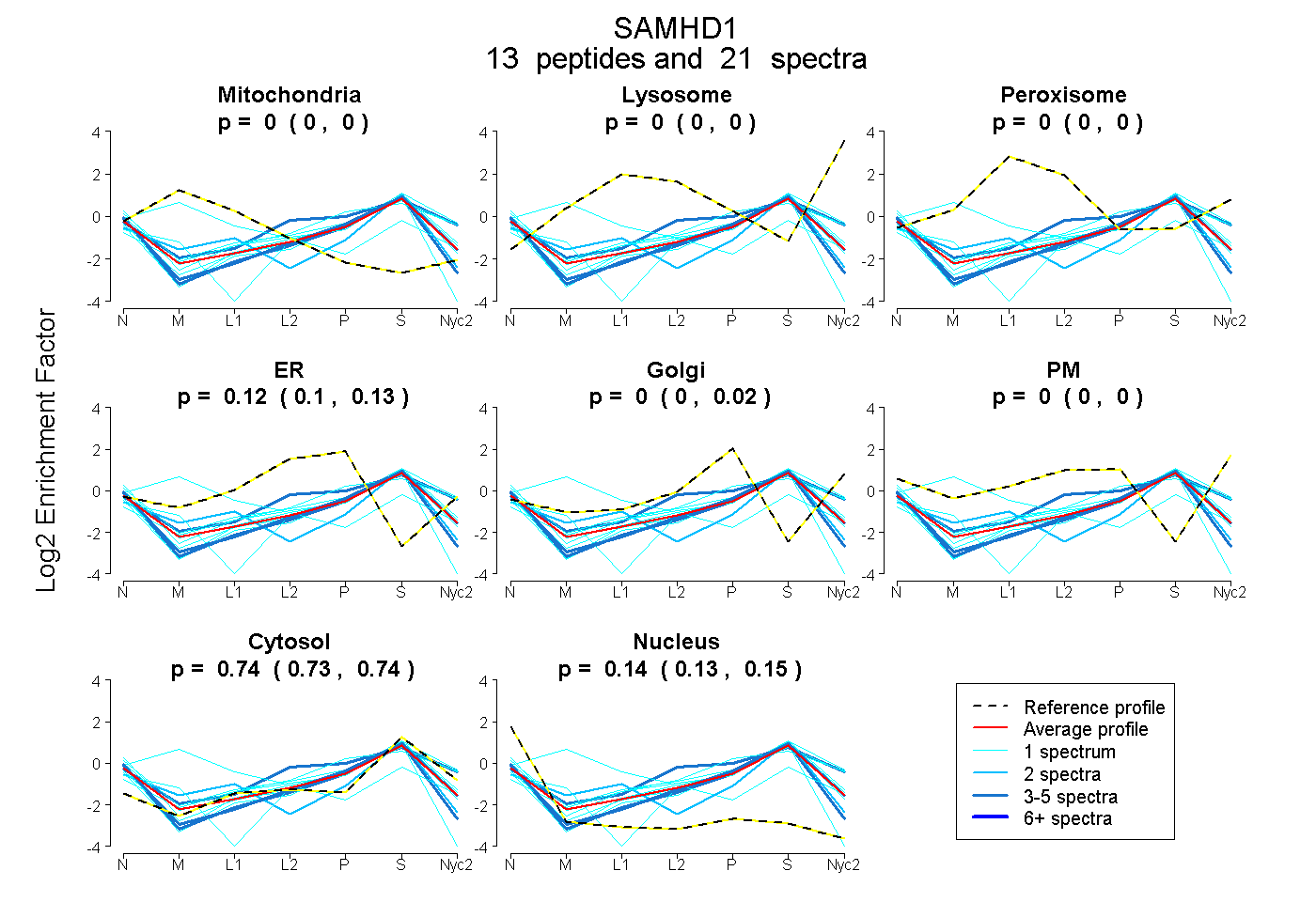
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.125 0.097 | 0.134 |
0.000 0.000 | 0.019 |
0.000 0.000 | 0.000 |
0.737 0.727 | 0.745 |
0.138 0.126 | 0.148 |
| 1 spectrum, TWGPEDVCSFLEK | 0.000 | 0.000 | 0.000 | 0.014 | 0.000 | 0.000 | 0.632 | 0.354 | ||
| 3 spectra, HFIQWCALR | 0.000 | 0.000 | 0.000 | 0.137 | 0.032 | 0.135 | 0.696 | 0.000 | ||
| 1 spectrum, DCLWPYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 | 0.779 | 0.176 | ||
| 1 spectrum, SFLYEIVANK | 0.000 | 0.000 | 0.000 | 0.050 | 0.036 | 0.000 | 0.802 | 0.113 | ||
| 1 spectrum, MIECIQK | 0.581 | 0.000 | 0.054 | 0.000 | 0.000 | 0.000 | 0.365 | 0.000 | ||
| 1 spectrum, SLDAAGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.047 | 0.120 | 0.833 | 0.000 | ||
| 1 spectrum, QPELQISER | 0.000 | 0.000 | 0.000 | 0.000 | 0.223 | 0.094 | 0.634 | 0.049 | ||
| 1 spectrum, EQIMGPPVSPVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.078 | 0.000 | 0.826 | 0.096 | ||
| 4 spectra, ICEVDDETR | 0.000 | 0.000 | 0.000 | 0.019 | 0.000 | 0.000 | 0.724 | 0.257 | ||
| 3 spectra, VLDIFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.088 | 0.000 | 0.746 | 0.166 | ||
| 1 spectrum, IIDTPQFQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.254 | 0.694 | 0.052 | ||
| 2 spectra, QLGGGYYVFPGASHNR | 0.133 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.721 | 0.145 | ||
| 1 spectrum, ADPHVEITGTEGK | 0.000 | 0.000 | 0.000 | 0.133 | 0.000 | 0.000 | 0.721 | 0.146 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
7 spectra |
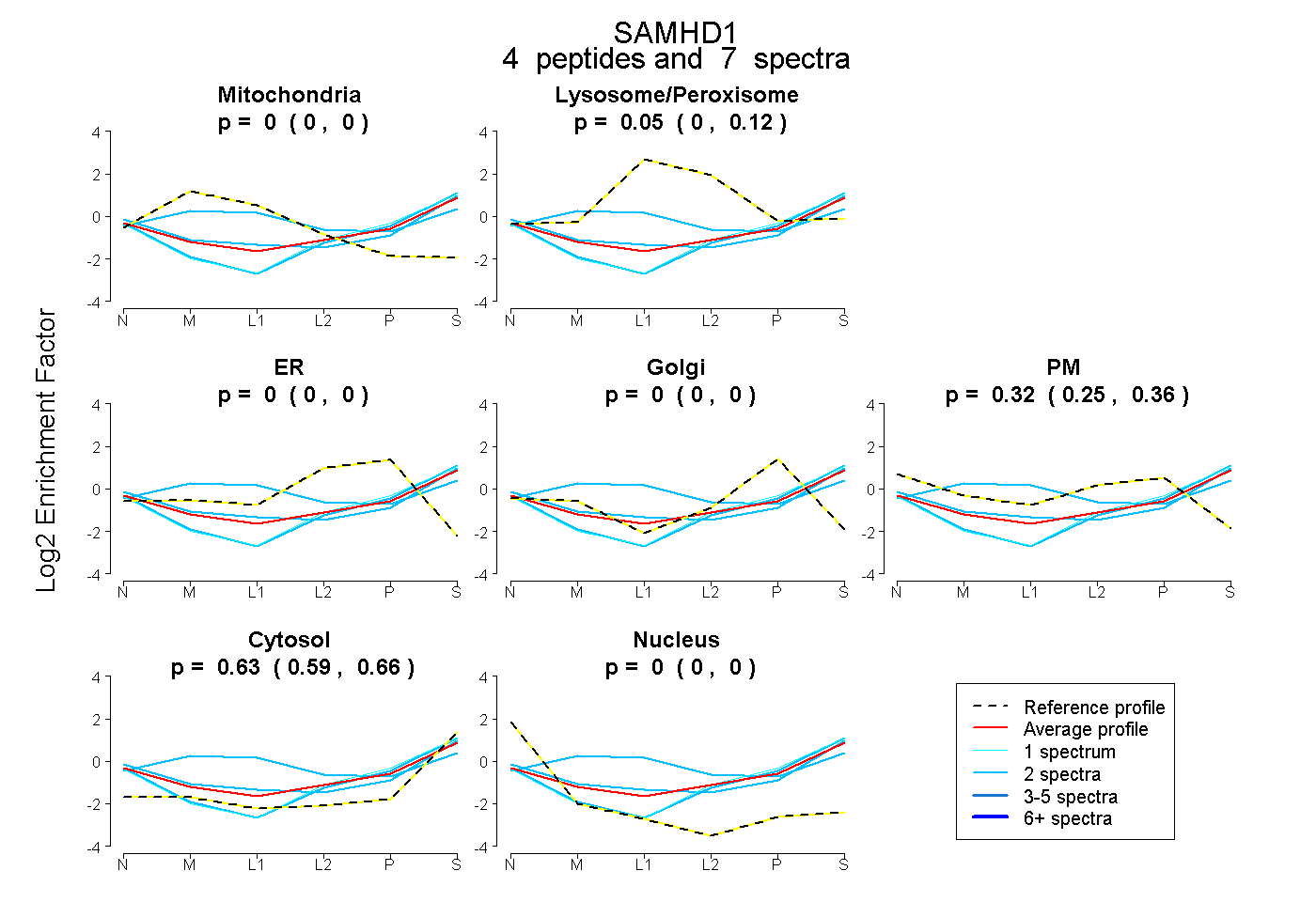 |
0.000 0.000 | 0.000 |
0.048 0.000 | 0.125 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.324 0.252 | 0.364 |
0.628 0.587 | 0.655 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
21 spectra |
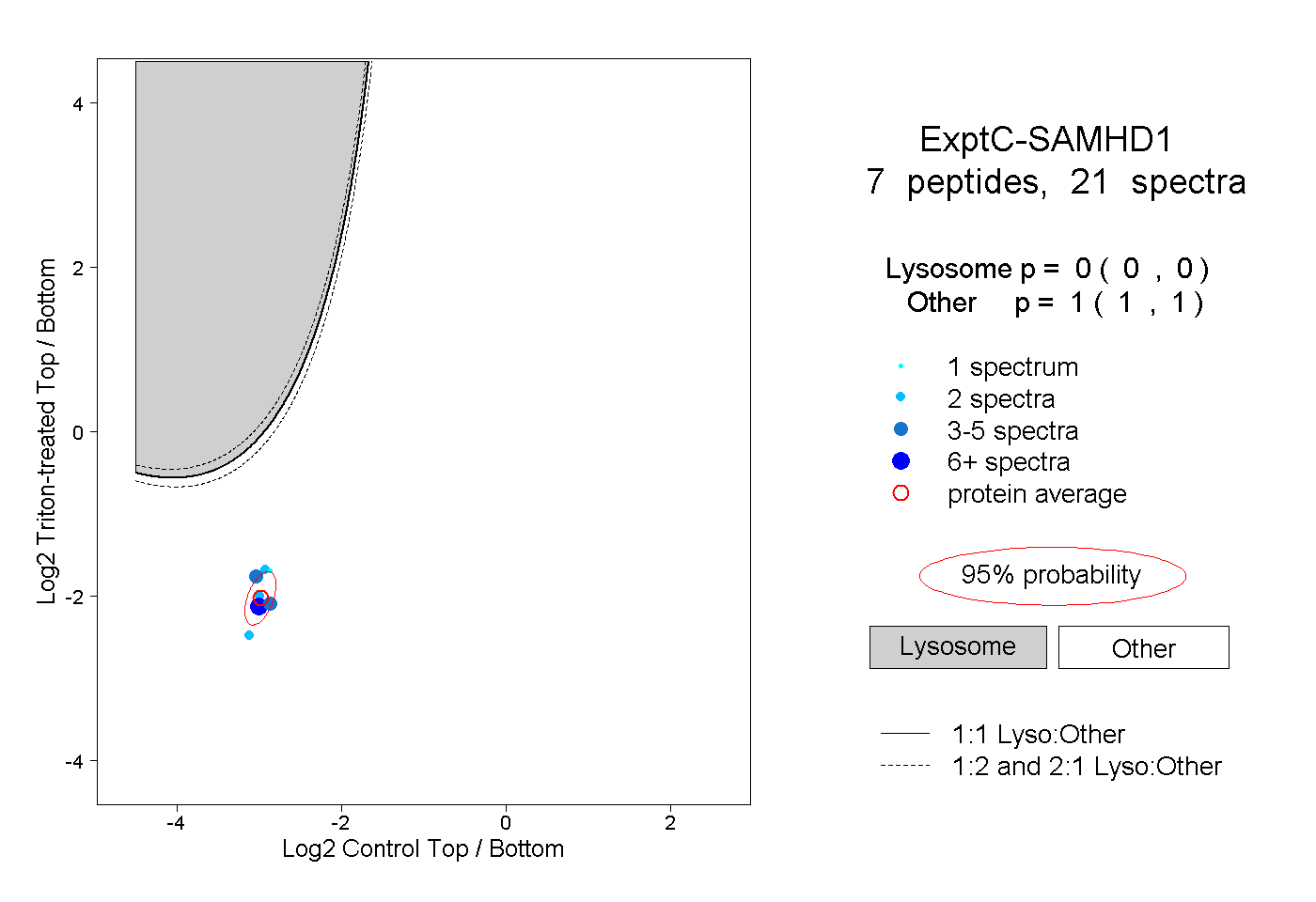 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
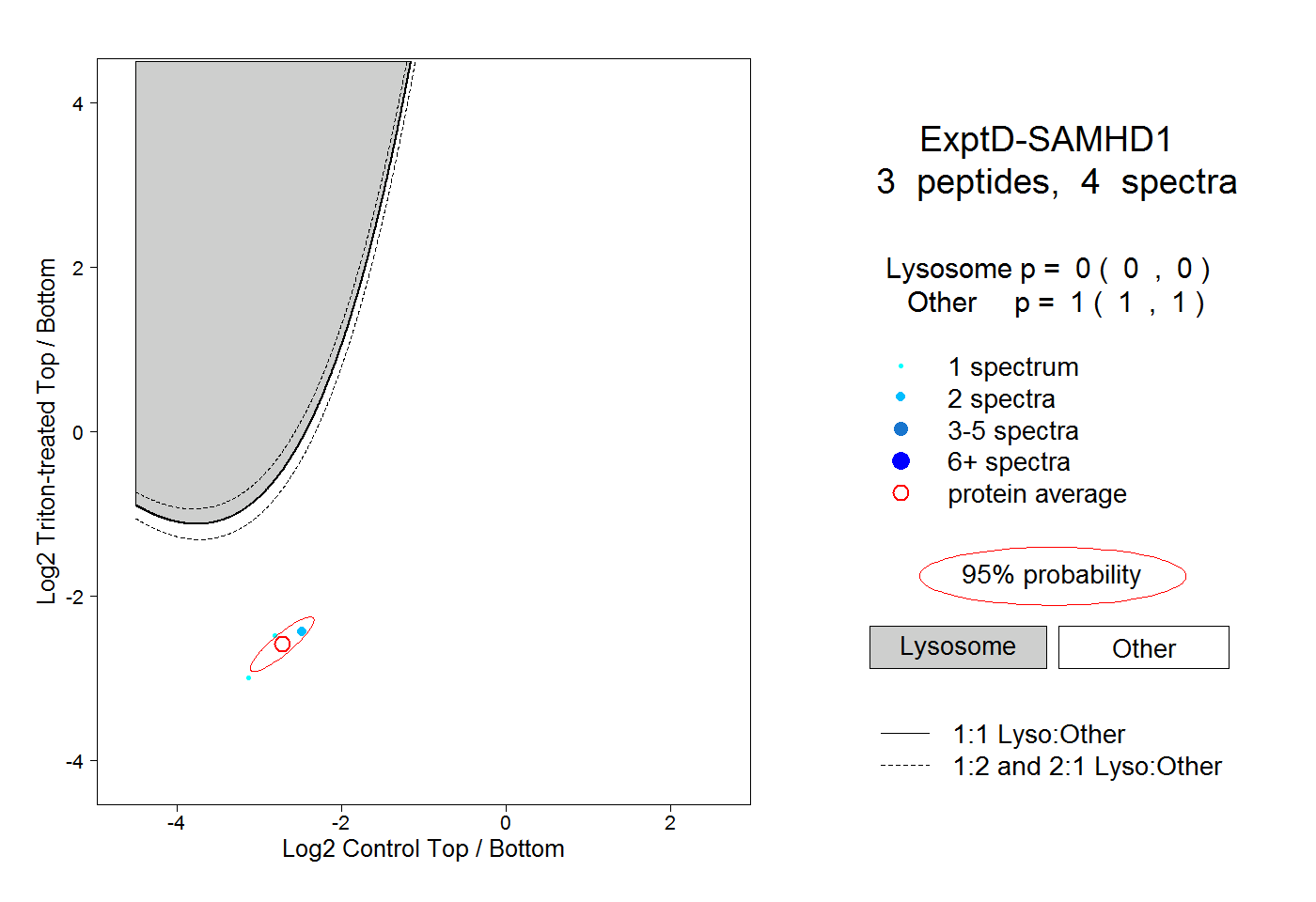 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |