peptides
spectra
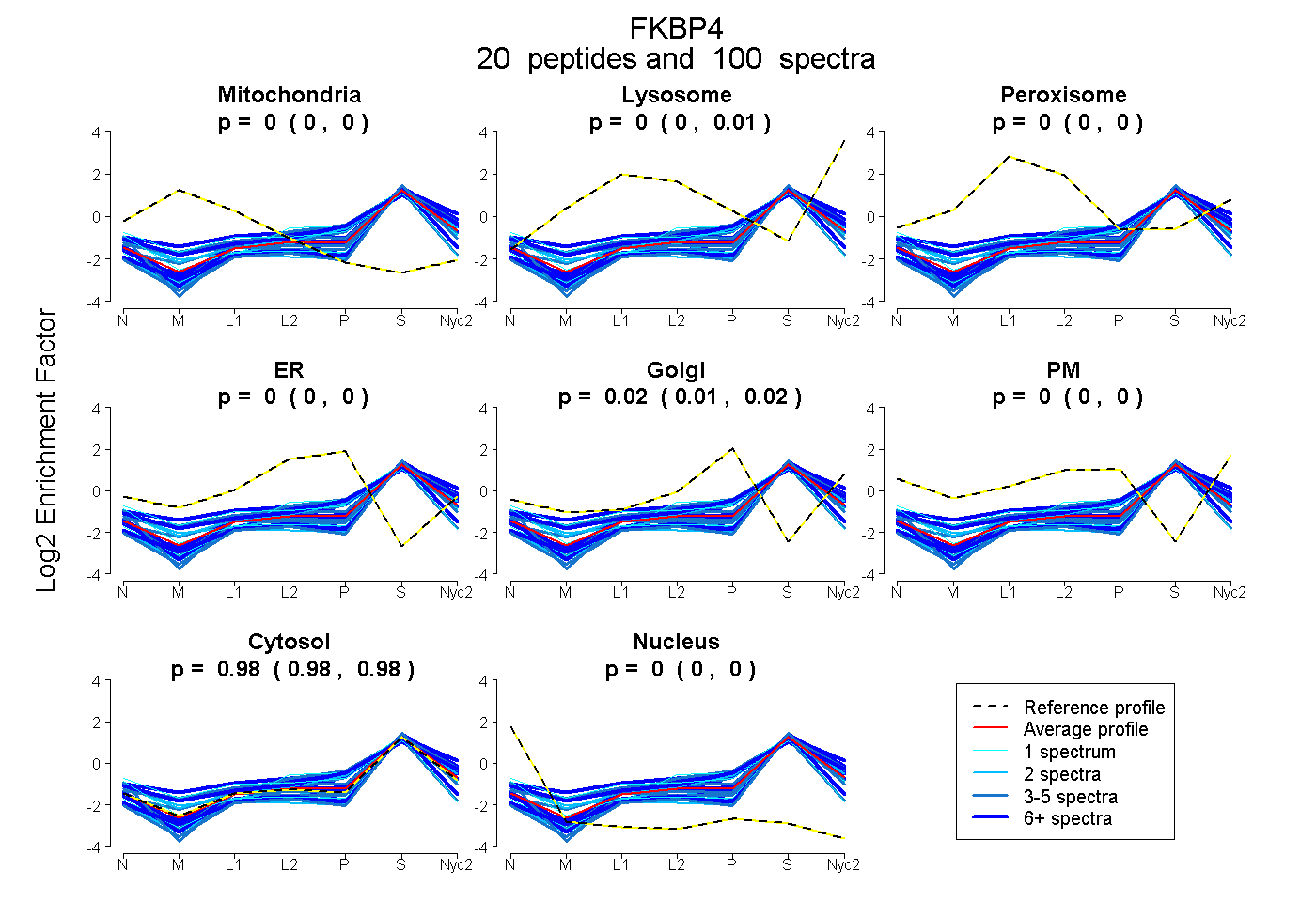
0.000 | 0.000
0.000 | 0.008
0.000 | 0.000
0.000 | 0.000
0.012 | 0.020
0.000 | 0.000
0.976 | 0.982
0.000 | 0.000
peptides
spectra
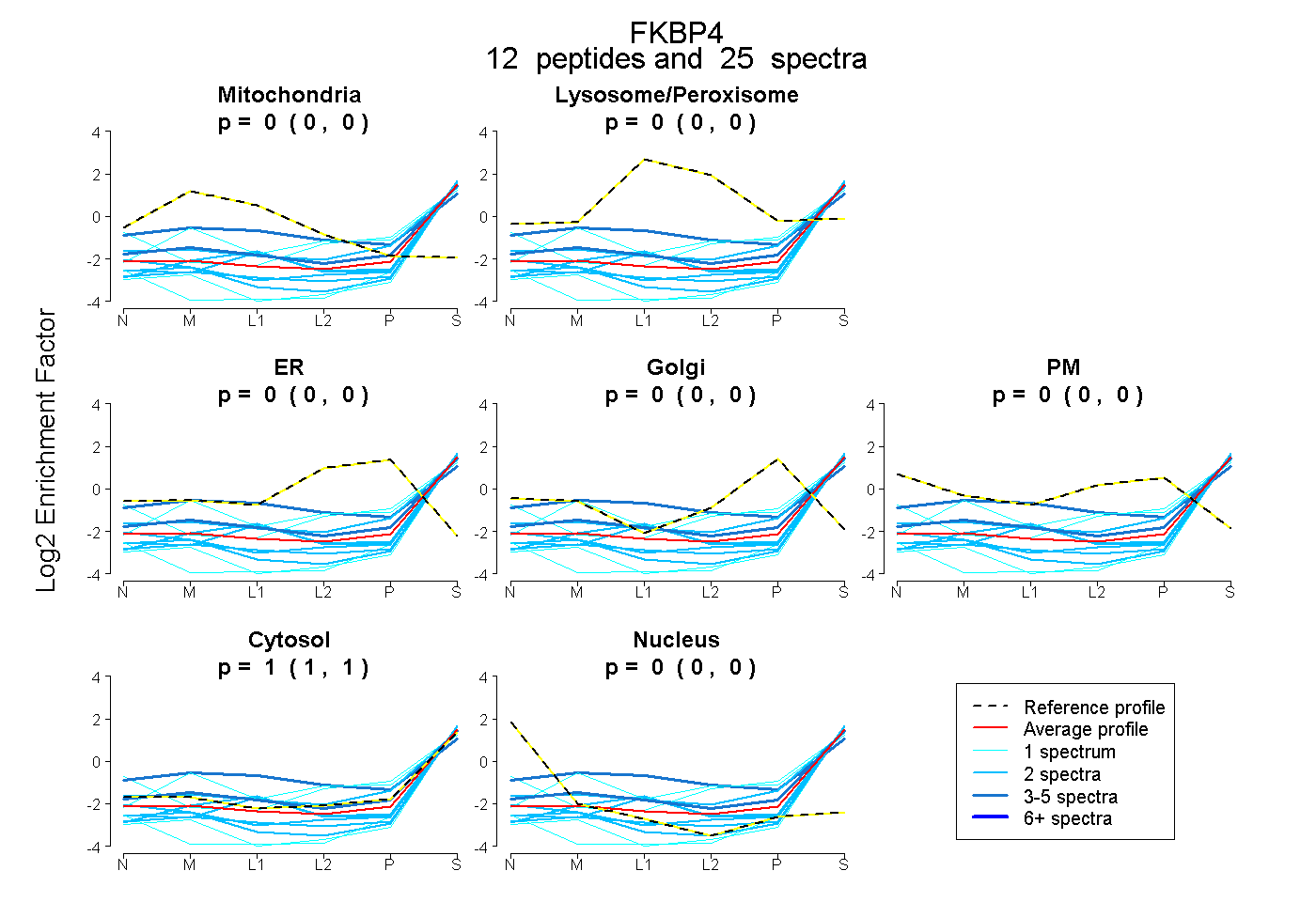
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
100 spectra |
 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.008 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.017 0.012 | 0.020 |
0.000 0.000 | 0.000 |
0.979 0.976 | 0.982 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, LAEEEHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.979 | 0.021 | |||
| 1 spectrum, TQLAVCQQR | 0.031 | 0.087 | 0.087 | 0.000 | 0.000 | 0.795 | 0.000 | |||
| 2 spectra, LASHLNLAMCHLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, IVSWLEYESSFSGEEMQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, FDSSLDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, GEAHLAVNDFDLAR | 0.000 | 0.050 | 0.000 | 0.019 | 0.000 | 0.931 | 0.000 | |||
| 5 spectra, YEVHLK | 0.034 | 0.012 | 0.000 | 0.000 | 0.000 | 0.954 | 0.000 | |||
| 1 spectrum, EGTGTETAMIGDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, LQAFSAAIESCNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.004 | |||
| 1 spectrum, AWDIAVATMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.174 | 0.826 | 0.000 | |||
| 4 spectra, FQIPPHAELR | 0.132 | 0.236 | 0.000 | 0.000 | 0.000 | 0.632 | 0.000 | |||
| 2 spectra, LYANMFER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
80 spectra |
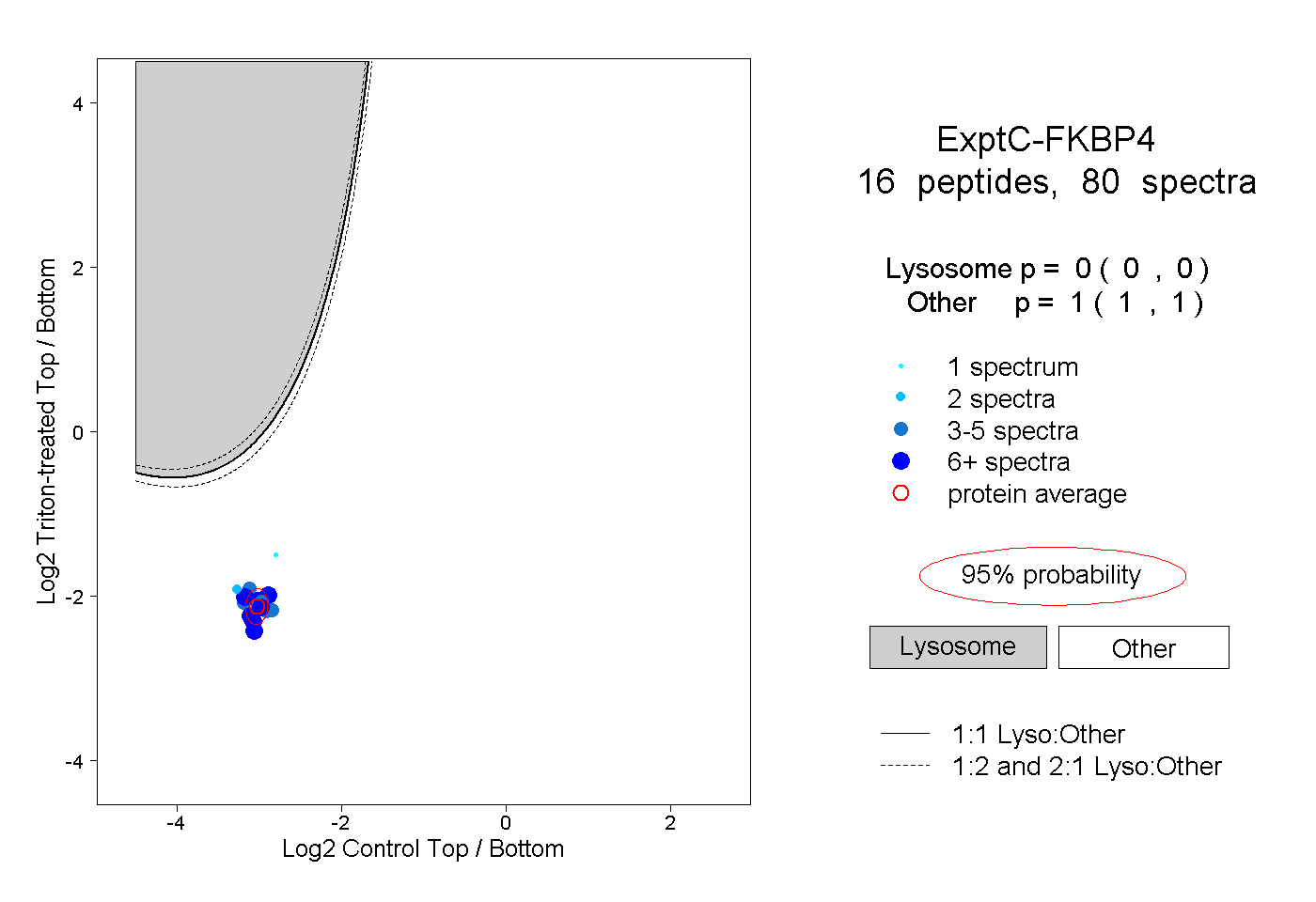 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
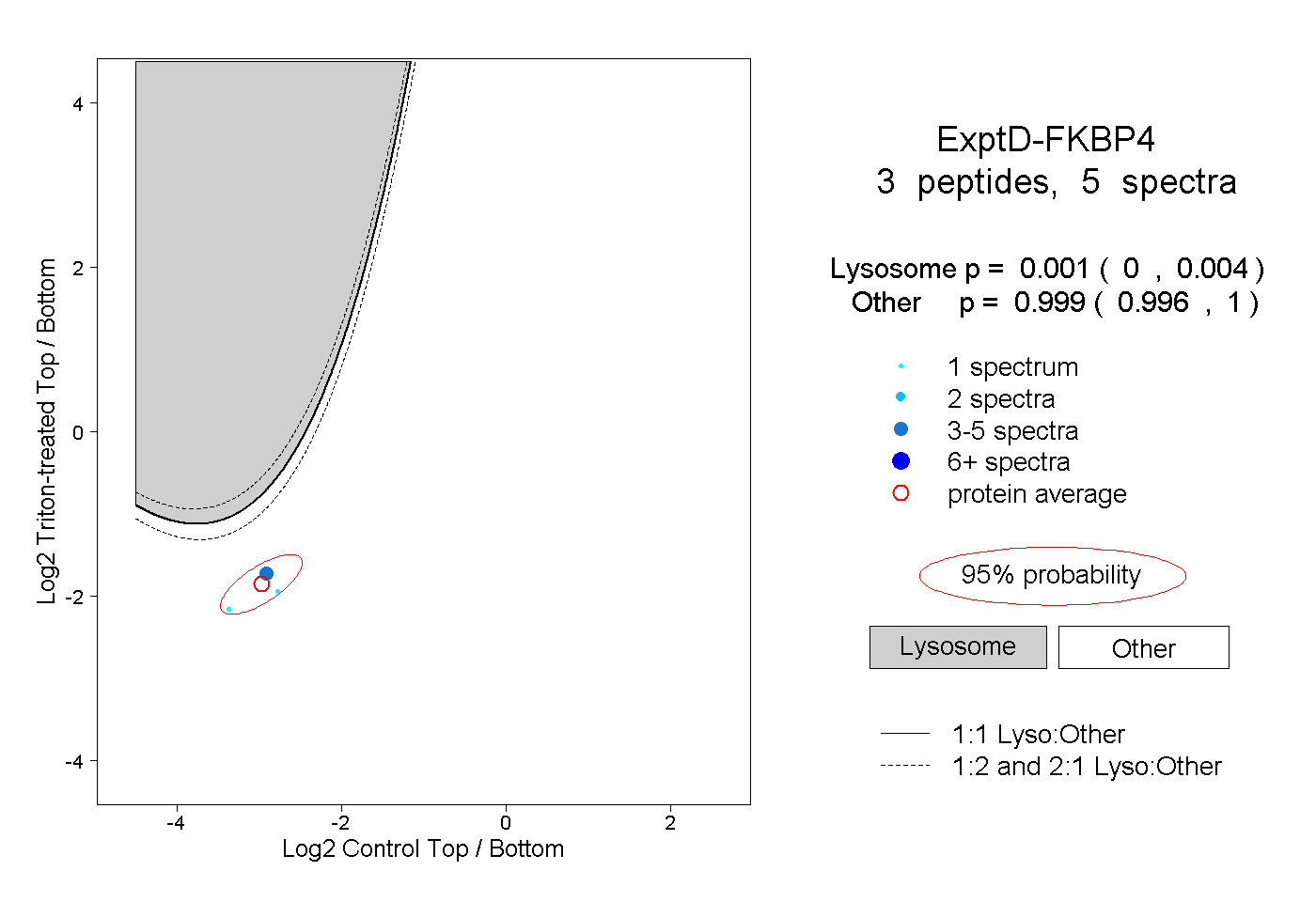 |
0.001 0.000 | 0.004 |
0.999 0.996 | 1.000 |