peptides
spectra
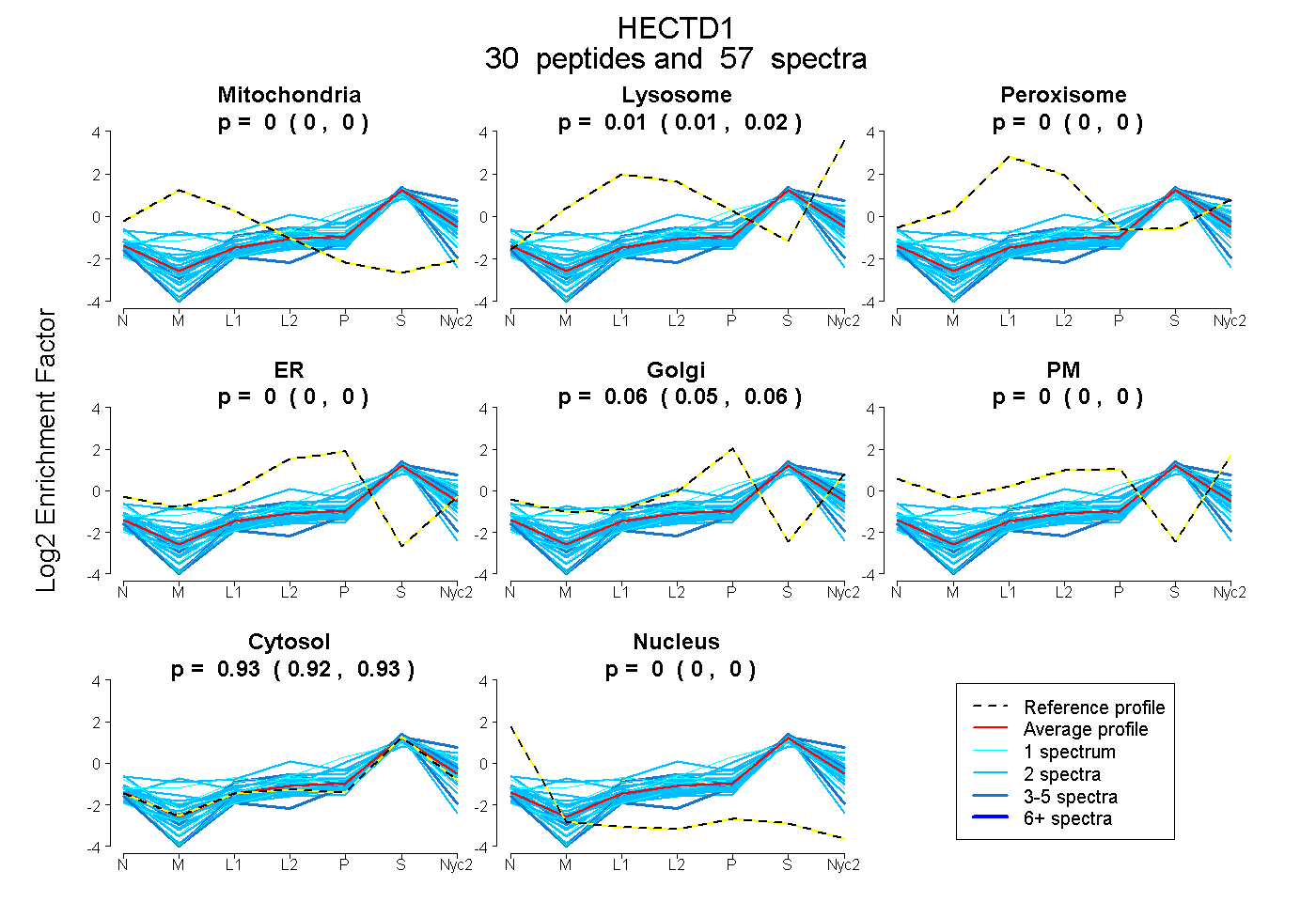
0.000 | 0.000
0.009 | 0.018
0.000 | 0.000
0.000 | 0.000
0.054 | 0.062
0.000 | 0.000
0.924 | 0.931
0.000 | 0.000
peptides
spectra
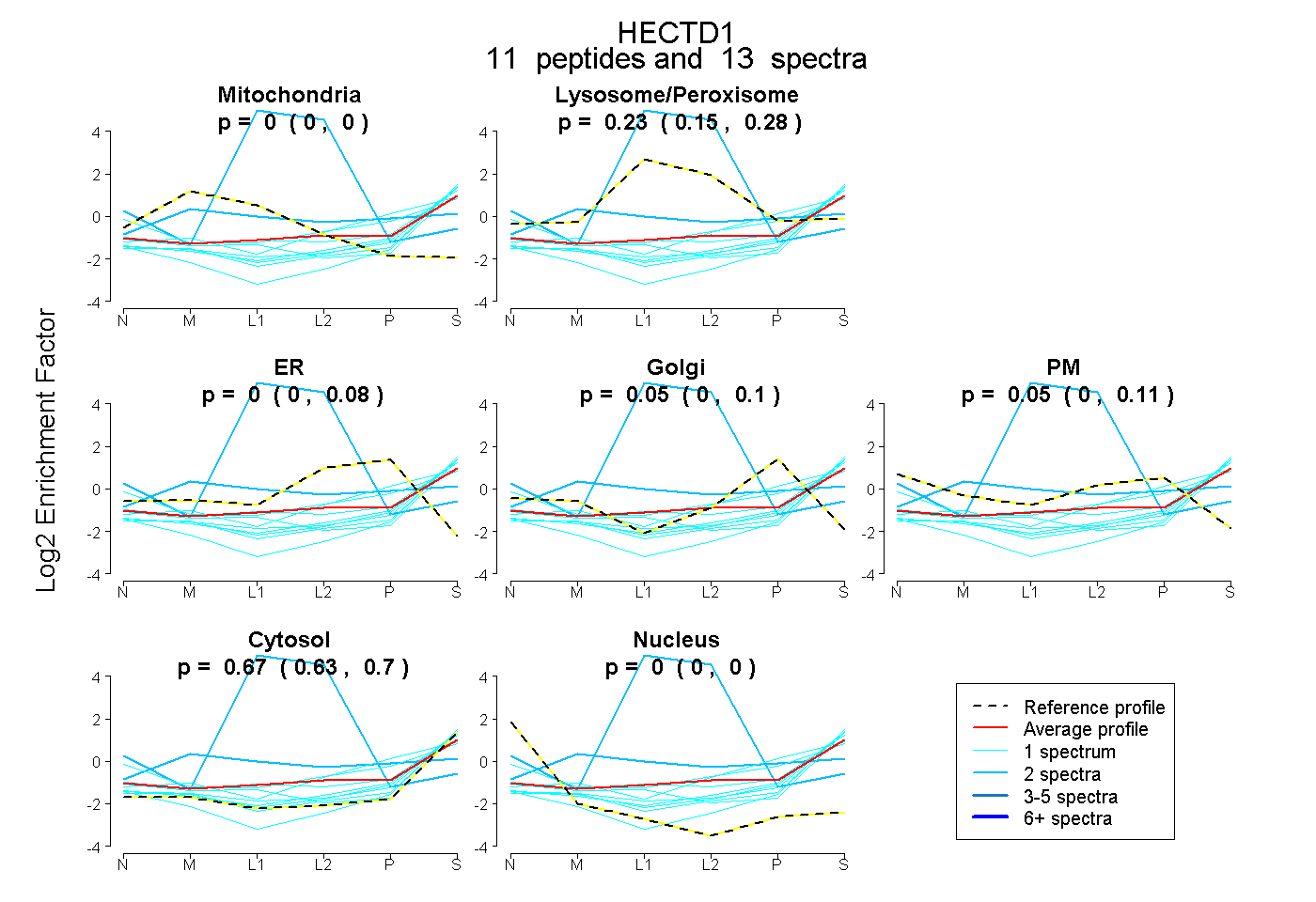
0.000 | 0.000
0.153 | 0.282
0.000 | 0.077
0.000 | 0.096
0.000 | 0.115
0.634 | 0.698
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
57 spectra |
 |
0.000 0.000 | 0.000 |
0.014 0.009 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.058 0.054 | 0.062 |
0.000 0.000 | 0.000 |
0.928 0.924 | 0.931 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
 |
0.000 0.000 | 0.000 |
0.230 0.153 | 0.282 |
0.000 0.000 | 0.077 |
0.053 0.000 | 0.096 |
0.050 0.000 | 0.115 |
0.667 0.634 | 0.698 |
0.000 0.000 | 0.000 |
| 1 spectrum, SSFVFVR | 0.000 | 0.113 | 0.088 | 0.235 | 0.000 | 0.564 | 0.000 | |||
| 2 spectra, DDPGEFR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LQELVLK | 0.000 | 0.131 | 0.000 | 0.000 | 0.337 | 0.533 | 0.000 | |||
| 1 spectrum, APGETALIDR | 0.000 | 0.000 | 0.000 | 0.048 | 0.010 | 0.942 | 0.000 | |||
| 1 spectrum, ETSSLESFVR | 0.000 | 0.221 | 0.000 | 0.062 | 0.010 | 0.707 | 0.000 | |||
| 1 spectrum, LIAVLESIER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.950 | 0.050 | |||
| 1 spectrum, VTGLGTTR | 0.000 | 0.052 | 0.000 | 0.103 | 0.000 | 0.845 | 0.000 | |||
| 1 spectrum, LEDILSR | 0.000 | 0.022 | 0.000 | 0.100 | 0.000 | 0.879 | 0.000 | |||
| 1 spectrum, QLIDCIR | 0.000 | 0.127 | 0.000 | 0.000 | 0.000 | 0.820 | 0.054 | |||
| 1 spectrum, EGQNFIFR | 0.000 | 0.072 | 0.000 | 0.048 | 0.000 | 0.880 | 0.000 | |||
| 2 spectra, LLYESR | 0.160 | 0.365 | 0.000 | 0.226 | 0.000 | 0.250 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
35 spectra |
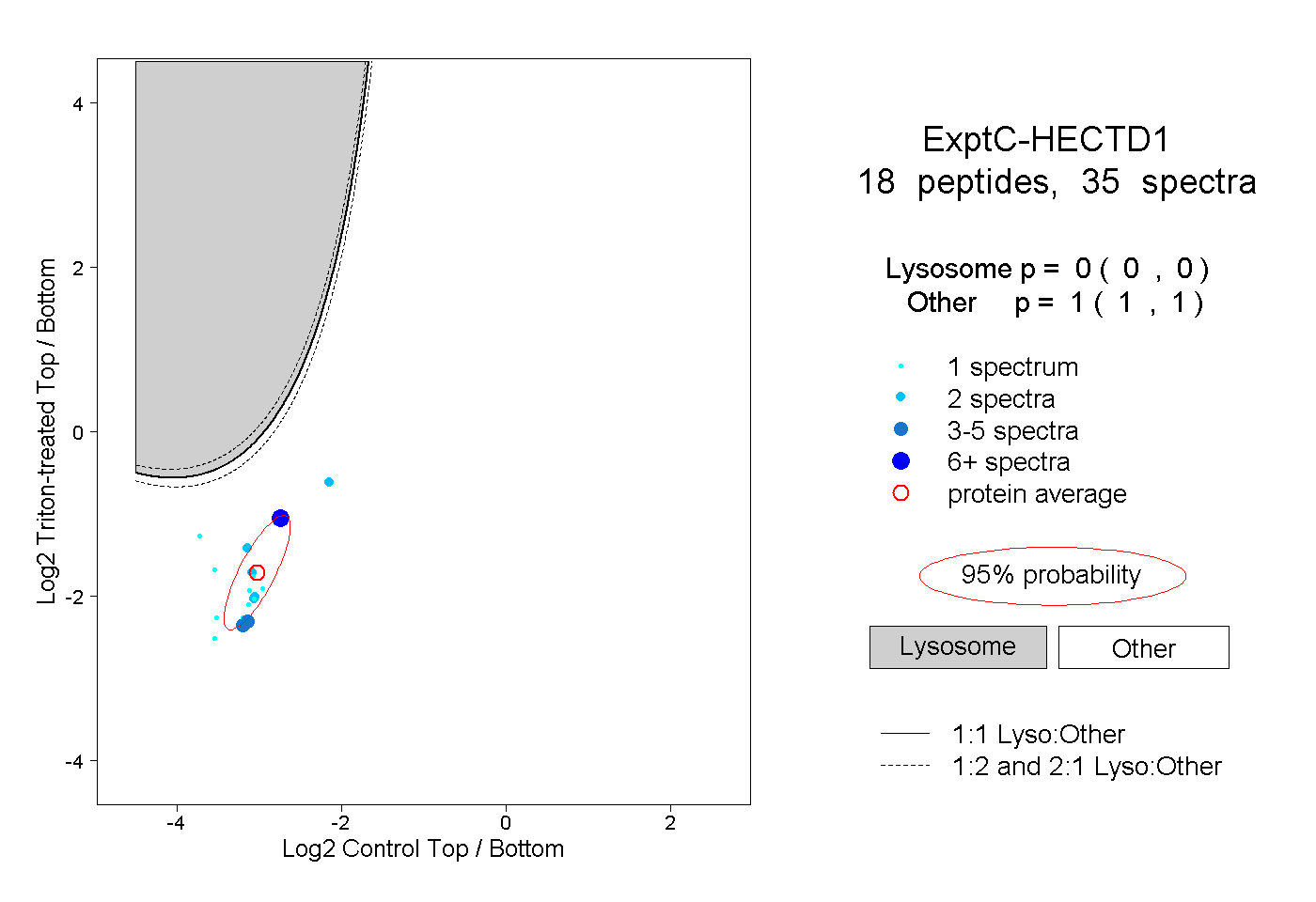 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
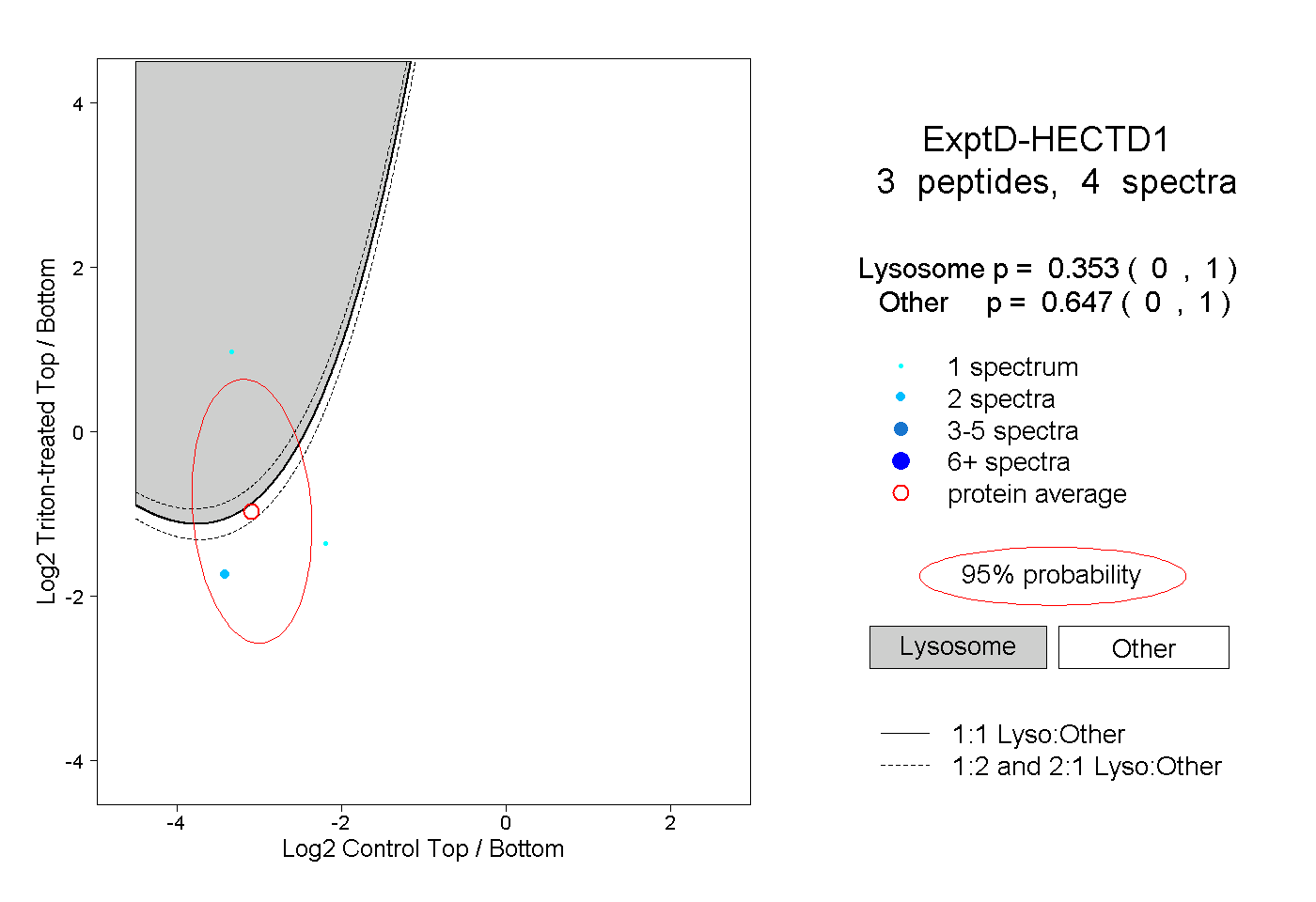 |
0.353 0.000 | 1.000 |
0.647 0.000 | 1.000 |