peptides
spectra
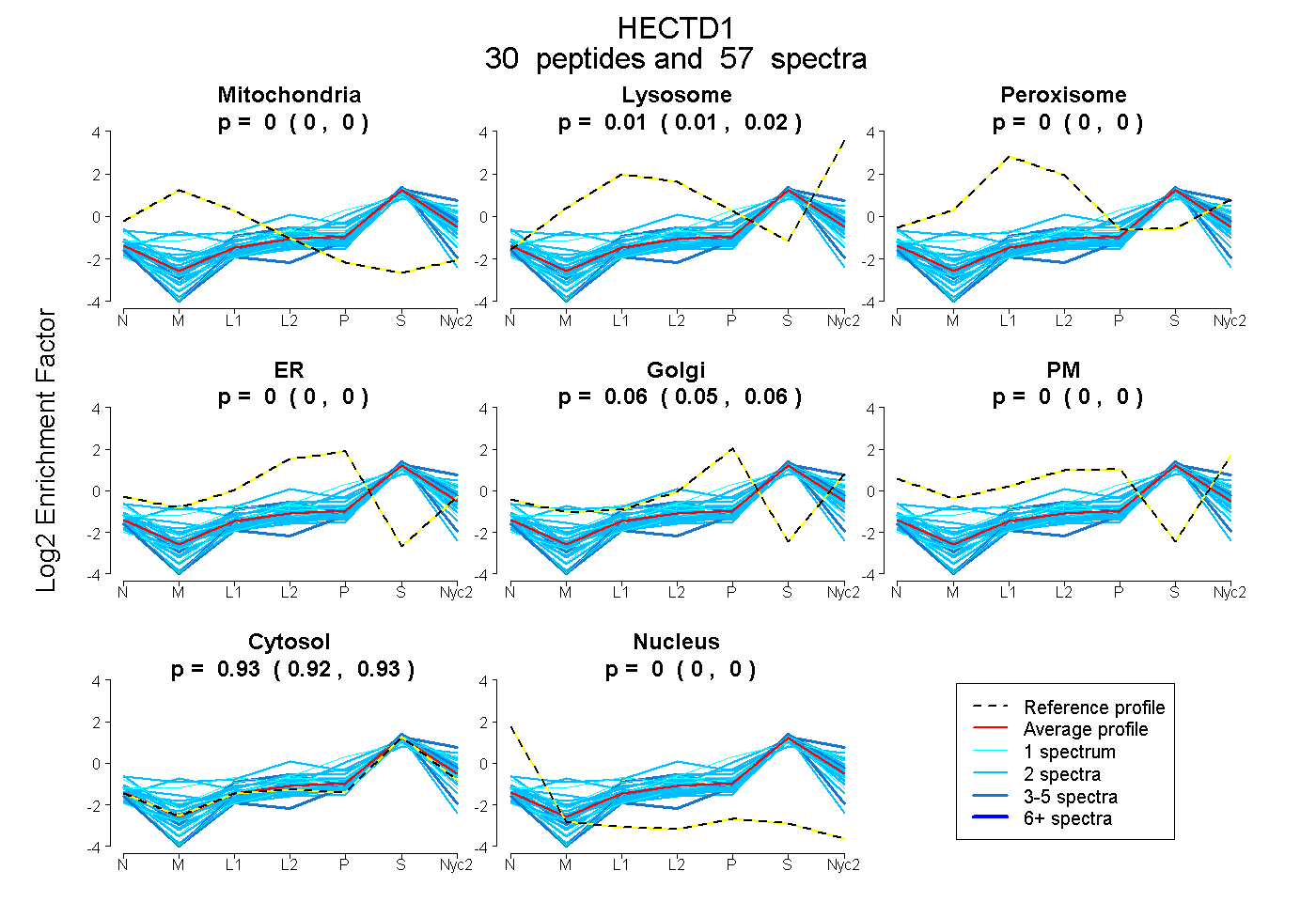
0.000 | 0.000
0.009 | 0.018
0.000 | 0.000
0.000 | 0.000
0.054 | 0.062
0.000 | 0.000
0.924 | 0.931
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
57 spectra |
 |
0.000 0.000 | 0.000 |
0.014 0.009 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.058 0.054 | 0.062 |
0.000 0.000 | 0.000 |
0.928 0.924 | 0.931 |
0.000 0.000 | 0.000 |
| 1 spectrum, MAAAGGTVSGPSSACKPGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LQELVLK | 0.000 | 0.004 | 0.000 | 0.000 | 0.039 | 0.189 | 0.767 | 0.000 | ||
| 2 spectra, SLSEDEK | 0.000 | 0.030 | 0.011 | 0.136 | 0.000 | 0.000 | 0.823 | 0.000 | ||
| 1 spectrum, AITYYLDVSAECTR | 0.048 | 0.001 | 0.000 | 0.000 | 0.043 | 0.000 | 0.907 | 0.000 | ||
| 1 spectrum, TSAAAGSSSR | 0.000 | 0.031 | 0.000 | 0.000 | 0.000 | 0.002 | 0.967 | 0.000 | ||
| 2 spectra, NWVFQVSK | 0.000 | 0.079 | 0.000 | 0.000 | 0.000 | 0.000 | 0.921 | 0.000 | ||
| 2 spectra, AIVWLQNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.986 | 0.014 | ||
| 3 spectra, EAASQRPLSSSASNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.895 | 0.105 | ||
| 2 spectra, QFSALVPAFDPRPGR | 0.000 | 0.156 | 0.065 | 0.000 | 0.000 | 0.183 | 0.595 | 0.000 | ||
| 2 spectra, GSPLVTHDLLR | 0.000 | 0.091 | 0.000 | 0.000 | 0.004 | 0.000 | 0.904 | 0.000 | ||
| 4 spectra, TNATNNMNLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, DLYDDHFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.004 | ||
| 1 spectrum, SGLNQGASSSLQSSDILNLTK | 0.000 | 0.128 | 0.003 | 0.035 | 0.000 | 0.000 | 0.834 | 0.000 | ||
| 2 spectra, VTGLGTTR | 0.000 | 0.081 | 0.000 | 0.000 | 0.000 | 0.007 | 0.912 | 0.000 | ||
| 2 spectra, NADAAFLR | 0.000 | 0.138 | 0.000 | 0.000 | 0.036 | 0.000 | 0.826 | 0.000 | ||
| 2 spectra, EGQNFIFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LPEYSSEEIMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, HGLTEELLSR | 0.000 | 0.026 | 0.000 | 0.000 | 0.136 | 0.000 | 0.837 | 0.000 | ||
| 2 spectra, DDPGEFR | 0.000 | 0.031 | 0.000 | 0.000 | 0.010 | 0.087 | 0.873 | 0.000 | ||
| 2 spectra, EVELPLSNFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, APGETALIDR | 0.000 | 0.018 | 0.000 | 0.000 | 0.000 | 0.000 | 0.982 | 0.000 | ||
| 1 spectrum, YMVPGAR | 0.000 | 0.000 | 0.000 | 0.072 | 0.203 | 0.000 | 0.724 | 0.000 | ||
| 3 spectra, HEDHQVSDGALR | 0.000 | 0.180 | 0.000 | 0.000 | 0.000 | 0.000 | 0.820 | 0.000 | ||
| 2 spectra, DTLHSAMAVVSR | 0.236 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.764 | 0.000 | ||
| 2 spectra, VLELICTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.905 | 0.095 | ||
| 2 spectra, LEDILSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, TWDDDYVLK | 0.027 | 0.236 | 0.000 | 0.000 | 0.000 | 0.000 | 0.738 | 0.000 | ||
| 1 spectrum, EQPQAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.020 | 0.000 | 0.980 | 0.000 | ||
| 2 spectra, DWSVIR | 0.041 | 0.038 | 0.000 | 0.000 | 0.000 | 0.000 | 0.920 | 0.000 | ||
| 2 spectra, LTVGNWSLTCLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.158 | 0.000 | 0.842 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
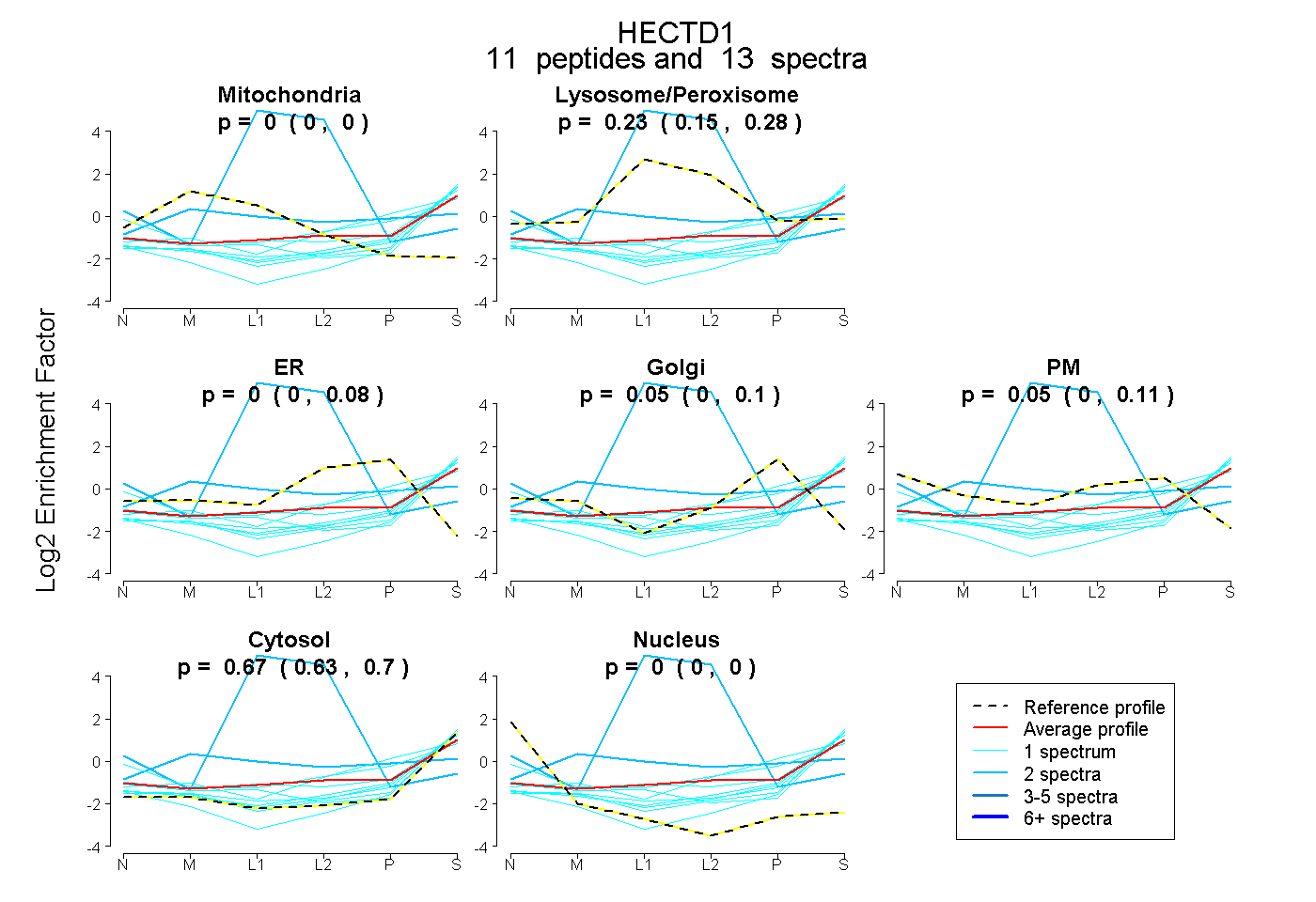 |
0.000 0.000 | 0.000 |
0.230 0.153 | 0.282 |
0.000 0.000 | 0.077 |
0.053 0.000 | 0.096 |
0.050 0.000 | 0.115 |
0.667 0.634 | 0.698 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
35 spectra |
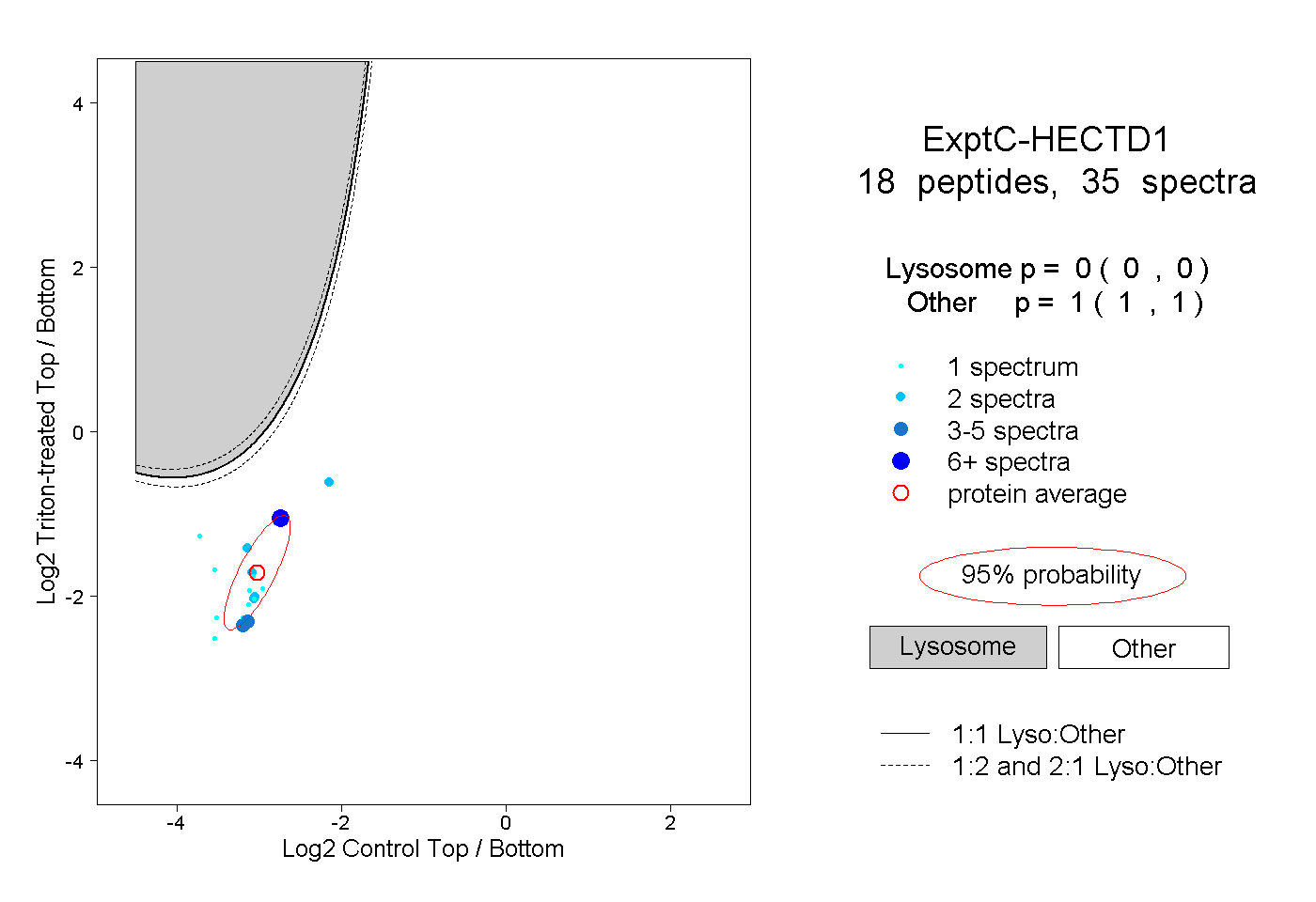 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
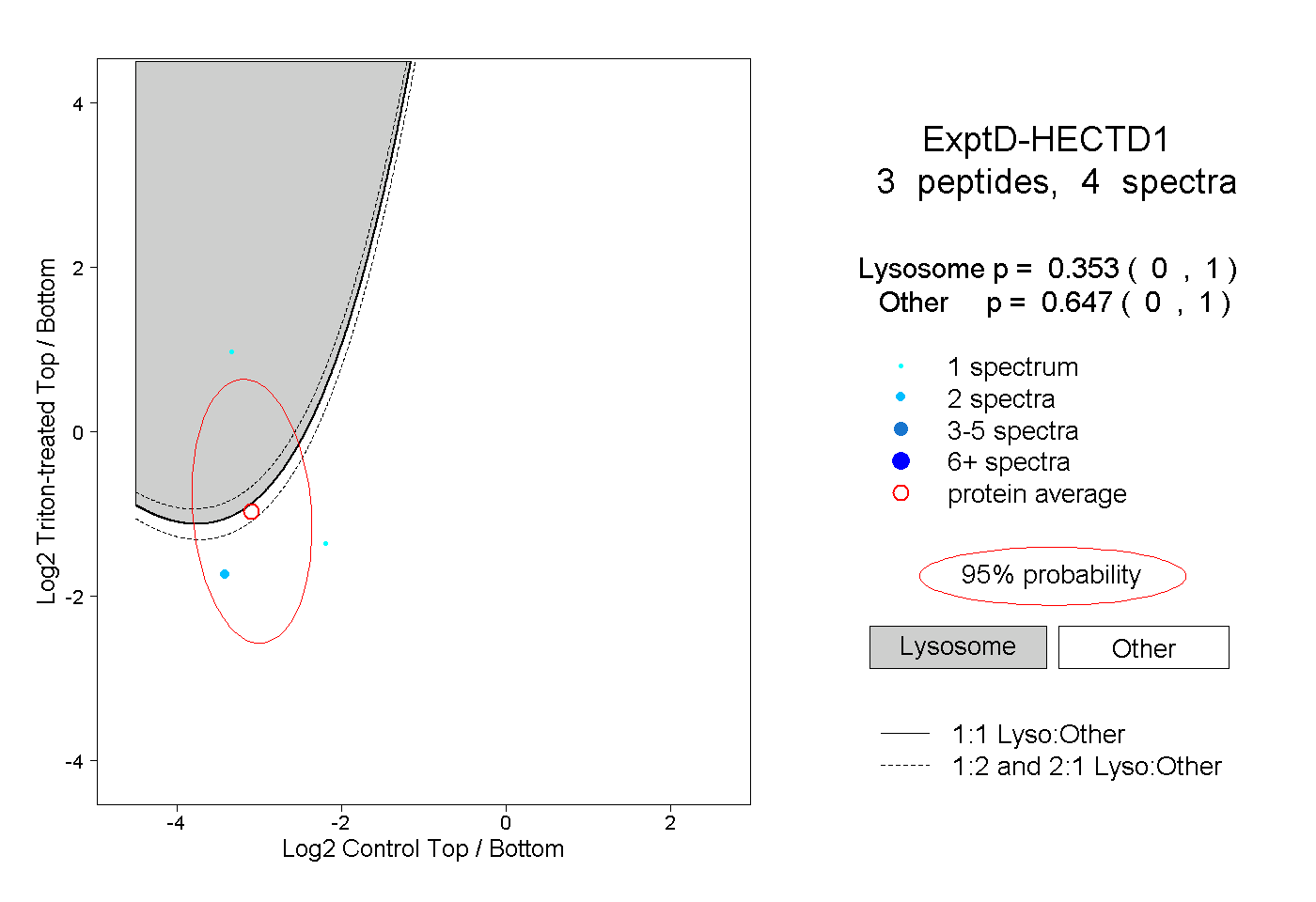 |
0.353 0.000 | 1.000 |
0.647 0.000 | 1.000 |