peptides
spectra
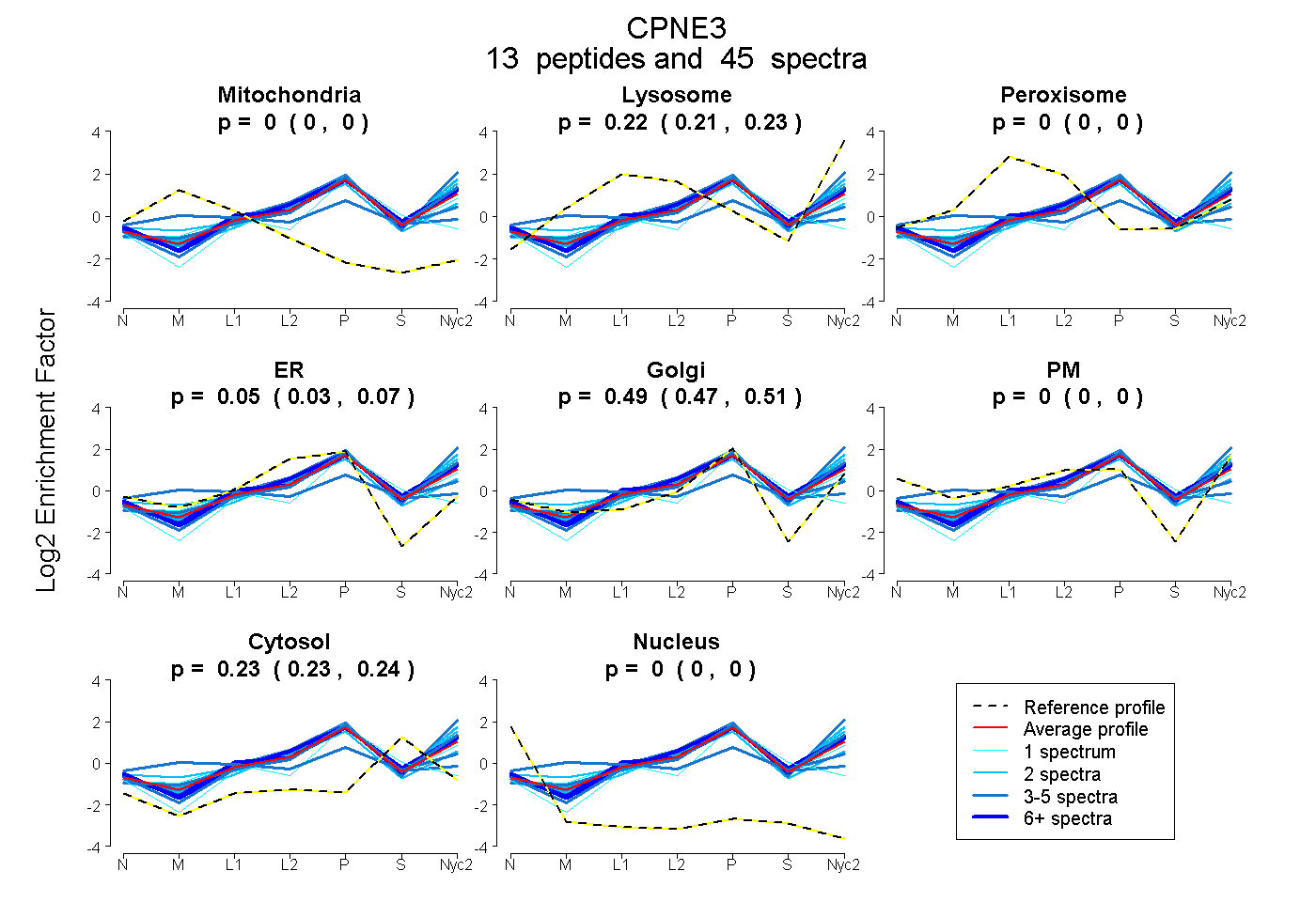
0.000 | 0.000
0.212 | 0.228
0.000 | 0.000
0.031 | 0.070
0.474 | 0.509
0.000 | 0.000
0.228 | 0.238
0.000 | 0.000
peptides
spectra

0.000 | 0.000
0.189 | 0.205
0.287 | 0.326
0.363 | 0.396
0.000 | 0.000
0.106 | 0.118
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
45 spectra |
 |
0.000 0.000 | 0.000 |
0.221 0.212 | 0.228 |
0.000 0.000 | 0.000 |
0.053 0.031 | 0.070 |
0.493 0.474 | 0.509 |
0.000 0.000 | 0.000 |
0.233 0.228 | 0.238 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.198 0.189 | 0.205 |
0.308 0.287 | 0.326 |
0.381 0.363 | 0.396 |
0.000 0.000 | 0.000 |
0.112 0.106 | 0.118 |
0.000 0.000 | 0.000 |
| 5 spectra, SDPYLEFHK | 0.000 | 0.312 | 0.025 | 0.572 | 0.000 | 0.091 | 0.000 | |||
| 2 spectra, FGIYDIDNK | 0.000 | 0.163 | 0.365 | 0.293 | 0.000 | 0.179 | 0.000 | |||
| 5 spectra, DIVQFVPFR | 0.000 | 0.134 | 0.420 | 0.332 | 0.000 | 0.114 | 0.000 | |||
| 6 spectra, APSGEVAIR | 0.000 | 0.176 | 0.265 | 0.452 | 0.000 | 0.106 | 0.000 | |||
| 1 spectrum, SSPVEFECINEK | 0.000 | 0.055 | 0.684 | 0.134 | 0.000 | 0.127 | 0.000 | |||
| 2 spectra, TCLPQIR | 0.000 | 0.104 | 0.583 | 0.171 | 0.000 | 0.142 | 0.000 | |||
| 2 spectra, LYGPTNFSPIINHVAR | 0.000 | 0.185 | 0.518 | 0.181 | 0.000 | 0.116 | 0.000 | |||
| 1 spectrum, NSGVIVVK | 0.000 | 0.367 | 0.019 | 0.613 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QFQNAPK | 0.000 | 0.289 | 0.117 | 0.594 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QAIVSAAK | 0.000 | 0.151 | 0.333 | 0.401 | 0.000 | 0.115 | 0.000 | |||
| 3 spectra, VVLFEMEAR | 0.000 | 0.261 | 0.302 | 0.329 | 0.000 | 0.109 | 0.000 | |||
| 1 spectrum, LTRPLVLK | 0.000 | 0.150 | 0.504 | 0.230 | 0.000 | 0.117 | 0.000 | |||
| 1 spectrum, ISLNSLCYGDMDK | 0.000 | 0.304 | 0.000 | 0.632 | 0.000 | 0.065 | 0.000 | |||
| 2 spectra, VELNISCNSLLDTDLTSK | 0.000 | 0.148 | 0.256 | 0.365 | 0.000 | 0.232 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
82 spectra |
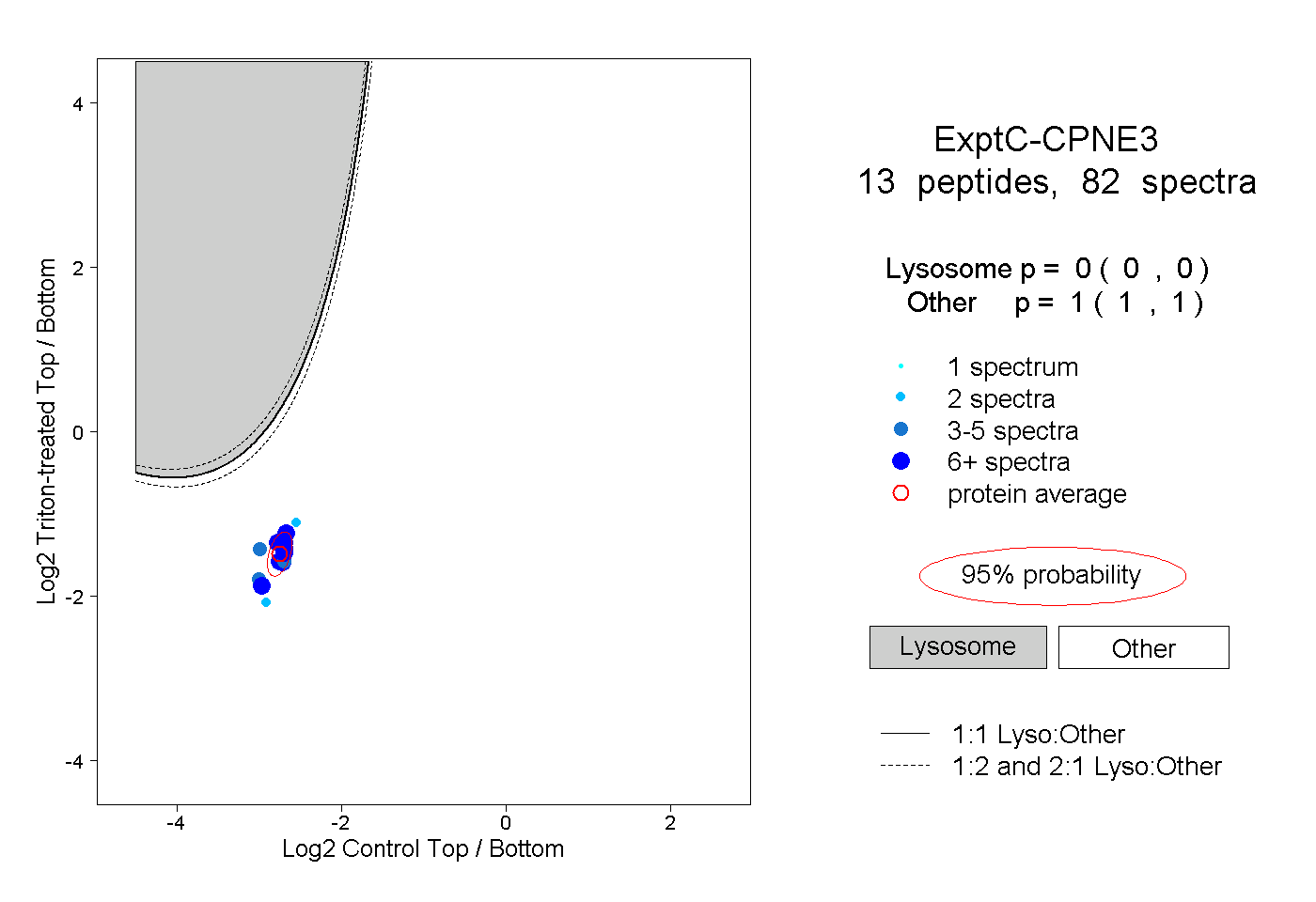 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
 |
0.078 0.001 | 0.732 |
0.922 0.258 | 0.999 |