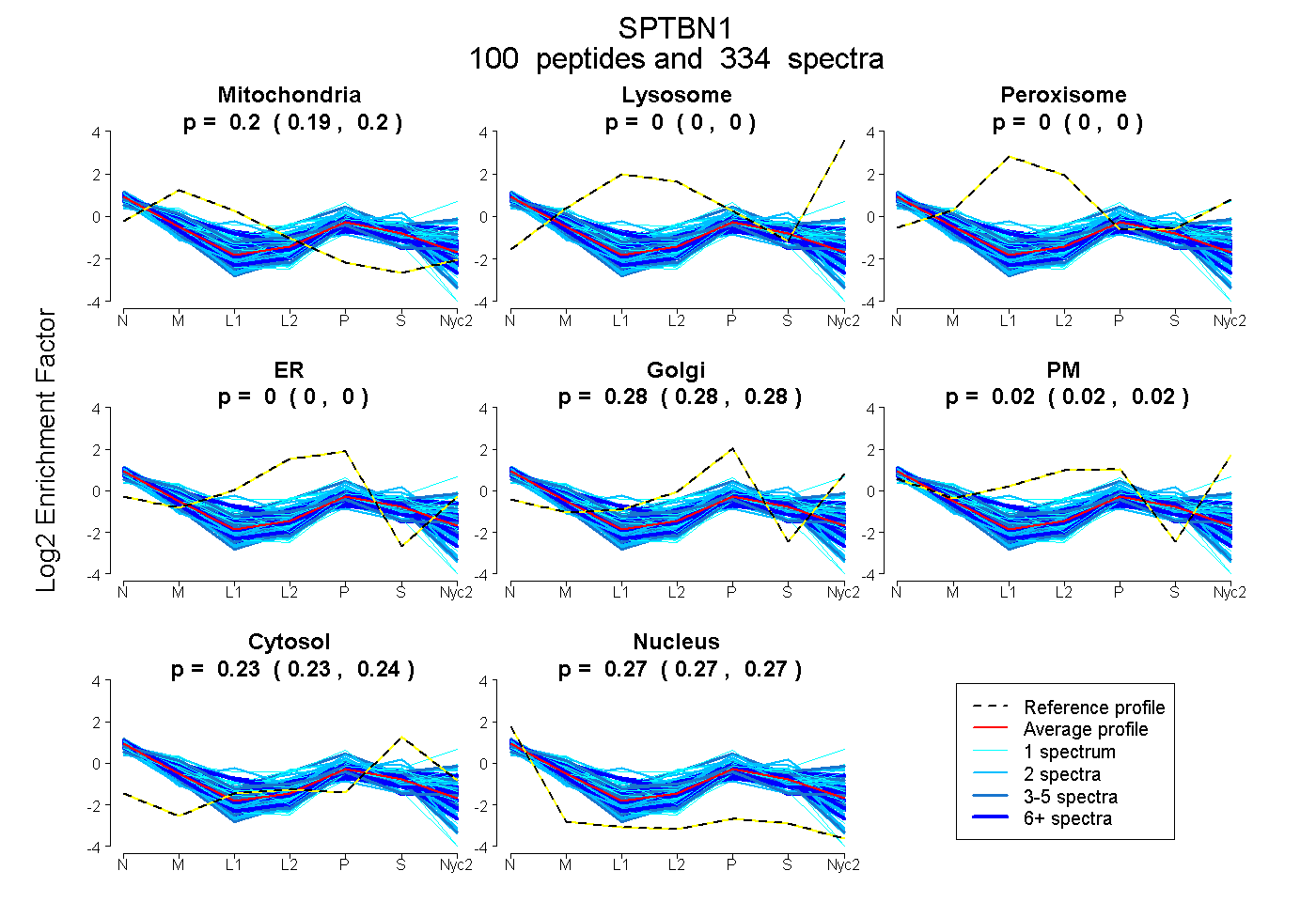
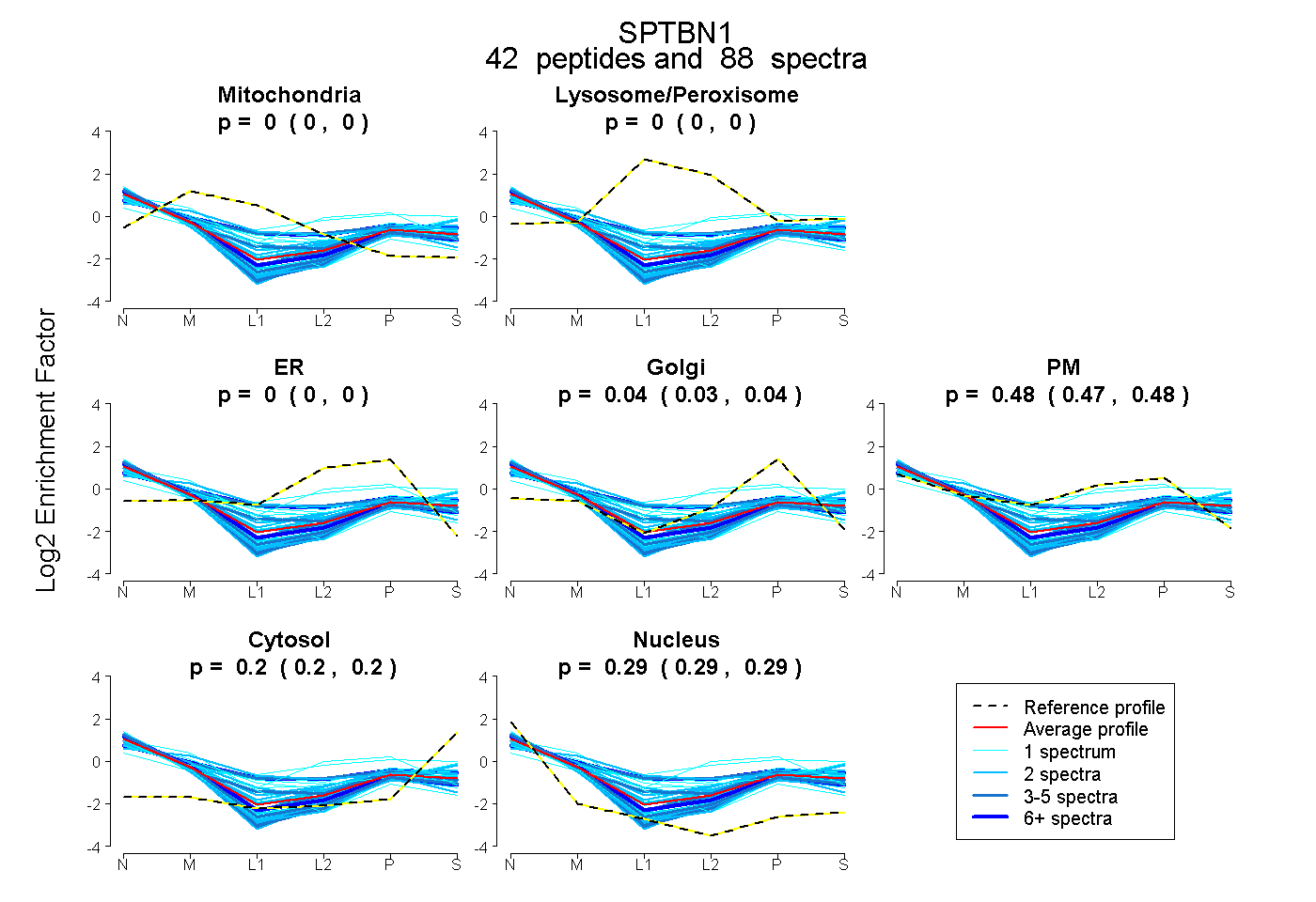
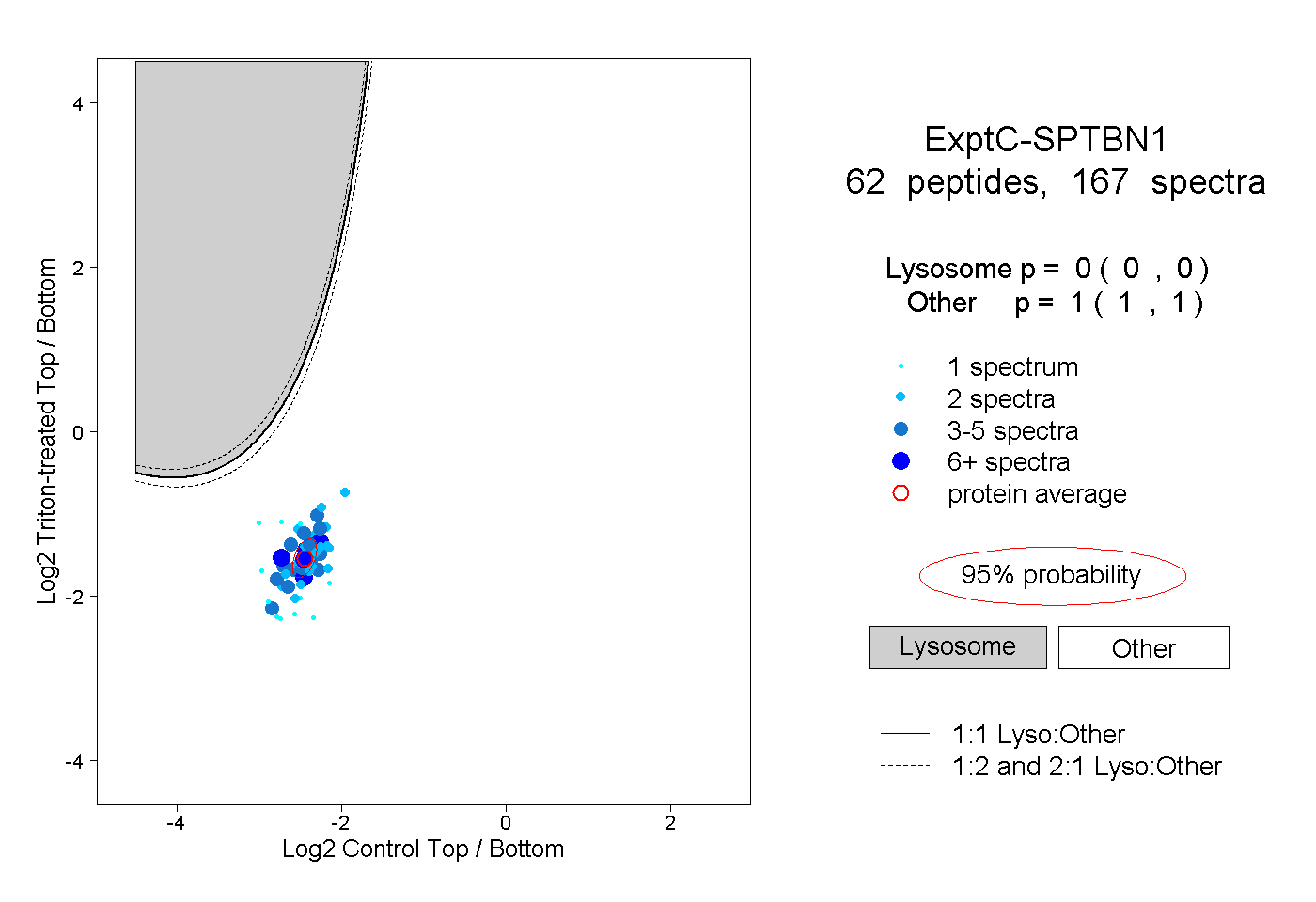
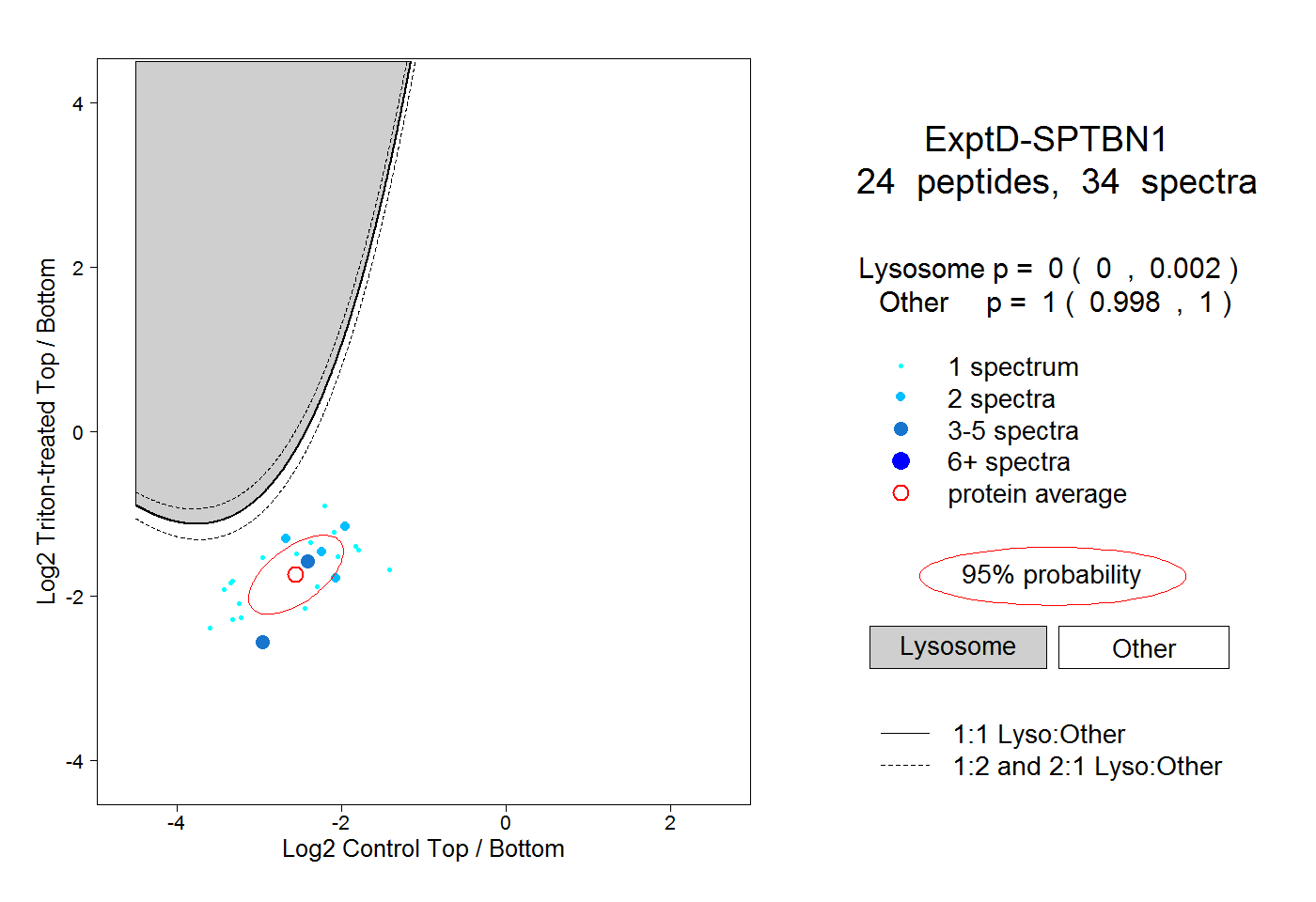
| 2 spectra, LTTLELLEVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VAVVNQIAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, MLTAQDMSYDEAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, HEAFEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, FYHDAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LLEVLSGER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DGMAFNALIHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TQTAIASEDMPNTLTEAEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ESSPVPSPTSDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SLLDACEGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FESLEPEMNNQASR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LQEFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LISDINK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LEEFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FATDGEGYKPCDPQVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EIGQSVDEVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QLQEDAAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LPEELGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LLQLTEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ETWLSENQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ILSSDDYGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LILEVHQFSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EIHQFNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EIQGHEPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ALQFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ALVADSHPESER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EGMQLISEKPETEAVVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VLLLSQDYGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DVSSVELLMNNHQGIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IHCLENVDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LYAGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DLVAIEAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ITDLYTDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GVNASAQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, HLLGVEDLLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LQQFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SGHFEQAIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EAASELLMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LQALDTGWNELHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, TVEKPPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ENEVLEAWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LTVQTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VLDNAIETEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LFDANK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, FSIFGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IDDIFER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LFQLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VDSIDDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SALPAQSAATLPAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DTGNIGQER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LEDLEVIQHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, FMELLEPLNER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FFSMVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LEEAHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, AFEDEMSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FSALER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EASLGEASK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DQNTVETLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SQNIITDSSSLNAEAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EIQGHQPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VQAVVAVAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QIEAQEKPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |