peptides
spectra
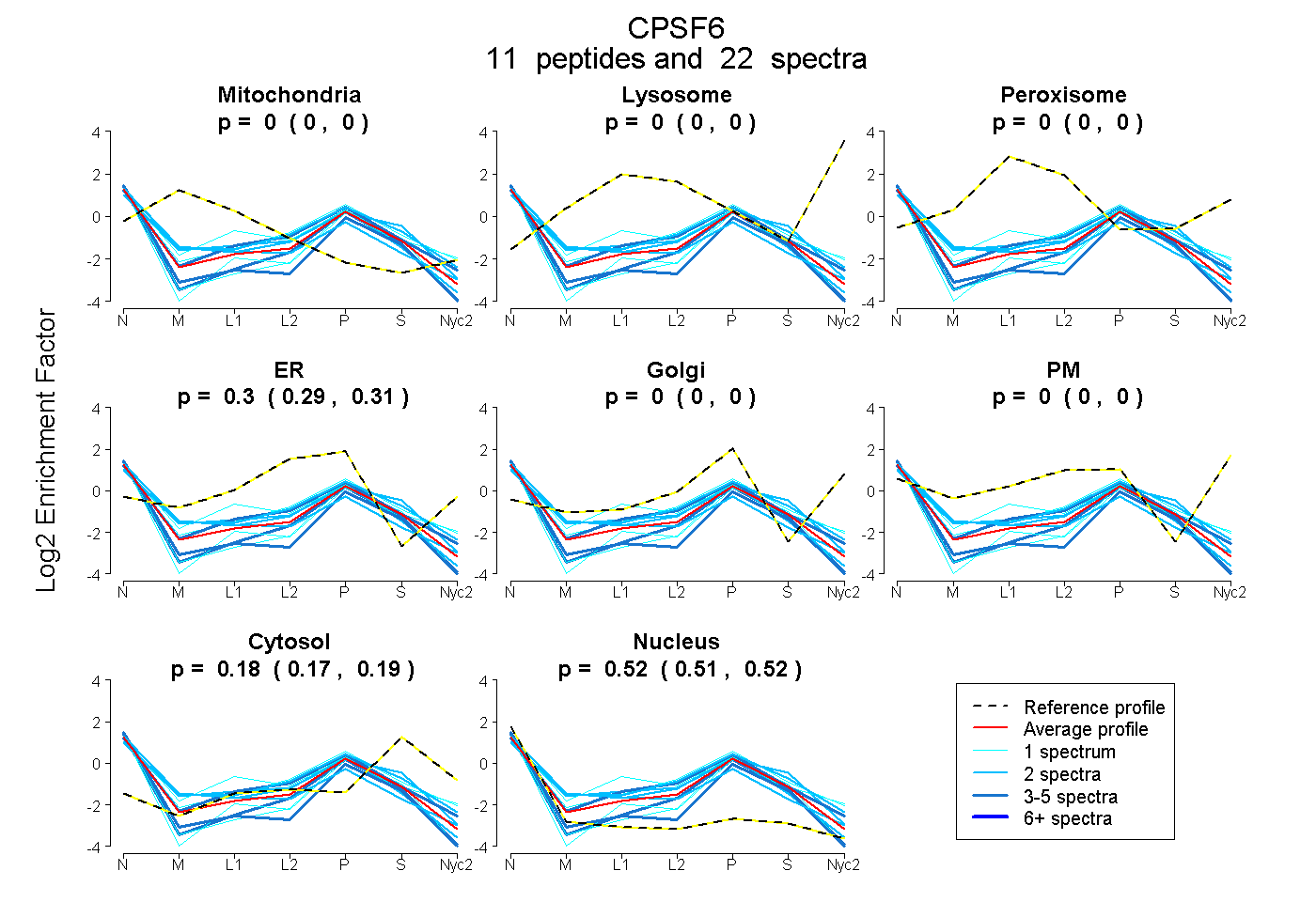
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.294 | 0.314
0.000 | 0.000
0.000 | 0.000
0.168 | 0.187
0.506 | 0.525
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.305 0.294 | 0.314 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.179 0.168 | 0.187 |
0.517 0.506 | 0.525 |
| 2 spectra, TPLSEAEFEEIMNR | 0.055 | 0.000 | 0.000 | 0.321 | 0.000 | 0.000 | 0.075 | 0.549 | ||
| 4 spectra, AISSSAISR | 0.000 | 0.000 | 0.000 | 0.210 | 0.000 | 0.000 | 0.148 | 0.642 | ||
| 1 spectrum, ELHGQNPVVTPCNK | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 | 0.000 | 0.219 | 0.642 | ||
| 2 spectra, DYMDTLPPTVGDDVGK | 0.000 | 0.000 | 0.000 | 0.322 | 0.000 | 0.000 | 0.300 | 0.377 | ||
| 1 spectrum, GFALVGVGSEASSK | 0.000 | 0.000 | 0.077 | 0.380 | 0.000 | 0.000 | 0.173 | 0.370 | ||
| 1 spectrum, EMDTAR | 0.000 | 0.000 | 0.000 | 0.419 | 0.000 | 0.000 | 0.243 | 0.338 | ||
| 2 spectra, GDYGPPGR | 0.000 | 0.000 | 0.000 | 0.398 | 0.000 | 0.000 | 0.066 | 0.536 | ||
| 3 spectra, GPPPTDPYGRPPPYDR | 0.000 | 0.000 | 0.000 | 0.398 | 0.000 | 0.000 | 0.192 | 0.410 | ||
| 3 spectra, QFLSQFEMQSR | 0.000 | 0.000 | 0.000 | 0.128 | 0.000 | 0.000 | 0.152 | 0.719 | ||
| 1 spectrum, LMDLLPK | 0.000 | 0.000 | 0.000 | 0.172 | 0.000 | 0.000 | 0.145 | 0.682 | ||
| 2 spectra, HDDYYR | 0.000 | 0.000 | 0.000 | 0.403 | 0.000 | 0.000 | 0.256 | 0.341 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
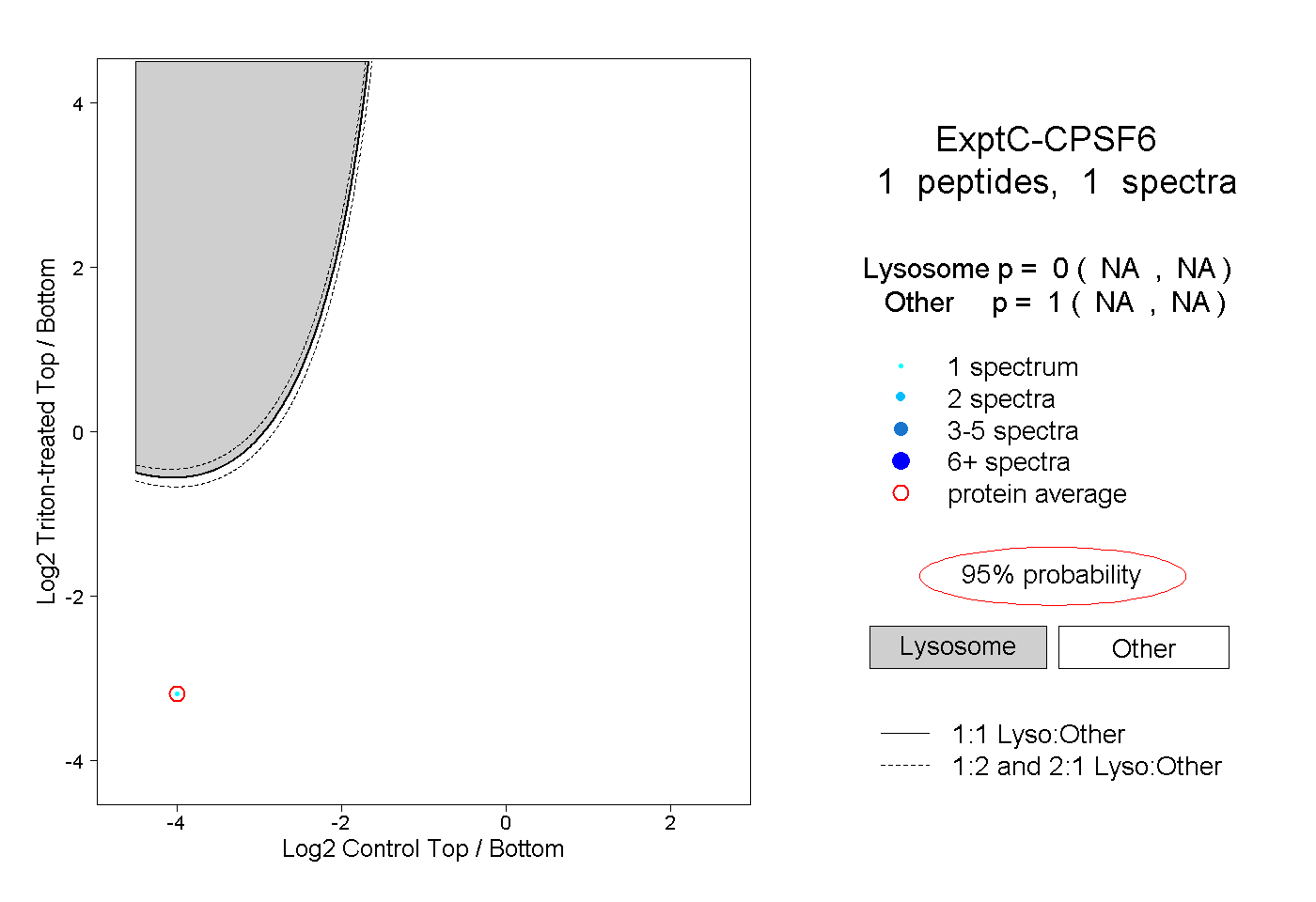 |
0.000 NA | NA |
1.000 NA | NA |