peptides
spectra
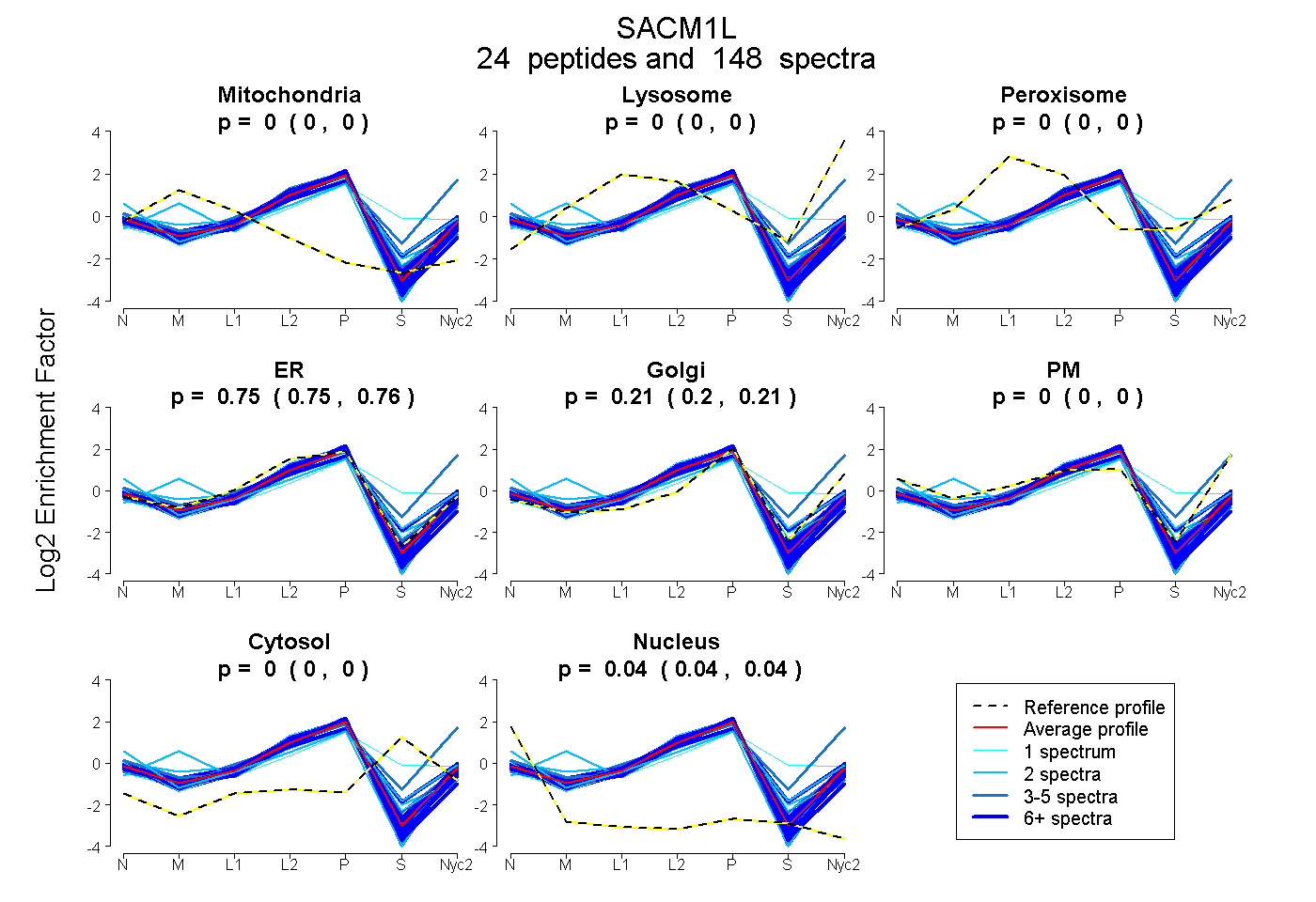
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.747 | 0.756
0.201 | 0.211
0.000 | 0.000
0.000 | 0.000
0.040 | 0.043
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
148 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.752 0.747 | 0.756 |
0.206 0.201 | 0.211 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.042 0.040 | 0.043 |
| 12 spectra, LEEQDEFEK | 0.000 | 0.000 | 0.000 | 0.733 | 0.230 | 0.000 | 0.000 | 0.037 | ||
| 4 spectra, FVWNGHLLR | 0.000 | 0.000 | 0.000 | 0.873 | 0.106 | 0.000 | 0.000 | 0.022 | ||
| 6 spectra, VANHMDGFQR | 0.000 | 0.000 | 0.000 | 0.586 | 0.208 | 0.089 | 0.112 | 0.005 | ||
| 17 spectra, SNCMDCLDR | 0.000 | 0.000 | 0.000 | 0.911 | 0.000 | 0.000 | 0.000 | 0.089 | ||
| 13 spectra, TNVIQSLLAR | 0.000 | 0.000 | 0.000 | 0.772 | 0.196 | 0.000 | 0.000 | 0.032 | ||
| 14 spectra, YIAFDFHK | 0.000 | 0.000 | 0.000 | 0.887 | 0.052 | 0.000 | 0.000 | 0.061 | ||
| 3 spectra, AATAYEHLK | 0.000 | 0.000 | 0.000 | 0.810 | 0.163 | 0.000 | 0.000 | 0.027 | ||
| 1 spectrum, DFVDAPR | 0.000 | 0.000 | 0.059 | 0.327 | 0.263 | 0.000 | 0.351 | 0.000 | ||
| 4 spectra, LHITPEK | 0.000 | 0.000 | 0.000 | 0.778 | 0.187 | 0.000 | 0.000 | 0.036 | ||
| 3 spectra, QVIINLVNHK | 0.000 | 0.000 | 0.000 | 0.758 | 0.192 | 0.000 | 0.017 | 0.033 | ||
| 2 spectra, ATDFDVLSYK | 0.098 | 0.000 | 0.000 | 0.760 | 0.060 | 0.000 | 0.058 | 0.024 | ||
| 1 spectrum, VSTEVTLAVK | 0.000 | 0.000 | 0.000 | 0.819 | 0.087 | 0.000 | 0.030 | 0.064 | ||
| 11 spectra, SLQAQLQR | 0.000 | 0.000 | 0.000 | 0.760 | 0.217 | 0.000 | 0.000 | 0.023 | ||
| 5 spectra, GSIPVFWSQRPNLK | 0.000 | 0.000 | 0.000 | 0.876 | 0.040 | 0.000 | 0.000 | 0.084 | ||
| 17 spectra, MVSSLGSGMIR | 0.000 | 0.000 | 0.000 | 0.783 | 0.213 | 0.001 | 0.000 | 0.003 | ||
| 6 spectra, VVTNQEGVFR | 0.000 | 0.000 | 0.000 | 0.718 | 0.229 | 0.000 | 0.000 | 0.054 | ||
| 8 spectra, ASFVQTR | 0.000 | 0.000 | 0.000 | 0.727 | 0.206 | 0.000 | 0.000 | 0.067 | ||
| 2 spectra, NNFSDGFR | 0.176 | 0.000 | 0.000 | 0.514 | 0.310 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, NAWADNANACAK | 0.000 | 0.000 | 0.000 | 0.904 | 0.041 | 0.000 | 0.000 | 0.054 | ||
| 6 spectra, TQLGLVMDGFNSLLR | 0.000 | 0.000 | 0.000 | 0.741 | 0.221 | 0.000 | 0.000 | 0.038 | ||
| 4 spectra, VGEFFNHVIWK | 0.000 | 0.000 | 0.000 | 0.807 | 0.127 | 0.012 | 0.000 | 0.054 | ||
| 3 spectra, LGVLHVGQK | 0.000 | 0.268 | 0.000 | 0.034 | 0.464 | 0.153 | 0.081 | 0.000 | ||
| 1 spectrum, LSNTSPEFQEMSLLER | 0.000 | 0.000 | 0.000 | 0.783 | 0.209 | 0.000 | 0.000 | 0.008 | ||
| 2 spectra, YKPDPQINK | 0.000 | 0.000 | 0.000 | 0.459 | 0.157 | 0.220 | 0.084 | 0.079 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
50 spectra |
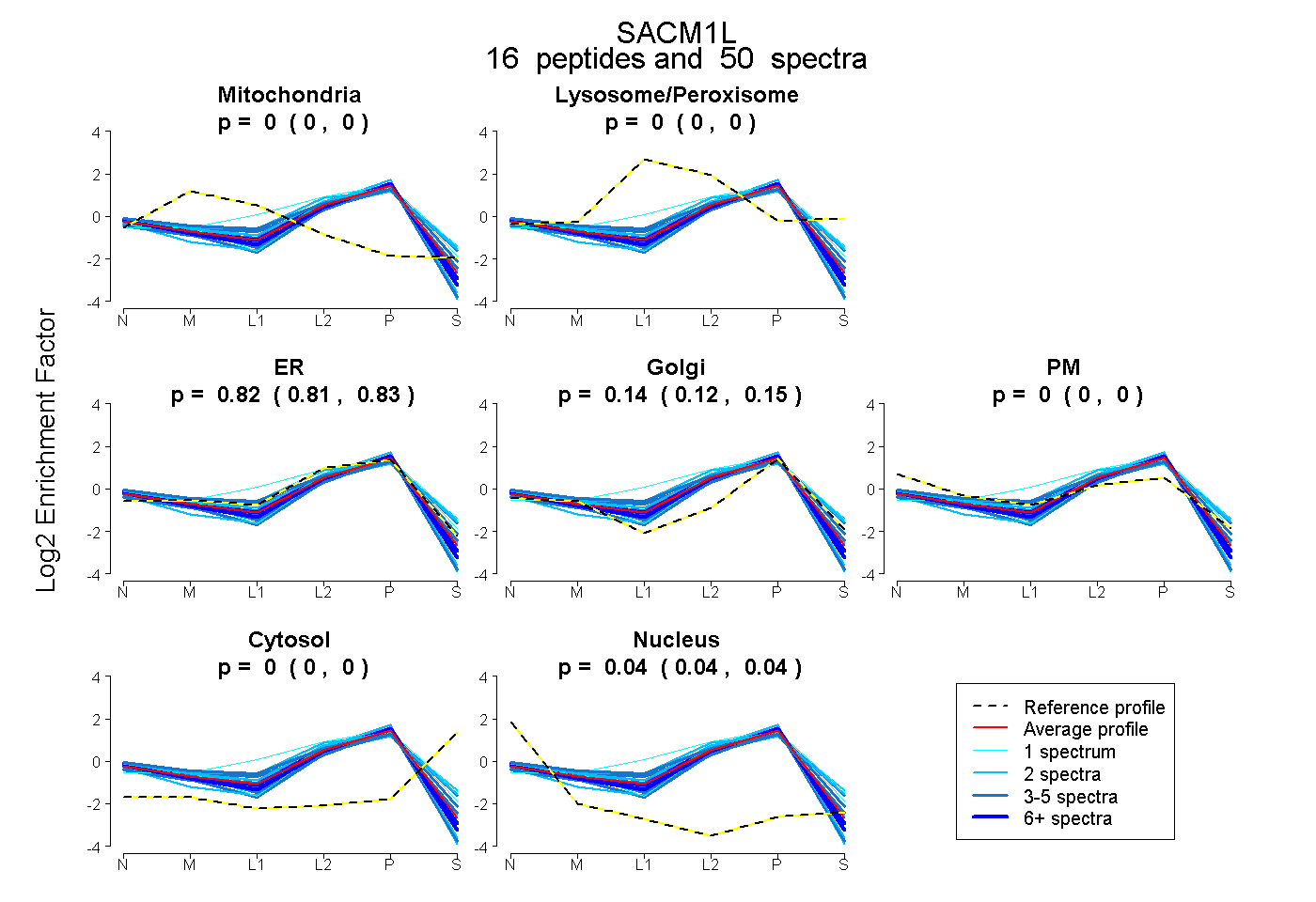 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.822 0.812 | 0.831 |
0.138 0.125 | 0.148 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.040 0.038 | 0.043 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
174 spectra |
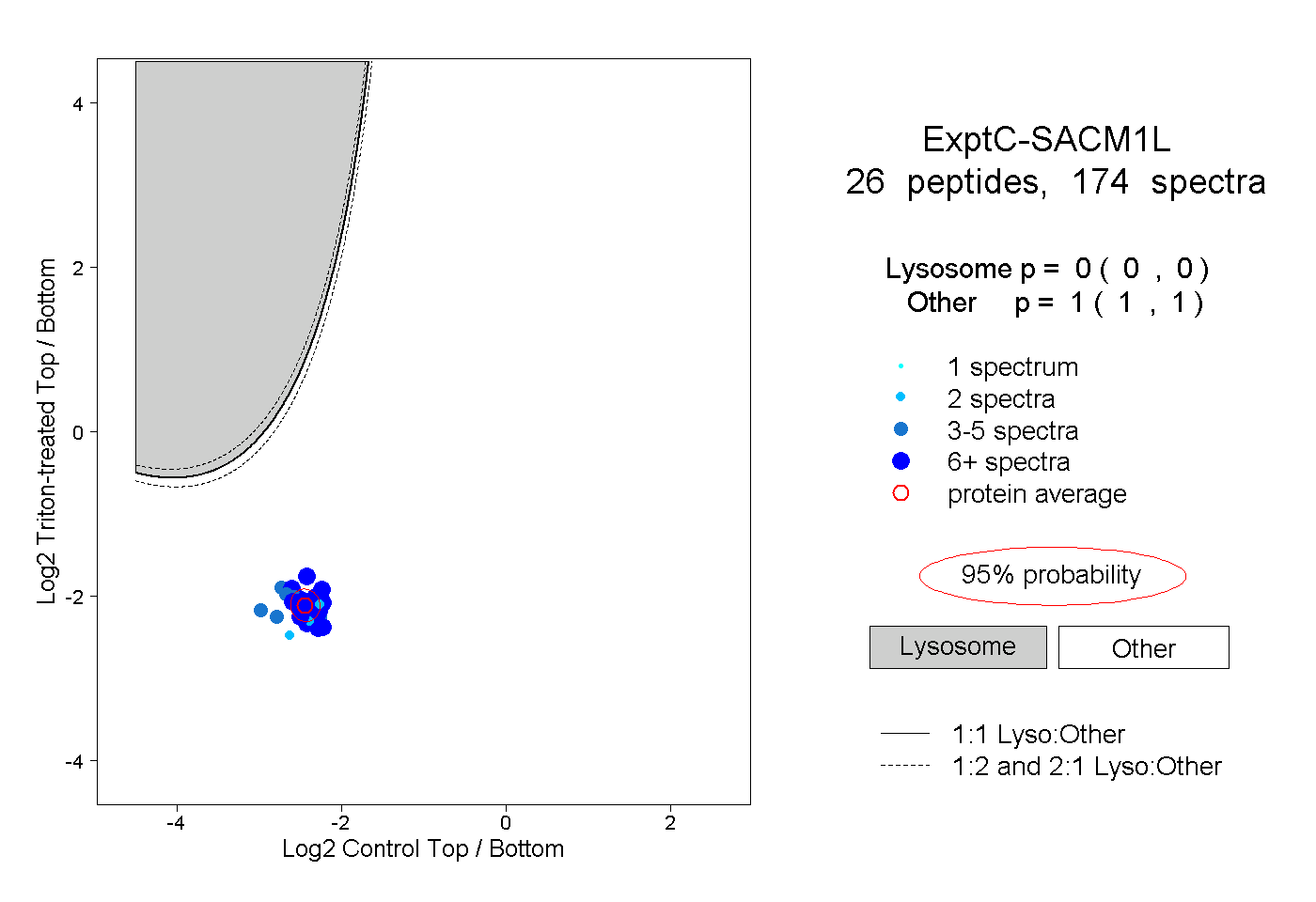 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
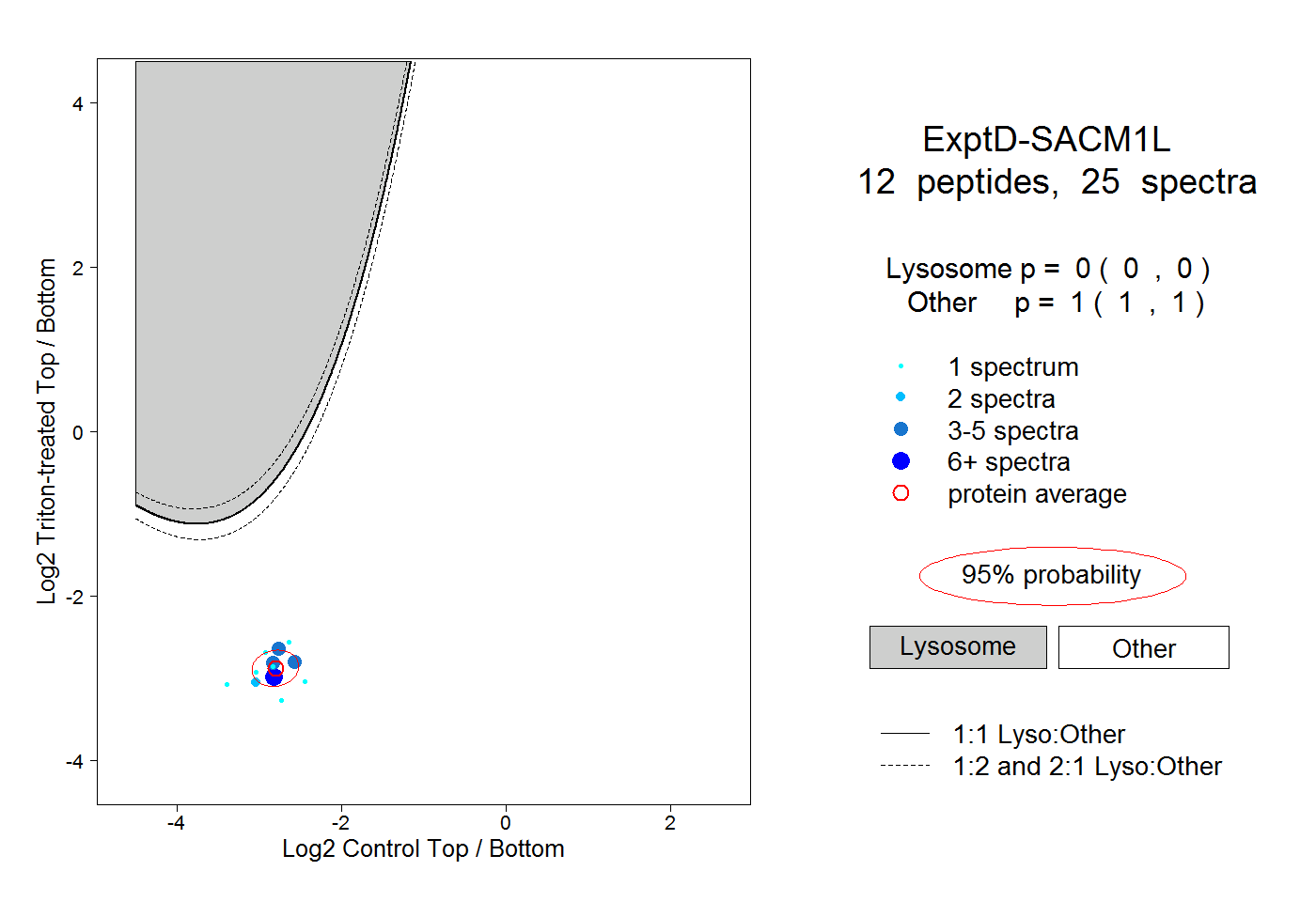 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |