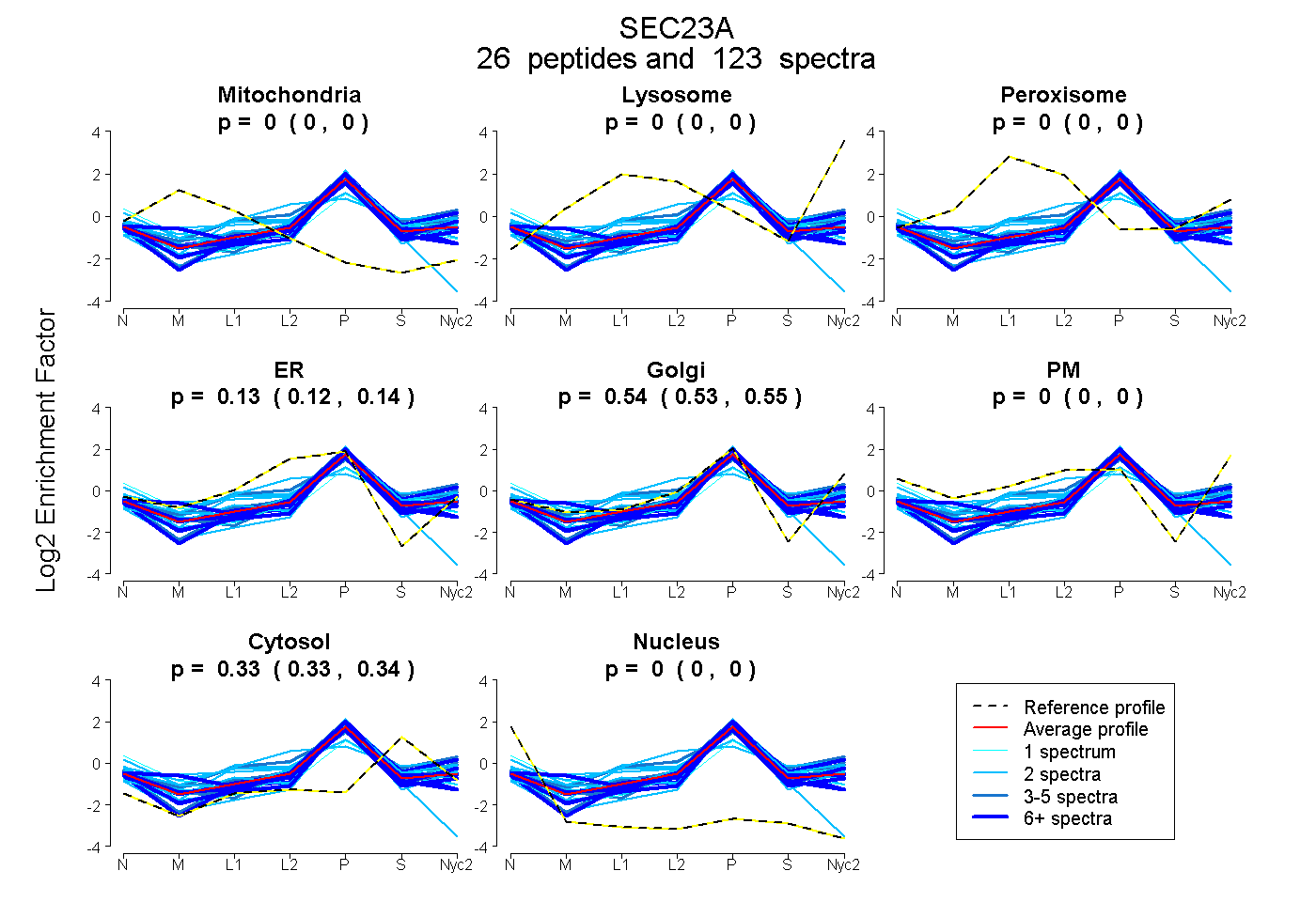
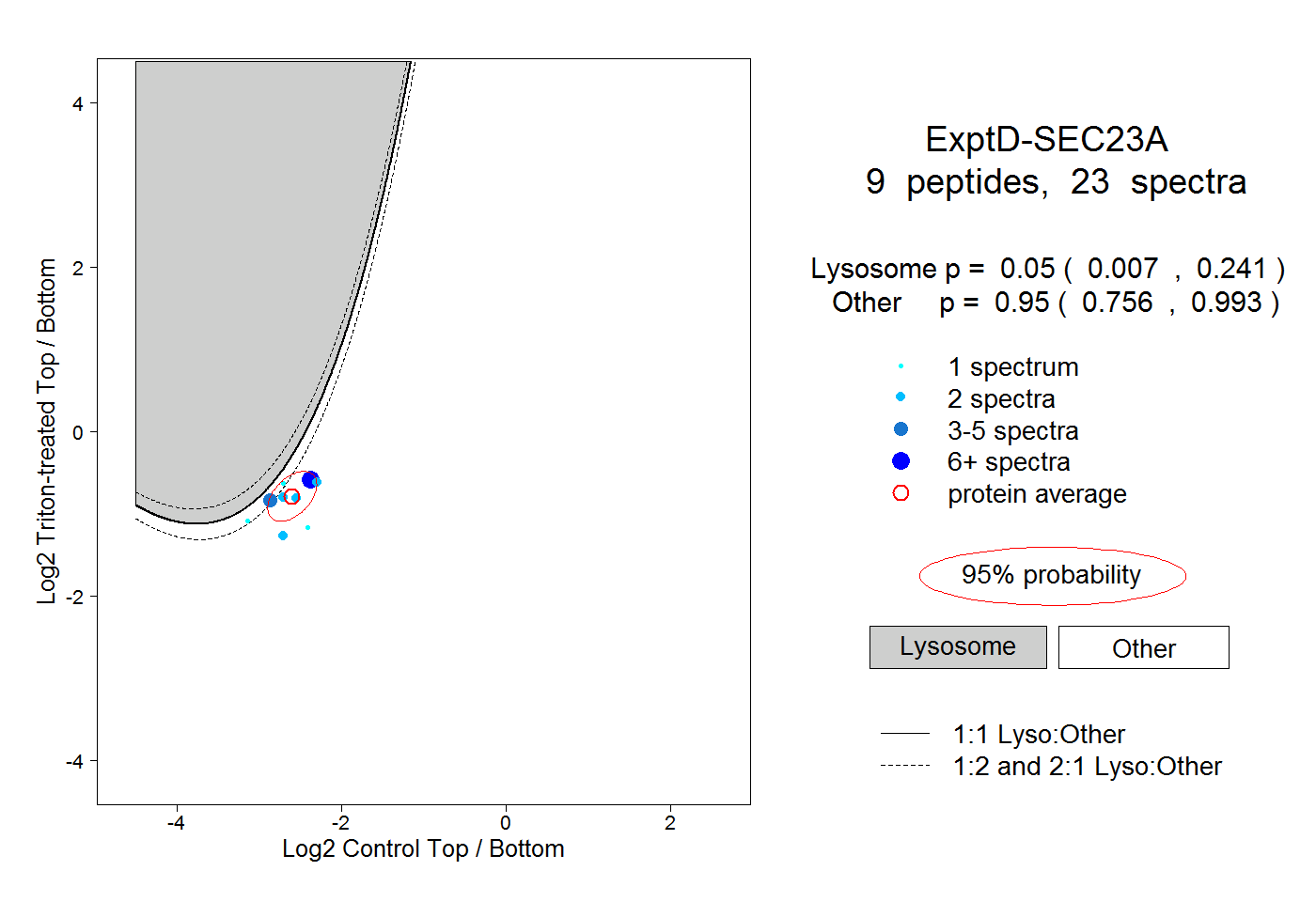
| 13 spectra, LWACNFCYQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, HFEALANR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, AETEEGPDVLR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 7 spectra, FGEYHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SPFLQVFNNSPDESSYYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GPCVSENEIGTGGTCQWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, ERPDLPPIQYEPVLCSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, SGYQDMPEYENFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, MVQVHELGCEGISK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, HLLQAPVDDAQEILHSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, FLQPVQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, DPWPVPQGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YIDTEHGGSQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, VTTIAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DDPNSFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IDMNLTDLLGELQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, MGFGGTLEIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, AVLNPLCQVDYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ISGAIGPCVSLNSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, FSWNVWPSSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GPQVQQPPPSNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QLQEMLGLSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, DIHGQFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VPVTQATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |