peptides
spectra
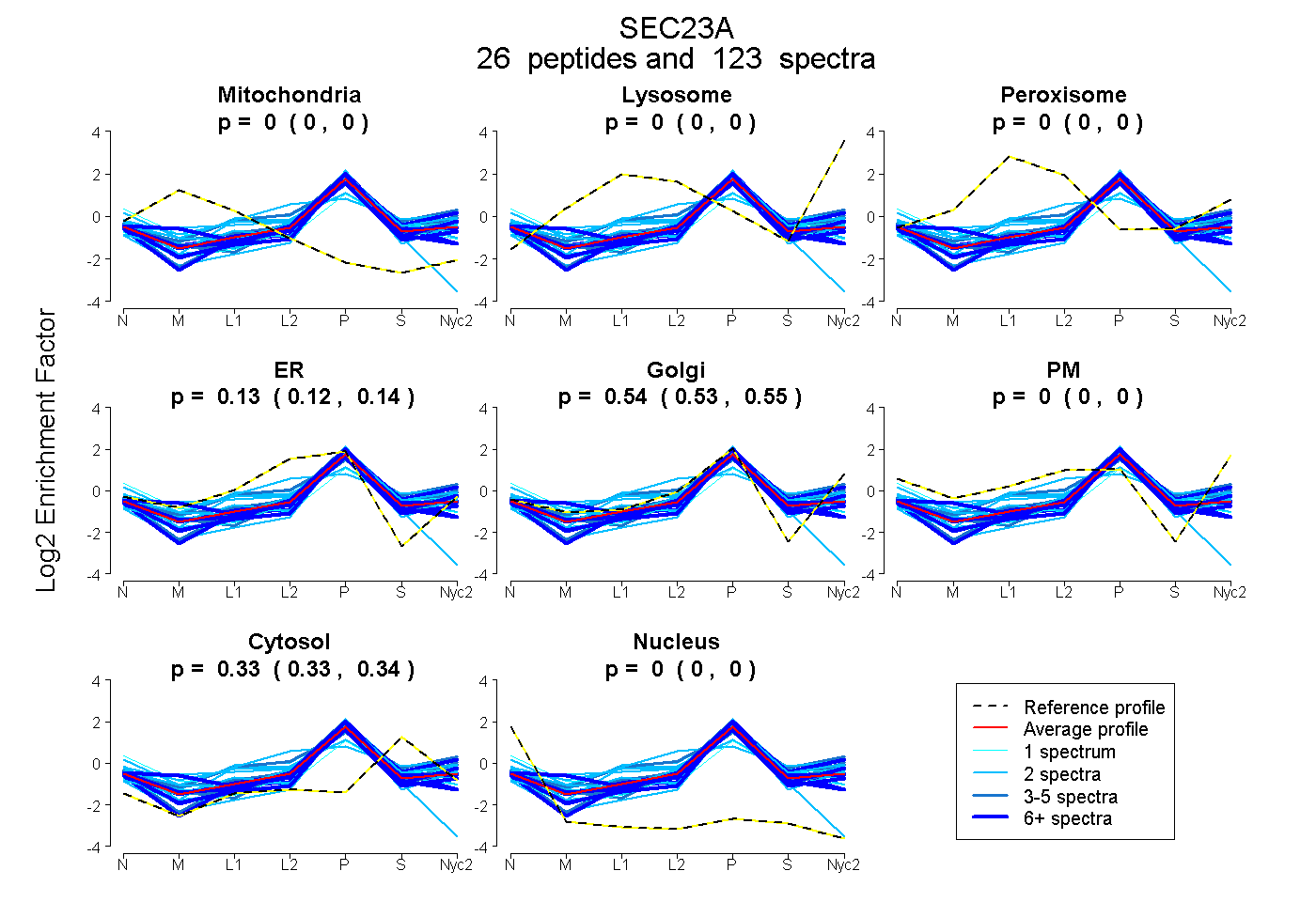
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.120 | 0.135
0.529 | 0.546
0.000 | 0.000
0.331 | 0.335
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
123 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.128 0.120 | 0.135 |
0.538 0.529 | 0.546 |
0.000 0.000 | 0.000 |
0.333 0.331 | 0.335 |
0.000 0.000 | 0.000 |
| 2 spectra, LWACNFCYQR | 0.000 | 0.000 | 0.000 | 0.492 | 0.000 | 0.000 | 0.247 | 0.260 | ||
| 3 spectra, HFEALANR | 0.000 | 0.000 | 0.000 | 0.000 | 0.625 | 0.000 | 0.375 | 0.000 | ||
| 12 spectra, AETEEGPDVLR | 0.000 | 0.000 | 0.000 | 0.026 | 0.655 | 0.000 | 0.293 | 0.026 | ||
| 1 spectrum, IMMFIGGPATQGPGMVVGDELK | 0.040 | 0.000 | 0.026 | 0.000 | 0.506 | 0.063 | 0.310 | 0.055 | ||
| 2 spectra, FGEYHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.560 | 0.000 | 0.413 | 0.027 | ||
| 2 spectra, ERPDLPPIQYEPVLCSR | 0.000 | 0.000 | 0.005 | 0.592 | 0.000 | 0.000 | 0.404 | 0.000 | ||
| 8 spectra, SGYQDMPEYENFR | 0.000 | 0.000 | 0.000 | 0.134 | 0.518 | 0.000 | 0.348 | 0.000 | ||
| 1 spectrum, MVQVHELGCEGISK | 0.000 | 0.000 | 0.000 | 0.092 | 0.526 | 0.000 | 0.354 | 0.028 | ||
| 4 spectra, FLQPVQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.745 | 0.000 | 0.255 | 0.000 | ||
| 2 spectra, DPWPVPQGK | 0.000 | 0.000 | 0.090 | 0.209 | 0.335 | 0.000 | 0.366 | 0.000 | ||
| 7 spectra, YIDTEHGGSQAR | 0.087 | 0.000 | 0.000 | 0.071 | 0.598 | 0.000 | 0.225 | 0.019 | ||
| 10 spectra, VTTIAR | 0.000 | 0.000 | 0.000 | 0.028 | 0.711 | 0.000 | 0.261 | 0.000 | ||
| 2 spectra, DDPNSFR | 0.000 | 0.000 | 0.000 | 0.164 | 0.521 | 0.000 | 0.298 | 0.018 | ||
| 3 spectra, IDMNLTDLLGELQR | 0.000 | 0.000 | 0.000 | 0.015 | 0.704 | 0.000 | 0.281 | 0.000 | ||
| 5 spectra, MGFGGTLEIK | 0.000 | 0.000 | 0.000 | 0.156 | 0.591 | 0.000 | 0.253 | 0.000 | ||
| 9 spectra, AVLNPLCQVDYR | 0.000 | 0.000 | 0.000 | 0.197 | 0.385 | 0.000 | 0.363 | 0.055 | ||
| 2 spectra, ISGAIGPCVSLNSK | 0.093 | 0.000 | 0.000 | 0.337 | 0.336 | 0.000 | 0.234 | 0.000 | ||
| 7 spectra, FSWNVWPSSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.689 | 0.000 | 0.311 | 0.000 | ||
| 5 spectra, GAVQFVTQYQHSSGQR | 0.000 | 0.000 | 0.188 | 0.009 | 0.545 | 0.000 | 0.258 | 0.000 | ||
| 2 spectra, GPQVQQPPPSNR | 0.000 | 0.000 | 0.114 | 0.244 | 0.000 | 0.289 | 0.354 | 0.000 | ||
| 2 spectra, TTYLEFIQQNEER | 0.000 | 0.000 | 0.000 | 0.157 | 0.623 | 0.000 | 0.195 | 0.025 | ||
| 2 spectra, QLQEMLGLSK | 0.000 | 0.000 | 0.092 | 0.149 | 0.563 | 0.000 | 0.196 | 0.000 | ||
| 7 spectra, MVVPVAALFTPLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.629 | 0.000 | 0.371 | 0.000 | ||
| 3 spectra, DIHGQFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.651 | 0.000 | 0.349 | 0.000 | ||
| 2 spectra, SWHDIEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.663 | 0.000 | 0.337 | 0.000 | ||
| 18 spectra, VPVTQATR | 0.000 | 0.000 | 0.000 | 0.047 | 0.569 | 0.000 | 0.284 | 0.100 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
81 spectra |
 |
0.000 0.000 | 0.000 |
0.146 0.139 | 0.153 |
0.000 0.000 | 0.000 |
0.718 0.711 | 0.723 |
0.000 0.000 | 0.000 |
0.136 0.132 | 0.140 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
151 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
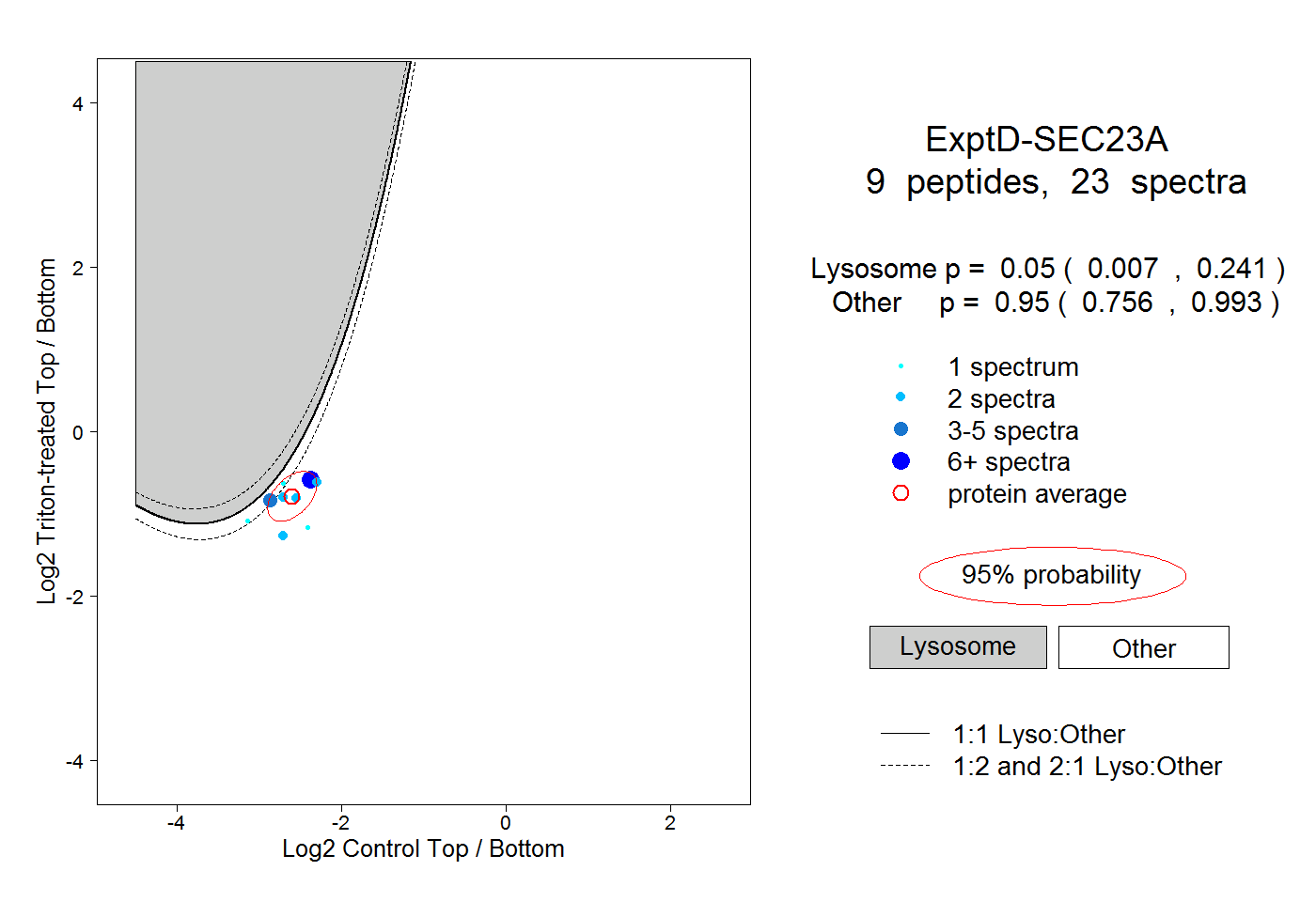 |
0.050 0.007 | 0.241 |
0.950 0.756 | 0.993 |