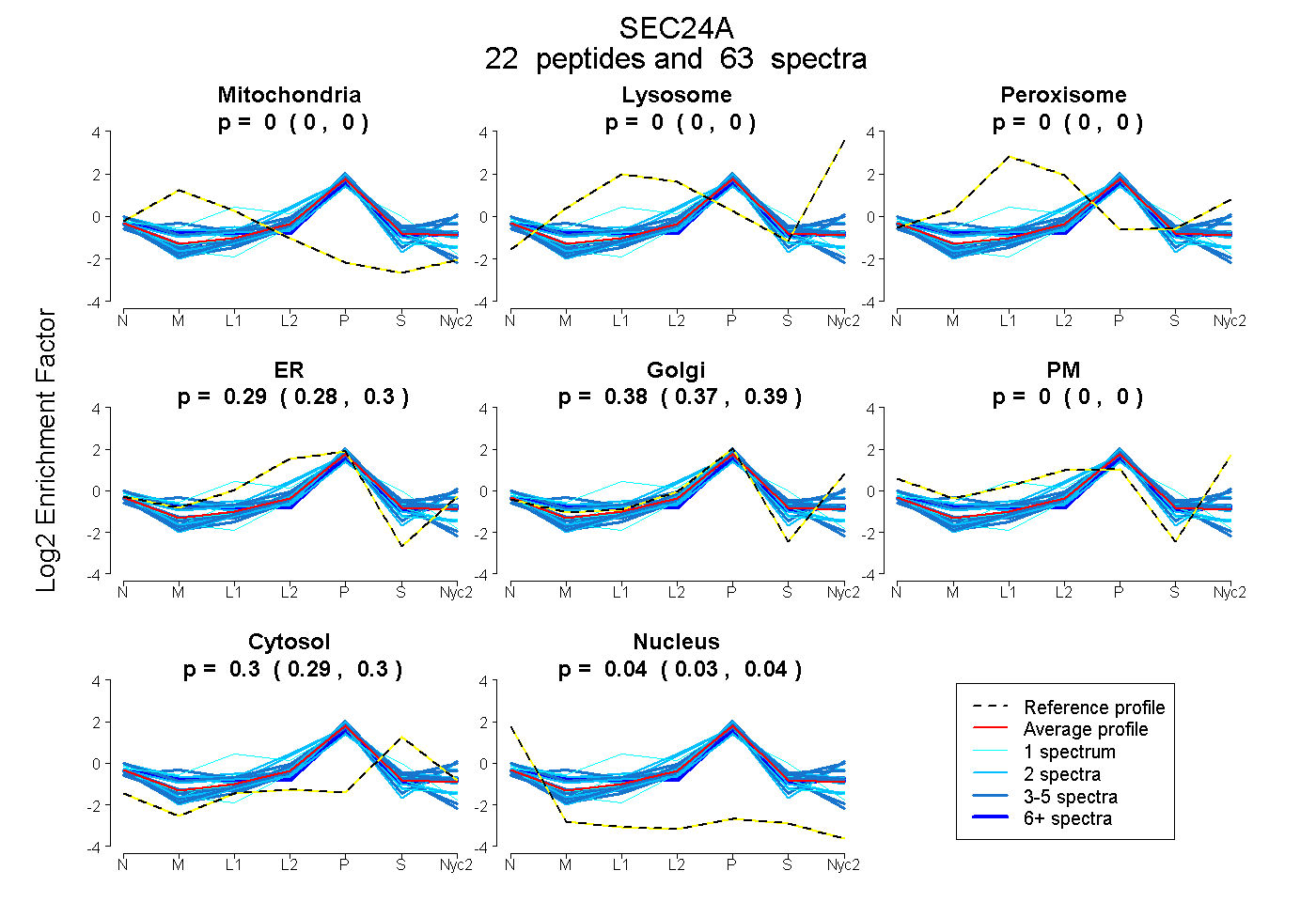
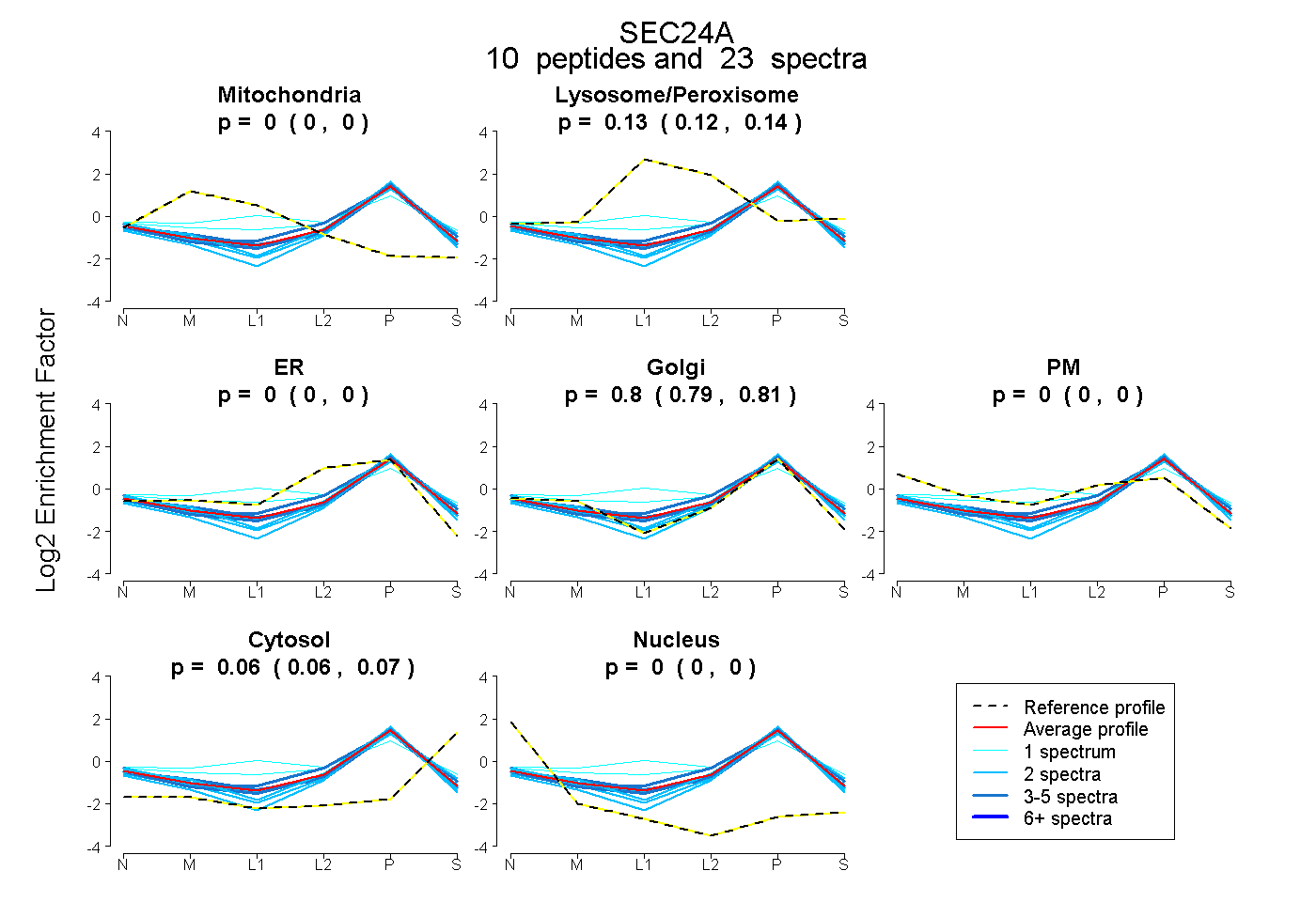
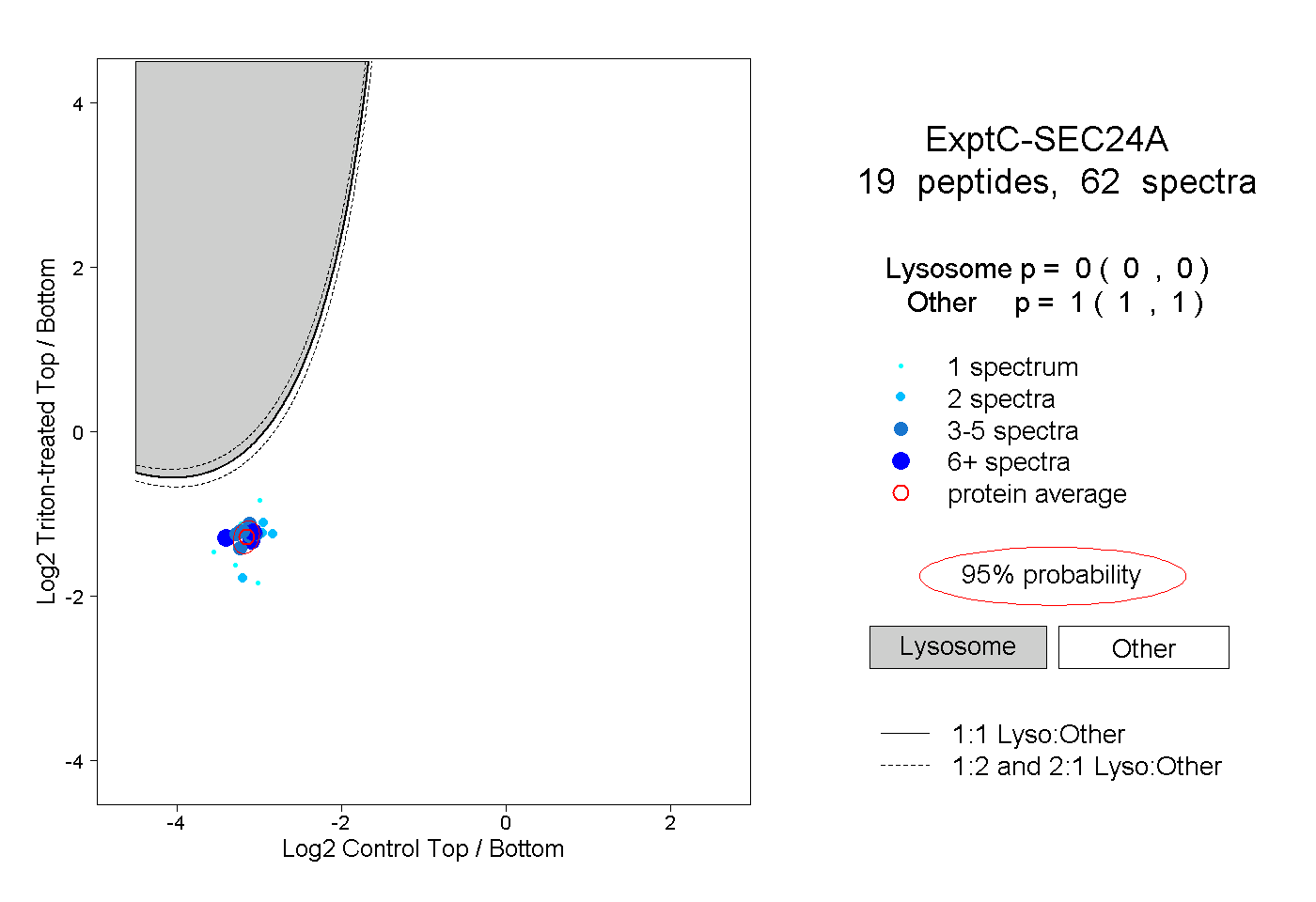
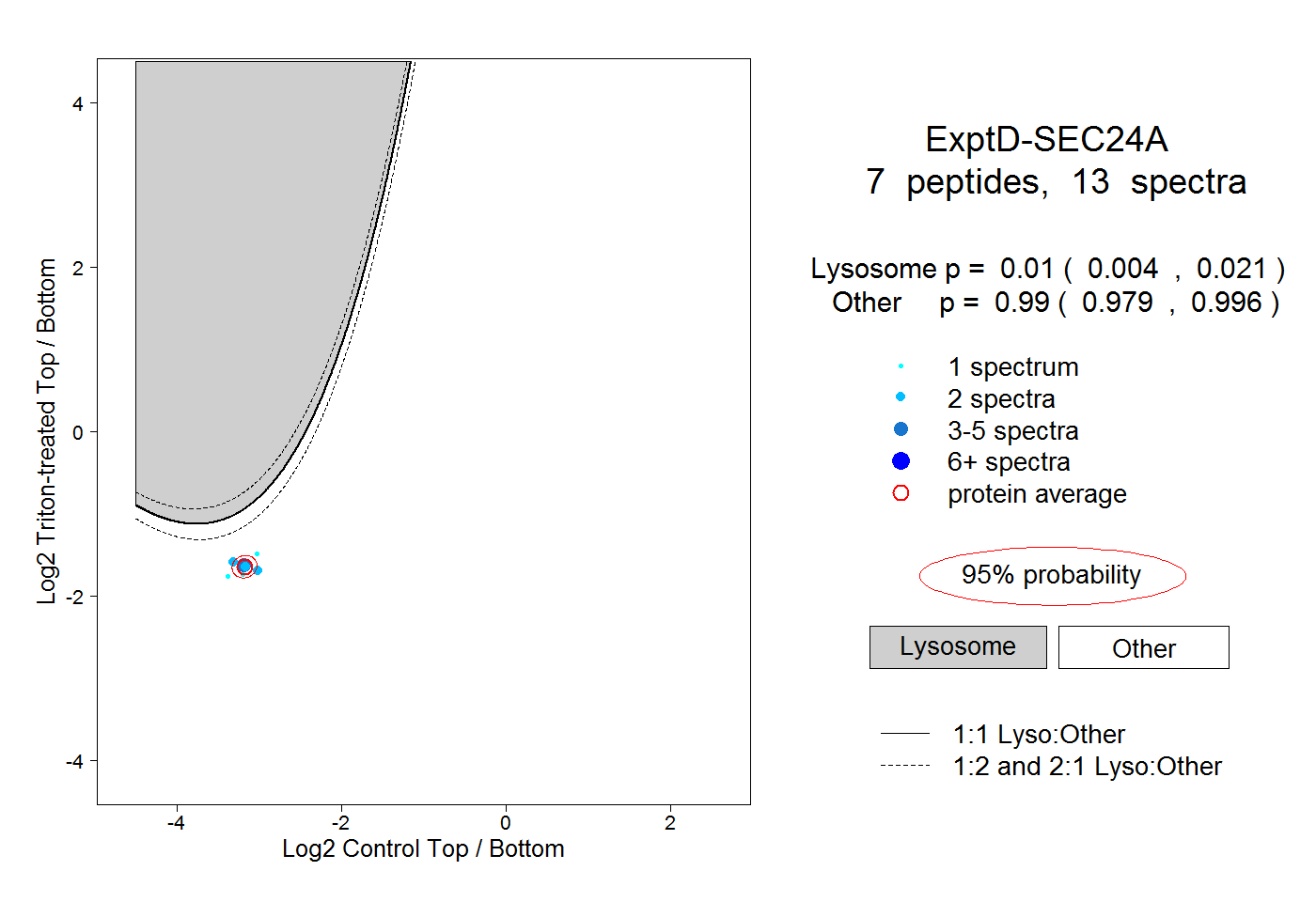
| 4 spectra, IFAMCQVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, CTLTSVPQTQALLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, EQRPFFPILYVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VYGEPHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, TLPQMFTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ELVQDLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DLVQLPVVTSSTIVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VNDVPEEFMYNPLTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LISPTGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VVNLLQER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LNCNPELFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VDNLSDEGALNINDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IGFEAVMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LPLGLLLHPFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, SVTASLSDAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TIPQPPILQLSVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, SFQTGTNVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TLETQSALGPALQAAFK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 2 spectra, AAFLQNLVEDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |